-

 国家认可委 CNAS L23010 认可项目:微生物宏基因组 | 16S rRNA扩增子
国家认可委 CNAS L23010 认可项目:微生物宏基因组 | 16S rRNA扩增子

 二级病原微生物安全实验室
二级病原微生物安全实验室 国家高新企业 | ISO9001认证 | 肠道健康精准检测高新技术研发中心 | 专精特新企业
国家高新企业 | ISO9001认证 | 肠道健康精准检测高新技术研发中心 | 专精特新企业- 联系电话:+13336028502
- +400-161-1580
- service@guheinfo.com


谷禾健康


卵巢早衰
卵巢早衰(premature ovarian insufficiency,简称POI)在生殖系统疾病中位居首位,这些疾病可能会损害多个功能系统,降低生活质量,最终剥夺女性患者的生育能力。
目前的激素替代疗法不能改善受孕或降低全身并发症的发生率,可部分缓解症状。
日常食物中的营养成分包括碳水化合物、脂肪和脂蛋白、蛋白质和多肽、维生素以及含有植物雌激素的蔬菜或水果。这些是功能性营养素,在更年期期间具有增殖、抗炎、抗氧化和线粒体保护潜力。
除此之外,微生物相关营养物质,包括益生菌、益生元和合生元组合,在支持卵巢活力和调节其他重要生殖功能方面显示出很高的潜力。
本文主要介绍卵巢早衰的症状、发病率、风险因素,发病机制,与肠道菌群及阴道菌群的关联,后面着重介绍现有的关于卵巢早衰的膳食补充研究。
卵巢早衰,也称为原发性卵巢功能不全(简称POI)。


/ 卵巢早衰
健康女性的卵巢会产生雌激素。这种激素控制月经期并让人拥有生育能力(能够怀孕)。随着年龄的增长,卵巢最终会停止制造雌激素。有时,卵巢在预计绝经前很久就会停止工作。
注:绝经的平均年龄是 51 岁。
如果不到 40 岁,卵巢不再产卵,且月经停止,则可能是原发性卵巢功能不全,也就是我们通常所说的“卵巢早衰”。 甚至部分女性在青少年时期就开始了。
卵巢早衰不同于过早绝经。绝经是不可逆的;而有些卵巢早衰的女性,这种功能丧失是暂时的,也就是说,月经会在未来的某个阶段恢复。
对于大多数女性来说,最常见的症状是月经停止(或月经稀少)。
其他症状可能包括:
对于部分卵巢早衰的女性,月经变得不规律,卵巢可能会继续间歇性排卵并产生激素;这些女性可能会在卵巢完全关闭之前继续月经周期数月或数年。
对于大约十分之一的卵巢功能不全 (POI) 女性,她们的月经还没有开始,在很小的时候就出现了 POI,通常不到 20 岁。
什么时候应该怀疑自己可能有 POI?
POI可能在月经期突然停止时突然发生。或者,POI可以在月经停止前随着月经不规律的月份逐渐出现。
对一些人来说,怀孕困难可能是卵巢早衰的最早也是唯一的迹象。当症状被注意到时,通常是由于卵巢功能不良或功能不全导致雌激素分泌不足。
POI还会导致哪些问题?
在过去的几十年中,伴随着生活方式的快速改变和环境的恶化,POI 发病率的急剧上升。
在 40 岁以下的女性中,大约每 100 名女性中就有 1 名患有卵巢早衰。
在 30 岁以下的女性中,大约每 1000 名女性中就有 1 名会发生卵巢早衰。
在大约 90% 的情况下,POI 的确切原因是未知的。
研究表明,POI 与卵泡问题有关。卵泡是卵巢中的小囊,卵子在里面生长成熟。
一种卵泡问题是比正常情况更早地用完了工作卵泡。另一中问题是卵泡不能正常工作。
在大多数情况下,卵泡问题的原因是未知的。
某些因素会提高女性POI的风险:
注:
脆性 X 综合征,是常见的遗传性疾病,造成智力低下。
特纳综合征,指先天性卵巢发育不全。
艾迪生病,一般指肾上腺皮质功能减退症。
POI 的发生率逐渐增加,它与已知的致病基因高度异质,并影响多种生物活动,包括激素信号、代谢、发育、DNA 复制、DNA 修复和免疫功能。目前已知的 POI 基因只能解释一小部分患者。
细胞凋亡与 POI 密切相关,与卵母细胞在从原始卵泡到窦卵泡的成熟过程中丢失相关。
卵巢颗粒细胞凋亡是影响卵巢储备和功能下降的重要机制。女性一生当中只有0.1%卵泡可以发育成熟并完成排卵,其余卵泡在不同阶段发生闭锁,颗粒细胞凋亡是卵泡闭锁的重要因素之一。
正常卵巢与POI卵巢的卵泡生成受损
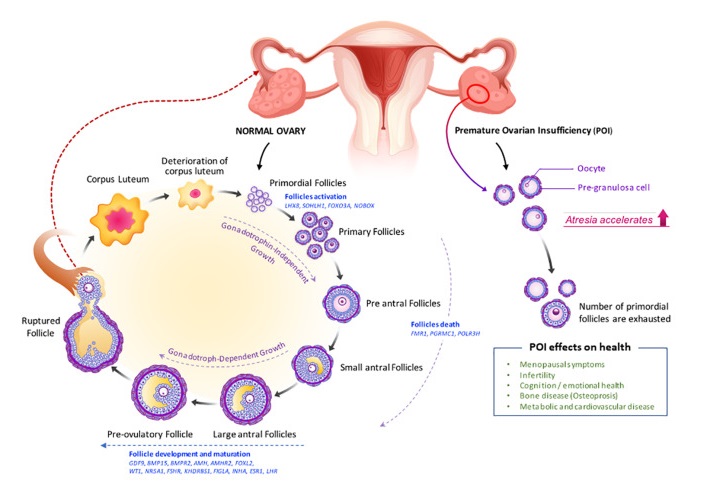
doi: 10.3389/fcell.2021.672890
在卵巢内因子和促性腺激素的调节下,初级卵泡发育成腔前卵泡和早期窦状卵泡,最容易发生闭锁或卵泡死亡。
然后,它们成为排卵前卵泡,导致卵母细胞释放和黄体形成。卵泡发生缺陷(如原始卵泡减少、闭锁增加和卵泡成熟度改变)导致POI。
涉及 DNA 损伤和修复、同源重组 (HR) 和减数分裂的基因中的大量基因突变。
这些基因包括基质抗原3(STAG3)、联会复合体中心元件1(SYCE1)、参与DNA修复的支架蛋白(SPIDR)、蛋白酶体26S亚基ATP酶3相互作用蛋白(PSMC3IP)、ATP依赖性DNA解旋酶同源物(HFM1)、mutS同源物(MSH)4、MSH5、MCM8、MCM9、cockayne综合征B-piggyBac 3(CSB-PGBD3)、核孔蛋白107(NUP107),以及乳腺癌易感基因(BRCA1和BRCA2).
内源性和外源性因素触发原始卵泡中DNA 双链断裂,由于细胞代谢的变化和氧化应激的升高,作为卵巢衰老的一部分,DNA损伤在原始卵泡中积累。在原始卵泡的氧化呼吸过程中,少量氧气首先在线粒体中转化为超氧化物,然后转化为羟基自由基。这些羟基自由基导致DNA单链断裂,如果双链断裂发生在多个相邻病变中,则会导致双链断裂和原始卵泡丢失。
线粒体是个多功能的细胞器,其异常与多种人类疾病相关,卵母细胞和颗粒细胞中的线粒体功能对卵巢的发育、功能维持都十分重要。
线粒体功能障碍可通过多种途径,如线粒体DNA 异常或逐渐积累的损伤、氧化应激、Ca2+ 对线粒体的直接损伤,导致卵子的发育潜能障碍,诱导卵子的凋亡而引起卵巢储备功能下降,进而发展成卵巢早衰。
▸TGF⁃β/ Smad 信号通路
TGF⁃β1/Smad 主要效应分子在卵巢组织中广泛表
达,参与病理性卵巢功能衰退,主要通过下调 TGF⁃β1/Smad3 信号通路因子表达,同时活化卵泡细胞质内 Smad2 表达;在生理性卵巢功能衰退中该信号通路的生物学效应可能与通过 Smad7 代偿性抑制通路的调节有关。
GDF-9 对窦状卵泡阶段的发育主要是通过减弱依赖 FSH的LH受体形成,防止卵泡过早发生黄素化和凋亡,直接决定卵泡池中卵泡数量,反映卵巢储备。
▸PI3-K / AKT 信号通路
磷酸酶和紧张素同系物(PTEN)/磷脂酰肌醇3激酶(PI3-K)/蛋白激酶B(AKT)/叉头转录因子3(FOXO3)信号通路在初级和进一步发育卵泡的卵母细胞的募集中起着重要作用。
PI3-K 和 AKT 过度激活可使原始卵泡过早发育及卵泡过快凋亡,进而发展成为卵巢早衰。
FOXO3a 是 PI3-K / AKT 信号通路下游的重要靶蛋白之一。FOXO3a的下调未能挽救颗粒细胞的凋亡死亡,导致卵母细胞丢失。卵母细胞特异性PTEN缺失导致全球原始卵泡激活,导致POI.
▸Wnt/ β⁃catenin 信号通路
合成类固醇激素是卵巢的重要功能之一。 目前现代医学认为卵巢 Wnt 信号通路可能是促性腺激素信号调节类固醇生成的重要信号途径之一。Wnt2 通过影响 β⁃catenin 的细胞定位来调节颗粒细胞增殖;β⁃catenin 参与合成卵巢甾体激素和黄体生成。
▸ SIRT 信号通路
SIRT1 通过调节氧化还原状态参与卵母细胞的成熟,以此减少氧化应激损伤导致的卵母细胞破坏和卵巢功能下降。
早发性卵巢功能不全患者存在系统性免疫失调,外周血T细胞亚群比例异常,Th1细胞占比显著升高,同时Treg细胞占比显著降低,提示细胞免疫参与早发性卵巢早衰发病。
注:Treg细胞是免疫抑制性淋巴细胞亚群,在维持免疫环境的稳定性和控制自身免疫疾病的发生中起重要作用。
免疫性卵巢早衰可能与辅助性Th17细胞过度活跃关系密切,E2水平低下时Th17细胞可过度激活,使机体免疫应答增强。
研究显示,卵巢早衰患者 Th17/Treg 水平较健康妇女明显增高,Th17和Treg 细胞表达失衡引发免疫调节紊乱,最终导致卵巢组织破坏和衰竭。
■ 为什么说肠道菌群与POI之间存在关联?
▸ 卵巢的自身免疫损伤
卵巢通过 T 细胞亚群的改变、T 细胞介导的损伤、产生自身抗体的 B 细胞的增加、效应抑制/细胞毒性淋巴细胞的减少以及自然杀伤细胞的减少而受到自身免疫的损害。
▸ 肠道菌群在自身免疫过程中发挥关键作用
肠道微生物群产生的肽可能会诱导免疫细胞产生自身反应和交叉激活。肠道微生物群的失调不仅会影响B淋巴细胞的激活和自身抗体的产生,还会诱导先天免疫细胞的异常激活,从而导致促炎细胞因子的上调。
▸ 肠道菌群在卵巢早衰中发挥重要作用
肠道微生物组在POI相关症状中发挥重要作用,包括自身免疫功能障碍、骨骼健康、认知、神经健康等。肠道微生物群及其代谢产物还具有调节炎症途径激活、脑肠肽分泌和胰岛β细胞破坏的能力。
我们具体来看相关的研究 ↓↓

2021年,深圳妇幼保健院检测了部分患者的肠道菌群,卵巢早衰女性(n = 35),健康女性( n = 18).
▸ POI患者中肠道菌群变化
下列菌群在POI女性中较少:
而下列菌群在POI女性中更丰富:
▸ 肠道菌群与自身免疫反应的关联
可以看到,拟杆菌属、双歧杆菌属和普氏菌属的相对丰度在该研究的POI组中均有所增加。这些菌群与自身免疫反应有何关联呢?
注:Th17细胞能够分泌产生IL-17A、IL-17F、IL-6以及TNF-α等,其功能主要就体现在它分泌的这些细胞因子集体动员、募集及活化中性粒细胞的能力上。
▸ 肠道菌群代谢产物诱导免疫调节活性
此外,双歧杆菌属、Blautia、Clostridium、Faecalibacterium、Roseburia和Ruminococcus可在人体肠道中产生短链脂肪酸,短链脂肪酸可以发挥什么作用呢?
综上,POI组肠道微生物组的所有这些变化可能通过某些细菌菌株及其代谢产物诱导免疫调节活性,这可能与自身免疫有关,进而影响POI的发展。
▸ POI肠道微生物群的改变与性激素有关
在这项研究中,在POI受试者中观察到显著较低的E2水平,通过调整BMI,E2水平与拟杆菌属、厚壁菌属和粪杆菌属的比例显著相关。FSH、LH和AMH水平也与某些微生物有关。
▸ 肠道菌群影响雌激素水平,雌激素调节的反应与POI相关
肠道微生物组通过分泌β-葡萄糖醛酸酶影响雌激素水平,使雌激素解凝,影响相关生理过程。
越来越多的研究表明,雌激素调节糖脂代谢、骨形成和炎症反应,其减少可损害雌激素依赖性过程,引发心血管疾病、骨质疏松等。这些症状都与POI有关。
肠道微生物群的失调与POI的发展有关,然而在进一步的研究中,还应考虑大样本量和多中心研究,来探索潜在的因果机制。
■ 为什么说阴道菌群与POI之间存在关联?
研究表明,细菌性阴道病与不孕有关。细菌性阴道病也被证明会改变阴道微生物组。
先前的一项研究表明,阴道微生物组在卵巢早衰的病理生理学中起着重要作用,卵巢早衰患者中乳杆菌属细菌的相对丰度显著低于健康对照组。因此,阴道微生物组和POI之间可能存在关系。
▸ POI患者中阴道菌群变化
下列菌群相对较少:
下列菌群显著增加:
我们具体来看相关的研究 ↓↓

2021年,深圳市妇幼保健院检测了部分患者的阴道菌群,卵巢早衰女性(n = 28),健康女性( n = 12).
▸ 阴道菌群与自身免疫反应的关联
可以看到,POI组中乳杆菌属、Odoribacter和Brevundimonas显著减少,链球菌属显著增加。这些菌群变化与自身免疫反应有何关联呢?
▸ 性激素水平会影响女性生殖道的防御能力和生殖期内的阴道微生物群
激素促进增生并增加糖原生成;糖原可以被阴道中的优势细菌乳酸杆菌转化为乳酸。这有助于保持阴道的酸性环境,抑制病原体的生长,并增强免疫系统。
在这项研究中,乳杆菌的比例与雌激素水平呈正相关,但与FSH水平呈负相关。POI患者的乳酸杆菌丰度和雌激素水平显著下降,FSH水平显著增加。
此外,AMH、FSH、LH、PRL、P和睾酮水平也与一些微生物有关,包括 Streptococcus, Odoribacter, Brevundimonas, Anaerococcus, Atopobium, Peptoniphilus, Prevotella, Veillonella,这增加了阴道微生物群改变与性激素相关的证据。
▸ 雌激素可以调节POI相关症状
越来越多的证据表明,雌激素可以调节POI相关症状,包括GLU和脂质代谢、骨形成和炎症反应。
在该研究中,GLU水平与Odoribacter和普雷沃氏菌属呈负相关。此外,PRL可以抑制FSH和促性腺激素释放激素以促进生育,这与厌氧球菌和嗜酸乳杆菌呈正相关。
▸POI患者阴道菌群的失调与卵巢功能密切相关
由于半乳糖和半乳糖代谢产物的积累,卵巢功能容易受损。先前的一项研究发现,半乳糖抑制了卵巢卵泡的数量和类固醇分泌。半乳糖代谢产物,包括1-磷酸半乳糖、半乳糖醇和尿苷二磷酸半乳糖,在干扰卵巢细胞凋亡和促性腺激素信号传导方面发挥重要作用。
患有POI的女性LACTOECAT-PWY通路的活性显著降低。这表明,患有POI的女性体内可能会积聚半乳糖,从而损害卵巢功能。患有POI的女性ARGONPROST-PWY通路显著富集。L-精氨酸与卵巢功能的调节相关。这可能对卵巢功能不利。
DNA损伤通过激活线粒体凋亡途径导致生殖功能障碍。
该研究结果表明,在POI患者中,许多与核糖核苷酸生物合成相关的途径发生了改变。
其他来自同济医院绝经与卵巢衰老专科门诊的研究数据发现:
双歧杆菌主要定殖在人体肠道中,在阴道中仅以低水平存在。作为一种益生菌,它具有抗炎作用、提高免疫功能和抵抗氧化损伤。临床研究发现,双歧杆菌可以改善绝经后妇女的新陈代谢和心血管功能。
Gardnerella和Atopobium均属于放线菌,在研究中发现 POI 患者显着富集,并且与卵巢储备下降、内分泌紊乱和围绝经期综合征症状显着相关。
阴道微生物组不仅反映了阴道的细菌组成,还反映了宿主的一般状况,包括激素和免疫状态等。阴道微生物群的失调与POI的发展有关,然而在进一步的研究中,还应考虑大样本量和多中心研究,来探索潜在的致病机制。
➔
这些测试可能帮助找到不孕的原因,找出排卵发生的时间,找出月经不规律或停止的原因,确认更年期或围绝经期的开始等。
➔
如果患有与POI相关的疾病,那么也必须对其进行治疗。治疗可能涉及药物和激素。
目前,没有经证实的治疗方法可以恢复女性卵巢的正常功能。但有一些治疗卵巢早衰症状的方法,或者可以降低其风险并解决POI可能导致的疾病:
激素替代疗法(HRT)
HRT是最常见的治疗方法。它给身体提供了卵巢无法产生的雌激素和其他激素。HRT可以改善性健康,降低患心脏病和骨质疏松症的风险。通常需要服用到50岁左右;这大约是更年期开始的年龄。
体外受精(IVF)
如果患有POI并且想怀孕,可以考虑尝试试管婴儿。
有规律的体育锻炼
有规律的体育锻炼,维持健康的体重,可以降低患骨质疏松症和心脏病的风险。
其他相关膳食补充方式,将在下一章节详细介绍。
除了那些遗传、免疫或医源性因素之外,日常饮食和生活方式中的营养摄入对于 POI 患者来说是最容易获得和改变的。
关于不良饮食习惯影响女性生育力和更年期的营养状况和调节的研究较少,这里初步提出了一些主要饮食因素和营养素:
Han Q, et al., Front Microbiol. 2022
碳水化合物为所有生物提供了最丰富的生命支持能源,通常分为单糖、寡糖和多糖。
Han Q, et al., Front Microbiol. 2022
半乳糖:毒性作用
半乳糖是卵巢早衰和相关不孕疾病中报道的一种常见单糖,它对卵巢产生了毒性作用。
半乳糖还可能抑制卵泡向性腺区域的迁移,并导致卵巢储备和雌二醇合成减少。因此,糖-半乳糖代谢异常与卵巢早衰的发生和发展有关。

铁皮石斛多糖:保护作用
铁皮石斛多糖(DO)对自然老化啮齿动物的卵巢早衰过程产生保护作用。
口服给药剂量为70 mg/kg,有助于这些大鼠恢复正常体重,减轻卵巢的病理变化,如血管增殖减少和卵泡减少。
DO导向的多糖通过调节NF-κB和p53/Bcl-2信号通路,提高谷胱甘肽过氧化物酶(GSH-Px)和超氧化物歧化酶(SOD)活性,降低血清中丙二醛(MDA)浓度,从而发挥抗氧化作用,从而减少卵巢组织的炎症损伤。同时还操纵了线粒体功能,恢复了卵巢细胞的活力。
碳水化合物对卵巢早衰发病或进展的重要性应进一步评估。
脂肪和体重高可能与卵巢早衰严重程度的控制有关。


Han Q, et al., Front Microbiol. 2022
一些研究报告称,绝经早期与低体重指数相关。具体机制尚不清楚。
脂蛋白是可运输的脂肪形式,积极参与人体内的代谢活动。
研究人员对卵巢早衰患者进行了血脂分析,发现血清中较高的甘油三酯(TG)浓度和较低的高密度脂蛋白(HDL)水平与游离雄激素指数增加和性激素结合球蛋白丢失相关。这些发现表明,TG升高可能导致胰岛素敏感性降低。
在另一项回顾性临床研究中同样发现,与具有密切流行病学特征的正常女性相比,出现卵巢早衰综合征且既往无激素摄入史的年轻女性患者血清中总胆固醇(TC)和低密度脂蛋白(LDL)浓度更高。结果表明,女性卵巢早衰患者在雌激素缺乏的情况下会引发脂质改变。
然而,不同研究中HDL的浓度水平非常不一致,一些研究报告HDL水平升高,另一些研究报告更年期妇女HDL水平降低。
至于脂肪摄入对更年期的影响,不同种类的脂肪可能会造成差异,包括多不饱和脂肪、总脂肪和饱和脂肪。
有研究认为,多不饱和脂肪的高消费与绝经较早有关;同时,总脂肪和饱和脂肪摄入量几乎不影响绝经期和年龄。
然而,尚不清楚日常饮食中的不同脂肪类型是否会以某种方式影响卵巢早衰的发病机制。
“
高蛋白摄入有助于推迟更年期的提前到来


Han Q, et al., Front Microbiol. 2022
研究发现,海鲜(每周约3天)和新鲜鸡蛋(每周超过4天)的消费与绝经晚期发病呈正相关。其他几项研究也支持类似的结论。研究人员认为,高蛋白摄入有助于推迟绝经并延长生殖功能。欧洲癌症与营养前瞻性调查(EPIC)还进行了一项队列研究,其中早期绝经的发生与蛋白质摄入量呈负相关。
除了直接摄入蛋白质外,多肽对保护卵巢功能和延缓卵巢衰老也很重要。
通过酶解从牡蛎中纯化的牡蛎多肽,由于其DPPH(2,2-二苯基-1-苦酰肼基)自由基清除剂能力,能够保护其免受氧化应激和炎症,从而对卵巢早衰产生治疗作用。
牡蛎多肽可以纠正异常的发情周期,提高血清卵泡刺激素(FSH)和黄体生成素(LH)浓度。此外还增加了原始卵泡计数和分布,并通过模拟SOD清除显著减轻了卵巢细胞死亡。牡蛎多肽支持的卵巢细胞保护和存活在调节死亡受体BCL-2依赖性信号通路时被激活。因此,适当的蛋白质和肽摄入可能是影响卵巢早衰进展和严重程度的潜在途径。
维生素是一类仅来自食物的微量有机物质,在人体内维持一些重要的生理活动和功能。它们不提供能量,但调节代谢过程。许多维生素在支持女性健康方面发挥着关键作用,如维生素B、C、D、E和一些辅酶。


Han Q, et al., Front Microbiol. 2022
烟酸:改善卵泡发育,保护卵巢
烟酸属于维生素B家族,代谢细胞能量,并直接影响正常生理。除了许多神经和皮炎疾病外,烟酸还通过抑制氧化应激来改善卵泡发育,从而减少卵巢细胞死亡。
有趣的是,烟酸还能够改变卵巢早衰表型并恢复化疗或辐射刺激诱导的雌性卵巢早衰小鼠。作者进一步证实,添加10 Mmol烟酸可以降低卵泡阻滞标记FOXO3的表达水平,并增加卵母细胞标记DDX4的表达水平以发挥卵巢保护作用。
叶酸:妊娠率更高,提高卵母细胞的质量和成熟度
叶酸是一种水溶性维生素B,对蛋白质合成、红细胞分裂和生长很重要。
一项基于小样本的临床研究报告称,与安慰剂治疗相比,低生育率女性在接受400μg叶酸治疗12周后的妊娠率更高。叶酸的摄入缩短了健康女性的备孕时间,并提高了卵母细胞的质量和成熟度。
MTHFR可以强烈影响叶酸循环,并帮助同时患有非霍奇金淋巴瘤和重复妊娠损失的卵巢早衰患者成功分娩出健康的男婴。
维生素C:显著刺激卵巢标志物的表达
维生素C是一种天然抗氧化剂,并积极参与干细胞调节。
据报道,维生素C修饰人羊膜上皮细胞(hAECs)的生物学特性,并显著刺激移植POI小鼠卵巢组织中卵巢标志物的表达。
注:羊膜细胞通俗地说就是包裹羊水的那层透明薄膜上的细胞。
可能的影响机制是维生素C依赖的几种重要生长因子的旁分泌,如肝细胞生长因子和表皮生长因子。
维生素D:有争议
维生素D属于脂溶性维生素,通过调节钙和磷酸盐代谢对维持生命至关重要。其活性形式1,25-二羟基维生素D3定位于许多器官,如肾脏、肝脏、大脑和卵巢。在女性生殖系统中,维生素D可以调节颗粒细胞中的抗苗勒氏激素(AMH)分泌,从而影响FSH水平。
然而,它在卵巢早衰发病机制中的作用是有争议的,因为一些人声称它不影响卵巢早衰的病理生理过程。
而另一些人则报告维生素D缺乏与凝血相关,是由于卵泡发育不良和芳香化酶水平降低而导致卵巢早衰的主要因素。
先前的研究也没有报告任何关于补充维生素D治疗卵巢早衰的证实性发现。研究发现,在约2个月内,每周摄入50000 IU的维生素D与临床上的妊娠改善无关。提高卵子受体患者的血清维生素D水平也不能改善IVF结局。
因此,维生素D对卵巢早衰患者的意义的解释仍然模糊,仍需进一步调查。
维生素E:增加卵巢体积并刺激初级卵泡的增殖
维生素E主要由生育酚和生育三烯醇组成,它们在生理和病理条件下对清除自由基很重要。维生素E缺乏可能导致雌性啮齿动物模型中的卵巢细胞死亡和发育异常。
在一项临床研究中,在40名患者中,维生素E与卵巢早衰的发病有关。在月经正常的女性中,维生素E-α生育酚的活性形式浓度显著高于卵巢早衰患者。进一步分析表明,这可能与AMH表达水平降低有关,并表明卵巢储备能力在卵巢早衰发病机制中受到损害。
在另一项随机对照试验研究中,向卵巢早衰患者服用400IU的维生素E 3个月,除改善AMH水平外,还显著增加了窦卵泡数和平均卵巢体积。
补充维生素E可能有助于缓解卵巢早衰过程,几乎不会产生副作用。
植物雌激素确实不是雌激素的一部分,但通过提供高亲和力的雌激素受体β作为激素补充剂,其功能类似。


Han Q, et al., Front Microbiol. 2022
它们通常包括大豆异黄酮和芝麻木脂素,这两种都是我们日常饮食中重要和普通的食物类型。几项研究证实了植物雌激素消耗对绝经后女性TC、LDL和血脂的降低作用。
大豆异黄酮摄入也显著缓解了髂动脉动脉粥样硬化,绝经前后5年内食用大豆食物的女性减少了冠状动脉斑块的大小。对于绝经后开始以大豆食品作为日常饮食的人来说,这种有益效果并不明显。
研究人员指出,大豆异黄酮可以通过卵巢切除术减少更年期啮齿动物的潮热。该效应基于肠道微生物群和雌激素样机制产生的异丙戊酸雌马。
芝麻籽木脂素(芝麻籽油中的一种成分)在小鼠模型中增加了脂肪酸的β-氧化,并抑制了胆固醇的吸收。芝麻酚是一种强抗氧化剂,也是芝麻的主要成分。它可以改善记忆,减轻焦虑情绪,减少中枢神经系统中的氧化剂损伤。同时,与卵巢切除后的绝经大鼠相比,芝麻酚还通过降低血清中肿瘤坏死因子-α(TNF-α)浓度来调节血清中的脂质成分,并降低炎症效应。
益生菌、益生元和合生元


Han Q, et al., Front Microbiol. 2022
益生菌促进营养物质的消化和吸收,提高免疫功能,维持肠道菌群的结构平衡,并增强人体的抗氧化水平。许多益生菌应用于食品补充剂和医疗。对于女性健康,激素水平与肠道或阴道微生物群之间存在密切相关性。
在平滑肌瘤和乳腺癌患者中,肠道微生物群被视为雌激素的替代代谢供应商,主要富含大肠杆菌、梭状芽孢杆菌、乳酸杆菌和拟杆菌。
考虑到这些现象,益生菌的调节作用也可以通过改变几种具有雌激素或抗雌激素性质的蔬菜成分(称为植物雌激素,如大豆异黄酮、木脂素等)的代谢活性和效率以间接方式调节肠道微生物群来发挥。
益生菌参与调节经前综合征、泌尿生殖道感染和骨质疏松症。雌激素缺乏是与卵巢早衰后骨炎症和吸收相关的骨质疏松症的主要原因。
先前的研究表明,肠道微生物群对骨形成和代谢有潜在影响。在接受益生元治疗的小鼠、大鼠和鸟类中发现骨骼增加。
在体外和去卵巢的啮齿类动物研究中,益生菌罗伊氏乳杆菌抑制了骨髓CD4+T淋巴细胞的上调和随后的破骨细胞活化。研究人员假设罗伊氏乳杆菌可以直接使T细胞失活并抑制TNF-α的产生,并通过T细胞间接使基质细胞失活以减少破骨细胞因子的形成,从而增加骨代谢活性并减少骨损失。
在一项由60名40至60岁绝经后妇女组成的随机对照试验中,益生菌还增强了异黄酮的代谢活性,以缓解泌尿生殖系统问题,如阴道干燥和绝经后的不良性体验,连续治疗16周。该效果与低剂量阴道雌激素相当,后者是治疗更年期泌尿生殖系统综合征的金标准疗法。
研究人员在一项为期12周的随机临床试验中报告,1×1010菌落形成单位(CFU)浓度的多菌益生菌影响肠道通透性和心脏代谢参数,如脂多糖水平、胰岛素、葡萄糖、尿酸、脂肪质量、皮下脂肪和胰岛素抵抗指数。
研究人员在一项试点临床研究中发现,乳酸杆菌和蔓越莓提取物复合物可以防止女性患者在绝经前或绝经前后连续26周反复发生尿路感染。
益生元是发酵的膳食纤维,其在肠道微生物群的成分和/或生物活性方面都含有一定的修饰,对人体健康状况产生有益影响。目前,益生元主要包括双歧杆菌、不易消化的低聚糖(尤其是低聚半乳糖、菊粉及其水解产物低聚果糖)。
大量的营养益生元可能有助于钙的生物吸收,如酪蛋白磷酸肽(CPP),酪蛋白的蛋白水解产物,与钙一起构建可溶性复合物。此外,一些复杂的有机酸,如苹果酸或柠檬酸,可以增加肠道中生物可吸收钙的可溶性复合物的百分比。
益生元依赖性钙代谢的潜在机制包括来自结肠中细菌发酵碳水化合物的酸代谢产物,如乳酸、乙酸和丙酸,降低了pH值,以提高钙离子的管腔水平,并增加钙的被动生物吸收。此外,电荷可以通过Ca2+-H+复合物进行修饰。因此,益生元在女性绝经后骨质疏松症的预防和抑制中发挥了保护作用。
研究人员表明,壳聚糖和柑橘果胶这两种益生元增强了葡萄糖耐量,降低了血脂异常,并提高了血清精氨酸、丙酸、亮氨酸和丁酸水平。此外,壳聚糖更有助于调节肠道微生物群,从而影响绝经后症状。
还尝试将益生菌和益生素结合起来生产合生元。研究人员表明,副干酪乳杆菌和菊粉增强了异黄酮的生物活性可用性,有助于缓解更年期问题。
使用由发酵乳杆菌和花椰菜蘑菇中的β-葡聚糖组成的合生元作为益生菌和益生元,可以降低啮齿动物尾巴的皮肤温度,并保持血清和子宫指数中的17β-雌二醇水平。合生元依赖性机制进一步得到验证,因为它们激活了肝脏胰岛素信号,随后在雌激素缺乏大鼠中激活了AMPK磷酸化。
这些研究初步反映了益生菌、益生元和合生元在调节更年期综合征及其主要病理生理过程中的有益作用。这些发现对于研究卵巢早衰的发病机制和通过微生物营养策略治疗卵巢早衰至关重要。
营养对女性一生的健康至关重要,膳食营养素可以通过影响各个方面来延缓更年期,从直接提高卵巢活力和功能到抵消氧化应激、炎症、衰老和系统性内分泌失调。
越来越多的证据表明肠道菌群的改变与卵巢早衰相关,可能通过影响一些重要代谢物影响卵巢疾病进展,至于是否会导致血清代谢物失衡,进而导致更年期表现和相关健康问题,仍有待进一步验证。
从目前的研究来看,膳食和微生物营养素对于调节卵巢早衰等女性生殖障碍很重要且很有前途,因此,通过合理饮食、最佳生活方式对菌群进行干预是有希望的,值得更多研究人员的关注,希望为广大女性带来更健康的生活。
主要参考文献:
Han Q, Chen ZJ, Du Y. Dietary supplementation for female infertility: Recent advances in the nutritional therapy for premature ovarian insufficiency. Front Microbiol. 2022 Nov 17;13:1001209. doi: 10.3389/fmicb.2022.1001209. PMID: 36466679; PMCID: PMC9712792.
Chon SJ, Umair Z, Yoon MS. Premature Ovarian Insufficiency: Past, Present, and Future. Front Cell Dev Biol. 2021 May 10;9:672890. doi: 10.3389/fcell.2021.672890. PMID: 34041247; PMCID: PMC8141617.
Zhang X, Lu Y, Wu S, Zhao X, Li S, Zhang S, Tan J. Estimates of global research productivity in primary ovarian insufficiency from 2000 to 2021: Bibliometric analysis. Front Endocrinol (Lausanne). 2022 Oct 26;13:959905. doi: 10.3389/fendo.2022.959905. PMID: 36387882; PMCID: PMC9645456.
Wu J, Zhuo Y, Liu Y, Chen Y, Ning Y, Yao J. Association between premature ovarian insufficiency and gut microbiota. BMC Pregnancy Childbirth. 2021 Jun 5;21(1):418. doi: 10.1186/s12884-021-03855-w. PMID: 34090383; PMCID: PMC8180047.
Takahashi A, Yousif A, Hong L, Chefetz I. Premature ovarian insufficiency: pathogenesis and therapeutic potential of mesenchymal stem cell. J Mol Med (Berl). 2021 May;99(5):637-650. doi: 10.1007/s00109-021-02055-5. Epub 2021 Feb 27. PMID: 33641066.
Kim S, Lee SH, Min KJ, Lee S, Hong JH, Song JY, Lee JK, Lee NW, Lee E. Females with impaired ovarian function could be vulnerable to environmental pollutants: identification via next-generation sequencing of the vaginal microbiome. J Obstet Gynaecol. 2022 Jul;42(5):1482-1488. doi: 10.1080/01443615.2021.2006162. Epub 2022 Jan 7. PMID: 34996320.
Wu J, Ning Y, Tan L, Chen Y, Huang X, Zhuo Y. Characteristics of the vaginal microbiome in women with premature ovarian insufficiency. J Ovarian Res. 2021 Dec 8;14(1):172. doi: 10.1186/s13048-021-00923-9. PMID: 34879874; PMCID: PMC8655991.
Wen J, Feng Y, Yan W, Yuan S, Zhang J, Luo A, Wang S. Vaginal Microbiota Changes in Patients With Premature Ovarian Insufficiency and Its Correlation With Ovarian Function. Front Endocrinol (Lausanne). 2022 Feb 22;13:824282. doi: 10.3389/fendo.2022.824282. PMID: 35273569; PMCID: PMC8902819.
谷禾健康

最杰出的物理学家之一的斯蒂芬·威廉·霍金想必大家都知道,以及曾经风靡全网的“冰桶挑战”,它们都与一种罕见疾病有关,那就是渐冻症。
媒体的宣传让渐冻症成为了较为“知名”罕见病之一;2000年丹麦举行的国际病友大会上正式确定6月21日为“世界渐冻人日”。但我们多数人对这种疾病的认知还不足。
什么是渐冻症?渐冻症是“肌萎缩侧索硬化症(简称ALS)”的通俗化叫法,该病一般以从四肢向中心进展,肢体肌肉逐渐消失,功能逐步丧失,直至呼吸肌消失,呼吸功能丧失,患者最后往往因呼吸衰竭而死。
渐冻症一般不会损害一个人的智力推理、视觉、听觉或味觉、嗅觉和触觉,这意味着,患者在保持清醒的状态意识到自己的情况在一步步恶化,感受自己的能力一点点退化。
渐冻症是一种罕见且严重的神经退行性疾病,会影响上下运动神经元,导致弥漫性肌肉麻痹,治疗选择较少。病因学和发病机制在很大程度上仍不清楚,但一些环境、遗传和分子因素被认为与疾病过程有关。
风险因素包括接触有毒物质、生活方式、饮食习惯、职业、体重等。研究表明,一些食物和营养素,包括红肉、钠、谷氨酸等,都可能是渐冻症的危险因素。我们知道饮食习惯、生活方式等因素都与肠道菌群状况息息相关。
新的研究确定了肠道菌群失调与神经退行性疾病(例如帕金森病、阿尔茨海默病、渐冻症)存在关联。
在这些疾病中,神经炎症越来越被认为是疾病发作和进展的驱动因素。肠道细菌在维持和调节免疫系统中起着至关重要的作用,肠道微生物组成的变化可以通过影响神经免疫相互作用、突触可塑性、髓鞘形成和骨骼肌功能来影响神经功能。
本文从渐冻症的症状、风险因素、形成原因、胃肠道和代谢功能障碍、与肠道菌群的关联和作用机理、可能的临床相关性、诊断(与其他一些神经退行性疾病的区别),带大家深入了解这一“特殊疾病”。文章的最后列举了一些现有的关于渐冻症干预方式的研究。
渐冻症
肌萎缩侧索硬化症 (ALS)
▪ 致命的神经退行性疾病
▪ 运动神经元退化,停止向肌肉发送信息
▪ 肌肉逐渐变弱、开始抽搐并萎缩
▪ 最终大脑失去启动和控制运动的能力
▪ 症状会随着时间的推移而恶化
▪ 晚期将背负巨大的心理压力和经济负担
不同的国家有不同的ALS发病频率。虽然这种疾病的世界平均发病率约为每100,000人每年1.9例。文献报道一些西方国家的ALS发病率很高,例如瑞典和苏格兰,每100,000人每年有3.8例,相反,东方国家,如中国每10万人年0.8例。
•中国渐冻症发病率相对较低
中国ALS患病率和发病率低于发达国家,并保持相对稳定的趋势。
一项研究调查研究共调查了7个省的城乡社区居民727,718人,其中城市居民占65.74%,农村居民占34.26%。
筛出肌萎缩侧索硬化患者9名,得出中国7个省肌萎缩侧索硬化总患病率为1.24/100,000。
•地区职业直接存在差异
不同省份患病率差别很大:
按区域划分:
按城乡划分:
从职业分布看:
7人职业为农民,占77.78%。
多在中年后发病,9例患者平均患病时间为50.33±13.90岁。
•医院渐冻症患者的性别占比:男性较多
在医院调查的169名肌萎缩侧索硬化患者中,117名男性,52名女性,男女性别比为2.25:1,在职业分布中,50.3%是农民,其中男性农民患者群体占比最高,共有63人,占所有医院调查患者的37.28%。
患病高峰年龄为60~69岁,男性平均患病年龄为61.43±12.66岁,女性平均患病年龄为59.98±12.76岁,男性较女性晚1~2年。医院调查中51.48%的患者没有慢性病史。
结论
(1)在中国7省的人群抽样调查中,肌萎缩侧索硬化的总患病率略低于世界其他国家和地区,农村患病率高于城市,发病时间略早于国际报道,而生存时间略低于国际报道。家族性肌萎缩侧索硬化患者较散发型发病时间早,生存时间长。
(2)人群调查和医院调查一致发现,筛查出的肌萎缩侧索硬化患者中男性占比高于女性,农民患者所占比例最高,大多数患者不伴有其他慢性病。
► 早期发病
发病主要分三种情况:一是从上肢发病;二是从腿部发病;三是从口腔肌肉发病
约 80%的ALS病例 通常表现为手臂或腿部持续无力或痉挛。
✦上肢发病最常见
上肢发病最常见,占比最高,发病过程表现为:
✦下肢发病
从下肢起病,患者可能表现为一侧肢体在走路时,脚背下垂,路面不平衡容易绊到,但没有麻木和疼感,只表现为走路越来越困难,下肢发病临床相对少见。
✦口腔肌肉发病非常罕见
第三种是患者说话不利索,此种临床最少见。疾病开始是说话不利索,感觉大舌头,容易与脑卒中相混淆,但又有区别。脑卒中患者出现的说话不利索是突发的,渐冻症则是逐渐出现说话不利索,是一个渐进过程,接着会出现吞咽困难。
早期发病主要表现为以下的特征:
注:肉跳可能是渐冻症早期比较明显的特征之一。
什么是肉跳?
肌肉出现不能控制的颤动,就是我们通常说的“肉跳”,其实是一群肌肉细胞不规则的不随意的收缩所引起的,在医学上称为肌束颤动(束颤), 肉跳可以仅发生在局部一小群肌肉,如眼皮跳动,也可以是较广泛地面部、肢体、躯干肌肉跳动。
肉跳也可分为两种情况,一种是良性的,另一种可能是渐冻症导致的。
良性“肉跳”常见的原因:运动、急性病毒感染、甲亢、手足抽搐、药物使用、焦虑等,其中,长时间运动是最主要的原因。
上述的良性“肉跳”,当然不是“渐冻症”了,但是,如果肌肉的跳动伴有肌肉的无力、萎缩,就应该高度警惕,可能的疾病包括:运动神经元病(渐冻症)、周围神经病变及少数的肌肉疾病,患者要尽快到神经内科神经肌肉疾病亚专科就诊!
发病共性
这三种发病情况都有一个共性,即感觉上没有特别明显的麻木和疼痛感。
注:上肢起病容易与颈椎病相混淆;下肢发病容易被怀疑成腰椎间盘突出;语言或吞咽困难发病时易与脑卒中相模糊。
► 中期
肌萎缩侧索硬化的病情是逐渐发展的,每个人的疾病表现不同,发展的速度也会不同,一般至少需要1年,通常不会超过5年。
随着病情的发展到了中期,可能会出现运动无力、呼吸困难等症状。
•吞咽困难
中期的肌萎缩侧索硬化症患者,由于身体内的神经系统受到了损伤,会连带咽喉周围的神经也受到一定的损害。这种情况严重时会压迫到患者的气管,就会导致患者出现吞咽困难的症状。
•肌肉无力
这种症状也是肌萎缩侧索硬化症中期患者比较常见的一种症状,这是由于患者的神经受到了损坏,导致大面积的肌肉和肌张力出现了减退的情况。这种情况严重时会使肌肉出现无力的症状,随着病情的发展,这种症状会更加明显,严重时会使患者丧失自理能力。
•呼吸受阻
当肌萎缩侧索硬化症中期的患者病情严重时,就会使患者的脑干神经元造成损害。一旦脑干神经元系统遭到破坏,就会使患者出现呼吸受阻的情况,严重时还可能会丧失说话能力,只能靠呼吸器来维持生命。
一小部分患者可出现运动系统以外的表现,如痴呆、感觉异常和膀胱直肠功能障碍等,少部分患者还可出现眼外肌运动障碍。
► 晚期
进入病程后期,除眼球活动外,全身各运动系统均受累,累及呼吸肌,出现呼吸困难、呼吸衰竭等。渐冻症晚期症状有肌肉萎缩、四肢僵硬等,具体如下:
•肌肉萎缩
肌肉萎缩明显,有肌无力、肌挛缩、四肢无力、不能动,有些患者出现舌肌萎缩、肌肉痉挛、病理反射阳性、腱反射亢进、吞咽困难、饮水呛咳,需要呼吸机辅助治疗;
•四肢僵硬
四肢僵硬:不能动弹,通过面部眼球活动来表达,称为闭锁状态,需要置胃管支持对症治疗,维持生命体征;
•体征紊乱
体征紊乱:呼吸、心跳、血压波动紊乱,以及全身电解质紊乱、内环境失衡。
渐冻症还会导致一些严重的并发症,例如营养不良、感染、压疮(褥疮)、沮丧、焦虑等问题。
肌萎缩侧索硬化(ALS)的患者可能因控制吞咽的肌肉损伤而出现营养不良和脱水。他们将食物、液体或唾液吸入肺部的风险也更高,这可能引起感染性肺炎。
注意
肌萎缩性侧索硬化症通常不会影响大脑或导致认知(思维)问题。然而,缺乏足够的营养会导致认知障碍,而这种疾病对身体造成的破坏性影响会导致抑郁。
一些患有肌萎缩性侧索硬化症的人在记忆和决策方面会存在问题,而另一些患者则会最终确诊患有额颞叶痴呆症。
值得注意的是:
一些ALS 患者的胃肠道不适其实是早于神经系统症状的。
年 龄
尽管该病可在任何年龄发作,但症状最常出现在 55 至 75 岁之间。
注:也有数据认为该病风险随着年龄增长而增长,最常见在40-65岁左右。
也有个别儿童渐冻症案例。
性 别
男性比女性更容易患肌萎缩侧索硬化。然而,随着年龄的增长,在70岁之后,男女之间的差异消失了。
生理指标
➤ 代谢类疾病
糖尿病:
糖尿病 和 ALS 之间实际的临床和病理生理学相关性尚不清楚,目前研究如下:
糖尿病对老年人 ALS 的发生具有保护作用,而对年轻受试者则相反。
预先存在的胰岛素依赖型糖尿病与较高的 ALS 风险相关(OR 5.38,95% CI 1.87-15.51)
➤ 炎症
有几条证据表明炎症是 ALS 的主要组成部分。通常,免疫细胞不会大量存在于中枢神经系统中。然而,肌萎缩侧索硬化患者的神经系统中存在免疫细胞,这些细胞会引起神经炎症(中枢神经系统炎症,包括大脑)。
其他包括氧化应激、线粒体功能障碍、谷氨酸毒性等都与引起肌萎缩侧索硬化或促进其进展有关。
这在后面章节会详细阐述。
生活方式:抽烟
吸烟和烟草烟雾暴露可能通过炎症、氧化应激和香烟烟雾中存在的重金属或其他化学物质引起的神经毒性增加 ALS 的几率。
美国的一项大型前瞻性研究(414493名男性和572736名女性参与者;617名男性ALS死亡,539名女性ALS死亡)报告称,甲醛暴露会增加ALS的风险,甲醛是香烟烟雾的一种成分。
身体创伤
头部创伤或电烧伤都可能与ALS相关。
一项研究招募了n=188名ALS患者,并从相同地区的普通人群中进行了2:1的对照。
头部创伤与ALS风险增加相关(调整后的比值比[OR]1.60 95%置信区间[CI]1.04-2.45),对症状发作前10年或更长时间发生的损伤影响更大(P=.037)。
报告严重电烧伤的患者ALS风险增加(调整后OR 2.86,95%CI 1.37-6.03),30岁后烧伤的比值比最高(OR 3.14),症状发作前10年或更长时间烧伤的比值比值比(OR 3.09).
繁重的劳动
一项早期的研究发现,繁重的劳动是一个危险因素,一项针对新英格兰建筑工人的病例对照研究(109例,253例对照)发现患病几率上升(OR = 2.9, 1.2–7.2).
注:具体关于身体活动在ALS病因中的作用的证据仍然没有定论。
种 族
白种人和非西班牙裔最有可能患上这种疾病。
研究人员正在研究环境因素的影响,例如接触有毒或传染性物质、病毒、饮食、抽烟、职业因素。
居住因素和化学品
ALS与许多化学品的接触有关,大多数支持证据都涉及农药、化肥、除草剂和杀虫剂等农业化学品。
澳大利亚报告了179对病例对照的类似发现。经常园艺(非职业接触)与ALS显著相关(OR = 6.64,95%置信区间 = 1.61–27.4)。按性别分层后,仅在男性中显示出显著的相关性(OR = 4.90,95%置信区间 = 1.11–21.7).
对60岁以下的人来说,靠近工业的住宅和污水处理厂或农场之间的联系也得到了证明。住在这些地方附近可能会接触到各种空气、水和土壤污染物。
最近,一项对66对年龄、种族和性别匹配的病例和对照进行的研究发现,职业接触杀虫剂与ALS之间的显著关联(OR = 6.50,95%置信区间 = 1.78–23.77).
重金属
重金属(铅、汞、镉等),尤其是铅,可能在ALS的发病和进展中发挥多种作用。
接触到铅或其他物质可能的场所或职业:
从事机械、绘画或建筑工作与ALS有关,其他职业包括农业、渔业、伐木和狩猎也可能与ALS有关。
在许多病例对照研究中,铅暴露与ALS有关。在新英格兰(109例和256例对照),血铅和骨铅水平升高与ALS发病率增加相关(OR = 1.9,95%置信区间 = 1.4–2.6).
在波士顿(95例和106例对照),自我报告的铅暴露与ALS相关(p = 0.02).
此外,还研究了其他金属,特别是汞和镉,但结果也不一致。重金属暴露(铅和汞)的复合测量与ALS风险增加显著相关(OR = 3.65). 虽然铅暴露与ALS相关,但尚未显示汞、镉或其他金属的关联和因果机制。
在一项小型日本研究(21例,36例对照)中,ALS患者晚期血浆和血细胞中的汞和硒水平显著低于对照组,这是由于他们的残疾,包括食用液体饮食。
在意大利进行的一项非常小的研究(9例)显示,患者的血镉水平明显高于对照组(排除了功能受损最严重的晚期患者)。
注:将不同金属的暴露分组在一起可能会导致暴露分类错误和检测关联的能力下降,这是目前和早期研究的局限性。
灰尘/纤维/烟雾
几项研究间接表明ALS职业性接触颗粒物。在某些职业环境中发现的空气尘埃、烟雾和纤维可能是空气中颗粒物的重要暴露。在许多研究中,已经对颗粒物暴露与神经系统结果进行了检查,并在几种职业环境中与ALS相关。
注:被调查的职业环境(兽医、美发师、分级和分拣师)可能会增加溶剂、金属和可能的其他介质的共暴露。没有研究直接评估暴露在环境中的颗粒物与渐冻症之间的关系。
辐射/电磁场
辐射已被认为是ALS的潜在危险因素,因为脊髓神经根病表现可能由长潜伏期的电损伤引起。
此前有三项研究报告了辐射或电磁场暴露之间的关联;有必要对此类风险进行进一步调查。
电气相关职业(OR = 1.3, 95% CI = 1.1-1.6),以及暴露于电磁场(OR = 2.3,95%置信区间 = 1.29–4.09)与ALS相关。
在美国五家大型电力公司(139905名男性)的队列死亡率研究中,ALS的死亡率与电磁场暴露工作的时间有关(RR = 2.0,95%置信区间 = 1.0–9.8) .
注意
由于以上部分实验样本量较小,再加上可能存在其他因素干扰,因此,应当谨慎关联。
大多数ALS病例都被认为是偶发性的。这意味着该病似乎是随机发生的,没有明确相关的危险因素,也没有该病的家族史。尽管散发性ALS患者的家庭成员患此病的风险增加,但总体风险很低,大多数人不会患ALS。
家族性(遗传性)ALS
大约5%到10%的ALS病例是家族性的,这意味着一个人从父母那里遗传了这种疾病。ALS的家族形式通常只需要父母一方携带致病基因。十几个基因的突变被发现会导致家族性ALS,例如C9ORF72、SOD1、SPTLC1、FUS、TARDBP、TDP-43、OPTN、TBK1等基因。
关于基因突变的作用机理将在下一章节详解。
ALS 的病理生理过程是多因素的,反映了遗传和环境因素之间复杂的相互作用。
本章节从以下几大方面来具体阐述渐冻症的发病机理:
截止目前,有几十个基因与肌萎缩侧索硬化有关,这些基因的突变约占所有家族性病例的三分之二。
1993 年至 2016 年间 ALS 的遗传图谱
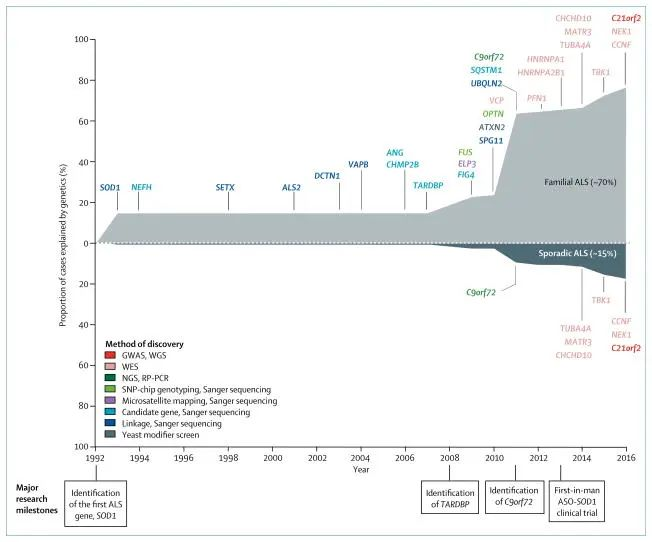
doi:10.1016/S1474-4422(17)30401-5
家族性肌萎缩侧索硬化病例约占所有肌萎缩侧索硬化病例的 10%。在这 10% 中,大约 70% 可以用遗传学来解释。
SOD1 :涉及运动神经元、神经胶质细胞和骨骼肌细胞
ALS家族病例与Cu/Zn超氧化物歧化酶(SOD1)的突变有关,这是一种保护细胞免受超氧化物自由基有害影响的关键抗氧化酶,表明SOD1功能的改变和/或异常的SOD1聚集对促进ALS发病有很大影响。
SOD1代谢的改变影响许多细胞功能,涉及不同的细胞类型(即运动神经元、神经胶质细胞和骨骼肌细胞),这些细胞类型可能相互作用以产生病理表型。
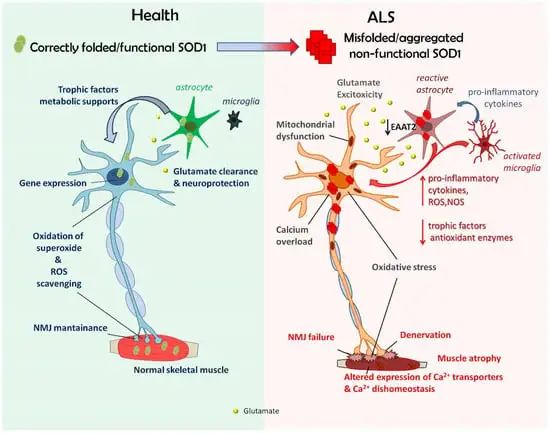
doi.org/10.3390/antiox11040614
在家族性肌萎缩侧索硬化症(FALS)和散发性肌萎缩侧索硬化症(SALS)中均发现了铜/锌超氧化物歧化酶-1(SOD1)基因,但在中国肌萎缩侧索硬化患者中研究较少,且大样本研究较少。
四川大学华西医院神经内科的 499 名 ALS 患者(487 名 SALS 和 12 名 FALS),并SOD1突变频率在SALS中为1.03%(5/487),在来自中国西南地区的FALS中为25%(3/12)。
OPTN :通过功能丧失突变引起ALS
OPTN是唯一已知的被认为通过功能丧失突变引起经典 ALS 的基因。
OPTN通常抑制 NF-κB 活性,这是先天免疫反应的一个关键组成部分,并且在其缺失或突变形式下,NF-κB 易位至细胞核并促进大量促炎基因的表达,从而增强小胶质细胞介导的神经炎症。
注:OPTN是否直接影响 NF-κB 是一个有争议的话题;然而,大多数研究都认为突变型OPTN与 NF-κB 通路失调有关,从而促进促炎反应。
TBK1 :参与多种 ALS 相关通路,如自噬和神经炎症
TBK1的突变与肌萎缩侧索硬化有关。TBK1 蛋白结合并磷酸化许多蛋白质,包括 OPTN 和 sequestosome-1/p62,并调节先天免疫和自噬。
TBK1 属于参与先天免疫信号通路的 IKK 激酶家族;具体而言,TBK1 是 1 型干扰素的诱导剂。TBK1 在自噬和线粒体自噬中也起着重要作用。
TBK1 的突变可能导致自噬受损,自噬缺陷可能导致运动神经元中蛋白质聚集体、自噬体和受损线粒体的积累。神经元损伤可能触发神经元周围细胞的先天反应,导致神经炎症,引发ALS。
在大约 1% 的家族性 ALS 患者和大约 1% 的散发性 ALS 患者中发现了TBK1突变。
TNIP1 :炎症信号传导的关键抑制因子
根据一项针对中国、欧洲和澳大利亚人群的大型全基因组关联研究,TNIP1的突变与肌萎缩侧索硬化有关。
TNIP1 在功能上与 OPTN 相关,并抑制 NF-κB 活化和肿瘤坏死因子 (TNF) 诱导的 NF-κB 依赖性基因表达。TNIP1 功能障碍或缺陷可能使健康细胞容易对其他无害的 TLR 配体暴露产生炎症反应。TNIP1还与几种免疫疾病有关,包括狼疮和牛皮癣。
SQSTM1 :损害聚集蛋白降解和自噬引起ALS
在 ALS 患者中发现了几种新的 SQSTM1突变。
SQSTM1基因编码 p62,一种调节自噬和氧化应激的主要病理蛋白(下图)。
自噬和炎性体通路在肌萎缩侧索硬化中的相互作用
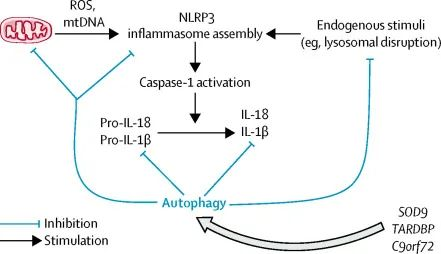
doi.org/10.1016/S1474-4422(18)30394-6
SQSTM1中的突变会改变 p62 的功能,并通过损害聚集蛋白降解和自噬来促进 ALS 的病理生理学。
VCP : VCP突变会影响肌肉、骨骼和大脑
VCP基因的突变与家族性和散发性肌萎缩侧索硬化有关。
VCP 是自噬和泛素化-蛋白酶体途径(另一种降解和处理受损、错误折叠和过量蛋白质的细胞机制)的重要组成部分。VCP中的突变会损害整体蛋白质降解并导致 TDP-43 沉积,从而导致包涵体肌病、Paget 病、额颞叶痴呆或 ALS. VCP突变是 1%-2% 的家族性ALS 病例的原因。
CX3CR1 :突变会损害小胶质细胞的神经保护反应
CX3CR1 是小胶质细胞上的一种特异性受体,可与 fractalkine(一种从运动神经元释放的蛋白质)结合,从而促进神经保护反应。受体 CX3CR1 的突变会损害 fractalkine 结合并导致 ALS 患者的生存时间缩短,但不会增加患病风险。
CX3CL1/CX3CR1 通讯系统具有抗炎和神经保护作用,在维持自噬活性中起重要作用。
然而,CX3CR1是一种 ALS 疾病修饰基因;CX3CR1的多态性会损害先天免疫小胶质细胞的神经保护反应,为其在 ALS 疾病发病机制中对神经炎症的作用提供证据。
这些突变基因提供了免疫系统诱导的炎症机制参与 ALS 发病机制的直接证据。此外,这些突变基因表明自噬抑制了 NLRP3 炎症小体的激活,并且这些免疫相关基因的突变阻止了炎症小体介导的激活的生理抑制,因此激活了炎症通路(IL-1β 和 IL-18 ) 并有助于 ALS 发病机制。
TARDBP :突变对细胞造成损害
ARDBP的突变与 ALS 和额颞叶痴呆的家族病例有关。
TARDBP基因提供了构建一种称为TDP-43的蛋白质的指令,这种蛋白质通常位于细胞核中,并参与蛋白质生产的各个步骤。TARDBP基因突变导致TDP-43蛋白在细胞核外形成聚集体(团块),对细胞造成损害。
约97%的ALS患者中发现了TDP-43聚集体,包括TARDBP基因没有突变的人。
C9orf72 :与神经变性、炎症、免疫相互作用有关
多项研究探索了C9orf72介导的疾病的致病机制。C9ORF72 与神经变性、炎症和我们与环境的免疫相互作用的调节有关。
C9orf72 突变难以发现的原因之一是该突变位于C9orf72 基因的一个内含子中。
在 ALS 患者的C9orf72中记录了小胶质细胞炎症活动的显着增加,并且与更快的疾病进展相关。
注:激活的小胶质细胞是 ALS/FTD 病理学的普遍特征,C9orf72在骨髓细胞中具有重要作用。
三种主要的疾病机制:C9orf72蛋白的功能丧失和C9orf73重复RNA或由重复相关的非ATG翻译产生的二肽重复蛋白的功能毒性增加。
注:NEK1 和 C21orf2 相互作用,参与微管组装、DNA 损伤反应和修复以及线粒体功能。
MATR3 :突变与神经肌肉功能退化相关
MATR3 是一种 RNA 和 DNA 结合蛋白,可与TDP-43 相互作用,TDP-43 是一种与ALS和额颞叶痴呆相关的疾病蛋白。
在具有MATR3突变的 ALS 患者中,上运动神经元和下运动神经元受到影响,生存期为 2-12 年。
过表达MATR3 蛋白的转基因小鼠出现后肢麻痹和肌肉萎缩,表明神经肌肉功能对 MATR3 水平敏感。
2014 年,MATR3 的四个突变(p.S85C、p.F115C、p.P154S 和 p.T622A)通过外显子组测序在四个单独患有 ALS 或同时患有 ALS 和痴呆症的欧洲血统家族中被鉴定出来。自 2014 年以来,已描述了 11 种其他变异,主要发生在散发性 ALS 患者中。
CCNF :突变导致异常的蛋白停滞
CCNF是Skp1-cullin-F-box E3泛素连接酶复合物的底物识别成分,该复合物负责用泛素标记蛋白质,并通过泛素蛋白酶系统标记其降解。
CCNF的突变可能导致异常的蛋白停滞,而TDP43蛋白病可能会加剧这种情况。因此,提高蛋白质清除率或减少泛素化的疗法可能是可行的治疗方法。
其他相对较为罕见的突变基因还包括:
CCHHD10、TUBA4A等。
与肌萎缩侧索硬化相关的基因之间的相互作用
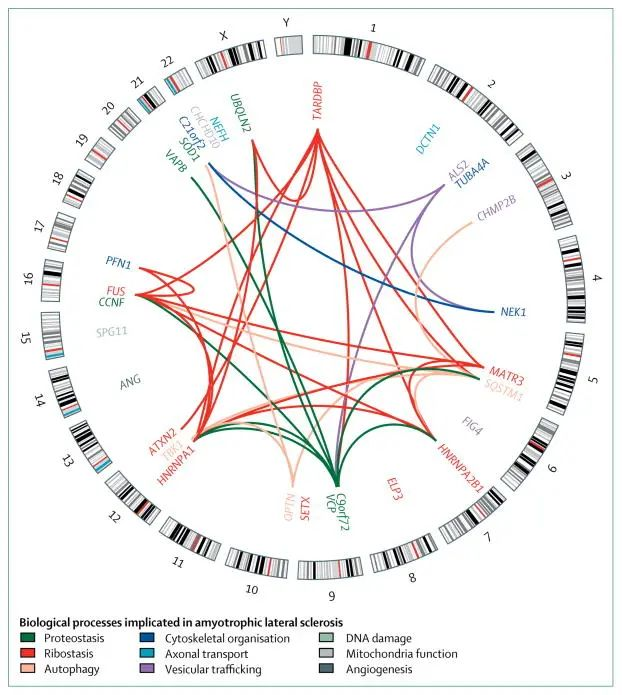
10.1016/S1474-4422(17)30401-5
外圈是核型表意文字,显示24条染色体(22条常染色体,X染色体,Y染色体);内圈显示每个基因的位置。基因之间的联系代表蛋白质或基因水平的相互作用。交互数据是从交互数据集的生物通用存储库中获得的。黑线表示细胞遗传学条带模式。与基因或相互作用有关的生物过程用颜色表示。
越来越多的证据表明整个 ALS 的免疫系统都存在异常。免疫细胞被激活并导致 ALS 周围和中枢神经系统中的慢性促炎微环境。
ALS的促炎症是全身性的,外周免疫系统(PIS)和中枢免疫系统(CIS)之间存在串扰。迄今为止,串扰还没有得到很好的定义。
随着对 ALS 的深入了解,研究人员已经意识到这两个系统持续互动和交流的重要性。CNS驻留免疫细胞和外周免疫细胞通过免疫分子相互作用。
功能失调的中枢神经系统屏障,包括血脑屏障(BBB)和血脊髓屏障(BSCB),为“串扰”打开了大门,也受到炎症环境的调节。因此,慢性全身炎症导致MN死亡、运动神经元轴突受损和神经肌肉接头功能障碍。
PNS和CNS之间的免疫串扰示意图
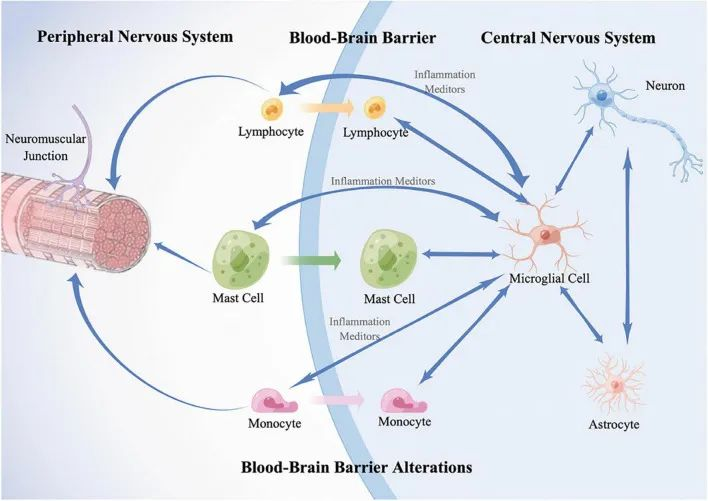
doi: 10.3389/fnagi.2022.890958
双头箭头表示两个细胞的通信。蓝色单箭头表示细胞释放炎症介质并影响其目标。橙色、绿色和紫色箭头分别表示外周细胞浸润到中枢神经系统。
在中枢神经系统中,常驻免疫细胞小胶质细胞被激活并通过释放促炎或抗炎物质(例如细胞因子)并与浸润的外周免疫细胞相互作用来介导神经炎症;星形胶质细胞控制小胶质细胞的活化、迁移和增殖。
在 PNS 中,常驻免疫细胞(包括 T 淋巴细胞、肥大细胞和单核细胞)被激活并沿外周运动神经和神经肌肉接头浸润。同时,它们渗入由小胶质细胞衍生的炎症介质触发的中枢神经系统。
此外,CNS 屏障功能障碍,包括血脑屏障 (BBB) 和血脊髓屏障 (BSCB),有助于外周免疫细胞浸润并加速有害相互作用。因此,跨越两个系统的炎症反应会导致运动神经元 (MN) 死亡、MN 轴突损伤和神经肌肉接头功能障碍。
▋ ALS中的中枢神经系统普遍存在炎症
神经胶质细胞,包括小胶质细胞和星形胶质细胞,触发神经炎症反应,与浸润的外周免疫细胞相互作用,最终诱导或加速 ALS 中枢神经系统的神经元死亡。
小胶质细胞 是中枢神经系统的常驻先天免疫细胞,通过释放包括细胞因子和趋化因子在内的免疫分子来介导神经炎症。小胶质细胞激活是异质的,取决于病理损伤的性质。
越来越多的研究证明,小胶质细胞在疾病发作时表现出抗炎表型并保护运动神经元,而终末期小胶质细胞转变为促炎表型并加重 ALS 中运动神经元的神经变性。
活化的小胶质细胞通过分泌活性氧和促炎细胞因子(包括 IL-1β、IL-6 和 TNFα)促进细胞毒性。
星形胶质细胞 是大脑中最常见的胶质细胞,维持中枢神经系统屏障,分泌神经营养和神经保护因子,调节神经递质摄取和循环,促进神经发生。研究已经确定星形胶质细胞作为免疫调节剂的作用,因为它们可以控制小胶质细胞的激活、迁移和增殖。
因此,星形胶质细胞和小胶质细胞释放的炎性细胞因子可能促进谷氨酸兴奋性毒性,从而将神经炎症和兴奋性毒性细胞死亡联系起来。
当达到临界阈值时,反应性星形胶质细胞和小胶质细胞可能引发不可逆的病理过程,随后导致 ALS 患者运动神经元的非细胞自主死亡。
在大脑和其他神经组织中,细胞因子在神经元、星形胶质细胞和小胶质细胞之间进行交流。
ALS 中主要病理生理事件的示意图
编辑
炎症通路失调不仅存在于 10% 的具有阳性家族史的 ALS 患者中,而且存在于 90% 的散发性 ALS 患者中。
散发性 ALS 患者的 CNS 反应性小胶质细胞和星形胶质细胞炎症也有所增加,并激活了浸润 CNS 的外周单核细胞和淋巴细胞。在散发性 ALS 患者中引发这种免疫失调的原因尚不清楚。炎症细胞因子 IL-6 由转基因 mSOD1 小鼠和 ALS 患者中活化的巨噬细胞和小胶质细胞分泌。
▋ ALS 外周的免疫激活
ALS 中存在外周免疫异常。一般来说,慢性外周免疫反应在 ALS 中是促炎性的。淋巴细胞、单核细胞(包括巨噬细胞)、中性粒细胞、自然杀伤 (NK) 细胞和肥大细胞 (MC) 是外周常驻免疫细胞。发现 ALS 患者血液中的总白细胞计数升高。
在外周血中大多数研究表明,神经保护性 CD4 T 淋巴细胞水平降低,而 ALS 患者的 CD4 T 淋巴细胞亚群,调节性 T 细胞 (Tregs) 减少和功能障碍。在 ALS 中,外周血中细胞毒性 CD8 T 淋巴细胞的数量存在争议。NK T 淋巴细胞被认为对 ALS 有害,并且在 ALS 患者的外周血中增加。
B 淋巴细胞仅在 ALS 中被讨论,研究表明它们在 ALS 的发病机制中起补充作用。据报道,单核细胞比例发生了变化,ALS 患者的循环单核细胞优先分化为促炎表型。外周血中的中性粒细胞数量增加,并显示与疾病进展显着相关。
NK 细胞是先天免疫细胞并介导细胞毒性。ALS 患者血液中的 NK 细胞水平升高,可能具有致病性。
在 ALS 小鼠中显示循环肥大细胞数量增加,而在 ALS 患者中缺乏证据。
远端轴索病变是 ALS 公认的病理特征 。在 ALS 中观察到活化的肥大细胞、巨噬细胞和中性粒细胞沿着坐骨神经和骨骼肌中退化的运动轴突募集。
外周免疫细胞也可渗入中枢神经系统,对运动神经元和神经胶质细胞产生影响,下文将对此进行讨论。外周免疫细胞在其预后作用方面的讨论越来越多。在这方面,随着技术和认识的发展,研究人员已经转向探索特定人群或单个骨髓亚群来对患者进行分类或监测。
▋ ALS中枢神经系统屏障的改变
CNS 屏障由一层内皮细胞形成,由内皮间紧密连接 (TJ)、粘附蛋白和细胞质连接。称为基底层 (BL) 的基底膜被周细胞和星形胶质细胞末端包裹,支持内皮细胞和相关的周细胞。
它们构成了 CNS 的物理屏障,而 CNS 的生化屏障是由各种运输系统赋予的。
在 ALS 患者和小鼠的早期观察到脑屏障的改变,表明损伤可能有助于发病机制。
这些变化总结如下:
CNS 障碍是中枢免疫系统和外周免疫系统之间基于体液的交流的中心点。更好地了解 CNS 屏障的完整性或功能是如何改变的,可能会提供终止 ALS 中有害串扰的方法。
★ 血脑屏障 (BBB) 和血脊髓屏障:维持CNS稳态
血脑屏障 (BBB) 和血脊髓屏障 (BSCB) 是基于毛细血管的屏障,分别将大脑和脊髓组织与外周血液循环分开。这两个屏障在形态上相似,因为它们都位于无孔毛细血管内皮细胞内,毛细血管内皮细胞通过紧密连接和粘附分子密封在一起。
虽然 BSCB 具有比 BBB 更高的连接渗透性,但这两个屏障严格调节营养物质、内源性化学物质、代谢物和异生素进出中枢神经系统 (CNS) 的细胞旁和跨细胞交换。 因此,它们在维持 CNS 微环境的稳态方面发挥着重要作用,这对于正常的神经元功能至关重要。
此外,这两种屏障都高度表达各种外源性外排传输泵,这些泵是 ATP 结合盒 (ABC) 转运蛋白超家族的成员。
★ 转运蛋白在两个屏障的表达水平的变化,改变大脑和脊髓组织中的药物浓度
P-糖蛋白 (P-gp)、乳腺癌耐药蛋白 (BCRP) 和多药耐药相关蛋白 2 (MRP2) 等多种外源性转运蛋白的管腔毛细管表达,是向大脑和脊髓输送药物的主要障碍脐带,因为它们的集中外排活性将药物从屏障内皮质膜或胞质溶胶隔室泵回血液以进行后续清除。
注:P-gp:P-糖蛋白是一个比较常见的保护细胞免受外来有害分子入侵的分子泵,它位于细胞膜上,不停的“搜查”着外来的疏水分子,就如同一个守护细胞的“保安”。
这些转运蛋白在两个屏障的表达水平的变化可以改变大脑和脊髓组织中的药物浓度。因此,了解 BBB 和 BSCB 的转运蛋白活动对于更准确地预测 CNS 中的药物药代动力学和药效学至关重要。
★ 利鲁唑在 CNS 中的全部治疗功效受这些转运蛋白的限制
在一些 ALS 患者的 CNS 屏障处诱导 P-gp 是可能的,并且可能解释了确定有效的 ALS 药物治疗的困难。此外,目前 FDA 批准的唯一用于 ALS 管理的药物利鲁唑被建议作为 P-gp 和BCRP底物。
由于利鲁唑是两种 ABC 异源外排转运蛋白 P-gp 和 BCRP 的底物,利鲁唑在 CNS 中的全部治疗功效可能会受到 BBB 和 BSCB 上的这些外排转运蛋白的限制。
最近在体内使用 ALS 小鼠模型的研究表明,在疾病进展的晚期,P-gp 和 BCRP 转运活性和表达在 CNS 屏障中被诱导。这些诱导可能会进一步限制利鲁唑在中枢神经系统中的治疗功效。
ALS 诱导的 P-gp 上调可进一步限制利鲁唑穿过 CNS 屏障的渗透性,并降低其在神经元靶位点的浓度,从而降低其治疗效果。在这种情况下,应在预期在 CNS 屏障处诱导 P-gp 的患者的整个 ALS 进展过程中,研究作为 P-gp 底物的 CNS 药物疗法的剂量或治疗窗口的适当调整。
总之,防止 P-gp 诱导或底物相互作用的药理学干预可用于提高在 CNS 屏障处显示 P-gp 诱导的 CNS 疾病(例如 ALS)的治疗效果。
★ ALS 物理屏障完整性的破坏
多项研究发现 ALS 患者 CNS 屏障的超微结构发生改变,包括微血管内皮细胞肿胀和细胞质空泡化、周细胞覆盖率降低以及 ALS 患者脊髓中星形胶质细胞末端足突与内皮细胞的分离。
在脑干、颈椎和腰椎脊髓中也观察到超微结构改变,但在 ALS 小鼠的运动皮层中没有观察到。已注意到这些改变发生在疾病的早期阶段,并随着疾病的进展而恶化。
TJ 由多种蛋白质形成,例如 zonula occludens-1 (ZO-1) 和 occludin,并阻止溶质的细胞旁运动。在 ALS 患者和小鼠的脊髓中观察到 TJ 和粘附蛋白(如 ZO-1 和 occludin)的表达显着降低。尽管粘附蛋白发生了变化,但在电镜下发现 ALS 患者死后脊髓中 TJ 的形态结构保存完好。尽管保留了 TJ 的形态结构,但 CNS 中内源性蛋白质的检测表明 CNS 屏障的细胞旁通透性和渗漏性增加。
ALS 患者和小鼠中均观察到基底层( BL )增厚:
内皮细胞的脱离使 BL 暴露于 BL 内的血浆蛋白、纤维蛋白和胶原蛋白 IV,然后积累,导致 BL 增厚。由于在 ALS 小鼠的早期阶段检测到 BL 异常,这些发现表明它可能作为补偿机制或修复过程发生。
基于这些发现,超微结构异常和 TJs 粘附蛋白表达减少可能导致连接完整性受损和细胞旁通透性增加,从而允许外周物质和细胞进入中枢神经系统。因此,它促进了外周免疫系统 和 中枢免疫系统 的交流,并加速了全身性炎症反应。
★ 生化中枢神经系统屏障的功能调节
生化中枢神经系统屏障由各种运输系统赋予,例如 ATP 结合盒 (ABC) 蛋白。它们可以有效地从内皮细胞中排除各种内源性和外源性毒素,以维持细胞稳态。研究最深入的 ABC 蛋白 P-糖蛋白 (P-gp) 是在 CNS 屏障上表达的脂溶性小分子的主要外排转运蛋白。
P-gp 的表达和活性在 ALS 患者和小鼠中均上调。 肿瘤坏死因子 α (TNF-α) 和生长因子-β 1(TGF-β1) 显示可上调小鼠和大鼠中 P-gp 的表达和活性。 由于 ALS 患者和小鼠体内 TNF-α 和 TGF-β1 水平升高,它们与 P-gp 的过度表达有关。
此外,星形胶质细胞也被怀疑是依赖于 ALS 基因型的 ALS 中 P-gp 表达增加的原因。例如,共培养的 ALS 相关突变体 SOD1 星形胶质细胞通过分泌 TNF-α、趋化因子和活性氧 (ROS) 等可溶性因子影响附近内皮细胞中的 P-gp。
同时,ALS 相关突变体 C9orf72 星形胶质细胞已被证明对内皮 P-gp 表达没有影响。此外,另一种外排转运蛋白乳腺癌耐药蛋白 (BRCP) 的表达在 ALS 患者和小鼠中上调。
一般来说,CNS 屏障中 P-gp 和 BRCP 丰度和活性的增加表明生化 CNS 屏障界面功能的调节,这可能最终影响 ALS 的发展。
▋ 屏障细胞分泌神经免疫相关物质
屏障细胞,包括内皮细胞、周细胞和星形胶质细胞,分泌神经免疫相关物质以响应外周或中枢免疫细胞的免疫刺激。脑内皮细胞 (BEC) 可以组成型分泌白细胞介素 6 (IL-6)、前列腺素和一氧化氮以响应不同的刺激。
由于 ALS 中周细胞数量减少,其炎症介导作用也可能导致 ALS 病理。与其他屏障细胞相比,周细胞对 TNF-α 最敏感,可以释放 IL-6 和巨噬细胞炎症蛋白-1α(MIP-1α,也称为 CCL3)作为反应。
炎症反应性周细胞通过释放 IL-8 和基质金属蛋白酶 9 (MMP-9) 支持中性粒细胞迁移,从而导致神经炎症的后续发展。
星形胶质细胞在 ALS 的免疫反应中被激活。
一方面,星形胶质细胞通过多种炎症因子控制小胶质细胞的激活、迁移和增殖,并分泌介导单核细胞迁移的 MCP-1 等蛋白质,从而放大 CNS 中的神经炎症。
另一方面,屏障上反应性星形胶质细胞释放的一氧化氮、血管内皮生长因子(VEGF)、胶质细胞源性神经营养因子(GDNF)和MM-9等生化物质调节TJ蛋白的表达和增殖内皮细胞,从而影响 CNS 屏障的完整性和渗透性。
因此,屏障细胞不仅可以将信息从一侧传递到另一侧(如 外周免疫系统 到 中枢神经系统),还参与介导炎症微环境。
在 ALS 中,受损的运动神经元与胶质细胞相互作用,它们释放一定水平的细胞因子和趋化因子,随后募集先天性和适应性免疫细胞浸润 CNS 以促进炎症。
促炎信号从中枢免疫系统传播到 外周免疫系统,从外周免疫系统传播到中枢免疫系统,从而促成了 ALS 的全身炎症环境。
▋ ALS中的细胞因子和趋化因子
许多细胞因子和趋化因子,例如 IL-1、IL-6、TNF 和 CC 趋化因子配体 2 (CCL2),已被证明可以穿过 中枢神经系统屏障,而这些屏障介导它们的运输、渗透和摄取。
一方面,由于免疫细胞的激活,ALS中细胞因子和趋化因子的水平发生显着变化(见表)
另一方面,促炎介质水平升高会增加 CNS 屏障的通透性,直接作用于它们的受体以改变驻留细胞的功能,诱导免疫细胞运输,并加剧屏障破坏和神经炎症。
细胞因子和趋化因子在 ALS 中的主要作用



doi: 10.3389/fnagi.2022.890958
▋ 周围免疫细胞的中枢神经系统浸润
越来越多的证据表明,许多外周血白细胞首先在外周免疫系统中被激活,然后在 ALS 中迁移到中枢免疫系统。
白细胞向中枢神经系统运输的调节是多方面的,取决于白细胞的激活状态、内皮界面的 TJ 复合物以及 中枢神经系统和 PNS 中的炎症微环境。
由于外周白细胞可以很容易地监测,并且鞘内或脑室内与多种风险相关,因此在 ALS 治疗中靶向外周白细胞可能是可行的。因此,需要更好地了解外周免疫细胞如何渗入中枢神经系统。
★ T 淋巴细胞
ALS 中 T 淋巴细胞的浸润是众所周知的。趋化因子和趋化因子受体对于实质浸润至关重要。慢性炎症环境诱导内皮细胞表面白细胞粘附的上调,内皮细胞与 T 淋巴细胞上表达的 CD6 结合,使其进入脑实质。此外,T 淋巴细胞衍生的 TNF-α 和 IL-17 诱导免疫细胞和运动神经元分泌 MM-9,促进 T 淋巴细胞浸润到 CNS。
大量证据强调了 T 细胞亚群之间的差异及其在 ALS 中进入 CNS 的特定机制。例如,内皮细胞分泌 CXCL9、CXCL10、CXCL11、CCL19、CCL21 和 MCP-1 等趋化因子,通过 CNS 屏障募集 CD4 + T 细胞。对神经炎症具有抑制作用的 Treg 细胞被激活并通过CCL5/CCR5 和 CCL6/CCR6 机制募集到 CNS,以抑制疾病早期小胶质细胞的激活。
CD8 + T 细胞显示出强烈的浸润,并通过在活化的小胶质细胞和受损的运动神经元中表达的 MHC-I诱导运动神经元死亡。
★ 肥大细胞
先前研究的结果表明,肥大细胞在 PNS 的早期退化中发挥作用,并对神经元损伤产生连锁反应。后来的研究证实了肥大细胞在 ALS 患者脊髓中的浸润。MC 上受体的表达受激活的小胶质细胞释放的 IL-6、CCL5 和 TNF-α 的影响,从而调节肥大细胞激活和 CNS 募集。
此外,肥大细胞可以向 TJs 和细胞外基质成分释放蛋白酶,从而影响 BBB 的通透性和完整性,导致 肥大细胞侵入 CNS。
★ 单核细胞
外周单核细胞可以很容易地取样。越来越多的证据表明,浸润性单核细胞来源的巨噬细胞是中枢神经系统小胶质细胞的同系物,并通过 ALS 中受损的血脑屏障进入中枢神经系统。人血单核细胞在体外很容易获得并且很容易分化成巨噬细胞。
有限数量的活化外周单核细胞浸润中枢神经系统, 并影响 ALS 中的神经炎症。先前的研究表明 ALS 中单核细胞的比例发生了变化。在快速进展的 ALS 患者中,外周循环中的单核细胞通常处于促炎状态。最近,外周单核细胞已被证明可以浸润 CNS,这与 ALS 中运动神经元存活率的提高有关,但浸润可能是有限的。
此外,单核细胞衍生的巨噬细胞在 ALS 中被激活。激活的巨噬细胞通过在疾病期间错误折叠蛋白质清除来发挥神经保护功能。巨噬细胞也显示出对中枢神经系统的有限浸润。
中枢神经系统中单核细胞的积累是由于浸润细胞的增殖,而不是积累的循环单核细胞的浸润。
★ Treg 细胞
Treg 是免疫耐受的细胞介质,具有抑制各种类型免疫反应的能力。Tregs 的主动抑制在控制自身抗原反应性 T 淋巴细胞和诱导体内外周耐受中起着关键作用。
Tregs 可防止激活的 Tresps 的激活和效应功能。
在从患有快速进展的 ALS 患者分离出的血液白细胞中,Tregs 的数量及其 FOXP3 蛋白表达均减少,并且这些水平与疾病进展率呈负相关。
FOXP3、TGF-β、IL-4 和 GATA-3(一种 Th2 转录因子)的 mRNA 水平在快速进展的患者中降低,并与进展率呈负相关;FOXP3 和 GATA3 都是进展率的准确指标。
在缓慢和快速进展的患者之间没有发现 IL-10、TBX21(Th1 转录因子)或 IFN-γ 表达的差异。
在表观遗传学上,Treg 特异性去甲基化区域的甲基化百分比在 ALS Treg 中更高。在体外扩增后,ALS Tregs 恢复了对对照 Tregs 水平的抑制能力,这表明扩增的 Tregs 的自体被动转移可能提供一种新的细胞疗法来减缓疾病进展。
★ 其他免疫细胞:中性粒细胞、自然杀伤细胞
很少有研究讨论中性粒细胞和 NK 细胞在神经免疫串扰中的作用。然而,考虑到外周血中中性粒细胞和 NK 细胞数量的增加与疾病进展之间存在显着相关性,以及它们在先天免疫反应中的作用, 它被认为以复杂的方式影响中枢神经系统的神经炎症。
例如,终末期 ALS 小鼠在脊髓中显示出高 NK 细胞频率。
NK 细胞衍生的 IFN-γ 诱导小胶质细胞向炎症表型发展,调节 CCL2 的释放,CCL2 是一种趋化因子,可调节来自运动神经元的 CNS 浸润,并损害 Treg 细胞迁移。
小 结
上文充分讨论了涉及中枢免疫细胞和外周免疫细胞、中枢神经系统屏障、细胞因子和趋化因子的串扰。所有这些元素的功能障碍导致运动神经元的非纤维素性死亡。这些交流在ALS的全身炎症环境中起着重要作用。
中枢神经系统屏障在串扰中起着至关重要的作用。值得注意的是,神经炎症的影响是双重的,因为它在疾病期间发挥神经毒性或神经保护作用。
使免疫串扰和稳态正常化而不是抑制炎症,可能为今后的研究提供潜在的治疗目标和方向。
与健康人相比,肌萎缩侧索硬化症(ALS) 患者的肠道微生物组发生了变化,其中包括潜在保护性菌群和其他具有促炎的菌群失衡。
编辑
最初进行的研究的特点是小规模和精选的患者队列,甚至只有不到 10 个个体,提供了相对一致的数据来支持 ALS 中的生态失调。
涉及肌萎缩侧索硬化的微生物群的系统发育分布
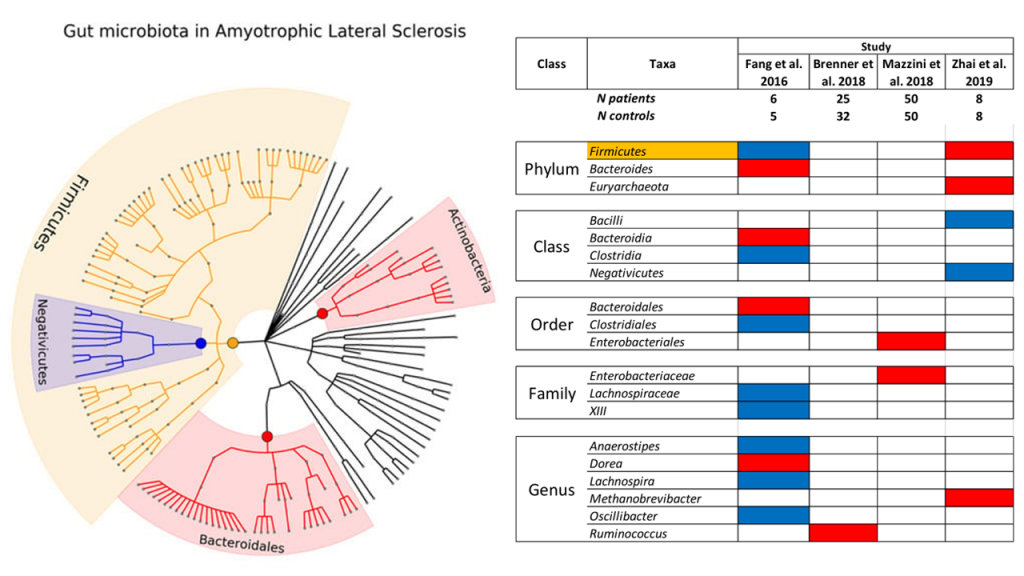

doi.org/10.3390/ijms232213665
以上数据来自六项关于 ALS 的研究,共涉及 159 名 ALS 患者和165名健康对照者。橙色表示不一致的结果,蓝色表示相对丰度下降,红色表示相对丰度增加。
综合一些研究报道,ALS 患者的肠道菌群主要变化如下:




Letizia Mazzin et al., Amyotrophic Lateral Sclerosis.2021 Jul 25
在2020年发表了一项关于ALS微生物群组成的前瞻性纵向研究,表明ALS患者的肠道菌群与对照组相比有所不同,与残疾程度无关。此外,他们观察到蓝细菌的增加(蓝细菌以神经毒性作用著称)。患者中蓝细菌门的成员明显高于对照组,支持蓝细菌在ALS发病机制中发挥基础作用的假设。
有研究发现,在ALS患者中,谷氨酸代谢细菌更丰富,主要丁酸盐产生细菌更低,这与谷禾渐冻症菌群分析结果相吻合。
现有的关于ALS的肠道菌群研究整理如下:






doi: 10.3389/fcimb.2022.839526
在这些研究中,促炎性生态失调的原因与微生物失衡有关,微生物失衡可能损害肠上皮屏障并促进免疫/炎症反应,从而导致改变并在 ALS 发病机制中发挥作用。
▋ ALS患者和配偶对照之间的肠道菌群差异
一项研究中,研究人员探讨了与ALS相关的微生物组组成的差异。
比较了ALS患者(n = 10) 其配偶(n = 10). 发现与配偶相比,ALS患者的肠道微生物群多样性更高,且普雷沃氏菌属缺乏。健康夫妇没有表现出这些差异。
ALS患者及其配偶的粪便和血浆炎症标志物相似。对微生物酶的预测分析显示,ALS患者在几种代谢途径中的活性降低,包括碳代谢、丁酸盐代谢以及涉及组氨酸激酶和反应调节剂的系统。
ALS患者的肠道菌群与配偶对照组相比存在差异。表明改变肠道菌群,例如通过改善普雷沃氏菌属缺陷和/或改变丁酸盐代谢,可能对ALS治疗具有转化价值。
使用109例渐冻症患者,相匹配的对照共442例
其中性别比例:
按年龄划分:
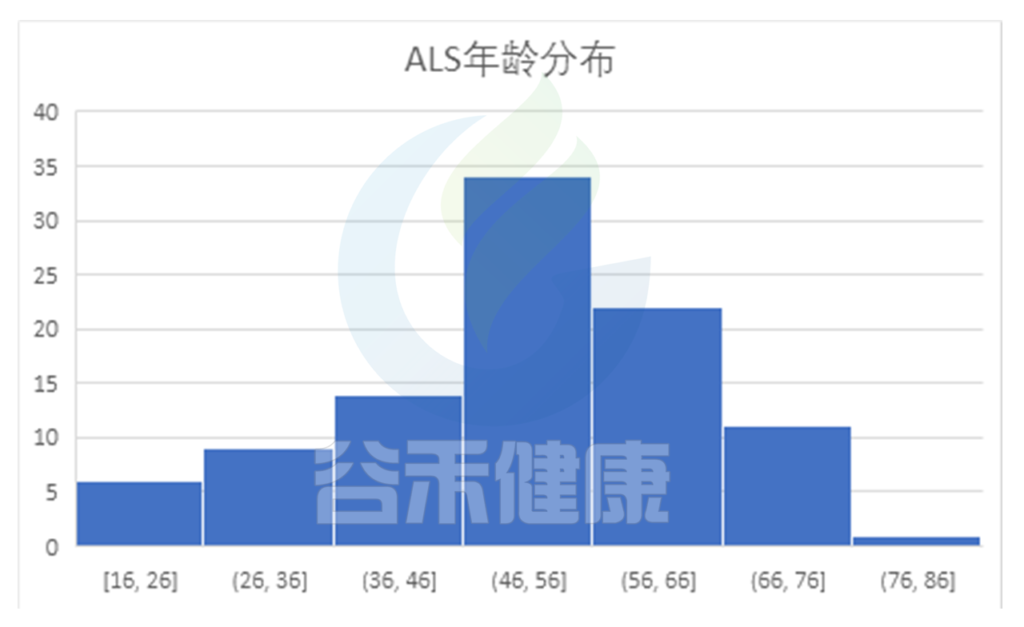
多样性上渐冻症人群稍低于对照人群,但差异不显著。
菌群特征总体存在一定差异:
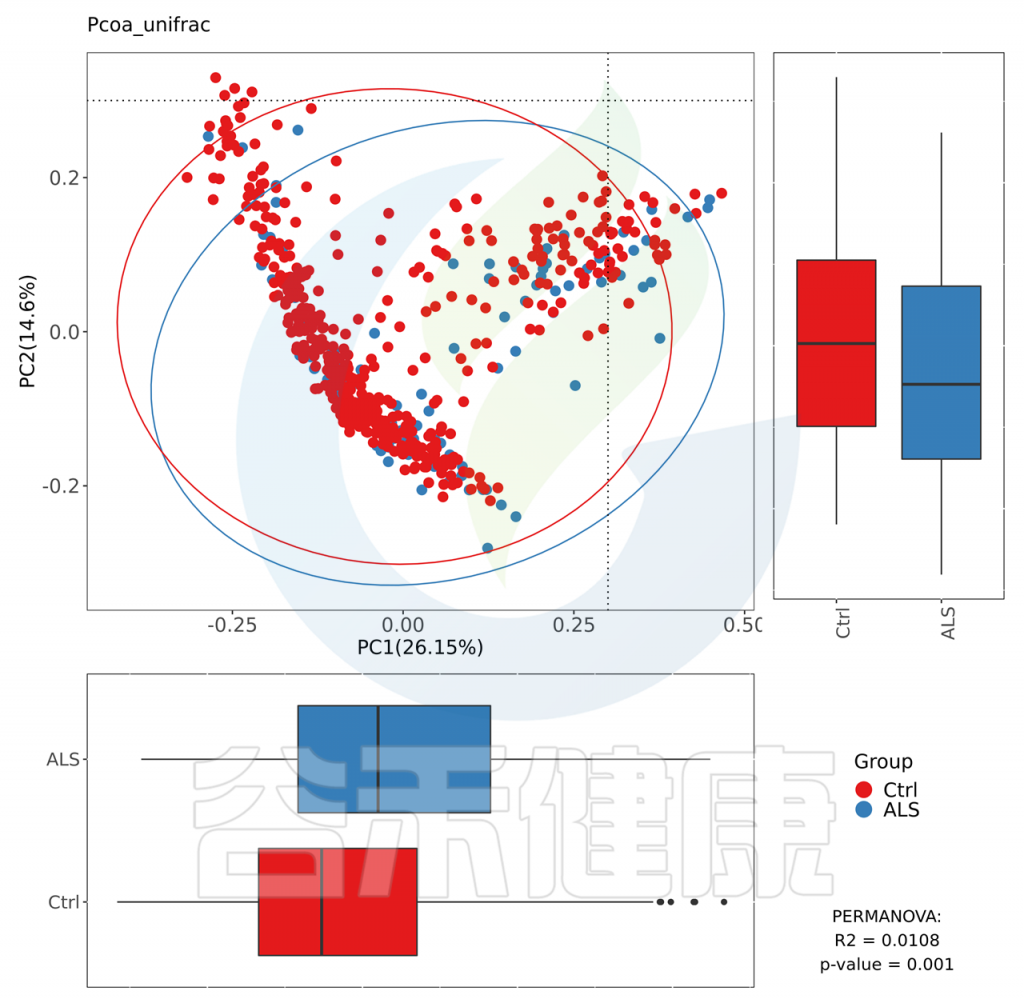

来看具体差异:
渐冻症人群拟杆菌显著高于对照;
Faecalibacterium则低于对照人群;
此外萨特氏菌属Sutterella渐冻症人群显著高于对照人群。
拟杆菌属(bacteroides)——重要的基石菌属,存在于人类肠道中,它们与人类具有共生关系。它们有助于分解食物并产生身体所需的营养和能量。然而,当拟杆菌进入到除胃肠区域以外的身体部位,可引起或加剧脓肿等感染,具体详见:
Faecalibacterium 是丁酸的重要生产者之一,具有抗炎作用,维持细菌酶的活性,保护消化系统免受肠道病原体的侵害。关于Faecalibacterium 的介绍详见:
肠道核心菌属——普拉梭菌(F. Prausnitzii),预防炎症的下一代益生菌
Sutterella 是变形菌门最丰富的菌之一,是一种厌氧或微需氧的、耐胆汁的菌,在人类胃肠道中具有轻度促炎能力,详见:

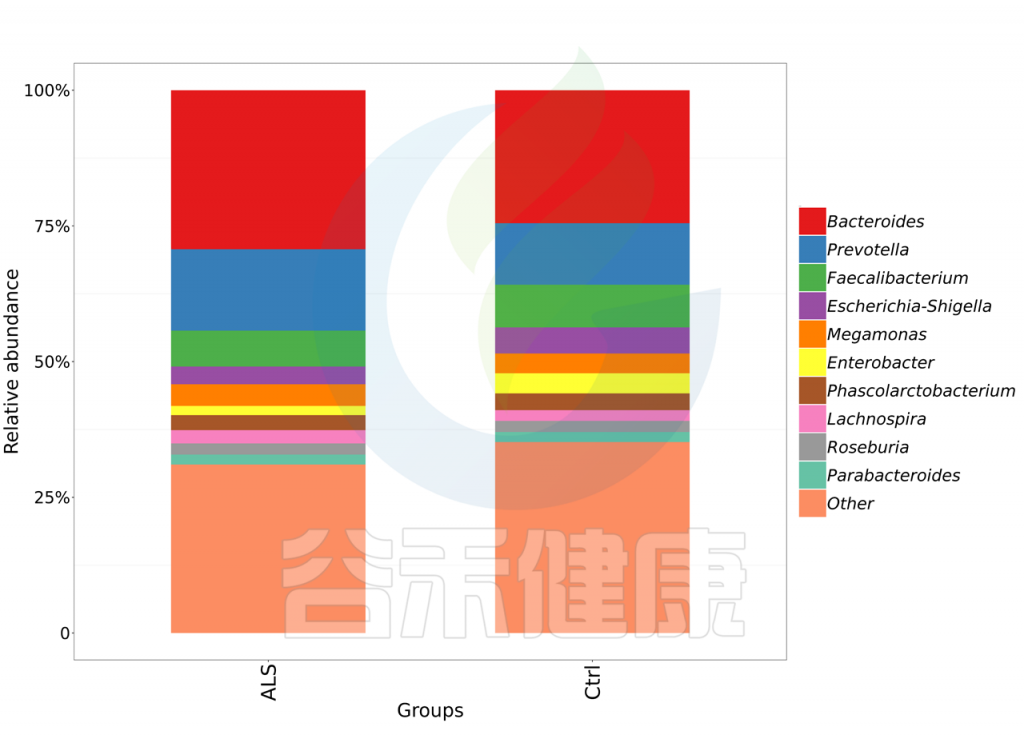
除了高丰度菌属外,双歧杆菌属和丁酸球菌属,渐冻症人群也低于对照:
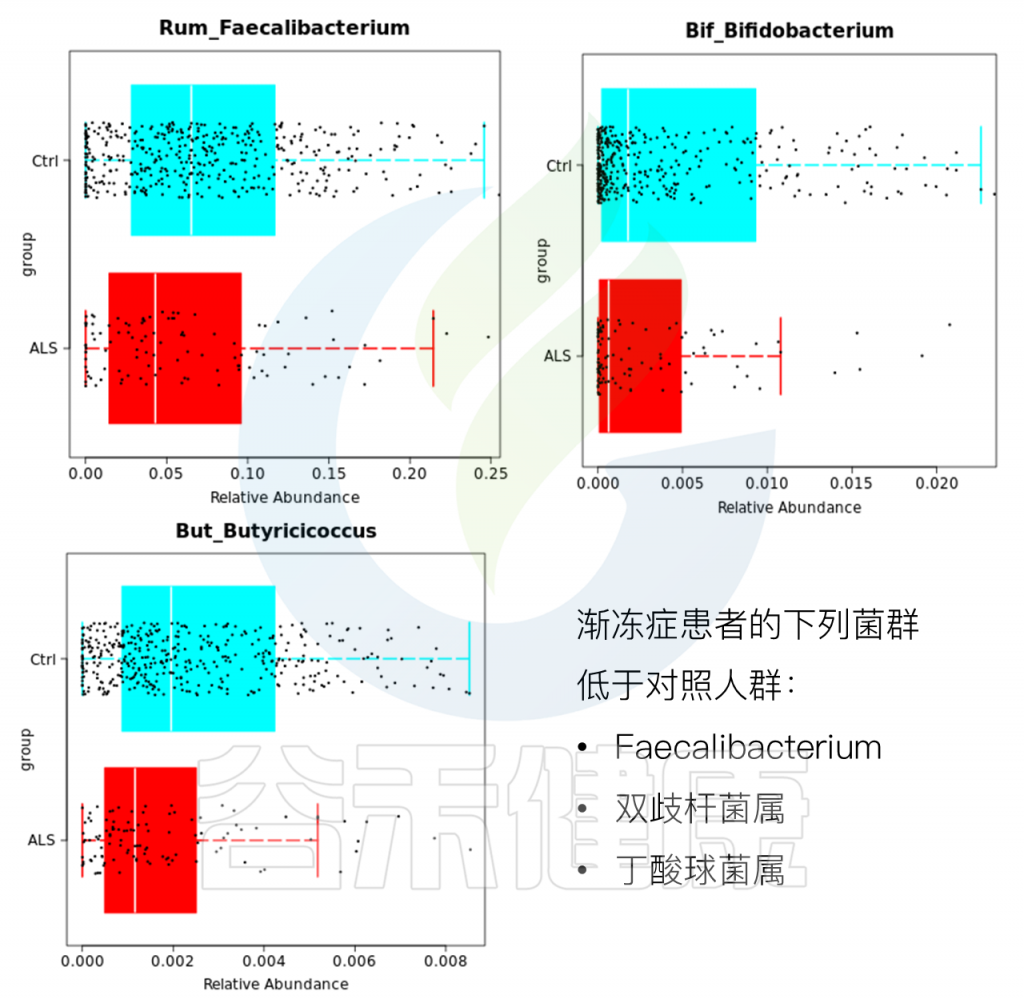

基于谷禾检测结果,渐冻症患者的有害菌丰度显著高于对照人群,益生菌和消化效率要低于对照人群。
此外维生素B1,维生素B12以及维生素C都显著低于对照人群,相对的维生素D水平要高于对照人群。
(来源:谷禾菌群数据库)
微生物群可能直接或间接的方式影响中枢神经系统和神经元健康:
■ 直接通过产生神经活性代谢产物和毒素
■ 间接通过调节免疫反应、饮食化合物或药物代谢
肠道微生物及其代谢产物可以直接刺激肠嗜铬细胞产生几种神经肽(如,肽YY、神经肽Y、胆囊收缩素)或神经递质(如,血清素),它们可以扩散到血液中,到达大脑,并影响中枢神经系统功能。
肠上皮调节特定细菌产物(如短链脂肪酸、维生素或神经递质)进入血液的易位,进而通过循环系统传播到中枢神经系统。通过这种方式,循环微生物群衍生的代谢产物、神经肽和神经递质可以进入中枢神经系统并直接影响其神经生物学。
ALS的微生物代谢产物调节
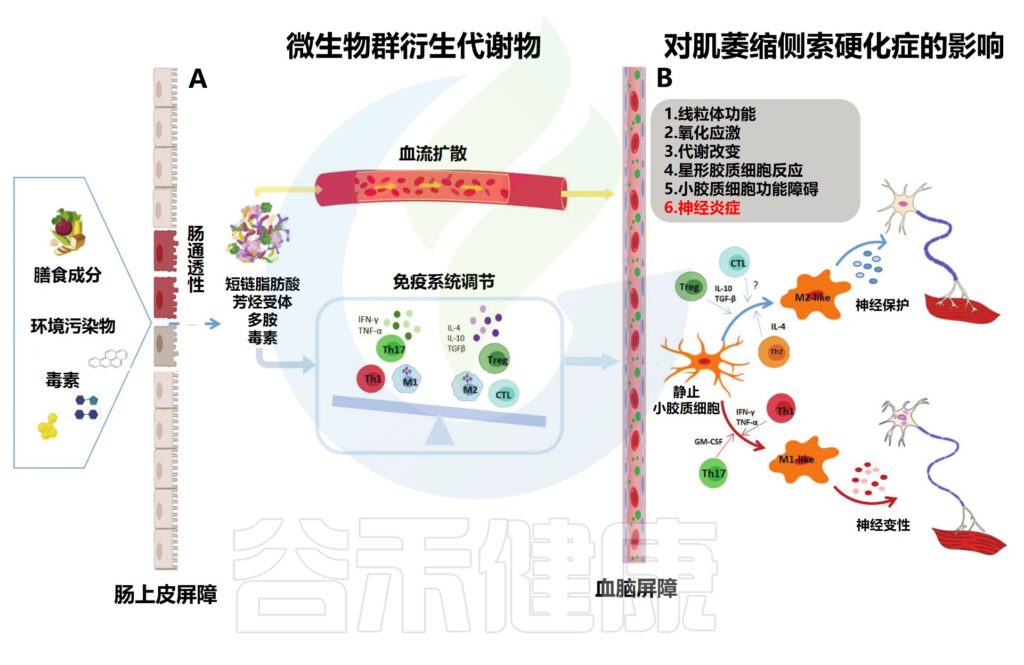
Letizia Mazzin et al., Amyotrophic Lateral Sclerosis.2021 Jul 25
A) 受损IEB或肠道细菌产生的毒素和神经活性代谢产物可以跨越血脑屏障,扩散到全身循环,并影响ALS发病机制;或者,微生物代谢终产物可能通过免疫系统调节间接影响中枢神经系统。
B) 细菌衍生的代谢产物可以改变能量稳态,促进氧化应激,并诱导线粒体功能障碍和神经炎症。特别是,外周免疫T淋巴细胞调节小胶质细胞的命运,从而调节神经元的退化或存活。
产生Th1、Th17和GM-CSF的CD4+T淋巴细胞有利于小胶质细胞M1样神经毒性表型;
Th2、Treg和某些CD8+T细胞类型可能有助于促进神经支持性M2样表型。
A.muciniphila给药可以改善小鼠的疾病进程,他们应用了非靶向血清代谢组学分析来确定可能的介体。有趣的是,A.muciniphila治疗的小鼠显示出NAM的血清水平升高,其直接给药显示出有益的效果,可能是通过调节线粒体功能和氧化应激途径。
注:NAM是能量转导、信号通路和抗氧化机制所需的辅酶的前体,可能在ALS相关的神经变性中受损。
与健康受试者相比,ALS患者的血清和脑脊液中的NAM浓度较低,粪便中NAM合成细菌基因的表达也较低,这支持了肠道菌群可以产生化合物,这些化合物能够渗透血脑屏障并影响神经元功能。
肠道菌群代谢物影响神经元健康
肠道内微生物代谢产物可通过中枢神经系统炎症直接或间接影响神经元健康。
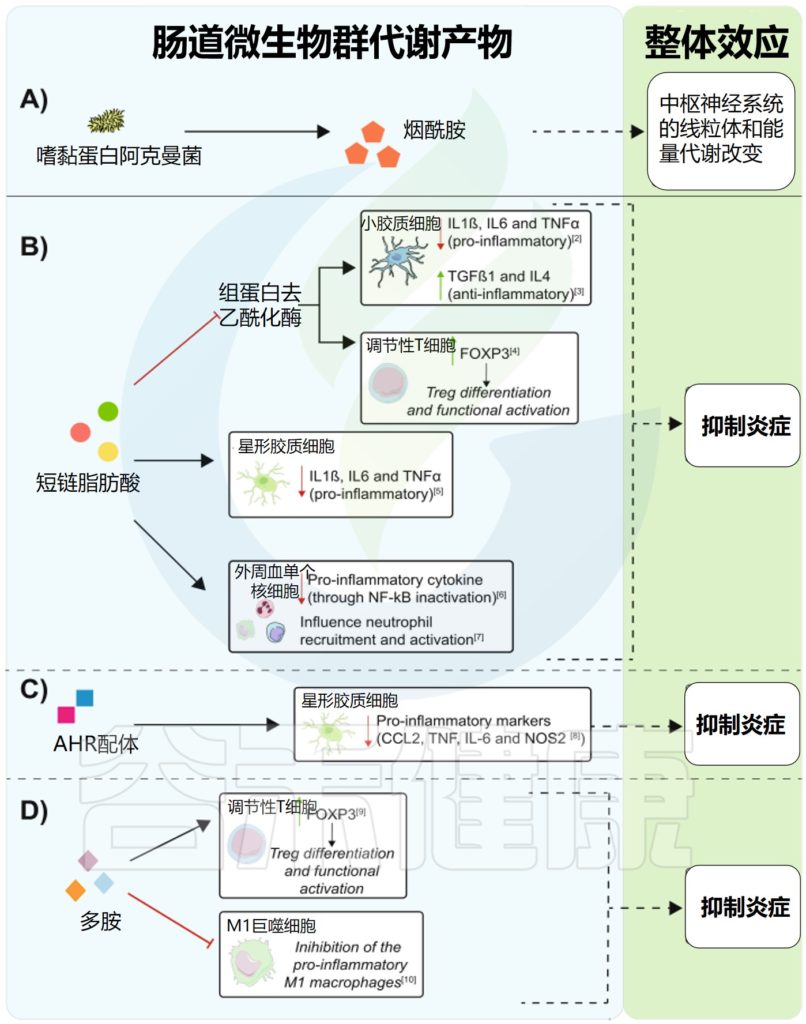
doi: 10.1186/s12916-020-01885-3
a) 肠道菌群释放的代谢物可以进入系统循环,在那里它们可以进入中枢神经系统;对于Akkermansia muciniphila释放的烟酰胺,这可能会改变能量稳态和氧化应激。
注:烟酰胺是 NAD 和 NADP 的前体,它们是能量转导和抗氧化途径以及其他细胞信号传导机制的适当功能所必需的辅酶,其中许多与 ALS 相关的神经变性有关。
b – d存在许多提议的机制,微生物代谢产物可以通过这些机制影响免疫反应并对中枢神经系统炎症状态产生影响:
b) 短链脂肪酸可通过抑制小胶质细胞内的HDAC来减少炎症,从而导致促炎因子(IL-1β、IL-6和TNF-α)的下调和抗炎标志物(TGF-β和IL-4)的上调。
c) 芳基烃受体(AHR)配体可调节星形胶质细胞活性并产生抗炎特性。
d) 多胺诱导Treg细胞中FOXP3表达,促进其分化和活化。这些分子还可以抑制炎性巨噬细胞(M1),从而防止巨噬细胞诱导的炎症。
在神经递质方面:
渐冻症患者的GABA(缺乏易焦虑、失眠等)、一氧化氮(抑郁、焦虑等),乙酸、丙酸(短链脂肪酸,缺乏导致炎症)水平均低于对照人群。
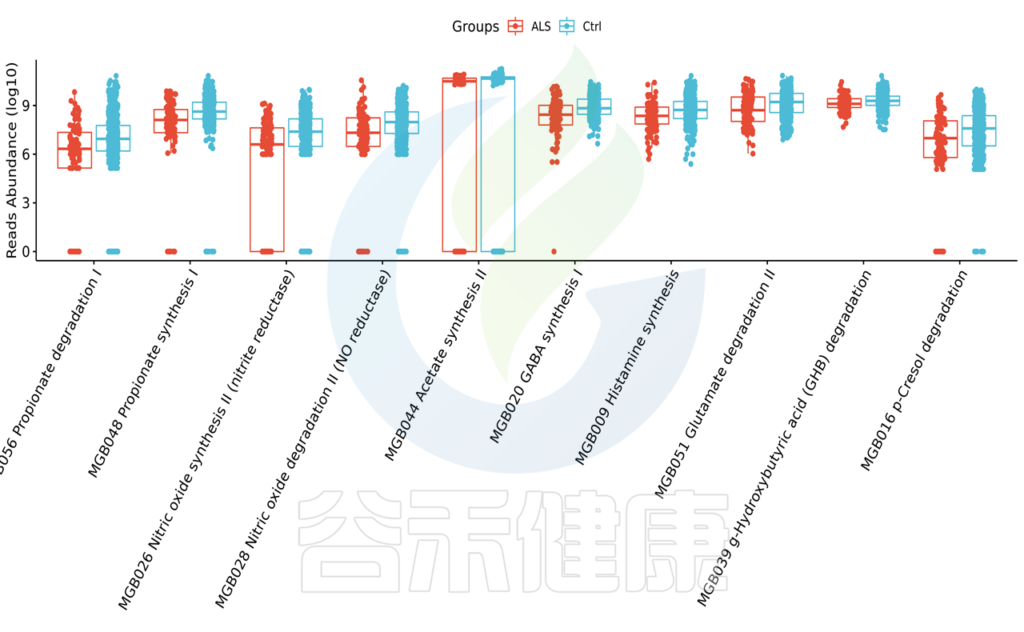
而对甲酚(毒性代谢物,引发便秘等)高于对照人群。这或许也与ALS患者中可能出现的便秘等胃肠道症状有关。
(来源:谷禾菌群数据库)
肠道菌群将饮食和环境化合物转化为神经毒素
β-甲基氨基-1-丙氨酸(BMAA)是一种众所周知的神经毒性氨基酸,在关岛的肌萎缩性侧索硬化症/PDC患者的大脑中发现,被认为是由肠道中的标准饮食化合物产生的。例如,蓝细菌和其他具有厌氧甲基化功能的细菌可以通过L-丝氨酸和L-丙氨酸的甲基化来生物合成BMAA。
肠道微生物还可以将L-色氨酸等氨基酸转化为吲哚等生物活性分子,一旦磺化,就会引发神经炎症和神经元损伤。肠道菌群可以将胆碱和L-肉碱代谢为三甲胺(TMA),然后将其脱甲基为二甲胺(DMA)和甲醛。
根据体外和体内研究,甲醛会导致线粒体膜损伤、危险自由基的产生以及神经元Tau蛋白的错误折叠和积累,从而导致ALS发病。
环境污染物也会通过微生物群的作用产生负面影响。
暴露于多环芳烃(PAHs)是ALS的危险因素,肠道微生物可以逆转PAHs的内源性解毒过程,将其再生为苯并[a]芘(BaP),其神经毒性作用已在斑马鱼中得到证实。
此外,肠道菌群失调可能是ALS中观察到的代谢改变的原因。有趣的是,肠道生物失调,特别是厚壁菌门的减少与更高的REE有关,这可能是ALS患者能量消耗增加的原因。
菌群诱导的炎症在ALS发病机制中的作用
▸ 肠道菌群影响先天性免疫系统和适应性免疫系统
ALS发病机制的一个既定关键点是神经炎症;它与驻留和外周免疫细胞的复杂失调有关(例如小胶质细胞和星形胶质细胞活化、T细胞浸润和促炎介质增加)。
肠道菌群与肠道免疫系统进行沟通,有助于维持免疫耐受性,并在炎症期间形成免疫反应。一旦病原体入侵或肠道内微生物渗漏,微生物相关的分子模式可以刺激先天细胞产生促炎细胞因子,进而激活适应性免疫细胞,从而促进免疫稳态的破坏。
除了先天免疫细胞外,肠道微生物还可以直接影响适应性免疫系统主要成分CD4+和CD8+T细胞的发育和分化。
▸ 肠道菌群失调会影响几个大脑生物学过程
无菌小鼠和抗生素治疗小鼠模型显示出广泛的免疫异常,包括改变小胶质细胞的密度、形态和成熟度,表明肠道菌群可以影响中枢神经系统免疫细胞的发育和功能。
▸短链脂肪酸影响Tregs,从而影响ALS
短链脂肪酸是膳食纤维的最终代谢微生物产物,主要由拟杆菌和厚壁菌门产生。已知它们通过组蛋白脱乙酰酶抑制介导调节性T细胞(Tregs)诱导。
ALS的特点是同时激活不同的淋巴细胞亚群Th1和Th17,并减少Tregs,Tregs在小鼠和人类中都具有保护作用;更多的Treg与疾病进展缓慢相关。
Tregs已被证明直接将巨噬细胞从M1状态分化为M2状态,M2小胶质细胞与稳定的疾病阶段相关,而Th1和M1小胶质细胞在快速进展阶段占主导地位,表明从保护转变为毒性。
▸肠道菌群改变影响ALS症状的发生和发展
一项研究发现,肠道菌群改变先于循环和CNS免疫系统的扩张和激活,以及症状的发生和发展。
肠道菌群驱动的促炎信号可能对神经胶质的生理功能、维持神经元健康至关重要。事实上,肠道菌群通过芳基烃受体(AHR)介导的涉及I型干扰素信号传导的机制调节星形胶质细胞活性。
肠道菌群对ALS药物疗效的影响
肠道菌群也可以通过肠道药物的代谢影响疾病。
2019年,一项研究评估了一组肠道细菌代谢一系列常用处方药物的能力,其中包括利鲁唑,这是唯一一种显示对ALS患者具有生存益处的药物。
筛选出的40种细菌对利鲁唑进行了显著的代谢,其中许多细菌在人群中的流行率不同。
据报道,与相对较高的患者间变异性相比,利鲁唑的血浆浓度显示患者内变异性较低,这不能通过肠道吸收后的代谢差异来解释。肠道菌群对利鲁唑生物利用度的修正可以解释患者间血浆水平的变化。
肠道菌群对非运动肌萎缩侧索硬化症状的影响
肠道菌群与影响ALS患者的其他症状有关,如抑郁、焦虑和便秘。肠道微生物群可以产生各种肽和神经递质,它们可以直接影响情绪,而大脑通过包括应激反应在内的多种机制影响肠道。解开肠道微生物群在调节与神经精神疾病相关的大脑功能方面的作用才刚刚开始,但这有可能成为改善ALS患者生活质量的一种手段。
关于便秘,ALS患者经常报告的另一种症状,管腔液中微生物组(胆汁酸的代谢、短链脂肪酸的产生和甲烷的产生)以及结肠粘膜层在调节液体进入血流中的吸收中的作用都已被提出。无论疾病进展如何,改善这些症状的管理都会提高生活质量。
以上我们可以知道肠道菌群可以通过代谢亢进和胃肠道异常影响 ALS,从而更深入地了解 ALS 背后的微生物组-宿主相互作用的复杂网络。
一些不太了解的人容易把渐冻症和其他神经退行性疾病搞混。四大常见的神经退行性疾病有:肌萎缩侧索硬化症(渐冻症)、亨廷顿氏病、阿尔兹海默症(老年痴呆)、帕金森氏病,在这里简单讲述一下区别。
▸ 阿尔兹海默症
阿尔茨海默病(AD)是一种起病隐匿的进行性发展的神经系统退行性疾病。临床上以记忆障碍、失语、失用、失认、视空间技能损害、执行功能障碍以及人格和行为改变等全面性痴呆表现为特征,病因迄今未明。
该病起病缓慢或隐匿,病人及家人常说不清何时起病。多见于70岁以上老人,少数病人在躯体疾病、骨折或精神受到刺激后症状迅速明朗化。女性较男性多(女∶男为3∶1)。
✦与渐冻症的区别
渐冻症也叫做运动神经病。病变主要累及到上下运动神经元,主要表现为肢体无力,肌肉萎缩,肌束颤动,可以伴饮水呛咳,吞咽困难等表现。
阿尔茨海默病主要是影响患者的精神行为能力,执行能力,思维反应,生活能力。肢体上一般不会出现萎缩无力的症状。
▸ 帕金森氏病
帕金森氏病又称为震颤麻痹,是一种影响患者活动能力的中枢神经系统慢性疾病,多发生于中老年以上的人群。
•表现症状
本病早期主要表现包括静止性震颤、肌强直、行动缓慢、动作起动困难和姿势异常等。静止性震颤即患者的手或臂不受控制地发抖,在休息时出现或情绪紧张时加重。
后来人们发现除了震颤外、还有慌张步态(走路时小碎步且越走越快)、小写症(写字越来越小)、行走时上肢无前后摆动等其它症状。
✦与渐冻症的区别
•发病原因不同
帕金森病由于脑部纹状体出现损伤导致多巴胺分泌障碍而导致的一种疾病,其发病原因和脑部外伤、年龄增大等因素有一定的关系。
而渐冻症的发生多数情况下病因不明,少数是遗传因素所导致的,常常会出现运动神经元的损伤。
•临床表现不同
临床表现:帕金森病患者会出现四肢发抖、不灵活等异常症状,一般不会出现肌肉萎缩。但是渐冻症发生以后常常会有肌肉萎缩的情况发生,会使患者逐渐丧失正常的运动功能。
•危害性不同
帕金森病是神经性系统病变,主要表现是颤抖,可引起运动迟缓,步态异常。
渐冻症是运动神经元疾病,主要表现是肌肉逐渐萎缩和无力,可出现吞咽困难、语言困难以及呼吸衰竭等比较严重的情况。
▸ 亨廷顿氏病
又叫大舞蹈病或亨廷顿舞蹈症。一种常染色体显性遗传性神经退行性疾病,主要病因是患者第四号染色体上的基因发生变异,产生了变异的蛋白质,该蛋白质在细胞内逐渐聚集在一起,形成大的分子团,在脑中积聚,影响神经细胞的功能。
•表现症状
一般患者在中年发病,表现为舞蹈样动作,随着病情进展逐渐丧失说话、行动、思考和吞咽的能力,病情大约会持续发展10年到20年,并最终导致患者死亡。
✦与渐冻症的区别
•运动方面
亨廷顿氏病表现出肢体的跳动或抽动,但渐冻症是肌肉萎缩导致无力运动,抽动也不同与渐冻症初期的“肉跳”,这是一种类似于“舞蹈”的大幅运动。
•认知方面
渐冻症患者的意识清晰,不会出现认知障碍。
但亨廷顿氏病会表现出进行性痴呆。日常生活和工作中的记忆和计算能力下降,患者记住新信息仅有轻度损害,但回忆有显著缺陷。
情感障碍是亨廷顿氏病最多见的精神症状,包括焦虑、紧张、兴奋易怒、或淡漠、或兴趣减退。
亨廷顿病患者还可出现人格行为改变,出现反社会行为、精神分裂症、偏执狂和幻觉。
渐冻症的诊断
在诊断上,由于仍不明确渐冻症的发病原因及机制,该病还未筛选出特异性诊疗标记物。
此外,前面我们提及的渐冻症早期症状不具有典型性,必须与其他神经退行性疾病相鉴别,所以早期患者会花费大量人力物力财力及时间做鉴别诊断来排除。
✦表现诊断
(1)检查要评估咀嚼和吞咽的肌肉力量,包括口腔、舌及咽喉肌。
(2)下运动神经元(LMN)功能,如肌肉萎缩情况,肌肉力量或肌肉跳动(称为肌束震颤)。
(3)上运动神经元(UMN)功能,如腱反射亢进和肌肉痉挛(肌肉紧张和僵直的程度)。
(4)情绪反应失去控制,如哭或笑的情绪变化。思维的变化如丧失判断力或失去基本的社会技能。检查者也会评估患者言语流畅性及文字识别能力。这些症状不常见,不容易引起重视。
注意:神经科医生还将询问如疼痛,感觉丧失或锥体外系问题。
✦检测诊断
肌电图(EMG):将针状电极穿过皮肤插入到各种肌肉中。该测试评估肌肉收缩和休息时的电活动。在肌电图中看到的肌肉异常可以帮助医生诊断或排除渐冻症。
神经传导研究:这项研究测量神经向身体不同区域的肌肉发送冲动的能力。该测试可以确定是否有神经损伤或某些肌肉或神经疾病。
核磁共振:核磁共振可以生成大脑和脊髓的详细图像。显示脊髓肿瘤、颈椎间盘突出或其他可能导致症状的情况。
血液和尿液检查:在实验室分析您的血液和尿液样本可能有助于鉴别诊断。
脊椎穿刺(腰椎穿刺):获取脑脊液来完善检查,帮助诊断及排除渐冻症。
肌肉活检:如果医师认为患有肌肉疾病而不是渐冻症,这项检查将在局部麻醉状态下获取您的肌肉组织,再进行分析检查。
使用菌群特征对渐冻症和对照人群进行预测
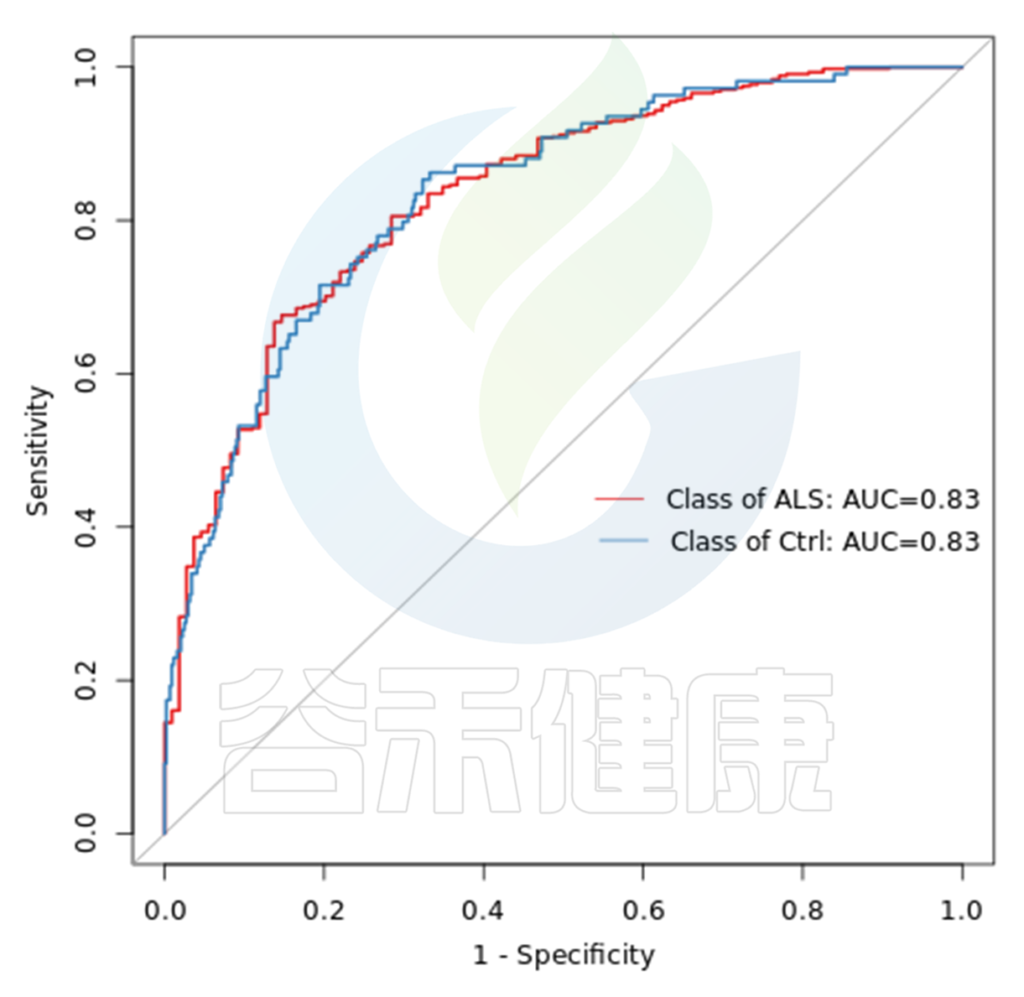
综合代谢和其他指标后:综合准确度:0.88
可以理解为基于菌群特征,可以分辨出84%的ALS患者。
(来源:谷禾菌群数据库)
虽然渐冻症目前无法彻底治愈,但有一些治疗方法可以减缓身体功能的丧失,并改善患者的生活质量。
基于神经系统的药物
Riluzole (Rilutek,利鲁唑)
是一种口服药物,是 FDA 证明的 ALS 疾病缓解治疗药物。
据报道可通过降低谷氨酸水平来减少对运动神经元的损害,谷氨酸在神经细胞和运动神经元之间传递信息。对肌萎缩侧索硬化患者的临床试验表明,利鲁唑可延长几个月的生存期,尤其是延髓型疾病。
注:有吞咽困难的人可能更倾向于在舌头上溶解的增稠液体形式 (Tiglutik) 或片剂 (Exservan)。
依达拉奉(Radicava)
通过静脉输注给药,已被证明可以减缓 ALS 患者日常功能临床评估的下降。
研究人员认为,依达拉奉通过清除自由基起作用,从而减少对神经系统的损害并减缓疾病进展。
苯丁酸钠-牛磺酸二醇(Relyvrio)
Relyvrio 治疗 ALS 的疗效在一项为期 24 周的多中心、随机、双盲、安慰剂对照、平行组研究中得到证实。
在 ALS 患者中使用苯丁酸钠-牛磺酸二醇。据报道,根据 24 周内的 ALSFRS-R 评分,苯丁酸钠-牛磺熊二醇导致的功能下降速度比安慰剂慢。
Relyvrio 可以通过将一包与 8 盎司室温水中混合来口服。它也可以通过饲管给药。前三周的推荐剂量是每天一包(3 克苯丁酸钠和 1 克牛磺熊二醇)。三周后,剂量增加到每天两次一包。药物可以在吃零食或用餐前服用。
注意:
Relyvrio 最常见的不良反应是腹泻、腹痛、恶心和上呼吸道感染。Relyvrio 含有牛磺熊二醇,一种胆汁酸,可能会导致患有干扰胆汁酸循环的疾病的患者腹泻恶化。这些患者在服用 Relyvrio 之前应考虑咨询专科医生。
巴氯芬(Baclofen)
巴氯芬通过放松身体肌肉帮助缓解肌肉痉挛。
研究表明,当巴氯芬与辅助或无辅助的运动范围物理治疗一起使用时,它在缓解肌肉痉挛方面特别有效。
注意:必须密切监测巴氯芬的剂量,以避免患者过早服用高剂量(如40至80mg)时出现四肢和躯干无力。
基于消化系统的药物
格隆溴铵
多种药物可以降低唾液分泌量。随着吞咽变得更加困难,它通常会积聚在嘴里。最常见的药物之一是格隆溴铵( Robinul )。
硫酸阿托品
硫酸阿托品有助于缓解唾液过多。阿托品 0.4 mg片剂
三己基苯
三己基苯甲酰也有助于控制过多的唾液。
医生可能会开其他消化系统疾病的药,以帮助缓解 ALS 的其他症状,如便秘等。
基于人体其他系统的药物
替扎尼定(Tizanidine)
替扎尼定通过放松肌肉帮助缓解肌肉痉挛。
替扎尼定通过阻断从大脑发送到肌肉的神经信号起作用。
替扎尼的给药剂量范围为每天 2-10 毫克。
注意:副作用虽然不常见,但偶尔可能包括虚弱、便秘、头晕和其他问题。
甲基钴胺素
甲基钴胺素或甲基B12是一种每日注射的药物,用于提高能量和增强肌肉力量。这些成分需要处方:25 mg/1mL(pH 2.7-3.0)
谷胱甘肽
谷胱甘肽经常对四肢力量有效。它是静脉注射的。需要蝶形注射器。这些成分需要处方:复方谷胱甘肽200mg/ml。
硫酸奎宁
硫酸奎宁可减少痉挛。
睡前一晚应该停止或显著减少肌肉痉挛。需要324毫克胶囊的处方,不含填料/防腐剂。
通常,当替扎尼定和/或巴氯芬未成功治疗ALS患者时,使用硫酸奎宁。
注意:药物的副作用可能包括过敏反应、血栓形成(血管内形成血块)或肾脏问题。
Nuedexta
Nuedexta可以改善咀嚼和吞咽,此外还可以缓解假性延髓的影响——过度大笑和/或哭泣。即使这些不是当前的问题,Nuedexta也经常作为预防剂,可能会延迟延髓问题的发生。通用配方右莫特沙芬25毫克/奎尼丁10毫克
美西律Mexilitine
每天服用300毫克美西律可以缓解肌肉痉挛。这种药物可以由神经科医生或医生开具。200 mg胶囊(普通)
NeuRx隔膜起搏系统
NeuRx隔膜起搏器采用微创方法,经科学和临床证明可保持隔膜肌的力量和由此产生的肺活量。
其他,例如地西泮(Diastat、Valium )等止痛药或肌肉松弛剂有助于缓解痉挛。
非甾体抗炎药 (NSAIDs)
由于炎症 促进ALS的发展,研究人员推测NSAIDs(抗炎药)可能具有保护作用。然而,一些临床试验并未发现对ALS患者的总体生存率有任何有益的影响。
非甾体抗炎药,如布洛芬或萘普生,可能有助于缓解全身疼痛和不适。
注意:由于潜在的胃肠道和心血管副作用,非甾体抗炎药只能按照指示服用。
加巴喷丁 (Gabapentin)
加巴喷丁是抗癫痫药物,但也可用于ALS。
动物研究表明,加巴喷丁可以改善ALS患者的生存率,临床试验表明,它可以减少ALS患者肌肉痉挛和抽搐。
加巴喷丁通过调节谷氨酸水平(类似于利鲁唑)发挥作用。
注意:加巴喷丁的副作用包括疲劳、体重增加、消化不良、嗜睡、头晕、共济失调和震颤。
三环类抗抑郁药(Tricyclic antidepressants)
这些药物广泛用于ALS的治疗,具有多种作用。特别是,抑郁和焦虑在ALS中很常见,适当剂量的三环类药物可以缓解抑郁。
注意:副作用,如口干和体重增加,也可能帮助ALS其他症状,如口腔唾液过多和体重减轻。
吗啡(Morphine)
吗啡是一种阿片类药物,可用于治疗疼痛。吗啡有助于缓解晚期ALS患者呼吸不足的感觉。
在情绪不稳定的情况下,可以使用选择性 5-羟色胺再摄取抑制剂、阿米替林、苯二氮卓类药物和氢溴酸右美沙芬/硫酸奎尼丁等。
饮 食
营养对肠道微生物群有直接影响,肠道微生物群会影响局部肠道免疫反应,进而影响自身免疫反应。
饮食中存在具有抗氧化潜力的化合物,例如维生素、姜黄素、辅酶 Q10等,可用作治疗策略。
应排除或限制的食物
▸ 避免海鲜类
文献报道,日本Kii半岛ALS的高发病率可能与β-甲基氨基-L-丙氨酸(BMAA)有关。BMAA是一种天然的神经毒性非蛋白氨基酸,由苏铁种子根部的共生蓝藻产生,苏铁种子在该地区尤为常见。假设该区域的ALS患者无法阻止BMAA积聚。
BMAA的饮食来源可能是海鲜,如鱼、贻贝、螃蟹和牡蛎。关岛也报告了ALS的高发病率,该岛的人口使用潜在的苏铁衍生产品。BMAA污染的另一个可能来源可能是果蝠或飞狐,因为它们食用苏铁种子,它们是当地居民饮食的组成部分。
尽管还需要更多的研究,但最近研究人员使用斑马鱼幼虫模型证明了BMAA与微囊藻毒素亮氨酸和精氨酸(其他氰毒素)之间的关系。此外,暴露于BMAA的新生大鼠受到运动缺陷的影响,这表明神经发育过程中的暴露可能导致ALS。先前的研究研究了BMAA对神经变性的作用机制:BMAA杀死NADPH黄递酶阳性运动神经元,并对影响运动神经元损伤的神经胶质细胞起毒性作用。
▸ 避免高脂饮食 (有争议)
ALS患者过度摄入脂肪食物,尤其是饱和脂肪食物,以及ROS防御机制的丧失,如SOD1基因的突变,是ALS患者出现的主要方面。因此,将某些国家大量食用脂类食品与发现ALS病例的可能性更大联系起来是合理的。
这可以部分解释为什么在瑞典和苏格兰等州ALS发病率如此之高,众所周知,这些州的饮食特别注重脂肪食物的摄入。
然而,脂肪摄入在ALS中的作用存在争议,因为不同的研究显示了相反的结果。Nelson等人证明,高脂肪摄入与ALS发病相关。另一项研究显示了相反的结果:脂肪摄入量较高的受试者患ALS的风险降低。
▸ 避免谷氨酸盐饮食
据报道,ALS中存在谷氨酸的不良反应。它是大脑中的主要兴奋性神经递质,蘑菇、牛奶和富含蛋白质的食物中存在的高水平谷氨酸会导致细胞内钙水平升高,从而促进神经元死亡。
▸ 避免重金属饮食
暴露于金属被认为是ALS的一个可能的风险因素,但结果并不确凿。研究表明,镉和铅可能与患ALS和锌的风险增加有关,而根据疾病前血液中的金属水平,其风险降低,其中铅具有最强的先验联系。
汞被怀疑是ALS发病机制的一部分,但结果尚无定论,尤其是饮食中的汞暴露,尤其是海鲜消费。汞由几个行业生产,并储存在鲨鱼、旗鱼、鲭鱼和金枪鱼等水生食肉生物中。
汞可以产生氧自由基,促进兴奋毒性,减少DNA、RNA和蛋白质合成,所有这些过程都与ALS相关。然而,一些研究报告称,ALS患者和非ALS患者接触的汞量相同。差异可能是ALS患者由于遗传/表观遗传倾向而更易受汞影响。
注意
不同研究之间的差异可能是由于单一金属分析可能无法充分评估健康风险的相关性,这表明毒物暴露与添加剂或协同效应相互作用的可能性。
可以引入的饮食
早期研究表明,存在于水果、蔬菜、咖啡、茶和全谷物中的多酚(例如,白藜芦醇、姜黄素、表没食子儿茶素没食子酸酯、槲皮素和酚酸)可能对 ALS 具有良好的神经保护作用。
在体内和体外观察到,这些生物活性化合物可能具有调节线粒体生物发生、改善能量代谢、减少有毒蛋白质聚集、减少小胶质细胞和星形胶质细胞炎症以及改善运动功能和生存的潜力。
ALS 患者的营养护理应包括多摄入水果、蔬菜、高纤维谷物和瘦肉蛋白质来源,如鱼和鸡肉等。
——哥伦比亚大学临床流行病学和营养学副教授Nieves
多摄入水果蔬菜
一项包括超过 302 名 ALS 患者的研究中,水果、蔬菜、抗氧化剂和 β-胡萝卜素被证明与 ALS 功能增强有关。
在一项针对 77 名韩国人的小型研究中,当具体研究水果和 β-胡萝卜素的好处时,增加摄入量与散发性肌萎缩侧索硬化的风险降低有关。
遵循地中海饮食
一种已知的高酚饮食是地中海饮食,也被证明通过高橄榄油含量减少神经退化。暴露于高初榨橄榄油饮食的SOD1G93A小鼠寿命延长,运动能力提高。
第二项支持性研究表明,特级初榨橄榄油提取物在从SOD1G93A小鼠模型获得的培养物中充当神经保护剂。该提取物通过下调SOD1突变刺激的活化胶质细胞释放的一氧化氮的量来减少神经变性。此外,TLR4信号通路(ALS中已知的致病通路)被橄榄油提取物抑制。
另一组关注草莓中富含花青素的提取物,这是一种以抗氧化、抗炎和抗凋亡特性而闻名的化合物。花青素属于黄烷类,是一种植物酚类。他们发现,补充了该提取物的hSODG93A小鼠表现出延迟发病和延长生存期。
饮食习惯
ALS发病的主要因素之一似乎是以脂质为主的饮食,由于ROS的高释放,在神经退行性变中起着至关重要的作用。
25–68% 的 ALS 患者表现出能量消耗增加的代谢亢进表型,尤其是在休息时。
晚期ALS患者可能需要高脂饮食作为补偿热量摄入
最近的研究表明,与健康个体相比,症状前ALS患者可能会增加每日总能量消耗。
在 ALS 中,体重减轻是一个独立的预后因素,体重指数 (BMI) 每下降 1 点,死亡率就会增加 30%.
高脂肪含量的高热量食物补充剂可以稳定晚期ALS患者的体重减轻。这可以通过症状前小鼠的研究报告的代谢变化来解释。
ALS患者因吞咽困难和食欲不振而导致的食物摄入不足和体重减轻,可能反映出代谢过度和分解代谢需求增加(下图)。这可能导致ALS患者通过摄入脂肪食物来增加热量摄入,作为补偿措施。
健康个体与肌萎缩侧索硬化症患者之间的代谢差异
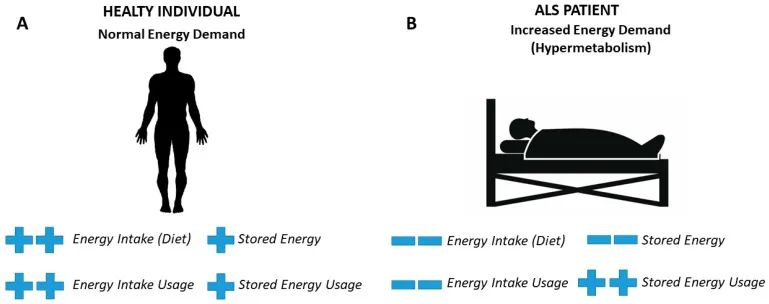
(A) 在健康个体中,在正常能量需求期间,能量摄入用于满足能量需求,但当存在过量能量时,能量储存在脂肪组织和肝脏中。无法维持能量供应会导致负能量平衡,在这种情况下,脂肪组织和肝脏中的能量储备用于满足能量需求。
(B) 肌萎缩侧索硬化症患者出现高代谢,即能量需求增加。事实上,在ALS中,能量摄入减少导致脂肪组织和肝脏中能量储存减少,并增加对储存能量使用的依赖性。因此,ALS患者体重指数的下降是负能量平衡和高代谢的结果。
益生菌
发表在《自然》杂志上的一项详细研究表明,肠道补充Akkermansia muciniphila(一种在肠道粘蛋白降解中起重要作用的肠道微生物)可以改善转基因SOD1G93A小鼠的ALS症状。
在代谢产物水平上,肠道补充的Akkermansia muciniphila的有益作用被证明依赖于SOD1G93A小鼠中枢神经系统中烟酰胺水平的增加,同时也证明ALS患者体内烟酰胺水平下调。然而,在ALS模型和患者中,粘蛋白降解产生短链脂肪酸,一些产生SCFA的细菌受到负面影响。
关于AKK菌详见:
在每天接受6个月益生菌治疗的ALS患者中,Rikenellaceae的丰度显著增加。
益生菌配方是五种乳酸菌的混合物:嗜热链球菌ST10–DSM 25246、发酵乳杆菌LF10–DSM 19187、德氏乳杆菌LDD01–DSM 22106、植物乳杆菌LP01–LMG P-21021和唾液乳杆菌LS03–DSM 22776。无因补充益生菌引起的不良事件。与对照组相比,可调节ALS患者的细菌多样性,ALS患者门、科和属水平的蓝细菌显著增加,益生菌组和安慰剂组的蓝藻丰度都随着时间的推移而减少,尽管差异并不显著。
益生元
2013年发表的研究报告了转基因SOD1G93A小鼠中最常用的益生元的有益效果,其中一项研究就是在该动物模型中施用低聚半乳糖,延缓了疾病的发作,延长了小鼠的寿命,显著减少了运动神经元的损失和肌肉萎缩,并改善SOD1G93A小鼠中枢神经系统的炎症反应。
其他被广泛使用的益生元化合物是多不饱和酸。特别是,在一项包括美国五个ALS患者的前瞻性队列的纵向研究中,表明摄入Omega-3多不饱和酸可以延缓疾病的发作。
然而,转基因SOD1G93A小鼠在症状前阶段的膳食中补充二十碳五烯酸加速了疾病的进展,缩短了小鼠的寿命,这表明这种多不饱和酸的毒性醛氧化产物在动物的脊髓中增加了,增加了反应性小胶质细胞。
后生元
后生元制剂是生物家族的最新成员,包括由食品级微生物在发酵过程中产生的生物活性化合物,如短链脂肪酸、微生物组分、功能蛋白、分泌多糖、细胞外多糖(EPS)、细胞裂解液、磷磷磷酸、肽甘聚糖衍生的肽和柱状结构。
丁酸盐的施用增加了血液中Treg淋巴细胞的水平,有利于降低炎性细胞因子IL-17的水平,并减缓SOD1G93A转基因小鼠的疾病进展。
粪菌移植
一例ALS女性患者,他们在12个月的随访中通过经内镜肠内管接受了冲洗微生物群移植(WMT),一种改良的粪便微生物群移植术(FMT)。
该病例报告首次展示了使用WMT治疗ALS的直接临床证据,表明WMT可能是控制这种所谓不治之症的新治疗策略。
值得注意的是,患者后来遭受的意外头皮创伤用处方抗生素治疗,导致ALS恶化。随后的抢救性WMT成功地阻止了病情的发展,并迅速改善。
其他补充剂
★ 肌酸
肌酸是一种膳食补充剂,因其有益效果值得关注。它是由精氨酸、甘氨酸和蛋氨酸合成的内源性化合物。由于大部分肌酸储存在骨骼肌中,运动员习惯于将其融入饮食中,以改善肌肉张力。
最近的研究描述了肌酸在预防或延缓神经退行性疾病发病方面的新用途。特别是长期补充肌酸可提高存活率和改善运动协调性。他们测量了肌酸的神经保护作用,研究了SOD1基因改变版本的转基因小鼠。结果表明,肌酸给药保护神经元免受氧化损伤。补充肌酸的运动员无不良副作用。
然而,2003年和2004年完成的两项临床试验测试了口服肌酸补充剂,仅在ALS患者的寿命和肌肉强度方面提供了很少的显著改善。因此,需要更多的研究来了解肌酸的实际作用量,因此,东北肌萎缩侧索硬化症联盟(NEALS)目前正在分析补充肌酸的长期影响。
★ 辅酶Q10
辅酶Q10(CoQ10)或泛醌,一种内源性产生的脂质,存在于我们的饮食中,作为线粒体呼吸系统的辅因子发挥作用。
泛素醇是辅酶Q10的还原形式,具有抗氧化和抗炎作用。它避免了自由基的形成、蛋白质、脂质和DNA的变化,并降低了脂质过氧化的浓度。
此外,在包括神经系统疾病在内的许多疾病中,ROS的增加与辅酶Q10的缺乏之间存在关联。
一些研究报告了CoQ10在不同疾病中的有益作用,如高血压、纤维肌痛和男性不育。辅酶Q10还用于几种神经退行性疾病,如ALS和帕金森病。均衡的饮食可以获得足量的辅酶Q10,但脆弱的受试者可能需要补充。尽管辅酶Q10耐受性良好,但研究仅限于孕妇和儿童。
注意:辅酶Q10可能会导致腹泻、呕吐和皮疹等副作用。此外,辅酶Q10可能会降低华法林等几种药物的治疗效果。
★ L-丝氨酸补充剂
氨基酸 L-丝氨酸的膳食补充剂也可作为神经保护剂。
L-丝氨酸的补充被确定为一种防止 BMAA 中毒的细胞保护剂,并导致 L-丝氨酸补充作为一种潜在的治疗方法。2018 年发表的 1 期临床试验报告称进展斜率降低了 34%.
★ 维生素
维生素参与神经系统的发育,可作为预后因素。由于其细胞抗氧化特性,它们也可用于ALS的治疗。它们通常具有良好的耐受性,不会造成显著的不良影响。然而,它们作为补充剂的用途仍存在争议。
——维生素E
补充维生素E对认知功能和神经系统疾病的影响是有争议的。几项研究表明,认知缺陷或阿尔茨海默病患者没有效果。其他研究发现,在ALS患者服用3个月的维生素E和利鲁唑后,维生素E可以降低OS标志物,这是一种有益的效果。然而,维生素E不影响患者的生存。
最近的研究表明,维生素E还具有调节功能,包括信号转导、抑制蛋白激酶C活性、炎症反应和基因表达调节。大量摄入维生素E(与鱼和海藻油中存在的多不饱和脂肪酸,如Omega-3相关)与患ALS的风险降低50-60%相关。尽管补充维生素E对神经退行性疾病有保护作用,但其疗效仍有待证明。
——维生素C
另一种在ALS中具有潜在作用的维生素是维生素C。已经进行了有限的研究,并使用了少量样本。在ALS之前,在动物模型中补充维生素C不会影响ALS的发病,但可以减少疾病导致的瘫痪的进展。
谷禾数据库中也发现,ALS患者肠道菌群检测结果中维生素C显著低于对照组。
——维生素A
据报道,在帕金森病和阿尔茨海默病等神经退行性疾病中,维生素A水平较低。然而,关于维生素A在ALS患者中的作用,存在着相互矛盾的结果。菲茨杰拉德等人报告说,类胡萝卜素中含有的维生素A摄入量高与ALS发病风险低相关。其他研究发现维生素A与ALS之间没有显著关联。
★ 植物化学物质
中国神经退行性疾病的低发病率可能是由于水果和蔬菜的广泛消费,这与植物化学物质的大量存在有关。
先前的研究表明,植物衍生的生物活性化合物,即植物化学物质,在神经退行性疾病中具有神经保护作用。事实上,越来越多的研究证实了它们的抗氧化特性。植物化学物质存在于蔬菜、谷物和水果中,在文献中通常被描述为“营养食品”。
植物化学物质包括广泛的化合物,如类胡萝卜素、酚类化合物和萜类化合物。
类胡萝卜素
类胡萝卜素是一种广泛存在于许多水果中的植物色素,具有典型的红色、黄色和橙色。它们的目标是过氧基。它们也是另一种抗氧化剂维生素A的前体。
文献报道了β-胡萝卜素与维生素E和C在清除活性氮物种方面的协同效应。先前的研究表明,类胡萝卜素的摄入与ALS风险呈负相关。
多酚
多酚是一类由多种分子组成的化合物。其特征在于存在至少一个对抗氧化和抗肿瘤活性重要的酚环,羟基、甲基或乙酰基取代氢。
在ALS动物模型中进行的几项研究表明,多酚具有神经保护作用。黄酮类化合物是酚类化合物的主要成分。它们属于一大类植物色素,其化学结构源自黄酮。它们由以下亚类组成:花青素、黄烷酮、黄烷-3-醇、黄酮、黄酮醇和异黄酮。
黄酮类化合物在神经炎症中发挥作用,抑制小胶质细胞激活并与神经元受体相互作用。人类神经元SH-SY5Y神经元细胞是一种神经退行性疾病模型,用几种黄酮类化合物,即槲皮素、异槲皮素和阿夫泽林进行治疗。治疗显示出下调环氧化酶-2表达和凋亡途径的有益效果。
白藜芦醇是一种在葡萄中发现的抗氧化化合物,由于其神经保护特性而受到广泛研究。它调节Sirtuin 1(SIRT1),Sirtuin脱乙酰化蛋白的主要成员,通过表观遗传基因沉默调节基因表达。一项研究表明,白藜芦醇增加了皮层和海马中SIRT1的表达,减少了认知障碍。
白藜芦醇可降低ALS 患者脑脊液 (CSF)的体外神经毒性,防止神经元丢失并改善 Ca2+ 稳态,这似乎与白藜芦醇的抗氧化能力有关。奇怪的是,与利鲁唑共同使用会抑制这种保护作用。
事实上,Ca 2+失稳与神经退行性疾病(包括肌萎缩侧索硬化)中自噬机制受损和毒性蛋白聚集有关。旨在调节自噬途径的治疗干预似乎是一种减少蛋白质聚集的有趣方法,主要是在 ALS 的早期阶段。
扩展阅读:
姜黄素
姜黄素是从姜科姜黄根茎中提取的,由于其抗炎和抗氧化特性,可能对神经退行性变具有有益作用,实验动物模型证明了这一点。然而姜黄素的临床疗效仍有争议。鉴于姜黄素作为抗氧化剂的强大活性,它可能在神经元退化中发挥关键作用。
事实上,活性氧(ROS)水平的增加会刺激促炎基因的转录和细胞因子的释放,如TNF-α、IL-1、IL-6以及导致神经炎症过程的趋化因子。因此,神经炎症的慢性可被认为是神经元变性的原因。
在小鼠模型中的几项研究表明,姜黄素可以降低氧化应激条件,增加抗氧化剂(如谷胱甘肽和超氧化物歧化酶)的水平。特别是,文献报道了家族性ALS中TAR DNA结合蛋白43(TDP-43)的过度表达和突变版本的存在。其结果是其在神经炎或细胞质中的聚集和定位错误。
研究人员使用突变的人类TDP-43产生的细胞ALS样模型分析了姜黄素作为治疗药物的潜在作用。他们证明姜黄素中存在的二甲氧基姜黄素对线粒体膜电位具有保护作用,降低了解偶联蛋白2的水平。
一项临床研究表明,纳米姜黄素和利鲁唑治疗1年可提高ALS患者的生存率。姜黄素对大鼠和人类均无不良毒理学影响。然而,在剂量反应研究中,一些患者表现出腹泻和恶心的发作,可能是副作用。
扩展阅读:
萜类化合物
萜类化合物是一个非常大的植物次级代谢产物家族。体外研究表明,从芳香植物中提取的二萜、单萜和倍半萜具有显著的抗氧化活性,表明它们是抗神经变性的化合物。
Omega-3 + 维生素E
并非所有显示出显著健康益处的天然化合物在神经系统疾病中也具有神经保护作用。例如,在ALS小鼠模型中补充Omega-3报告了细胞损伤的增加,可能会增加疾病进展。在最近的一项对家族性ALS小鼠模型的研究中也获得了类似的结果。然而,Omega-3和维生素E的组合可以降低ALS的风险。
其他疗法
物理治疗和特殊设备可以在ALS的整个过程中增强个人的独立性和安全性。
热疗或漩涡疗法以缓解肌肉痉挛。
建议适度锻炼,但可能有助于保持肌肉力量和功能。温和、低冲击的有氧运动,如散步、游泳和骑自行车,可以增强未受影响的肌肉,运动范围和拉伸运动有助于防止肌肉痉挛和挛缩。
物理治疗师可以推荐在不过度锻炼肌肉的情况下提供这些益处的锻炼。
职业治疗师可以建议使用夹板、坡道、矫正支架、助行器、扶手、伸展器、轮椅等设备,帮助个人节省能量并保持活动。
言语治疗和沟通训练,以尽可能多地保持口头沟通技巧。
特殊设备,如轮椅、电动床或床垫,以最大限度地提高功能独立性。
正念减压
发表在《欧洲神经病学杂志》上的一项研究结果,基于正念的计划可能有助于改善ALS患者的焦虑和抑郁。
进行了开放标签、随机临床试验,以评估正念练习是否改善了 100 名 ALS 患者在诊断后 18 个月的抑郁和焦虑。患者被分配接受常规护理或为期八周的正念减压 (MBSR) 计划。
注:
正念可以被认为是以非判断的方式,通过注意当前的时刻是如何新奇的,将注意力转移到时刻体验的过程。
MBSR计划的目标是将注意力转移到当下(“我现在在做什么;我现在的感觉如何”),并接受感觉、知觉和情绪,而不加评判。
研究表明,与接受常规护理的患者相比,使用 ALS 特异性 MBSR 的干预组报告了更好的生活质量和较低的抑郁水平。
注意:在疾病的所有阶段,都应考虑患者的个人意愿,并尽早开始预先护理计划。
ALS患者表现出不同的疾病严重程度,尽管已经确定了一些风险因素,但这些因素仍不足以充分解释这种异质性。肠道微生物组可能对解决这些差异至关重要,因为它可能直接或间接影响ALS。
进一步的研究对于识别ALS中的相关微生物参与者至关重要,以便在未来的治疗中将其作为目标,以改变肠道微生物群,调节疾病进展并改善生活质量。这种干预措施很可能会针对不同环境和不同基因型的患者进行个性化定制。
总的来说,有希望根据致病机制对病例进行更好的分类,以便进行具有有益效果的靶向治疗,并且ALS在未来将成为一种可治疗的疾病。
关爱渐冻症人群

编辑
目前虽然渐冻症难以彻底治愈,但科研人员从未放弃探索各种渐冻症的治疗方法。谷禾也将在肠道菌群领域帮助探索渐冻症患者的菌群特征,尽早发现疾病风险及时干预,同时也希望通过更多的数据和案例帮助像渐冻症一样的罕见病患者找到适合的基于自身菌群的干预方式。
注:本文未经作者授权不得转载。
本账号内容仅作交流参考,不作为诊断及医疗依据。
主要参考文献:
Stopińska K, Radziwoń-Zaleska M, Domitrz I. The Microbiota-Gut-Brain Axis as a Key to Neuropsychiatric Disorders: A Mini Review. J Clin Med. 2021 Oct 10;10(20):4640. doi: 10.3390/jcm10204640. PMID: 34682763; PMCID: PMC8539144.
Zhang Y, Ogbu D, Garrett S, Xia Y, Sun J. Aberrant enteric neuromuscular system and dysbiosis in amyotrophic lateral sclerosis. Gut Microbes. 2021 Jan-Dec;13(1):1996848. doi: 10.1080/19490976.2021.1996848. PMID: 34812107; PMCID: PMC8632307.
D’Antona S, Caramenti M, Porro D, Castiglioni I, Cava C. Amyotrophic Lateral Sclerosis: A Diet Review. Foods. 2021 Dec 17;10(12):3128. doi: 10.3390/foods10123128. PMID: 34945679; PMCID: PMC8702143.
Yu W, He J, Cai X, Yu Z, Zou Z, Fan D. Neuroimmune Crosstalk Between the Peripheral and the Central Immune System in Amyotrophic Lateral Sclerosis. Front Aging Neurosci. 2022 May 3;14:890958. doi: 10.3389/fnagi.2022.890958. PMID: 35592701; PMCID: PMC9110796.
Beers DR, Appel SH. Immune dysregulation in amyotrophic lateral sclerosis: mechanisms and emerging therapies. Lancet Neurol. 2019 Feb;18(2):211-220. doi: 10.1016/S1474-4422(18)30394-6. PMID: 30663610.
Chan GN, Evans RA, Banks DB, Mesev EV, Miller DS, Cannon RE. Selective induction of P-glycoprotein at the CNS barriers during symptomatic stage of an ALS animal model. Neurosci Lett. 2017 Feb 3;639:103-113. doi: 10.1016/j.neulet.2016.12.049. Epub 2016 Dec 21. PMID: 28011392; PMCID: PMC5278641.
Chen L, Liu X, Tang L, Zhang N, Fan D. Long-Term Use of Riluzole Could Improve the Prognosis of Sporadic Amyotrophic Lateral Sclerosis Patients: A Real-World Cohort Study in China. Front Aging Neurosci. 2016 Oct 24;8:246. doi: 10.3389/fnagi.2016.00246. PMID: 27822184; PMCID: PMC5075535.
Chiu IM, Phatnani H, Kuligowski M, Tapia JC, Carrasco MA, Zhang M, Maniatis T, Carroll MC. Activation of innate and humoral immunity in the peripheral nervous system of ALS transgenic mice. Proc Natl Acad Sci U S A. 2009 Dec 8;106(49):20960-5. doi: 10.1073/pnas.0911405106. Epub 2009 Nov 20. PMID: 19933335; PMCID: PMC2791631.
Cragnolini AB, Lampitella G, Virtuoso A, Viscovo I, Panetsos F, Papa M, Cirillo G. Regional brain susceptibility to neurodegeneration: what is the role of glial cells? Neural Regen Res. 2020 May;15(5):838-842. doi: 10.4103/1673-5374.268897. PMID: 31719244; PMCID: PMC6990768.
Erickson MA, Banks WA. Neuroimmune Axes of the Blood-Brain Barriers and Blood-Brain Interfaces: Bases for Physiological Regulation, Disease States, and Pharmacological Interventions. Pharmacol Rev. 2018 Apr;70(2):278-314. doi: 10.1124/pr.117.014647. PMID: 29496890; PMCID: PMC5833009
Chua JP, De Calbiac H, Kabashi E, Barmada SJ. Autophagy and ALS: mechanistic insights and therapeutic implications. Autophagy. 2022 Feb;18(2):254-282. doi: 10.1080/15548627.2021.1926656. Epub 2021 May 31. PMID: 34057020; PMCID: PMC8942428.
Oakes JA, Davies MC, Collins MO. TBK1: a new player in ALS linking autophagy and neuroinflammation. Mol Brain. 2017 Feb 2;10(1):5. doi: 10.1186/s13041-017-0287-x. PMID: 28148298; PMCID: PMC5288885.
Peggion C, Scalcon V, Massimino ML, Nies K, Lopreiato R, Rigobello MP, Bertoli A. SOD1 in ALS: Taking Stock in Pathogenic Mechanisms and the Role of Glial and Muscle Cells. Antioxidants (Basel). 2022 Mar 23;11(4):614. doi: 10.3390/antiox11040614. PMID: 35453299; PMCID: PMC9032988.
Calvo AC, Valledor-Martín I, Moreno-Martínez L, Toivonen JM, Osta R. Lessons to Learn from the Gut Microbiota: A Focus on Amyotrophic Lateral Sclerosis. Genes (Basel). 2022 May 12;13(5):865. doi: 10.3390/genes13050865. PMID: 35627250; PMCID: PMC9140531.
Lu G, Wen Q, Cui B, Li Q, Zhang F. Washed microbiota transplantation stopped the deterioration of amyotrophic lateral sclerosis: the first case report and narrative review. J Biomed Res. 2022 Jun 28:1-8. doi: 10.7555/JBR.36.20220088. Epub ahead of print. PMID: 35821195.
Cox LM, Calcagno N, Gauthier C, Madore C, Butovsky O, Weiner HL. The microbiota restrains neurodegenerative microglia in a model of amyotrophic lateral sclerosis. Microbiome. 2022 Mar 11;10(1):47. doi: 10.1186/s40168-022-01232-z. PMID: 35272713; PMCID: PMC8915543.
Zeng, Q., Shen, J., Chen, K. et al. The alteration of gut microbiome and metabolism in amyotrophic lateral sclerosis patients. Sci Rep 10, 12998 (2020).
Alonso R, Pisa D, Carrasco L. Searching for Bacteria in Neural Tissue From Amyotrophic Lateral Sclerosis. Front Neurosci. 2019 Feb 26;13:171. doi: 10.3389/fnins.2019.00171. PMID: 30863279; PMCID: PMC6399391.
Boddy SL, Giovannelli I, Sassani M, Cooper-Knock J, Snyder MP, Segal E, Elinav E, Barker LA, Shaw PJ, McDermott CJ. The gut microbiome: a key player in the complexity of amyotrophic lateral sclerosis (ALS). BMC Med. 2021 Jan 20;19(1):13. doi: 10.1186/s12916-020-01885-3. PMID: 33468103; PMCID: PMC7816375.
Sun J, Huang T, Debelius JW, Fang F. Gut microbiome and amyotrophic lateral sclerosis: A systematic review of current evidence. J Intern Med. 2021 Oct;290(4):758-788. doi: 10.1111/joim.13336. Epub 2021 Jul 8. PMID: 34080741.
Martin S, Battistini C, Sun J. A Gut Feeling in Amyotrophic Lateral Sclerosis: Microbiome of Mice and Men. Front Cell Infect Microbiol. 2022 Mar 11;12:839526. doi: 10.3389/fcimb.2022.839526. PMID: 35360111; PMCID: PMC8963415.
Nicholson K, Bjornevik K, Abu-Ali G, Chan J, Cortese M, Dedi B, Jeon M, Xavier R, Huttenhower C, Ascherio A, Berry JD. The human gut microbiota in people with amyotrophic lateral sclerosis. Amyotroph Lateral Scler Frontotemporal Degener. 2021 May;22(3-4):186-194. doi: 10.1080/21678421.2020.1828475. Epub 2020 Nov 2. PMID: 33135936.
Garofalo S, Cocozza G, Porzia A, Inghilleri M, Raspa M, Scavizzi F, Aronica E, Bernardini G, Peng L, Ransohoff RM, Santoni A, Limatola C. Natural killer cells modulate motor neuron-immune cell cross talk in models of Amyotrophic Lateral Sclerosis. Nat Commun. 2020 Apr 14;11(1):1773. doi: 10.1038/s41467-020-15644-8. PMID: 32286313; PMCID: PMC7156729.
Hertzberg VS, Singh H, Fournier CN, Moustafa A, Polak M, Kuelbs CA, Torralba MG, Tansey MG, Nelson KE, Glass JD. Gut microbiome differences between amyotrophic lateral sclerosis patients and spouse controls. Amyotroph Lateral Scler Frontotemporal Degener. 2022 Feb;23(1-2):91-99. doi: 10.1080/21678421.2021.1904994. Epub 2021 Apr 5. PMID: 33818222.
Andrew AS, Bradley WG, Peipert D, Butt T, Amoako K, Pioro EP, Tandan R, Novak J, Quick A, Pugar KD, Sawlani K, Katirji B, Hayes TA, Cazzolli P, Gui J, Mehta P, Horton DK, Stommel EW. Risk factors for amyotrophic lateral sclerosis: A regional United States case-control study. Muscle Nerve. 2021 Jan;63(1):52-59. doi: 10.1002/mus.27085. Epub 2020 Oct 18. PMID: 33006184; PMCID: PMC7821307.
Masrori P, Van Damme P. Amyotrophic lateral sclerosis: a clinical review. Eur J Neurol. 2020 Oct;27(10):1918-1929. doi: 10.1111/ene.14393. Epub 2020 Jul 7. PMID: 32526057; PMCID: PMC7540334.
谷禾健康
Eubacterium 通常翻译为真杆菌属或优杆菌属
Eubacterium,革兰氏阳性细菌,属于真杆菌科,厚壁菌门。
Eubacterium 是在健康人结肠中发现的一种重要的肠道细菌,它是人类肠道微生物群的核心菌属之一,并显示出在大部分人群肠道,口腔等部位的广泛定植,对机体有营养代谢和维持肠道平衡有重要的作用。但是少数菌种可与其它兼性厌氧菌造成混合感染,引起人心内膜炎,盆腔炎等疾病。
这个家族的成员很重要,因为许多菌种产生短链脂肪酸,尤其丁酸。短链脂肪酸普遍被认为对维持人体健康具有多种重要作用,例如充当肠道上皮特殊营养和能量组分、保护肠道黏膜屏障、降低人体炎症水平和增强胃肠道运动机能等等。
F.prausnitzii、Eubacterium rectale、Eubacterium hallii、Roseburia gutis和Ruminococcus bromii是人类肠道中产生丁酸的主要物种。真杆菌属的几个成员均产生丁酸盐,丁酸盐在能量稳态、结肠运动、免疫调节和肠道炎症抑制中起着关键作用。
同时真杆菌属成员还被证明在以下过程中发挥关键作用:
胆汁酸和胆固醇转化
参与草酸盐分解代谢
促进抗炎分子的产生
预防气道过敏性炎症
降低胰岛素分泌并增加“健康”脂肪的水平
与下腹部脂肪之间的关联
…
在越来越多的肠道菌群研究中发现,Eubacterium的减少或缺乏与很多疾病相关,比如抑郁和/或疲劳、肥胖、IBD、II型糖尿病、心脑血管、结直肠癌、自闭症、老年肌少症、肠道健康以及肿瘤预后良好和肠道稳态状态等。
该属的多个物种目前被认为是微生物治疗的有希望的目标。事实上,基于谷禾长期的菌群检测实践与肠道微生物科学研究等达成的“共识”表明,肠道真杆菌属(Eubacterium)、罗氏菌属(Roseburia)和粪杆菌属, (Faecalibacterium, 也称为普拉梭菌)等的特定产丁酸盐微生物菌株属于对人类健康有益的菌属,其作用方式与乳杆菌属和双歧杆菌属菌株可能相同。
但是,需要注意的是,Eubacterium属正如下面进一步讨论的一样,很难定义,因为最初分配给该属的几个物种随后被重新分配给现有的或新的属。即使是现在,该属在系统发育上仍然是多样化的,成员可以被分配到几个谱系。认识到这种分类学的变化,我们将包括一些最近重新分配给其他属的前真杆菌属物种。此外,本文也将在很大程度上讨论对真杆菌属的与肠道以及健康相关的信息。
真/优杆菌属(Eubacterium)是人类胃肠道含量较为丰富的菌属,是人和动物口腔与肠道正常菌群的成员。
该属由系统发生学上和表型上不同的物种组成,使真杆菌属成为分类学上独特且具有挑战性的属。该属的特征是包含多种表型多样化的物种,革兰氏阳性,杆状生物属,非孢子形成,这些细菌的特点是坚硬的细胞壁。它们可以是能动的或不能动的。如果能动,它们就有鞭毛。通常单独出现,成对出现,或短链。偶尔与腹部、骨盆或泌尿生殖道的混合感染有关。
该物种是厌氧的,这使得真杆菌属的表型鉴定非常耗时,这可能一定程度抑制了对从粪便中分离的属成员的详细研究。
真杆菌属
Eubacterium
化能有机营养,发酵代谢,有些种利用碳水化合物。发酵葡萄糖或蛋白胨的主要产物通常包括大量的丁酸、乙酸或甲酸并有可测得的H2的混合酸。接触酶阴性,通常吲哚阴性。可能还原硝酸盐,可能液化明胶。
1938年首次提出,常在哺乳动物的口腔和肠道中发现,包括在反刍动物的瘤胃以及在环境中。
该属构成人类肠道微生物群的核心属之一,并显示出在全世界人类肠道的广泛定植,包括亚洲、非洲、澳大利亚、欧洲、南美洲、北美洲等不同人群中,表明该菌属具有高度的特异性和适应性。真杆菌属DNA(G + C)含量约为30~57mol%,代表菌种为黏液真杆菌。
多数物种要求特殊的厌氧培养技术和营养丰富的培养基,菌落通常低凸或平坦。这个属里的有些种在自然界中可被糖乳酸化或可运动。
本属细菌从碳水化合物或蛋白胨中产生有机酸混合物,其可能包括大量的丁酸、乙酸和甲酸。
根据Bergey的《细菌和古菌系统学手册》以及NCBI分类学的最新版本,真细菌属属于厚壁菌门、梭状芽胞杆菌目和真细菌科。
由于该属的定义相当宽松,目前该属中的许多物种不属于严格意义上的属,很可能会及时移至新的或现有的属中。
2020年爱尔兰Cotter 团队提供了该树的更新,以显示该属某些成员与其他密切相关物种之间的系统发育关系(下图)。
真杆菌属的系统发育关系
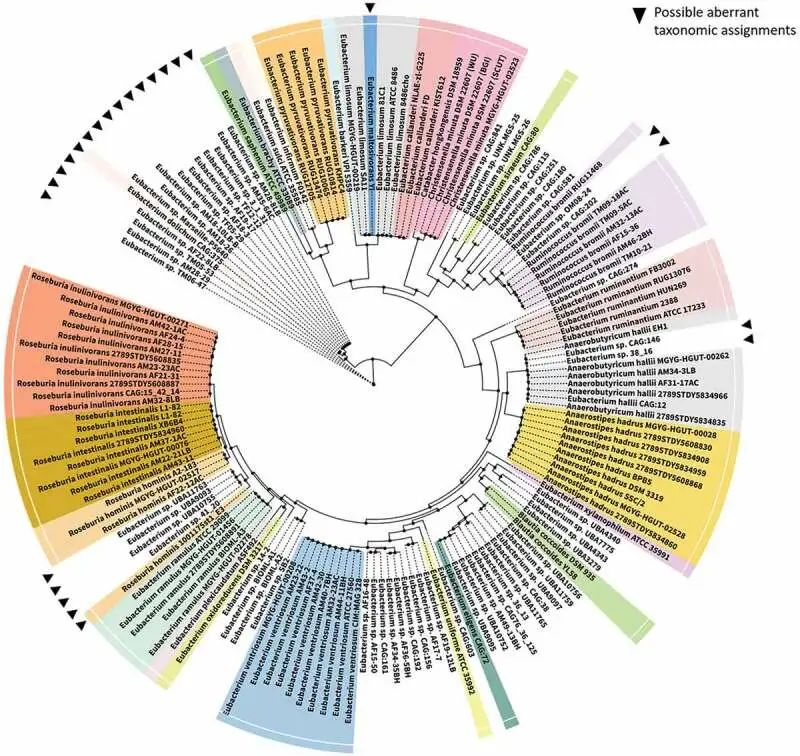
doi: 10.1080/19490976.2020.1802866
▸ 真杆菌属的重新分类
经过重新分类的真杆菌属的大多数成员被归入厚壁菌门,并广泛分布于其中。例如,E. formicgenerans和E. timidum,它们分别被重新分配到Dorea属和Mogibacterium属。
然而,其他几个成员已被重新分配到其他门;实例包括将真杆菌物种重新分配给Slackia 、Cryptobacterium和Eggerthela等属,所有这些属都属于放线菌门。
值得注意的是,某些E. cylindroides等真杆菌属物种可能同时表现出革兰氏阳性和革兰氏阴性特征,从而在分类学分配中经常实施的基本表型特征中产生歧义;这进一步导致了真杆菌属物种分类的相当大的混乱。
▸ 狭义的真杆菌属
有人提出,狭义真杆菌属的核心基因型仅限于该属的模式种Eubacterium limnosum,以及Eubacterium callanderi 、Eubacterium barkeri和Eubacterium aggregans,当有足够的基因组和系统发育证据支持时,其余物种可能被同化为/重新分类为现有或新属。
为实用起见,迄今为止,成员已根据系统发育特征分为子类别。提议的松散系统发育子类别之一包含E. rectale、E. oxidoreducens、E. ramulus、Roseburia cecicola和R. intestinalis,其中除E. oxidoreducens之外的所有物种都产生丁酸盐并且是糖分解的。
▸ 进一步分类的必要性
后来又有科学家提出了对其中一些物种进行重新分类的有力案例。E. eligens是一种重要的肠道真杆菌,已被发现与Lachnospira pectinoschiza具有相当大的系统发育和表型相似性,并且随着进一步证据的可用性而值得重新分类。
鉴于它们不同的表型和系统发育特征,某些对肠道健康很重要的真杆菌属物种已经或计划进行重新分类。例如,建议将E. hallii重新分类为Anaerobutyricum hallii Comb。
2020年11月,报道了一种类似的新型产丁酸盐和丙酸盐的物种Anaerobutyricum soehngenii。事实上,E. hallii与E. indolis、E. cellulosolvens、E. plexicaudatum、E. ruminantium、E. saburreum、E. xylanophilum、E. uniforme 和 E. ventriosum 一起构成了真杆菌属中有趣的种。
值得注意的是,这一群体的成员在系统发育上或表型上与该属中的其他物种没有亲缘关系,并表现出独特的特征,从而为每个物种创建一个新的属。
▸分类对人类微生物群研究影响大,重新分类需谨慎
此外,最近有人提议将最重要的肠道微生物之一直肠肠杆菌重新归类为直肠Agathobacter。然而,这种重新分类受到其他科学家等人的质疑。认为没有理由重新分类并指出其分类学或系统发育隶属关系的任何变化都将对人类微生物群研究产生重大影响。
可以理解的是,提出的分类学重新分配尚未被普遍接受,事实上,如前所述,在考虑真杆菌属任何成员的分类学分类和报告时必须小心。与属的分类有关的进一步努力应该主要关注基因型,并强调基因组特征。
真杆菌属目前的模式菌种为黏液真杆菌(Eubacterium limosum)。研究较多的是:
饮食是决定肠道菌群组成和多样性的最重要因素之一。就真杆菌属而言,它们在肠道中的存在在很大程度上与膳食纤维摄入量的增加有关,多项研究证真杆菌属对消化抗性复合碳水化合物的利用,并且已被证明随着饮食中蛋白质/脂肪百分比的增加而减少。
E. hallii和E. rectale被证明能够利用证明能够利用补充有抗性碳水化合物的培养基,即长链的果聚糖,如低聚果糖、高性能菊粉。
▸ 地中海饮食增加真杆菌属的数量
多项研究报告称,西方饮食中动物蛋白和脂肪的比例增加且纤维含量低,导致肠道细菌丰度显着下降,包括双歧杆菌和真杆菌属等理想的菌群。涉及地中海饮食的研究也表明,地中海饮食可以增加肠道中真杆菌属(Eubacterium)的数量。
研究显示45岁男性食用富含多不饱和 omega-3 脂肪酸的饮食时,肠道微生物群的变化,包括真杆菌在内的几种丁酸盐菌的丰度急剧增加,表明多不饱和脂肪酸对真杆菌的正向调节。
在衰老过程中,胃肠道会发生变化,包括粘膜屏障和肠神经系统的退化以及肠道运动的改变和胃肠道病变的增加。
▸老年菌群多样性↓,短链脂肪酸生成↓,肠道炎症↑
总的趋势是,老年人的微生物群多样性随着丁酸盐生产者的减少和潜在病原体数量的增加而减少。肠道中短链脂肪酸生成的减少可导致肠上皮细胞粘蛋白分泌受损,从而增加病原体进入肠粘膜的机会, 潜在的肠道炎症。
在老年人中,肠道相关淋巴组织 (GALT) 受损会加剧肠道炎症,导致无法有效控制常驻微生物群并导致肠细胞释放促炎细胞因子和趋化因子;后者驱动效应 TH1、TH2 和 TH17 细胞的分化。
与上面观察结果一致的是,在百岁老人中,在百岁老人中发现了E. hallii、E. rectale 和 E.ventriosum相对比例降低,而来自变形杆菌门的潜在致病细菌增加。
▸ 真杆菌:老年肠道微生物生态系统中的关键物种
后续的研究进行的一项广泛研究强调了真杆菌属的有益作用,其中调查了一大群老年人(n=612),以评估地中海饮食对其肠道微生物群的调节作用。作者报告称,真杆菌(Eubacterium)物种,如直肠真杆菌(E.rectale)和 E.eligens与一些较低虚弱、认知能力提高以及短/支链脂肪酸产量增加的标志物呈正相关。
真杆菌与炎症标志物如IL-2和C反应蛋白呈负相关。此外,网络分析显示,真杆菌属是老年肠道微生物生态系统中的关键物种。然而,与这些一般观察结果相反,其他研究推断出真杆菌属与年龄之间存在正相关。
短链脂肪酸有益于人类健康,它们由不同的结肠微生物群产生,包括来自真杆菌属的几种物种(上图)。
▸ E. rectale 是研究最广泛的真杆菌种之一
它首先从健康的日本-夏威夷男性的粪便中分离出来,被确定为主要的丁酸盐生产者,能够利用复杂的碳水化合物(如纤维二糖和淀粉)进行生长和增殖。
▸ 产丁酸的途径,与真杆菌相关
E. hallii也是人体肠道中的丁酸盐生产者。在肠道中,丁酸可以通过糖酵解从碳水化合物中产生,其中两分子乙酰辅酶A结合形成乙酰乙酰辅酶A,然后逐步还原生成丁酰辅酶 A。
目前已知丁酸CoA最终转化为丁酸的两种不同途径;这通过丁酸CoA:乙酸CoA转移酶途径或磷酸转丁酸酶和丁酸激酶途径进行。丁酰辅酶 A 转移酶途径与丁酸合成基因与直肠真杆菌和Roseburia等物种密切相关。
其他真杆菌种也采用相同的途径,例如E. hallii和E. biforme(现在重新归类为Holdemanella biformis)用于生产丁酸盐。
▸ 丁酸高产的真杆菌属——E. rectale 和 E. hallii
E. rectale和E. hallii随后被确定为肠道中的高产丁酸盐生产者。它们被发现是人类粪便微生物群中最丰富的 10 个成员之一,贡献了从 10 名健康志愿者的粪便样本中检索到的超过 44% 的丁酰辅酶 A:乙酸 CoA 转移酶序列。
瑞士最近的一项队列研究也表明,E. hallii 是婴儿肠道中丁酸的首批生产者之一。
▸ 转化为丙酸的1,2-丙二醇可被E. hallii 代谢
肠道微生物通过糖发酵的两种途径形成丙酸。虽然琥珀酸途径处理大多数戊糖和己糖产生丙酸,但丙二醇途径代谢脱氧糖如岩藻糖和鼠李糖。后者作为膳食(例如人乳低聚糖)或宿主衍生(粘蛋白)聚糖在肠道环境中很容易获得,并且在被各种肠道微生物利用后可以产生 1,2-丙二醇作为最终产物。虽然不能降解脱氧糖,但 1,2-丙二醇可被E. hallii代谢,已证明携带甘油/二醇脱水酶PduCDE,这是1,2-丙二醇转化为丙酸和丙醇并生成一个ATP的关键酶。
1,2-丙二醇转化为丙酸取决于维生素B12的有效性,并发生在称为多面体的小隔间内,以隔离有毒中间体丙醛。
虽然真杆菌属(Eubacterium)可以降解复合碳水化合物,但某些真杆菌属菌株可能缺乏降解特定复合碳水化合物的能力,并依赖于其他肠道微生物产生的代谢产物;然后,这些其他肠道微生物产生的发酵产物可以被真杆菌利用。
▸ 交叉喂养机制在真杆菌属生产短链脂肪酸中的重要性
已在多个实例中得到证明。在这些研究中,真杆菌与双歧杆菌在复合碳水化合物存在下共培养。这些双歧杆菌菌株能够降解阿拉伯木聚糖低聚糖和岩藻糖基乳糖等复合碳水化合物,可产生乙酸盐、乳酸和 1,2-丙二醇,所有这些物质又被真杆菌属吸收和利用,生成丁酸和丙酸。真杆菌属这种交叉喂养的证据。
这不仅强调了肠道微生物与抗性碳水化合物的产丁酸作用之间的协同相互作用,而且强调了肠道微生态整齐的生态互作,不是关注一个菌而是整体的菌群健康状况。同时也突出了真杆菌属在维持肠道健康中的生态作用。
研究已经证实丁酸盐构成了结肠细胞的主要能量来源,促进了它们的增殖、成熟,发育成健康的结肠。事实上,据报道,E. rectale (直肠真杆菌)优先定殖粘液层,从而增加丁酸盐对上皮结肠细胞的生物利用度。
▸ 短链脂肪酸促进肠道完整性
此外,短链脂肪酸已被证明在通过促进肠道完整性和调节免疫反应来调节肠道炎症方面发挥重要作用。短链脂肪酸可以通过上调紧密连接蛋白(例如 claudin-1 和 occludin)以及肠粘蛋白、粘蛋白 2 来改善肠上皮抵抗力。
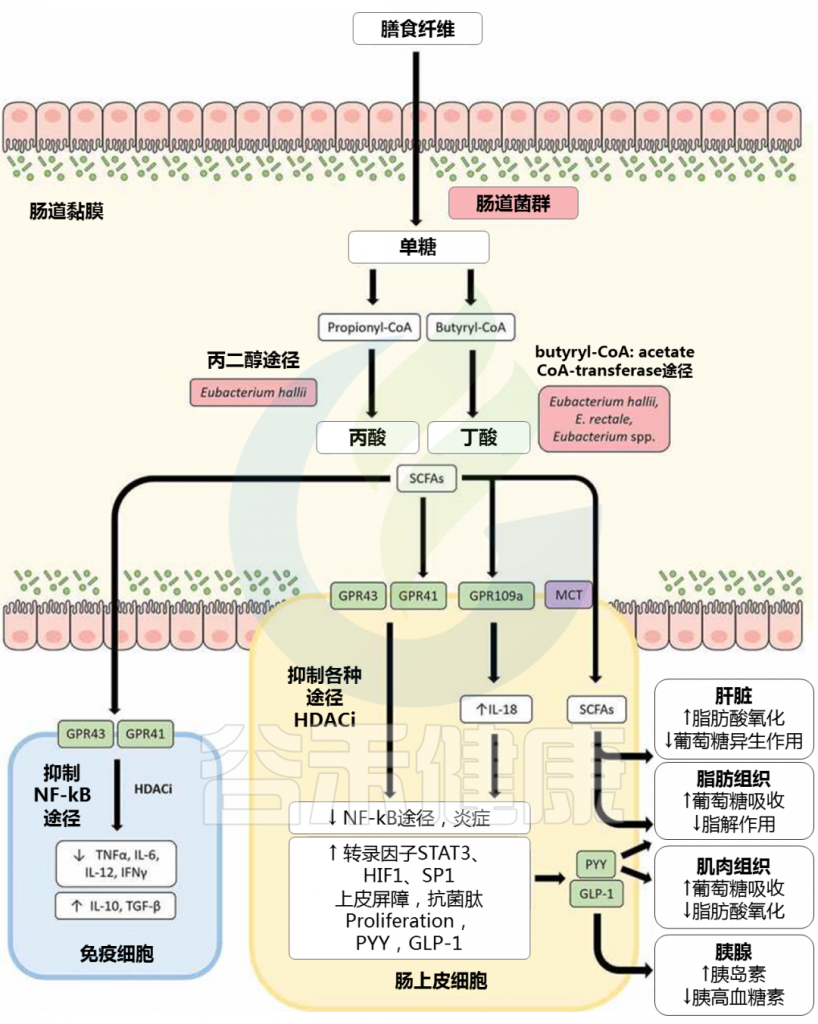
▸ 短链脂肪酸激活GPCR,抑制HDAC
短链脂肪酸对免疫反应的调节,包括G 蛋白偶联受体 (GPCR) 的激活和组蛋白脱乙酰酶 (HDAC) 的抑制。 短链脂肪酸可以结合至少四种离散的 GPCR——FFAR2(游离脂肪酸受体)、FFAR3、GPR109a 和 Olfr78 作为配体,尽管具有不同的特异性。
▸ 短链脂肪酸抑制促炎细胞因子,上调抗炎细胞因子
一些研究表明,短链脂肪酸可以通过抑制促炎细胞因子(如 IFN-γ、IL-1β、IL-6、IL-8 和 TNF-α)发挥抗炎作用,同时上调抗炎细胞因子例如 FFAR2/FFAR3 依赖性方式的 IL-10 和 TGF-β。
GPR109a 激活结肠巨噬细胞和树突状细胞中的炎性体通路,从而诱导调节性 T 细胞和产生抗炎性 IL-10 的 T 细胞的分化。

doi: 10.1080/19490976.2020.1802866
▸ 短链脂肪酸增加IL-18 的产生
短链脂肪酸在肠上皮细胞 (IECs) 中激活 GPR109a 也可以增加 IL-18 的产生,IL-18 是修复和维持肠上皮完整性的关键细胞因子。丙酸盐和丁酸盐对 HDAC 活性的抑制与 IEC 中促炎细胞因子和趋化因子(如 CXCL8 和 CCL20)的表达下调有关。
短链脂肪酸对 HDAC 的抑制也与 β-防御素和导管素(如 LL-37)的表达增加有关。鉴于如上所述,短链脂肪酸广泛参与调节肠道健康,尤其是丁酸盐,由于肠道中短链脂肪酸分布的改变,涉及短链脂肪酸生产者的肠道微生物群失调具有重大影响。
注:组蛋白去乙酰化酶(histone deacetylase,HDAC)是一类蛋白酶,对染色体的结构修饰和基因表达调控发挥着重要的作用。
炎症性肠病 (IBD) 是胃肠道的严重和慢性炎症,其特征在于两种主要的临床表型:克罗恩病 (CD) 和溃疡性结肠炎 (UC)。克罗恩病涉及上皮壁所有层的透壁炎症,而溃疡性结肠炎仅影响浅表粘膜层。
▸ IBD患者真杆菌属持续减少
一般来说,IBD 反复表现出肠道微生物群失调,其特征是微生物群的多样性和时间稳定性下降。虽然微生物干扰在 IBD 的发病机制或病因中的确切作用仍在阐明,但包括真杆菌属(Eubacterium)在内的丁酸盐生产者的比例在 IBD 受试者中肠道中的持续减少。
▸ IBD患者丁酸水平降低
事实上,与非 IBD、健康个体相比,IBD 患者中梭菌簇 IV 和 XIVa 的丰度减少以及伴随的致病变形杆菌增加构成了 IBD 微生物失调的特征,可以被视为生物标志物。因此,在患有 IBD 的患者中通常会观察到肠道丁酸水平降低,从而导致宿主免疫系统调节不当。IBD 和实验性结肠炎患者肠道中短链脂肪酸水平降低也与调节性 T 细胞功能降低和炎症增加相关。
▸ 真杆菌在IBD中提供了丁酸盐介导的保护作用
用溃疡性结肠炎和克罗恩病患者粪便微生物群的体外研究表明,丁酸盐产生者较少,定植能力和丁酸盐产生能力降低;用已知的丁酸盐产生菌(包括真细菌属)补充IBD微生物群可恢复丁酸盐的产生,并改善上皮屏障完整性和定植能力。
真杆菌的作用在接受抗 TNF-α 治疗的患有 IBD 的儿童中,进一步证明了肠道健康中的丁酸盐-抗炎轴;E. rectale基线丰度较高的患者对治疗更敏感,E. rectale(直肠真杆菌)的存在预示着炎症的成功减轻。
在体外和小鼠模型中已经证明了E. limosum(粘液真杆菌)及其产生的短链脂肪酸对肠道炎症的保护作用。当TNF-α处理刺激时,由E.limsum产生的短链脂肪酸诱导T84结肠细胞生长,并降低结肠细胞IL-6和TLR4的表达,其中丁酸盐是最显著的效应物。此外,与对照组相比,当提供5%的E. limosum时,小鼠在结肠炎诱导时显示出体重和结肠长度的显著保留。这些观察表明,真杆菌属对肠道健康具有丁酸盐介导的抗炎作用,并将其作为炎症性肠道疾病的一种有吸引力的生物治疗药物。
到目前为止,真杆菌属与肥胖的关系仍存在争议,有几份报告表明真杆菌属和肥胖呈正相关。BMI通常被认为是用来衡量肥胖的参数;一些基于BMI的研究也报告了肥胖受试者体内真杆菌的丰度更高。
▸ 为什么肥胖人群真杆菌的丰度更高?
有趣的是,据报道,在接受治疗的肥胖受试者中,粪便短链脂肪酸减少的肥胖个体中总丁酸水平较高,这表明碳水化合物和脂质的同化增强,这可能导致肥胖表型。这一观察结果可以解释肥胖个体中丁酸盐产生菌(包括真杆菌属)的丰度较高。
仔细观察饮食干预研究表明,肥胖受试者中真杆菌属和其他丁酸盐产生者的比例可能主要受饮食影响。在几项研究中,肥胖个体肠道微生物对复合碳水化合物的利用受到限制,一直有报道称真杆菌属的显著减少。
对印度肥胖和非肥胖儿童进行的一项研究没有发现各组间直肠大肠杆菌(Eubacterium rectale) 丰度的差异。
综合来看,目前的证据表明,当通过合理数量的复合碳水化合物的持续供应在肠道时,真杆菌属和其他丁酸盐产生菌在肥胖个体中的比例增加,从而促进肠道中的能量提取。肥胖个体的饮食而非改变的代谢参数也可能驱动丁酸盐产生菌(包括真杆菌属)的生长和增殖。
▸ 肠道微生物群调节肥胖的确切机制仍在阐明中
丁酸盐已被证明可以缓解饮食诱导的肥胖和改善葡萄糖稳态,这使得很难得出线性结论。在推断肠道菌群和肥胖之间的直接关联时必须谨慎,因为对于具有多因素影响的代谢综合征,任何的相关性结论可能会过于简单。我们在检测实践中也发现,菌群可能只能解释60%左右的肥胖,肥胖是一种多因素代谢综合征,还与菌群外的其他很多因素相关。
在几项研究中,真杆菌属和丁酸盐产生菌与胰岛素敏感性呈正相关。最近的独立研究比较了健康和2型糖尿病个体的宏基因组,明确表明肠道微生物群与2型糖尿病病理生理学之间的潜在相关性。
▸ 2型糖尿病患者真杆菌显著减少
一项在中国和欧洲人群中进行的研究均报告了2型糖尿病受试者中丁酸盐产生菌(包括真杆菌属)的显著减少。其他研究表明,在人和小鼠胰岛素抵抗模型中,丁酸盐生产商(包括从瘦个体移植的真杆菌属)具有恢复作用。
▸ 粪菌移植后真杆菌的增加,代谢改善
事实上,粪菌移植后真杆菌的增加与胰岛素抵抗个体的代谢改善相关。当向肥胖和胰岛素抵抗的db/db小鼠口服给药时,已表明E.hallii显著改善胰岛素敏感性和能量代谢。
▸ 2型糖尿病的代谢调节,与菌群代谢产物短链脂肪酸相关
短链脂肪酸对肠道激素的刺激和对食物摄入的抑制,是2型糖尿病个体肠道微生物群调节宿主代谢的可能机制。这种提出的机制与观察结果一致,即与FFAR2受体结合的丁酸盐和丙酸盐可以调节饱腹激素,例如生长素释放肽(促食欲肽)、胰高血糖素样肽-1(GLP-1)和PYY(促食欲肽) 。
短链脂肪酸对生长素释放肽和 GLP-1/PYY 的相反调节,其中 GLP_1/PYY 上调,生长素释放肽下调,确保减少食物摄入、饱腹感和减少肥胖。 Ghrelin,也与产生丁酸盐的E. rectale呈负相关。
注:Ghrelin,也被称为“饥饿激素”,刺激食欲,在饭前分泌,而 GLP-1 和 PYY 由肠内分泌 L 细胞合成和释放,刺激胰腺 β 细胞分泌胰岛素,减少食物摄入,使能量正常化摄入量和体重减轻。
▸ 直肠真杆菌高丰度与较低的餐后血糖反应呈正相关
一个大型队列(n=800)进行了一项基于机器学习的研究,以便使用从饮食习惯、肠道微生物群、人体测量、身体活动和血液参数中得出的综合特征数据集来预测个体的个性化餐后血糖反应,也支持真杆菌属在胰岛素敏感性中的肯定作用。在他们的研究中,肠道微生物组的72个特征被推断为具有预测性,其中直肠大肠杆菌(Eubacterium rectale)是最强大的特征之一,肠道中较高的细菌丰度与较低的餐后血糖反应呈正相关(n = 430)。
▸ 真杆菌产生的丁酸盐改善胰岛素敏感性和饱腹感
真杆菌产生的丁酸盐也可以通过HDAC(组蛋白去乙酰化酶)抑制介导的胰腺β细胞重编程来改善胰岛素敏感性和饱腹感,从而为2型糖尿病患者提供额外的益处。
▸ 真杆菌产生的短链脂肪酸有助于恢复炎症
据报道,2型糖尿病中存在低度炎症,其中炎症分子在胰岛素靶组织中上调,并导致胰岛素抵抗。例如,TLR4依赖性通过激活胰岛中的巨噬细胞和β细胞产生促炎细胞因子,导致β细胞的调节失调、功能受损和生存能力下降。由真杆菌产生的短链脂肪酸可通过上述机制有助于恢复生理炎症环境。2型糖尿病中其他肠道丁酸盐产生者的持续减少也加强了这种联系。因此,目前的观察结果一致表明,真杆菌属是缓解2型糖尿病的积极贡献者,应被视为一种潜在的治疗方法。
20世纪30年代首次报道了肠道细菌将胆固醇转化为粪甾醇(coprostanol),此后进行了几项研究,以确定能够将胆固醇转化成粪甾醇的细菌。许多已鉴定的微生物最终被归入真细菌属。
▸ 可降解胆固醇的真杆菌:
——Eubacterium coprostanoligenes HL
Eubacterium coprostanoligenes HL (ATCC 51222) 代表了一种这样的细菌,该菌是从生猪污水泻湖中分离出来的,并且由于其降低胆固醇的特性而受到相当大的关注。
尽管随后有报道称多氏拟杆菌 (Bacteroides dorei)、乳杆菌(Lactobacillus sp)和双歧杆菌(Bifidobacterium sp)具有胆固醇利用特性,但这些特性似乎是暂时性的,可能会丢失,从而使Eubacterium coprostanoligenes HL成为唯一可降解胆固醇的可培养肠道分离物。
▸ 肠道微生物群中E. coprostanoligenes 的存在与粪便粪甾醇密切相关
最近,在肠道宏基因组中发现了E. coprostanoligenes 的3β-羟基类固醇脱氢酶同系物,可将胆固醇转化为粪甾醇。
有趣的是,这些肠道甾醇代谢A基因(ismA)被归因于尚未培养的肠道微生物,它们与生命树中的真杆菌物种形成了一个连贯的分支,并可能代表了参与肠道胆固醇降低的新真细菌物种。
▸ Eubacterium coprostanoligenes的胆固醇代谢
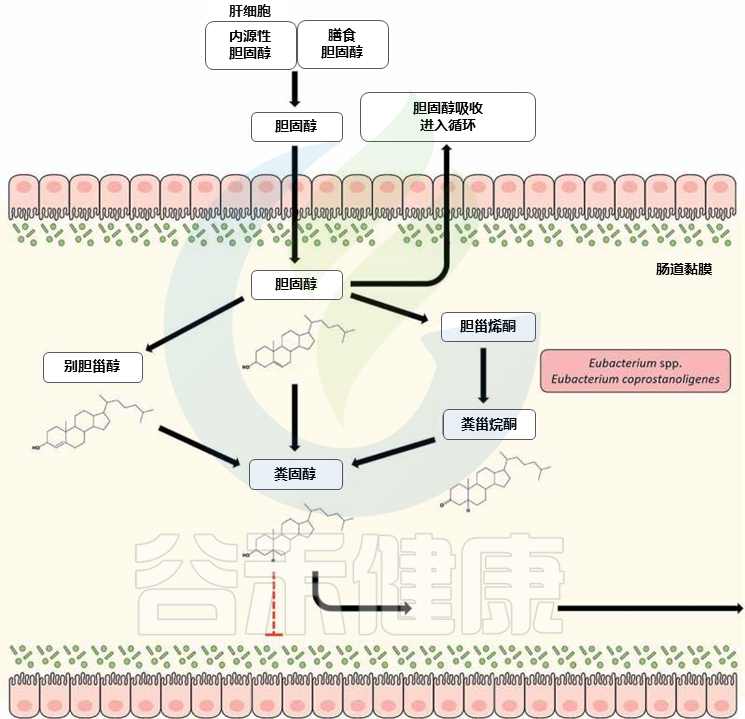
doi: 10.1080/19490976.2020.1802866
来自膳食和额外膳食来源的近1克胆固醇每天到达人体结肠,在那里由共生肠道细菌代谢为粪甾醇。与胆固醇不同,粪甾醇在肠道中吸收不良,并被认为对胆固醇代谢和血清胆固醇水平的调节有影响。
发现血浆胆固醇水平与粪便中胆固醇与粪甾醇的比例之间存在反比关系,这一观点得到了证实。因此,胆固醇向共甾醇的转化被认为是人类胆固醇稳态管理的新策略。作为一种延伸,研究了肠道内高度参与粪甾醇代谢的真杆菌属(Eubacterium spp)的降胆固醇作用。
▸ 动物实验发现E. coprostanoligenes降低胆固醇
据报道,喂食E. coprostanoligenes的高胆固醇血症兔子的血浆胆固醇水平降低,消化液中的粪甾醇/胆固醇比值增加。在这些兔子中观察到的效果进一步归因于E. coprostanoligenes降胆固醇,因为E. coprostanoligenes优先在空肠和回肠中定殖,这两个地方都是胆固醇吸收的场所。在无菌小鼠中也发现了类似的观察结果。
代谢组学和宏基因组学联合研究的其他结果已经确定了多种细菌门型,包括 Eubacterium eligens ATCC 27750 发光真杆菌ATCC 27750(p=1.477e-02)与高粪便粪便甾烷醇显着相关。
▸ 肠道菌群的变化与胆固醇转化速率直接相关,从而影响心血管疾病风险
动脉粥样硬化性心血管疾病 (CVD) 发展过程中的关键风险因素包括血液胆固醇水平失衡和血清低密度脂蛋白胆固醇浓度高。事实上,CVD 患者的肠道胆固醇吸收更高。值得注意的是,肠道微生物群的变化与胆固醇转化为粪前列醇的速率直接相关,而胆固醇转化为粪前列醇的效率高与 CVD 风险降低有关。
由于它们的降胆固醇作用,真杆菌属和其他降低胆固醇的微生物可以预防心血管疾病。
事实上,肠道真杆菌属在动脉粥样硬化受试者中,与已动脉粥样硬化标志物(如低密度脂蛋白、胆固醇和白细胞)呈显着负相关。当给小鼠喂食甲硫氨酸-胆碱饮食以诱发非酒精性脂肪性肝炎时,小鼠肠道中的Eubacterium coprostanoligenes 也减少了,其中对肝脏的损害会抑制内源性胆固醇的产生。
胆汁酸 (BA) 是宿主产生的代谢物,来源于肝脏周围肝细胞中的胆固醇。
我们来了解一下肝肠循环。
胆酸 (CA) 和鹅去氧胆酸 (CDCA) 是肝脏中产生的主要 BA,然后与牛磺酸或甘氨酸结合,然后暂时储存在胆囊中;这些胆汁酸随后经过餐后分泌到达肠道。肠道中 95% 的总胆汁酸池被有效吸收并通过门静脉循环回肝脏,这个循环过程被称为肠肝循环。其余的作为肠道细菌代谢的底物,构成胆固醇从体内排泄的关键途径。
胆汁酸可以以多种形式出现,包括初级胆汁酸、次级胆汁酸、共轭或非共轭。肠道微生物群的各种成员都能够转化胆汁酸,从而影响局部胆汁酸库的组成以及宿主生理学的其他各个方面。
有胆汁盐水解酶(BSH)酶的肠道微生物(包括真杆菌属)能够水解共轭胆汁酸中的C-24 N-酰基酰胺键,以释放甘氨酸/牛磺酸部分。
真杆菌对胆汁酸的修饰与肠肝循环
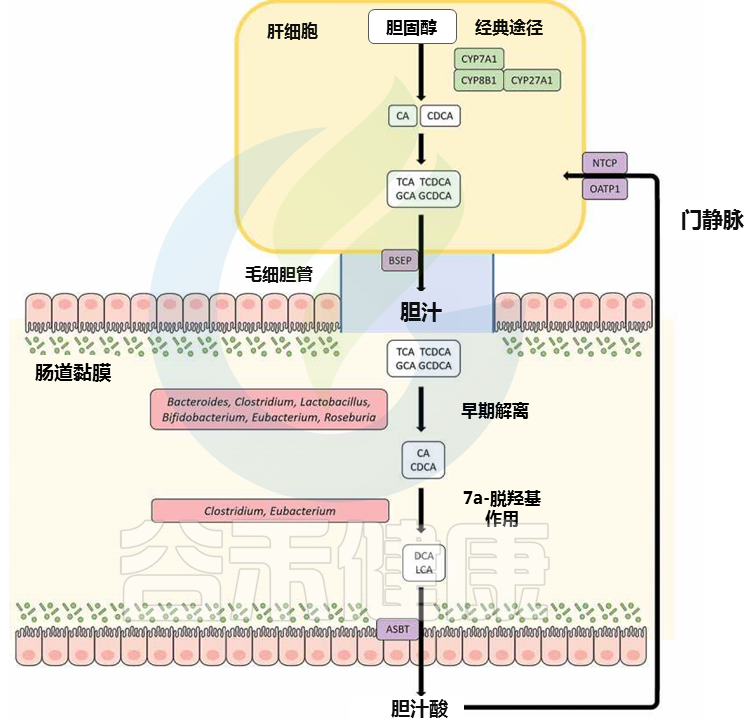
doi: 10.1080/19490976.2020.1802866
▸ 真杆菌参与人体代谢,通过影响胆汁酸的溶解率,影响胆固醇水平
事实上,真杆菌属与其他属(如Roseburia和Clostridium)一起构成了肠道中胆汁盐水解酶的主要储存库。解偶联使BAs的pKa增加到约5,从而使其不易溶解,这反过来导致胆固醇从头合成所损失的胆汁酸的吸收和补充效率低下。
▸ 调节胆汁盐水解酶活性来调节宿主的体重增加和胆固醇水平
胆汁盐水解酶活性广泛分布于肠道微生物群中,因此可以通过调节胆汁盐水解酶活性来调节宿主的体重增加和胆固醇水平。解偶联还通过产生的游离胆汁酸重新捕获和输出共转运的质子,从而帮助胆汁解毒,从而抵消 pH 值。
▸ 肠道细菌转化胆汁酸的方式:生成异胆汁盐
肠道细菌转化胆汁酸的另一种方式是通过C3、C7和C12位羟基的氧化和差向异构化,从而生成异胆汁盐(β-羟基)。
聚合涉及从α构型到β构型的可逆立体化学变化,反之亦然,生成稳定的氧代胆汁酸中间体。这一过程由α-和β-羟基类固醇脱氢酶(HSDHs)催化,可以由含有两种酶的单个细菌物种进行,也可以通过两种物种之间的原合作进行,每个物种贡献一种酶。据报道,包括真杆菌在内的几个物种具有HSDH活性。
▸ 肠道中胆汁酸的细菌转化,真杆菌能够进行
肠道中的细菌 7α-脱羟基酶将初级胆汁酸、CA 和 CDCA 分别转化为脱氧胆酸 (DCA) 和石胆酸 。尽管从数量上讲,7α-羟基化代表了肠道中胆汁酸最重要的细菌转化,但据报道只有少数肠道微生物群的不同成员,如真杆菌和梭菌XIVa 簇能够进行这种反应。
▸ 真杆菌:催化初级胆汁酸7α-脱氢化,对肠道健康有重要影响
对真杆菌菌株 VPI 12708 的研究已经鉴定出由胆汁酸诱导型 ( bai ) 操纵子编码的酶,该操纵子催化初级胆汁酸7α-脱氢化的多步途径。
脱氧胆酸DCA 和 石胆酸LCA 通过真细菌对初级胆汁酸的 7α-脱氢化作用产生属 可对主要通过胆汁酸信号受体表现出来的肠道健康和体内平衡产生重大影响。DCA 和 LCA 都是核激素受体法尼醇 X 受体 (FXR) 的高亲和力配体;DCA 或 LCA 激活肠道 FXR 会上调成纤维细胞生长因子 19 (FGF19) 的表达,后者又与肝成纤维细胞生长因子受体 4 (FGFR4) 结合,随后下调肝细胞中胆汁酸的合成。
胆汁酸诱导的信号通路影响胆汁酸稳态和炎症
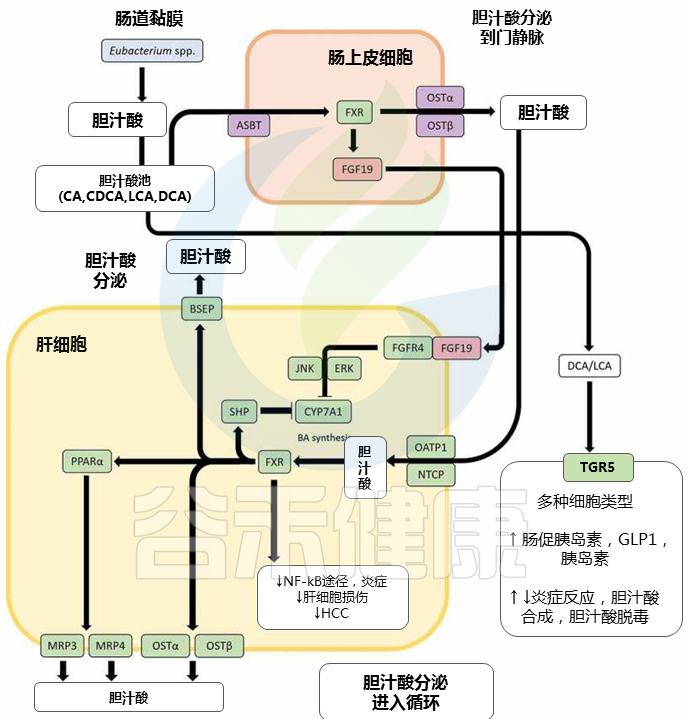
doi: 10.1080/19490976.2020.1802866
▸ FXR促进抗炎特性,有助于控制病原体
主要是通过抑制 NF-κB 通路和胆汁酸解毒,通过调节增殖物激活受体 α (PPARα)。据报道,FXR 激活可诱导抗菌肽的表达,从而有助于控制病原体。
▸ TGR5刺激GLP-1和胰岛素分泌,调节炎症反应
TGR5是一种在与胆汁酸相互作用后激活各种细胞内通路的 GPCR,它也以胆汁酸池中最高的亲和力结合 LCA 和 DCA。一旦被激活,TGR5 会刺激肠促胰岛素激素 GLP-1 和胰岛素的分泌,从而促进能量消耗。
此外,TGR5 可以调节炎症反应,这在本质上可以是促炎或抗炎的;BA-TGR5 信号在肠道促炎细胞因子和抗炎细胞因子的复杂平衡中起着关键作用。
LCA 和 DCA 还与孕烷 X 受体 (PXR)、维生素 D 3受体 (VDR) 和组成型雄激素受体 (CAR) 结合,以不同方式影响胆汁酸稳态和胆汁酸解毒。
生产LCA和DCA的真杆菌属是TGR5的高亲和力配体。
胆汁酸信号受体对微生物群诱导的次生胆汁酸的强亲和力,突出了包括真菌属在内的肠道菌群如何通过胆汁酸信号调节胆汁酸稳态、胆汁酸解毒、控制和维持肠道细菌生长、炎症和血糖反应。
▸ 高脂饮食过度刺激->次级胆汁酸的产生↑->促炎
受饮食和其他因素调节的肠道微生物群可导致特定的胆汁酸分布,进而产生重要后果。高脂肪饮食(HFD)(如西方饮食)过度刺激胆汁酸向肠道的排放,导致肠道微生物群失调,并增加次级胆汁酸的产生,特别是LCA和DCA。
DCA和LCA是胆汁酸池中最疏水的,升高的水平可能具有细胞毒性;DCA和LCA产生的有害影响可通过对DNA的氧化损伤、引发促炎反应和增加细胞增殖来破坏结肠上皮的结构和功能。
▸ LCA/DCA的增加间接与真杆菌相关
在喂食高脂肪饮食的小鼠中,LCA/DCA的增加与梭状芽孢杆菌(一种来自XI梭状芽胞杆菌簇的细菌)丰度的增加相关。令人惊讶的是,据报道,真杆菌属的梭状芽孢杆菌簇XIVa是次要的贡献者,尽管它们表现出7-α羟基化性质。
如上所述,这种观察结果与真细菌属一致,真细菌属受到高脂肪饮食(HFDs)的负调节。
高脂饮食引起的肠内继发胆汁酸的重吸收增加,随后转运至肝脏,导致肝脏炎症。由于炎症增加导致FXR信号减少,导致肝胆汁酸转运蛋白功能降低,这会导致持续的肝脏炎症,最终导致肝细胞癌。
肝脏疾病(如肝细胞癌、脂肪酸肝病(FLD)、纤维化和肝硬化)中的生物失调还表现为需氧、促炎、富含BSH的细菌(如肠杆菌和肠球菌)的增加,这也导致继发胆汁酸的产生增加。
▸ 肝病患者粪便真杆菌比例较低
事实上,在非酒精性脂肪肝(NAFLD)患者中,粪便中的初级和次级胆汁酸之间的比率以及血清中结合和非结合胆汁酸的水平更高,而真细菌在肝脏疾病中的比例始终较低。与健康个体相比,患有纤维化和肝硬化的受试者的肠道微生物组真细菌种类(如E. rectale, E. hallii 和 E. eligens )显著减少。
肠道微生物群产生的二级胆汁酸也可能在结直肠癌(CRC)的发展和建立中发挥关键作用。
▸ 结直肠癌患者中真杆菌属显著减少
如上所述,丁酸盐抑制结直肠癌的发生,并且在结直肠癌患者中通常观察到包括真杆菌在内的肠道中产丁酸盐菌的显著减少。几种丁酸盐生产者,包括属于梭状芽胞杆菌簇 XIVa 的真杆菌属,可以通过初级胆汁酸(BA) 的 7-α 羟基化额外产生次级 BA。
据报道,在患有肠道慢性炎症的 IBD 受试者中,二级 BA 水平显着降低,同时粪便结合 BA 增加,梭菌簇 XIVa 显着减少。
次级 BA 水平的降低导致次级 BA 对肠上皮细胞的抗炎作用丧失,从而加剧慢性炎症。尽管 IBD 中丁酸盐生产者和二级 BA 生产者的损失是分开进行的,但这两个群体有很大的重叠,并且都在肠道慢性炎症中被耗尽。
▸ 炎症性肠病患者中真杆菌属显著减少
事实上,最近对肠道宏基因组的生物信息学分析显示,IBD患者中丁酸盐产生者F.prausnitzii和E.rectale的数量显著减少。可以理解的是,这组丁酸和次级胆汁酸产生细菌(包括真杆菌属)的缺失促进了IBD的发展,并可能最终发展为结直肠癌,因为在那里观察到类似的肠道微生物群。
实际上,胆汁酸分布和/或肠道微生物群的调节正被作为肝癌和结直肠癌的新治疗方法。
▸真杆菌改善自闭症儿童症状和肠道问题
我国陆军军医大学的专家,去年在《Frontiers in Cellular and Infection Microbiology》上发表了研究报告,指出真杆菌是通过肠道菌群调整,改善自闭症患儿症状,及肠道问题的重要关键菌群。而且该研究验证了特定细菌,即真杆菌特别是其中的产粪甾醇真杆菌(Eubacterium coprostanoligenes)丰度变化,可以改善患自闭症患儿症状和多种肠道问题,也让调整肠道菌群成为治疗自闭症的新手段。
▸真杆菌可能避免患上痴呆症
来自日本东京工业大学的 Takuji Yamada 团队通过粪便 16S rRNA 基因测序比较了健康、轻度认知功能障碍(Mild cognitive impairment,MCI)和阿尔茨海默病组的肠道微生物组成,发现肠道关键菌株——普拉梭菌 Faecalibacterium prausnitzii(F. prausnitzii)具有保护人避免患上痴呆症的作用,此外,真杆菌属在两组之间也是存在显著差异,普拉梭菌和真杆菌都是产丁酸重要的肠道核心菌,可以推断真杆菌属可能也具有保护人避免患上痴呆症的作用。
▸重度抑郁症的真杆菌水平较低
来自中国和美国三个不同机构的的一组研究人员,最近在《Science Advances》上发表了一项研究,指出了人类肠道微生物组紊乱与重度抑郁症(MDD)之间的联系。研究人员从156名重度抑郁症患者和155名没有重度抑郁症的人中,收集了311份粪便样本进行基因分析,发现重度抑郁症患者的粪便样本中,出现了高水平的拟杆菌属 和较低水平的真杆菌和布氏杆菌(Blautia)。这意味着,重度抑郁症患者可能具有独特的肠道微生物特征,其中真杆菌是重要的菌群特征菌。
常驻微生物群对肠道中特定化合物的代谢转化对人类健康至关重要。人体无法解毒或分解的物质可能会进入肠道,从而导致毒性作用。
真杆菌属已被证明能够在肠道中进行重要的代谢转化,对人类健康产生积极影响,包括将有毒化合物解毒为更良性的形式。
▸E.hallii 将致癌物转化为不可用形式
最近报道了E.hallii的多种有益转化。E.hallii非常擅长将高度丰富的食物衍生杂环芳香胺致癌物2-氨基-1-甲基-6-苯基咪唑并(4,5-b)吡啶(PhIP)转化为生物学上不可用的形式7-羟基-5-甲基-3-苯基-6,7,8,9-四氢吡啶并[3′,2′:4,5]咪唑并[1,2-α]嘧啶-5-鎓氯化物(PhIP-M1)。
▸E.hallii 转化后的显示其作为保护剂的潜力
此外,在模拟的近端和远端结肠菌群存在的情况下,E.hallii的PhIP转化导致其丰度分别增加300倍和120倍,表明其作为保护剂的巨大潜力。
在同一项研究中,还观察到E.hallii能够将甘油代谢为3-羟基丙醛(3-HPA),其在水溶液中以罗伊氏菌素(Reuterin)的形式存在。有趣的是,罗伊氏菌素已被证明对革兰氏阳性和革兰氏阴性细菌、真菌和酵母具有抑制作用,可能通过调节细胞内谷胱甘肽增加氧化应激,从而使其成为治疗的一个有吸引力的靶点。
注:Reuterin是罗伊氏乳杆菌代谢甘油产生的一种特有广谱抗菌物质,它是一种复杂混合物,主成分为3-羟基丙醛,对多种病原微生物均有较强的抑制作用,在生物防腐方面极具潜力
除了生产短链脂肪酸,需要进一步的研究来真正开发真细菌属所能提供的所有潜在益处。
老年肌少症(Sarcopenia)是以肌肉量减少、肌力下降和肌肉功能减退为特征的增龄性疾病。研究表明肠道微生物可以通过参与宿主体内的多条代谢通路来影响宿主肌肉量与肌肉功能。
北京协和医院共招募87名受试者,包括11名肌少症患者、16名可能肌少症(Possible Sarcopenia)患者和60名健康对照受试者发现毛螺菌属(Lachnospira)、真杆菌属和瘤胃球菌属(Ruminococcus)与握力具有显著正相关性(P < 0.05),罗氏菌属(Roseburia)、真杆菌属(Eubacterium)和蓝绿藻菌属(Lachnoclostridium)与五次起坐时间具有显著负相关性(P< 0.01),结果提示这些菌属的降低与肌肉量的减少和功能的降低存在相关性。
Eubacterium
真杆菌属(Eubacterium)是一组系统发育多样的微生物,这一事实使得相关的分类学分配具有挑战性。
但是,该属的许多现任和前任成员都表现出与肠道健康密切相关,并且作为主要的丁酸盐生产者和核心肠道微生物群组成部分,非常重要。
真杆菌在调节炎症、调节免疫反应、维持肠道屏障完整性、调节血糖反应和胆固醇稳态等方面发挥重要作用。在几种临床条件下与有益效果的强相关性促使人们对该属产生了进一步的兴趣,多个物种被考虑作为下一代益生菌/生物治疗剂进行商业尝试。
最值得注意的是,目前国际上已正在创建含有E. hallii菌株的口服制剂作为生物治疗药物,以降低患有代谢综合征的个体的胰岛素抵抗并预防2型糖尿病的发展。
但是,应该警惕的是,我们对所有相关物种的肠道微生物群在多大程度上影响临床状况以及反之亦然的理解仍然有限。可能需要对严格控制的饮食方案进行纵向研究,在长时间内评估肠道微生物群和相关健康参数,谷禾也在积极推进这样的研究合作,以阐明此类因果关系。
关于真杆菌属的体外和体内表征,需要在基因组、代谢组以及最终在生态水平上进行研究。这将使我们能够更好地了解相对未被充分研究的真杆菌属与肠道微生物组的其他成员相互作用(这也是我们非常看重的),比如它们与其他潜在的下一代健康促进微生物(如Akkermansia muciniphila和F. prausnitzii)分离和组合,以确保其在循证肠道治疗中的有效实践(这也是我们非常看重的)。
主要参考文献
Mukherjee A, Lordan C, Ross RP, Cotter PD. Gut microbes from the phylogenetically diverse genus Eubacterium and their various contributions to gut health. Gut Microbes. 2020 Nov 9;12(1):1802866. doi: 10.1080/19490976.2020.1802866. PMID: 32835590; PMCID: PMC7524325.
Gomes AC, Hoffmann C, Mota JF. The human gut microbiota: Metabolism and perspective in obesity. Gut Microbes. 2018 Jul 4;9(4):308-325. doi: 10.1080/19490976.2018.1465157. Epub 2018 May 24. PMID: 29667480; PMCID: PMC6219651.
akansson A, Molin G. Gut microbiota and inflammation. Nutrients. 2011 Jun;3(6):637-82. doi: 10.3390/nu3060637. Epub 2011 Jun 3. PMID: 22254115; PMCID: PMC3257638.
Wing Sun Faith Chung, Marjolein Meijerink, Birgitte Zeuner, Jesper Holck, Petra Louis, Anne S. Meyer, Jerry M. Wells, Harry J. Flint, Sylvia H. Duncan, Prebiotic potential of pectin and pectic oligosaccharides to promote anti-inflammatory commensal bacteria in the human colon, FEMS Microbiology Ecology, Volume 93, Issue 11, November 2017, fix127,
Mukherjee A, Lordan C, Ross P & Paul D. Cotter. Gut microbes from the phylogenetically diverse genus Eubacterium and their various contributions to gut health, Gut Microbes, 12:1.
Chung W S F, Meijerink M, Zeuner B, Holck J, Louis P, Meyer A S, Wells J M, Flint H J, Duncan S H. Prebiotic potential of pectin and pectic oligosaccharides to promote anti-inflammatory commensal bacteria in the human colon, FEMS Microbiology Ecology, Volume 93, Issue 11, November 2017, fix127,
Chung WSF, Meijerink M, Zeuner B, Holck J, Louis P, Meyer AS, Wells JM, Flint HJ, Duncan SH. Prebiotic potential of pectin and pectic oligosaccharides to promote anti-inflammatory commensal bacteria in the human colon. FEMS Microbiol Ecol. 2017 Nov 1;93(11).
Peñaloza HF, Noguera LP, Riedel CA and Bueno SM. Expanding the Current Knowledge About the Role of Interleukin-10 to Major Concerning Bacteria. Front. Microbiol. 9:2047.
Iyer SS, Cheng G. Role of interleukin 10 transcriptional regulation in inflammation and autoimmune disease. Crit Rev Immunol. 2012;32(1):23-63.
Nauli A M and Matin S. Why Do Men Accumulate Abdominal Visceral Fat? Front. Physiol. 10:1486. December 2021.
Nie X, Chen J, Ma X, Ni Y, Shen Y, Yu H, Panagiotou G, Bao Y. A metagenome-wide association study of gut microbiome and visceral fat accumulation. Comput Struct Biotechnol J. 2020 Sep 20;18:2596-2609.

谷禾健康
什么是CAZymes?
CAZymes(碳水化合物活性EnZymes)是一种酶,主要以糖苷键为目标,降解、合成或修饰地球上的所有碳水化合物。CAZymes在植物和植物相关微生物中非常丰富。
例如,人体肠道是富含碳水化合物的环境,碳水化合物降解细菌的多样性非常高。肠道微生物组的CAZyme组合组成了数以万计的附加基因。
CAZymes对人类健康、营养、肠道微生物组、生物能源、植物疾病和全球碳循环的研究极为重要。
在过去的5年里,大量的微生物组测序,来自各种生态环境的数十万个宏基因组组装基因组 (MAGs) 现在可以在公共数据库中获得。
例如欧洲生物信息学研究所的MGnify数据库和 IMG/M联合基因组研究所数据库。目前,没有数据库从微生物组MAG中收集CAZymes和CAZyme基因簇(CGC)并在网络上提供它们。
✦CAZyme研究对人体健康非常重要
与此同时,CAZyme生物信息学领域继续发展。现在可以推断CAZymes和CGCs的碳水化合物底物,这对应用微生物组非常有兴趣。例如,基于微生物组的个性化营养旨在使用个性化饮食干预策略来调节人体肠道微生物组,以改善人体健康。
预测患者肠道微生物组可能对哪些益生元聚糖做出反应的能力将对营养师和营养学家提出个性化饮食建议非常有用。
✦最新更新了dbCAN-seq数据库
最近在内布拉斯加大学的团队在Nucleic Acids Research发表的题为:“dbCAN-seq update: CAZyme gene clusters and substrates in microbiomes”的文章,更新了dbCAN-seq数据库 ( https://bcb.unl.edu/dbCAN_seq)


包括以下新数据和特征:
(i)来自四种生态(人类肠道、人类口腔、牛瘤胃和海洋)环境的9421个MAG~498000个CAZyme和~169000个CAZyme基因簇(CGC);
(ii) 通过两种新方法(dbCAN-PUL 同源搜索和 eCAMI 亚家族多数表决)推断的41447(24.54%) 个CGC的聚糖底物(这两种方法就4183个CGC的底物分配达成一致);
(iii) 重新设计的CGC页面,包括CGC基因组成的图形显示、查询 CGC 和 dbCAN-PUL 的主题PUL(多糖利用位点)的比对,以及支持预测底物的 eCAMI 亚家族表;
(iv) 一个统计页面,用于根据底物和分类门组织所有数据,以便于CGC访问;
(v) 批量下载页面
总之,这个更新的dbCAN-seq数据库突出显示了预测来自微生物组的CGC的聚糖底物。
dbCAN-seq数据库于2018年发布,提供了5349株细菌分离株基因组的CAZyme和CGC (CAZyme基因簇)序列及注释数据。
CGC是研究人员定义的一个术语,用于描述微生物基因组中含有CAZyme的基因簇。
PUL指多糖利用位点,是一个更流行的术语,描述利用复杂碳水化合物底物的基因簇,例如XUL(木聚糖利用位点),ChiUL(几丁质利用位点)和XyGUL(木聚糖利用位点)。随着CAZyme在生物信息学领域的发展,dbCAN-seq也紧跟步伐,推出了新的版本。
在dbCAN-seq数据库的更新中,主要取得了两个重要的进展:
(i) dbCAN-seq现在提供了四个生态环境(人类肠道,人类口腔,牛瘤胃,海洋)的微生物组的全面的CAZyme和CGC目录。
(ii) dbCAN-seq使用了两种新的方法来预测微生物组CGCs的底物,并提供了底物查阅功能,允许搜索针对不同微生物组中预测的特定底物的CGCs。
对EBI MGnify数据库中的4个MAG数据集,选取其中质量最好的代表性基因组,如下表,一共9421个基因组,使用dbCAN2的run_dbcan程序进行注释,可见有近50万个蛋白质被注释为CAZymes。
人类肠道MAG中CGCs的CAZymes比例最高(55.87%),而牛瘤胃中CGCs的CAZymes比例最低(45.45%)。
在预测出CGCs之后,研究人员开发了两种计算方法来推断它们的糖基底物,如下图。
第一种方法
使用BLAST比对CGCs的蛋白质序列(图A)与dbCAN-PUL的612个PULs的蛋白质序列(图B),选择BLAST总评分最高的最佳命中且至少有一个CAZyme与至少一个来自其它特征基因类别,如TC、TF等相匹配(例如图C),然后通过表S1,PUL→底物的映射文件,获知对应的底物;
第二种方法
使用eCAMI工具对CAZyme亚家族进行注释(图D),确定了CAZyme蛋白的eCAMI亚家族和EC数量后,根据eCAMI亚家族和EC编号建立的CAZyme亚家族→EC→底物的映射文件(表S2),使用简单的多数投票规则来推断CGC中的底物分配。

通过以上两种方法,目前dbCAN-seq数据库中新增的预测底物的CGC计数如下图:
图A为用dbCAN-PUL方法和eCAMI亚族方法注释CGCs的韦恩图。
图B各数据集中丰度top20的底物。
dbCAN-seq的官网为:
如下图,网站也新增了版块:
图A可选五个数据集。
图B可按目录浏览。
图C和D分别为支持通过eCAMI或dbCAN-PUL预测的底物查询对应的CGCs
研究人员计划每年更新dbCAN-seq数据库,以包含更多生态环境的MAG数据集,例如来自小鼠、猪、山羊的肠道MAG,以及来自土壤和地球微生物组项目的MAG。
也会继续探索用于底物预测的方法,比如无监督机器学习方法,以预测自然界中未知的底物的新型CGCs。

谷禾健康
怀孕的母亲与体内的胎儿是息息相关的。由于婴儿接触母体微生物群,母亲和孩子之间的微生物联系在怀孕期间形成。而宿主与微生物群的联系在出生后成熟,并进化成为个体生命中最重要的共生关系之一,对响应营养和环境刺激的稳态调节至关重要。


最近,有报道称微生物群在子宫内发育,并在整个妊娠期间改变。这一发现表明,胎儿很可能通过胎盘早期暴露于母体微生物群。
✦多种因素共同作用婴儿的微生物群
婴儿的基因组成、分娩方式、抗生素使用、喂养类型、疾病状况和其他环境暴露可能影响新生儿微生物群的建立和成熟。
在子宫内和早期生活中的营养和环境暴露是形成健康肠道微生物群的关键因素。强大的微生物群有助于粘膜免疫系统的发育和成熟,有助于维生素合成和营养吸收,并在中枢神经系统的生化信号中发挥作用。
健康与疾病的发展起源

Mua B,et al.Comprehensive Gut Microbiota.2022
生命的前1000天,是发育可塑性窗口。这是一个快速成长和表观遗传调控的关键时期。
✦微生物群改变与许多疾病有关
这一发展时期允许通过多种因素调节妊娠结局和微生物组,包括母亲营养、药物滥用、吸烟、城市化、抗生素暴露以及婴儿的喂养类型。胎儿期对此类外部压力源的敏感性也会持续影响到成年的微生物组的组成和功能。
在这个早期时间点,微生物群多样性的改变还与许多疾病有关,包括但不限于慢性代谢紊乱、自身免疫性疾病和神经发育障碍。
本文总结了孕期和产后母婴微生物组的生理及病理变化。此外,我们将讲述常见的母体和营养因素对发育的影响及其在成年期疾病发病中的作用。
本文主要从以下几个方面讲述
●妊娠期间微生物组的变化
●影响婴儿微生物群的因素
●母体微生物对后代免疫的影响
●微生物对儿童疾病风险的影响
几十年来,人们对妊娠相关的激素和代谢变化进行了广泛研究,而对妊娠期间发生的微生物组成变化的研究则较少。
✦母体微生物群发生显著变化
母体微生物群在怀孕过程中发生了显著变化,其特征是微生物群落内丰度和多样性或α多样性降低,微生物群落间丰度或β多样性增加。
这些变化受育龄妇女营养、胎龄、遗传、种族和环境因素的差异影响。此外,孕期母体微生物群组成与母体饮食、孕前体重和孕期体重增加相关,并表明肠道、阴道、口腔和胎盘微生物群可能会根据母体生活方式和孕期环境暴露而发生变化。
孕期母体微生物组成变化
Mua B,et al.Comprehensive Gut Microbiota.2022
健康怀孕的特点是不同部位微生物组丰度和多样性的增加和减少。口腔、胎盘、肠道和阴道微生物组的改变与妊娠炎症和整体健康有关。
细菌的种类(放线菌属、变形菌属、厚壁菌门和拟杆菌门)分别按颜色(绿色、红色、蓝色和黄色)区分。微生物群落多样性在文本中用黑色箭头表示,它们各自的增加和减少。
在整个孕期,肠道微生物组对于营养素获取、免疫重塑和抵抗病原体至关重要。对人类微生物组的研究发现,肠道微生物组的组成在怀孕过程中发生变化,并与生理和代谢变化相关。
✦妊娠期间肠道微生物改变
妊娠前期体重指数较高或患有妊娠期糖尿病的女性在妊娠晚期发现β多样性微生物群落水平升高,且在产后持续存在。还发现,在适当的营养干预后,妊娠期糖尿病患者表现出α多样性增加。
这些发现表明,怀孕是一个动态过程,根据女性怀孕前和怀孕期间的身体状态(即体重和激素水平)、心理压力和环境因素,改变了微生物组特征;所有这些都会在怀孕期间影响肠道微生物组的组成。
•怀孕前三个月与正常妇女相似
例如,在怀孕的前三个月,母体肠道微生物组的组成与健康的非孕妇相似,其中厚壁菌(Firmicutes)比拟杆菌(Bacteroides)占优势。
•三个月后产丁酸的细菌减少
在头三个月后,母体肠道微生物群中产生丁酸的细菌(如普拉梭菌)减少,双歧杆菌(Bifidobacteria)、变形杆菌(Proteobacteria)和乳酸产生菌增加。
反过来,肠道微生物组的改变可能会对妊娠疾病的发生率、胎儿状况、妊娠结果和胎儿免疫发育产生重大影响。
✦激素变化影响细菌生长
•双歧杆菌增加
妊娠相关的激素变化也与宿主激素引起的微生物组组成改变有关。向雌性小鼠补充了孕激素,并确定双歧杆菌(Bifidobacteria)丰度增加,孕激素促进了孕晚期双歧杆菌的生长。
此外,母体胃肠粘膜免疫反应的变化,以及妊娠期间代谢激素的变化,可能引发低级促炎状态,从而诱导肠道通透性,促进葡萄糖从肠道上皮向内腔扩散。这可能会导致体重增加,进而改变肠道微生物组组成。
总的来说,最近的研究结果表明,整个孕期肠道微生物组组成发生了显著变化,与初始体重和饮食、体重增加、炎症水平和代谢参数有关。
✦怀孕对免疫性疾病存在有益影响
有趣的是,怀孕对某些自身免疫性疾病,包括炎症性肠病的病程有有益的影响。
炎症性肠病包括一组广泛的疾病,这些疾病具有潜在的免疫介导的失调和各种肠道炎症状态。
炎症性肠病的两种主要形式为溃疡性结肠炎(UC)和克罗恩病(CD)。
肠道微生物组的组成对炎症性肠病的临床过程很重要,在大多数炎症性肠病病例中,由于肠道失调,细菌多样性降低。
注:炎症性肠病与肠道菌群的关联在谷禾前不久的文章中有具体描述。
详见:肠道菌群失调与炎症性肠病的关联
•怀孕期间炎症性肠病改善
新出现的证据表明,在怀孕期间和怀孕后,炎症性肠病的总体病程有所改善。雌激素和孕酮通过积极调节肠道上皮,对疾病活动有有益影响。
这些激素缓解了压力,减少了促炎细胞因子的产生,刺激了伤口愈合,并增加了上皮屏障功能。
注意:妊娠对炎症性肠病的积极影响可能取决于患者的特征,例如潜在的遗传风险因素、妊娠前或妊娠期间持续的疾病严重程度、环境因素(即饮食、药物、酒精)以及随后对微生物组组成的影响。
阴道微生物组由许多细菌物种控制,包括乳杆菌属(Lactobacillus)以及梭状芽孢杆菌目(Clostridium)、拟杆菌(Bacteroidales)和放线菌目(Actinomycetales)的成员。
✦阴道微生物组在母婴健康中有重要作用
•抑制细菌和病毒
例如,乳杆菌属(Lactobacillaceae)的不同成员可以增强阴道健康的各种特征。这些产乳酸细菌在维持低pH值(<4.5)方面发挥了作用,从而形成了抵抗病原体入侵的屏障。它们还分泌可以抑制泌尿生殖道细菌和病毒感染的代谢物。
•产生细菌素,杀死病原体
此外,除了降低阴道pH值和增加阴道分泌物以防止致病菌进入子宫并引起感染外,乳酸杆菌还会产生细菌素,杀死入侵的病原体。
在母体阴道道中发现的某些细菌种类也可能具有抗菌特性,有助于预防细菌性阴道病和淋病奈瑟菌感染。
✦怀孕后阴道微生物多样性降低
在阴道分娩期间,新生婴儿接触阴道微生物群,这对婴儿微生物群的定植至关重要。重要的是,与未怀孕妇女相比,随着妊娠进展,母体阴道微生物组发生变化,总体细菌多样性降低,不过乳酸杆菌(Lactobacillales)、梭状芽孢杆菌(Clostridiales)、拟杆菌(Bacteroidales)和放线菌目(Actinomycetales)的优势增加。
最近证实,随着乳酸杆菌的增加,母体阴道微生物组的多样性降低,支原体和脲原体的含量降低,这两者都与早产和出生体重低等负面结果相关。
•微生物变化可能是为了保护胎儿
在孕妇体内观察到的阴道微生物组变化可能是保护胎儿健康和在出生时提供特定微生物种类的适应性反应的一部分,因为健康妊娠相关微生物组的变化可能会使母亲容易产生负面健康结果。
母体阴道微生物组组成取决于胎龄和种族。有趣的是,怀孕后期的母体微生物群落与未怀孕状态的相似。
注:也有研究整个怀孕期间没有发现阴道微生物组有任何显著变化。然而,他们发现产后阴道微生物群落与分娩后长达一年的肠道微生物群落更为相似。在他们的研究中,分娩后检测到从乳酸杆菌到各种厌氧细菌的转变,包括Peptoniphilus、Prevotella和Anaerococcus。
✦细菌性阴道病
通常,当阴道群落内的乳酸杆菌浓度改变时,会发生生物失调。阴道失调的特点是乳酸杆菌的丰度低,厌氧微生物增多。
细菌性阴道病(BV)是一种由阴道中自然发现的细菌过度生长引起的阴道炎症,是妊娠期最常见的一种生殖道感染。细菌性阴道病是一种由阴道环境变化引起的病症,它允许机会致病菌在阴道区域定居。怀孕期间的细菌性阴道病对母亲和孩子都是健康风险。
机会致病菌——正常菌群与宿主之间、正常菌群之间,通过营养竞争、代谢产物的相互制约等因素,维持着良好的生存平衡。在一定条件下这种平衡关系被打破,原来不致病的正常菌群中的细菌可成为致病菌,称这类细菌为机会性致病菌,也称条件致病菌。
•细菌性阴道病有更高的早产风险
一些初步研究表明,患有细菌性阴道病的孕妇存在更高的早产风险,这突出了怀孕期间阴道微生物组的重要性。
✦影响细菌性阴道病的因素
多年来,营养被认为是细菌性阴道病发展的一个因素。报告称,妊娠期缺铁和维生素D与细菌性阴道病风险增加有关。
扩展阅读:
人与菌对铁的竞争吸收 | 塑造并控制肠道潜在病原菌的生长
维生素D与肠道菌群的互作
•富含纤维的饮食发病率降低
在一项平行研究中,维生素A、维生素C、维生素E和维生素b-胡萝卜素的血清浓度较低与细菌性阴道病相关。最近的一项发现表明,富含纤维的饮食与细菌性阴道病发病率降低相关。
•超重和肥胖发病率更高
此外,一项流行率研究得出结论,超重和肥胖女性的细菌性阴道病发病率更高。这些发现强调了饮食对阴道微生物组组成的影响,进而强调了微生物组对怀孕期间阴道健康的重要性。
▸ 口腔含有仅次于肠道的第二大的微生物组,里面居住着700多种不同的细菌,包括链球菌(Streptococcus)、乳酸杆菌、葡萄球菌(Staphylococcus)和棒状杆菌。
微生物定植于牙齿的硬表面和口腔粘膜的软组织,通常以生物膜的形式存在。
注:微生物组研究的一个局限性是在没有交叉污染(即肠道或肺部)的情况下对微生物组进行采样。然而,由于口腔微生物组采样的简便性,它已成为迄今为止研究最深入的微生物组。
口腔微生物组在促进健康或疾病进展中起着关键作用。它对于维持口腔稳态、保护口腔和预防疾病发展至关重要。
✦怀孕期间口腔微生物发生变化
•总活菌数显著增加
在怀孕的不同阶段,口腔微生物组的组成会发生变化。在对非怀孕妇女口腔中存在的七种常见细菌种类的丰度进行比较时,妊娠早期、妊娠中期和妊娠晚期发现,与非怀孕妇女相比,怀孕期间的总活菌数显著增加。与其他妊娠阶段相比,妊娠早期存活微生物计数最高。
•妊娠中期致病菌水平升高
与未怀孕妇女相比,妊娠早期和中期组牙龈卟啉单胞菌(Porphyromonas)和放线聚集杆菌(均为致病菌)的水平升高。
牙龈卟啉单胞菌是一种非酵解糖的革兰氏阴性厌氧球杆菌,是研究广泛且证据充足的重要牙周致病菌之一。
最后,念珠菌(Candida)水平在妊娠中期和末期显著升高。有趣的是,雌激素与念珠菌感染有关,并可能解释怀孕期间念珠菌的丰富。
尽管口腔微生物组已被广泛研究,但口腔微生物组与饮食和妊娠结合仍是未来研究的领域。
▸ 胎盘是孕期母亲和胎儿之间的主要营养和激素调节界面。它在感知和引导母体营养信号到胎儿方面发挥着重要作用。
✦胎盘连接母体和胎儿的物质交换
胎盘促进氧气和生长因子向胎儿的交换,并将废物从胎儿转移到母体循环系统。
虽然长期以来认为胎儿和胎盘是无菌环境,不过这是一个有争议的话题。
最近有证据表明,在分娩前通过胎盘进行微生物交换。健康孕妇的脐带血、羊水和胎盘中检测到微生物颗粒。然而,这种细菌DNA是否是细菌从母亲血液中定植或易位的证据尚不清楚。
•细菌可能由母体经胎盘进入胎儿
一些理论表明,细菌可能由免疫细胞通过血流和淋巴进入胎盘,并通过胎盘进入胎儿一侧,以帮助启动胎儿免疫系统。事实上,在健康新生儿的胎盘组织中检测到几种细菌种类,包括放线菌属(双歧杆菌、丙酸杆菌、链霉菌、红球菌)、厚壁菌属(乳杆菌)、拟杆菌属(拟杆菌)和变形杆菌属(大肠杆菌、肠杆菌)。
此外,在通过剖宫产分娩的健康母亲的所有29例胎盘活检中发现了乳酸杆菌和双歧杆菌(Bifidobacterium)。
✦胎盘中的微生物组暂不明确
尽管如此,最近一项更有力的研究表明,没有证据表明人类胎盘内存在微生物组,尽管它可能含有潜在的病原体。他们证明,胎盘样本中的大多数阳性细菌信号是出生或实验室污染的结果。
然而,在同一项研究中,该小组在临产前采集的约5%的样本中发现了无乳链球菌(S.agalactiae)的证据。由于无乳链球菌是新生儿败血症的主要原因,胎盘可能是败血症新生儿感染的起始部位。
注:新生儿的败血症和早产也归因于母体口腔感染,如牙周病。此外,胎盘中发现的细菌门与母体口腔中发现的菌门最为相似。尽管似乎有一些证据表明母亲和胎儿之间存在胎盘微生物组交换,但对分娩期间或分娩后以及实验室中污染的担忧仍然是科学界争论的话题。
母亲的健康状况和微生物群状况对儿童微生物群的定植和发展有着深远的影响。同样,在出生时和婴儿早期建立健康的肠道微生物群对儿童免疫系统的发育和成熟至关重要。
由于共生微生物群在肠道免疫中起着关键作用,任何改变其组成的环境或宿主因素都可能导致负面健康结果。我们在此罗列了一些影响婴儿微生物群定植和发育的主要因素:母体营养、分娩方式、妊娠期和围产期抗生素的使用、喂养类型和胎盘微生物群。
什么是营养不良?
世界卫生组织将营养不良定义为“人体能量或营养摄入的不平衡(不足和过量)”。营养不足和营养过剩都被认为是营养不良的表现形式;然而,过度摄入某些特定营养素通常被称为肥胖。
营养不良包括缺乏基本的宏观和微观营养素,发育迟缓、消瘦和体重不足。营养过剩包括超重和肥胖,其特征是营养消耗过量和体质指数超标。这两种形式的营养不良都可能导致非传染性饮食相关疾病的发展,如心脏病、中风、糖尿病甚至是癌症。
✦营养不良的影响
•增加了疾病和死亡率
营养不良是一个全球性的问题,它影响着每个国家的人民,最脆弱的人群是中低收入国家的五岁以下儿童和育龄妇女。营养不良增加了母亲和儿童疾病和死亡的可能性,是五岁以下儿童死亡的主要原因,占所有死亡人数的近一半(45%)。
•导致肠道微生物失调
营养不足和营养过剩都会导致屏障功能和肠道完整性失调,从而导致生物失调。如前所述,在怀孕期间,健康且平衡的微生物组保护母亲和胎儿免受机会病原体的侵害,产生妊娠发育所需的营养物质,并将营养物质吸收到血液中,以促进胎儿健康成长。
当微生物组因营养不良而受损时,这些有益功能就会丧失,导致母体肠道炎症水平升高。孕期营养不良还与围产期并发症、流产和早产风险增加、出生体重低以及婴儿后期心血管疾病、中风、糖尿病和癌症等非传染性饮食相关疾病的发生有关。
✦母体营养对微生物群影响的一些研究
大多数关于母体营养在促进婴儿健康微生物群中的作用研究都是在动物模型中进行的。
怀孕期间高脂饮食与微生物组成的差异相关
与正常饮食对照组相比,热量限制的怀孕小鼠的细菌组成和肠道微生物组的多样性没有显著差异。
然而,与正常饮食的雌性小鼠相比,怀孕前和怀孕期间喂养高脂肪饮食的雌性老鼠在怀孕后期肠道微生物群发生了变化。
营养与婴儿的生长结果相关
检查了营养不良婴儿的母乳,发现与健康婴儿母亲的母乳相比,唾液酸化的母乳低聚糖(HMO)的含量显著降低。
在小鼠和小猪后代的饮食中添加唾液酸化的母乳低聚糖可以改善婴儿的生长结果。不过目前只有少数研究关注了孕期母体营养在人类中的作用。
素食导致罗氏菌和毛螺菌丰度增加
另一项研究指出,素食导致微生物中罗氏菌属(Roseburia)和毛螺菌科(Lachnospiraceae)的丰度增加,而与杂食性饮食相比,未检测到a多样性的差异。高脂肪、低纤维摄入孕妇的细菌密度较低。
此外,在怀孕早期,不饱和脂肪酸的高摄入量也与微生物密度降低相关。一项队列研究表明,早产母亲在怀孕期间维生素D和视黄醇摄入量较高,与微生物a多样性降低和促炎性及变形杆菌丰度增加相关。
视黄醇又称为维生素A,对于人体的多项生命活动都具有非常重要的作用。
反过来,维生素E的摄入与促炎性的减少相关。在超重孕妇中,膳食纤维和多不饱和脂肪酸导致微生物群丰富度更高,血清中zonulin蛋白水平降低。
zonulin是一种不利调节肠道紧密连接通透性的蛋白质。
✦营养不良导致微生物缺乏
一项纵向比较研究报告称,与健康对照组相比,严重急性营养不良儿童(由食物和水不安全以及母乳喂养不足引起)存在肠道微生物组缺乏和发育不成熟。
含有严重急性营养不良微生物群的小鼠也被发现具有较高水平的无害梭状芽孢杆菌(Clostridium)和沃氏嗜胆菌属(Bilophila wadsworthia),这两种细菌分别与免疫受损患者和炎症性肠综合征有关。
产妇产后时期微生物群的变化显著。母亲的微生物群在出生一个月后仍未恢复到基线水平。产后的特点是激素发生剧烈变化,包括孕酮和雌激素水平大幅下降。孕期不饱和脂肪酸消耗量的增加与分娩后变形杆菌(Proteobacteria)和厚壁菌(Firmicutes)的丰度相对于其他门的减少有关。
注:由于只有少量关于产后期的研究,因此需要进一步调查,以更好地了解这一阶段的微生物群。
✦母体营养不良会影响营养输送
•营养不良易导致宫内生长受限
母亲营养不良也会影响胎盘的营养输送和大小,并与炎症途径增加导致的宫内生长受限(IUGR)相关。
低出生体重与宫内生长受限相关,这涉及胎盘结构、形态受损和胎盘血管系统异常发育,从而损害胎盘营养物质的运输。在这些条件下,发育中的胎儿表现出较低的代谢率和较慢的生长率,以弥补营养不足。因此,胎儿的生长潜力低于其胎龄的正常水平。
•非传染性疾病风险增加
妊娠期间的母体营养限制也可能以男性特有的方式影响妊娠后半期胎儿脑内大麻素系统的发育,这在母体营养限制的狒狒模型中提供了证据。宫内生长受限可能导致非传染性疾病的风险增加,如代谢综合征、胰岛素抵抗易感性、2型糖尿病和成年期心血管疾病。
注意:除了营养不足,胎盘功能不全还可能由母亲年龄、吸烟和吸毒、高海拔妊娠、胎盘血流异常(子痫前期)、感染、炎症和胎儿先天性疾病引起。
// 建议
为了使母亲和婴儿拥有更好的健康,需要关注孕期和产后的营养摄入,尽量保证饮食均衡且有营养,不缺乏也不过量。
✦分娩类型对婴儿早期微生物群有影响
分娩类型对婴儿早期微生物群的定植有影响。由于暴露于阴道、粪便和皮肤微生物群,大多数早期微生物定植发生在自然分娩期间。
•阴道分娩
阴道分娩期间,兼性厌氧菌(如大肠杆菌、葡萄球菌和链球菌)定植于新生儿肠道,并允许严格的厌氧菌(例如拟杆菌和双歧杆菌)增殖。
•剖腹产分娩
相比之下,剖腹产出生的婴儿改变了微生物组,这可能会影响以后的健康。剖腹产婴儿的双歧杆菌和拟杆菌定植延迟,艰难梭菌水平较高。
基于丙酸杆菌、棒状杆菌和链球菌(Streptococcus)在剖腹产婴儿中增加,新生儿肠道微生物组存在显著差异,这与皮肤微生物组相似,而在阴道产婴儿中观察到乳酸杆菌和普雷沃氏菌(Prevotella)水平增加,这与母体阴道微生物组相似。
✦出生地也会影响婴儿早期微生物
有趣的是,婴儿出生的地点也会影响婴儿早期微生物群的定植。发现,与家庭分娩相比,在医院阴道分娩的婴儿中梭状芽孢杆菌(Clostridium)和肠杆菌(Enterobacteriaceae)的水平更高。
通过对771名足月医院出生的婴儿和母亲进行纵向抽样和宏基因组分析,在剖腹产婴儿和阴道分娩时使用母体抗生素预防或未在新生儿期母乳喂养的婴儿中,拟杆菌的母体传播受到干扰,以及肠球菌、肠杆菌和克雷伯氏菌等机会性病原体的高度定植,观察到的影响持续到出生后一年。
// 建议
阴道分娩相较于剖腹产分娩微生物群更健康。作为一种在新生儿中引入阴道微生物群的方法,阴道接种是一种很有前途的方法,可以恢复剖腹产婴儿的微生物组成。
该方法需要对新生儿进行擦拭,新生儿通常缺乏双歧杆菌和拟杆菌,这些细菌在出生时存在于母亲的阴道微生物组中。使用这种方法,已经被证明剖腹产婴儿的微生物组组成部分得到恢复。
改变早期微生物组的另一个主要因素是妊娠期和围产期使用抗生素。怀孕期间的抗生素治疗与新生儿第一次粪便中细菌多样性的减少以及肠道中乳酸杆菌和双歧杆菌的丰度降低有关。
✦使用抗生素导致多样性降低
在生命早期使用抗生素也会导致物种和菌株水平上的微生物多样性降低,某些有益物种如梭状芽孢杆菌减少,抗生素抗性细菌如肠球菌的数量增加。抗生素暴露对后代微生物组更深远的影响将在后面继续讲述。
// 建议
由于抗生素的使用,婴儿的微生物多样性会降低,还会对健康造成一定影响。因此建议不是必要情况,尽量减少抗生素的使用。
✦母乳促进免疫发育
出生后,儿童微生物群发育的最重要因素是母乳喂养。母亲母乳是细菌、抗原、营养素和生物活性物质的唯一来源,所有这些都能促进婴儿免疫系统发育、新陈代谢和肠粘膜屏障功能。
•母亲的饮食影响母乳组成
母亲的饮食是母乳组成的重要因素。最近证明,母亲的饮食显著改变了母乳低聚糖的组成,地理位置和体重也在一定程度上影响母乳的组成。
一项全面系统综述得出结论,母亲饮食中脂肪酸、脂溶性维生素、维生素B1和维生素C都与母乳成分有关。
注:虽然强烈建议母乳喂养,但有时这是不可能的或不充分的,只能用配方奶粉代替。婴儿配方奶粉试图模仿母乳,通常以补充维生素、铁、脂肪酸和益生菌的大豆或牛奶等替代品为基础。
•母乳喂养下的主要菌群
尽管母乳成分因母亲健康状况、饮食、分娩方式和哺乳时间而异,但母乳主要由几个微生物属(葡萄球菌、链球菌、丙酸杆菌、鞘氨醇杆菌、双歧杆菌和乳酸杆菌)构成,并导致双歧杆菌、拟杆菌的早期定植,以及大肠杆菌和艰难梭菌的水平较低。
•配方奶喂养下的主要菌群
相比之下,配方奶喂养与母乳喂养婴儿相比,艰难梭菌(C. difficile)、脆弱拟杆菌(Bacteroides fragilis)和大肠杆菌(E. coli)的定植率更高,其肠道微生物组与更典型的成人模式相似。
✦母乳对于婴儿十分重要
母乳不仅作为细菌来源,还含有细菌抗原和其他生物活性物质,可刺激免疫系统的发育和成熟。最近,使用宏基因组方法发现,母乳喂养的样本中与免疫、代谢和生物合成活动相关的基因的共表达相比配方奶粉喂养的样本增加。
•促进免疫系统发育和调整
母乳中含有益生母乳低聚糖,可促进双歧杆菌生长,进而在免疫系统的发育和微调以及抑制致病物种生长方面发挥重要作用。这些研究证明了母乳喂养在早期婴儿微生物群发育和成熟中的重要性。
// 建议
条件允许的话,最好还是用母乳喂养婴儿(不过母乳喂养的前提需要保证母亲是健康的)。如果不行的话也应选用成分相似的配方奶进行喂养。
在婴儿期建立健康的肠道微生物群对于儿童日后免疫力的发育和成熟至关重要。孕期母体肠道微生物组可能通过细菌代谢物或免疫球蛋白直接或间接影响胎儿免疫发育。
肠-乳腺通路是肠道细菌在怀孕期间通过肠系膜淋巴网络从母体胃肠道向乳腺的生理易位机制,可能有助于后代的免疫发展。
尽管确切的机制尚待确定,但研究表明母体微生物组与胎儿免疫之间存在联系。
产前母子之间的微生物联系
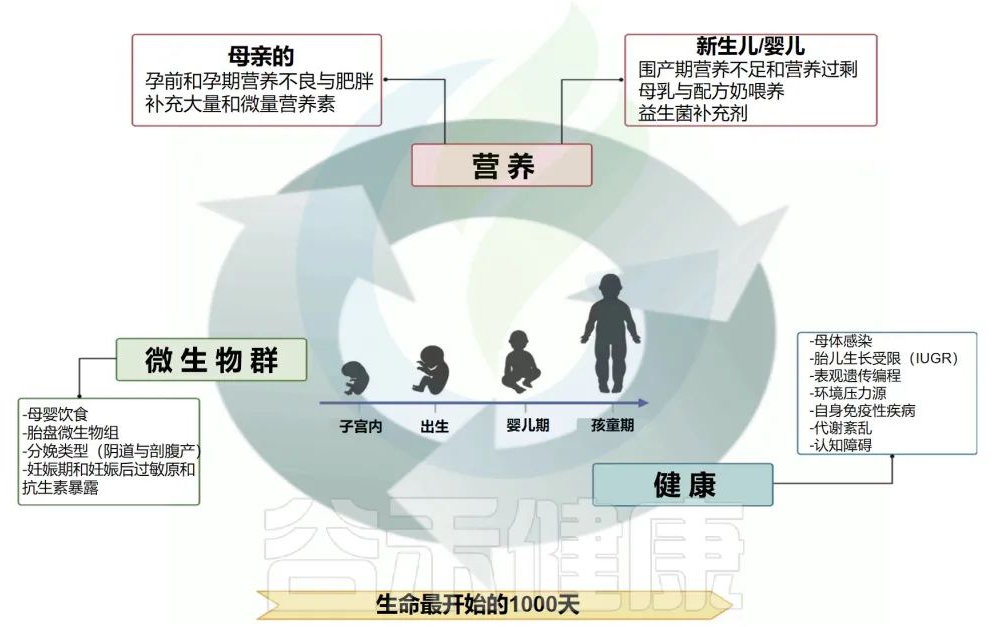
Mua B,et al.Comprehensive Gut Microbiota.2022
怀孕期间,母婴界面存在定向微生物群影响。所谓的肠乳途径是怀孕期间肠道细菌通过肠系膜淋巴网络易位的潜在机制,被认为通过表观遗传变化诱导后代的免疫发育。
母体肠道细菌和代谢产物从母体胃肠道输送到乳腺,通过肠道-母乳轴影响产后肠道定植和免疫。母体的口腔和胎儿胎盘串扰会导致子宫内共生肠道细菌的早期定植,从而获得终身免疫。
怀孕期间,母体肠道中产生的代谢物(如短链脂肪酸)会转移到乳腺,在乳腺中通过母乳喂养传递给婴儿。
对微生物和代谢物的动物和人类研究为孕期微生物易位及其对胎儿免疫的影响提供了证据。例如,怀孕小鼠在妊娠晚期口服乳酸菌菌株乳酸乳球菌和唾液乳球菌,然后在小鼠的母乳和组织中检测到。
肠道微生物组产生代谢产物,在调节宿主免疫、生理和能量产生中发挥关键作用。
✦有助于婴儿生理发育
由于短链脂肪酸与人类微生物群、免疫和神经内分泌系统的相互作用,短链脂肪酸在人体稳态中发挥着关键作用,并可能有助于婴儿的神经、代谢和免疫发育。
母乳中由细菌或肠道人类细胞产生的代谢物,通过促进或抑制细菌生长的机制,帮助调节乳汁和婴儿微生物组组成。
将具有特应性表型的母亲与非特应性母亲的乳汁成分进行了比较,发现特应性妈妈的乙酸和丁酸水平明显较低,与婴儿体重指数呈负相关。
母亲特应性状态定义为有过敏症状,如特应性皮炎、哮喘和食物过敏等。同样,母乳激素瘦素和胰岛素水平的变化与婴儿肠道微生物多样性和通透性的差异有关。
✦调节宿主免疫
•母体视黄酸提高后代免疫力
母体视黄酸作为胎儿3型先天性淋巴细胞的调节因子,并通过诱导小鼠胎儿发育过程中的次级淋巴器官来提高后代的免疫力。
视黄酸——又称维A酸,是体内维生素A的代谢中间产物,主要影响骨的生长和促进上皮细胞增生、分化、角质溶解等代谢作用。
3型先天淋巴细胞(ILC3)具有抗原呈递作用,可以激活T细胞反应。
•短链脂肪酸调节肠道免疫,防止致病性感染
微生物短链脂肪酸(包括丁酸、乙酸盐和丙酸盐)影响肠道免疫,调节结肠调节性T细胞(一种免疫T细胞的特殊亚群),增强口腔对食物的耐受性,并防止肠道致病性感染。
•对哮喘有积极影响
同样,妊娠期间的细菌代谢产物和母体饮食通过补充纤维和乙酸盐增强调节性T细胞的丰度和功能,对哮喘的发展产生积极影响,这在人类哮喘小鼠模型研究中得到了证明。
细菌代谢产物在母体-胎儿之间的联系是母亲和社会普遍关注的一个话题,因此,应在进一步的实验和综合研究中加以解决。
在妊娠期间,母体免疫球蛋白(IgG)通过胎盘转移至胎儿,诱导出生前的被动体液免疫和出生后的先天免疫,以防止感染。
免疫球蛋白G(IgG)是血清中免疫球蛋白的主成分,约占血清中免疫球蛋白总含量的75%。
✦母体免疫球蛋白影响胎儿免疫力
母乳中的IgG抗体会影响产后微生物群和哺乳期的免疫力。母亲的母乳抗体也可以通过与细菌结合的胎盘运输,从而影响胎儿在子宫内的免疫规划。
母体IgG抗体在胎盘的合胞体滋养层细胞内主动运输并与新生儿Fc受体(FcRn)结合。一旦结合,IgG被包装到内体中,并保护其不被降解,直到其达到胎儿循环。
✦母体健康会影响免疫球蛋白
孕期母体健康状况也是免疫球蛋白转移至胎儿的关键因素。妊娠期高血糖降低了母亲母乳和血液中的免疫球蛋白丰度,并降低了IgG通过胎盘向胎儿的转移。
注:跨胎盘免疫调节也可能由其他细菌成分介导,如脂多糖、细胞因子和激素。
微生物的组成因身体部位而异,并在不同个体内部和个体之间形成了不同微生物群落的独特环境。
✦肠道是微生物最丰富的区域
胃肠道内发现了最丰富的微生物多样性和丰度,主要以厚壁菌门(Firmicutes)、拟杆菌门(Bacteroidetes)、放线菌门(Actinobacteria)和变形菌门(Proteobacteria)的兼性厌氧菌为特征。
✦微生物变化时会产生一系列影响
宿主-微生物关系复杂,当发生变化时,会对免疫、代谢和神经系统的稳态产生负面影响,导致对环境过敏原和营养刺激过敏。
这些影响主要通过免疫、神经、胃肠和内分泌调节肠-脑轴(一种调节体内稳态的双向神经体液系统)的组成部分对子宫中的后代进行表观遗传编程。
表观遗传机制是细胞分化的关键调节因子,通过在生物和病理条件下将环境线索印记到细胞和组织的生理学中来发挥作用。
注:与健康变化相关的所有暴露量的测量被称为暴露量,从怀孕开始就涉及环境和职业暴露。
在妊娠期间,DNA甲基化和组蛋白修饰打开和关闭基因,允许不同的细胞类型分化并获得胎儿暴露体的表观遗传记忆,这将在个体的整个生命周期中保存。
✦环境因素影响表观遗传
孕期母亲的生活方式、饮食、年龄、压力、感染和其他环境因素会影响母亲和胎儿的表观遗传途径,导致后代的遗传、代谢和神经发育改变。
在生命的前1000天,表观遗传调节和可塑性、胎儿器官发育和成熟与疾病易感性的印记一起被编程。如果外部因素不健康,可能会发生表观遗传变化,从而改变基因表达,增加成年后患病的风险。
后代的表观遗传调控是通过母亲在肠-脑轴中的饮食成分进行的。这些成分包括叶酸和营养素,它们在母体肠道中代谢和吸收,从而帮助维持健康的肠道微生物群落。
✦肥胖和正常体重的母亲微生物组成不同
怀孕肥胖母亲的微生物群组成与正常体重母亲的明显不同,其特征是葡萄球菌(Staphylococcus)和肠杆菌(Enterobacteria)水平升高,拟杆菌和双歧杆菌水平降低。
•影响后代的健康
胃肠道改变扰乱了母体微生物群,影响了后代对代谢紊乱的敏感性,并产生长期影响。
例如,高脂饮食的母亲因脂多糖增加而导致的叶酸水平变化会影响肠道通透性和微生物组,进而影响婴儿的微生物定植,从而增加成年后的疾病风险。
动物模型为这一假设提供了进一步的支持
在妊娠期高脂饮食的狒狒模型中发现,高脂饮食会影响妊娠前和妊娠期间后代肝脏内源性大麻素成分的发育调节。胎儿大麻素系统的改变会增加成年后肝脏损伤和肥胖的风险。
综上所述,母体微生物组间接影响后代的代谢发育,因此可能是预防成年期胃肠道疾病的有效靶点。
✦母体代谢成分对后代的影响
•增加后代心血管病风险
很少有研究探讨孕期母体代谢成分通过表观遗传机制在后代免疫中发挥的调节作用。母亲饮食中长链多不饱和脂肪酸摄入量低会诱导血管生成因子基因的DNA甲基化,导致胎盘排列、血管调节发生改变,并增加后代晚年的心血管疾病风险。
通过胰岛素生长因子(IGF-1)启动子的组蛋白修饰,母体高血糖可能会增加成年后对胰岛素抵抗的敏感性。
•调节炎症反应
母亲补充膳食DNA甲基化物,如叶酸、维生素B12、胆碱、蛋氨酸和锌,可能有助于在胎儿细胞快速生长和增殖期间调节炎症反应。
胎儿发育过程中的炎症也可能诱导免疫系统过度激活并增加疾病风险。
•影响胎儿发育及免疫功能
母亲补充胆碱会影响DNA和组蛋白甲基化,从而改善成年期胎儿大脑发育和功能。维生素D是另一种必需的微量营养素,当缺乏时,会改变表观遗传途径,并通过胎盘中的DNA甲基化和组蛋白修饰导致炎症、先兆子痫和不良妊娠结局。
细菌代谢物和其他环境分子也可能通过母胎界面驱动的表观遗传调节影响胎儿免疫发育。研究发现,怀孕期间接触醋酸可以增强调节性T细胞的数量和功能,抑制后代的过敏性呼吸疾病,最有可能是因为FoxP3启动子乙酰化程度增加。
妊娠期间胃肠道成分的调节已被证明对儿童的免疫和代谢发育有强烈的影响,因此应在该领域的未来研究中加以解决。
✦母乳喂养对儿童健康有积极影响
•不易发生肠道感染
母乳喂养对儿童的健康结果有积极影响。头两年的亚最佳母乳喂养与死亡率增加相关。母乳喂养的婴儿较不容易发生肠道感染,从而导致慢性炎症和腹泻概率降低。
•母乳喂养降低儿童肥胖和2型糖尿病风险
然而,如果过早暂停母乳喂养,以引入配方食品或固体食品,则会使婴儿的肠道微生物组向成人样成分转变,并与儿童肥胖风险增加相关。
有证据表明,母乳喂养的婴儿青春期肥胖和2型糖尿病的风险降低。剖腹产也会破坏母亲和孩子之间的正常微生物群交换,这与儿童期和成年期乳糜泻、1型糖尿病和肥胖的风险增加有关。
其他研究人员报告称,孕前和孕期母亲超重、剖腹产和婴儿微生物群丰富的厚壁菌增加了儿童肥胖的风险。反过来,儿童肥胖可能会导致其他负面的短期和长期健康后果,包括低自尊、心血管问题以及成人肥胖和糖尿病。
✦孕期使用抗生素与儿童感染有关
孕期母亲使用抗生素是影响母亲肠道和母乳微生物群的另一个因素,并与儿童肥胖风险增加相关。最近,研究了孕期母亲抗生素治疗与生命后期感染风险之间的关系。他们发现,妊娠期抗生素治疗会增加四岁以下儿童患扁桃体炎的风险。
此外发现,孕期抗生素治疗与儿童因感染而住院的风险增加有关,并且在临近分娩时服用抗生素的风险更高。
小结
这些研究强调了一个事实,即母亲的微生物多样性在新生儿微生物组组成和健康的发展中至关重要。
早产儿长期接受抗生素治疗会增加其败血症、坏死性小肠结肠炎和死亡的风险。此外,生命早期的抗生素治疗会增加生命后期超重和肥胖的风险。
孕期和生命早期的抗生素治疗可还能会改变婴儿微生物组组成的发育,导致生命后期的负面健康结果。
在婴儿和儿童中,包括皮肤、呼吸道和食物过敏在内的自身免疫性疾病是全球关注的问题。研究发现,新生儿和婴儿微生物组参与肠道耐受性的调节和免疫系统的调节。
最近的研究集中于肠道微生物组在先天性和适应性免疫发展以及过敏性疾病发病中的作用。晚年过敏症的发展与新生儿和婴儿期微生物组发育和成熟的变化有关。这些情况也可能源于导致不同表型和症状的遗传和环境因素。
✦皮肤过敏
健康的人类皮肤微生物组主要由丙酸杆菌属(主要在皮脂部位丰富)、棒状杆菌属和葡萄球菌属(主要存在于潮湿的微环境中)以及马拉色菌属组成。
皮肤微生物组的组成受性别、年龄、种族、环境暴露和生活方式等因素的影响。婴儿最典型的过敏表现之一是湿疹或特应性皮炎,这是新生儿对过敏原的先天反应改变和皮肤微生物多样性受损的结果。
•患有特应性皮炎婴儿的菌群变化
患有急性和慢性特应性皮炎的婴儿的特征是表皮葡萄球菌(Staphylococcus)的数量减少,多于金黄色葡萄球菌,这可能通过下调表皮蛋白和促进皮肤蛋白酶而增加过敏原致敏的风险,从而导致皮肤屏障损伤。
•特应性皮炎受到微生物的影响与调节
新生儿表皮葡萄球菌的皮肤定植与toll样受体2诱导的抗菌信号和调节性T细胞介导的宿主免疫应答的调节和激活有关。
特应性皮炎的发展也受到肠道微生物群的影响。特应性皮炎患者的肠道微生物组中双歧杆菌(Bifidobacterium)的浓度较低,普拉梭菌(Faecalibacterium prausnitzii)的丰度较高,这与克罗恩病患者中这些细菌的比例较低以及抗炎粪便细菌代谢物有关。
然而,一项大型前瞻性研究表明,在儿童期患上特应性皮炎的婴儿中,普拉梭菌(Faecalibacterium)和毛螺菌属(Lachnobacterium)的比例明显较低。
尽管有些矛盾,但这些结果表明,微生物类群丰度的改变可能对特应性皮炎的发病起到保护作用。产前和产后补充口服双歧杆菌和乳酸杆菌可以诱导T细胞介导的反应改变,降低婴儿特应性皮炎的风险。
✦食物过敏
动物和人类研究表明,肠道微生物组可能与生活早期对饮食抗原的口服耐受、食物致敏和过敏结果密切相关。
•饮食过敏影响微生物多样性
与健康婴儿相比,对食物敏感的婴儿的α多样性微生物群和拟杆菌(Bacteroidetes)数量减少,厚壁菌(Firmicutes)丰度增加。人类这些特定结果的可能原因包括抗生素的直接和间接使用以及膳食纤维的消耗减少。
早期喂养的类型也可能导致不同的健康结果。食用牛奶配方的奶粉会增加总厌氧菌的数量,并增加患牛奶过敏的风险。与肠杆菌和双歧杆菌相比,患有牛奶过敏的婴儿的乳酸杆菌感染率更高。
此外,从婴儿期到儿童期,牛奶过敏儿童中厚壁菌(Firmicutes)和梭状芽孢杆菌(Clostridia)的丰度均升高。有趣的是,与对照组相比,坚果过敏儿童的肠道微生物组显示拟杆菌(Bacteroidetes)种类比例增加,微生物多样性降低。
同样,与健康对照组相比,鸡蛋过敏儿童的毛螺菌科(Lachnospiraceae)和瘤胃球菌科(Ruminococcaceae)浓度增加。
•细菌可能有助于解决食物过敏
添加Lactobacillus rhamnosus GG的牛奶配方有助于解决婴儿早期的牛奶过敏,最有可能是通过肠道微生物组中丁酸盐产量的增加。
L. rhamnosus GG还可能诱导花生过敏儿童的免疫变化和口服耐受性。口服微生物补充剂可能是食物过敏的一种潜在治疗策略,但需要进一步研究以阐明微生物菌株对饮食中过敏原的持续敏感性的影响。
✦呼吸道过敏
•肠道微生物影响哮喘
与其他过敏表现相比,出生第一个月的肠道微生物组成是与学龄期哮喘发作相关的最相关因素之一。
在婴儿早期和整个儿童期进行的观察和纵向研究表明,毛螺菌属(Lachnospira)、普拉梭菌(Faecalibacterium)和小杆菌属(Dialister)细菌类群的减少,与儿童期哮喘风险增加有关。
•其他影响哮喘的因素
然而,与婴儿微生物组相关的其他因素也可能在哮喘风险中发挥重要作用,包括接触抗生素、动物皮毛、阴道分娩与剖腹产以及母体孕龄。
抗生素增加了哮喘风险
抗生素的使用和出生前后的暴露与小鼠的气道超敏反应和反应性有关,并增加了人类患哮喘的风险。
母乳喂养可降低哮喘风险
婴儿期的喂养类型也是婴儿早期形成肠道微生物群的一个重要因素,当婴儿长时间母乳喂养时,在生命的头两年内发生哮喘的风险可以降低。
•微生物多样性紊乱易导致儿童后期哮喘
婴儿微生物组多样性的紊乱也是儿童后期哮喘发病的关键因素。粪便杆菌和双歧杆菌的多样性降低是有哮喘风险的婴儿肠道微生物组的特征。
这些婴儿的无菌粪水用于刺激成人外周血单核细胞(PBMC),这导致调节性Foxp3细胞减少,CD4+IL-4产生细胞增加。
新生儿肠道微生物组环境的改变通过调节CD4+T细胞功能和增殖影响儿童过敏性哮喘的易感性。
•肺部微生物影响呼吸健康
生命早期的肺部微生物多样性影响呼吸健康。婴儿出生头两周内的肺部微生物组促进树突状细胞中程序性死亡配体1(PDL1)的表达,这是调节性T细胞抑制过敏性呼吸道免疫反应所必需的。
在出生的头两个月,婴儿的气道被链球菌、莫拉克氏菌或嗜血杆菌定植,这与婴儿和儿童的严重下呼吸道感染和哮喘有关。变形杆菌和拟杆菌也与哮喘和其他免疫相关的加重有关。
如前所述,这些细菌类群的副产物和代谢物可能介导其保护作用。丁酸盐和其他短链脂肪酸作为膳食纤维的发酵产物,如普拉梭菌(Faecalibacterium prausnitzii),它们通过诱导Tregs促进上皮屏障通透性和抗炎作用,和粘膜B细胞产生IgA。
实验研究和人体临床试验还表明,通过补充肠道微生物组衍生的丁酸,可以降低变应原敏感性和哮喘的发病率。
不足之处
过敏性疾病发病和严重程度的生理机制仍在研究中,一些介入性研究表明,补充益生菌和益生元可以预防和下调此类综合征,然而,与哮喘相关的研究报告,补充和不补充益生药的婴儿之间没有显著差异,因此需要更多的研究来进一步检验这些影响。
生命的前1000天除了肠道微生物组的建立,还是神经健康规划和中枢神经系统后期正常运作的关键时期。
肠-脑轴由肠道和中枢神经系统以及神经和下丘脑-垂体-肾上腺轴(HPA轴)调节。因此,该轴的任何损伤,包括神经元损伤或死亡,都会导致神经变性,并可能导致神经变性疾病的发生和发展。
✦营养不良对认知障碍有影响
母婴营养不良通常与认知技能、入学准备和表现、不良生长结果、感染和死亡等方面的损害有关。由于母亲健康和营养不良以及婴儿护理和喂养不当而发育不良的儿童会出现身体和认知延迟。孕期母亲炎症和高脂饮食影响微生物群定植,增加成年期神经退行性疾病的风险。妊娠期以性别特异性的方式影响发育中胎儿大脑中的内源性大麻素途径。
✦孕期母亲的生活方式会导致神经发育障碍
因此,孕期母亲的生活方式和环境暴露可能导致神经发育障碍的发作,包括胚胎神经管缺陷、唐氏综合征、自闭症、雷特综合征和其他神经心理缺陷。
✦肠道微生物调节认知与行为
微生物群组成与认知和行为发育改变之间的双向相互作用已在肠-脑轴中得到确认,有证据支持这种相关性。
缺乏肠道微生物群的无菌小鼠表现出与焦虑相关的表型增加,神经递质水平和与神经可塑性有关的代谢物发生变化,从而表明肠道定植对大脑发育和功能有积极影响。包括双歧杆菌和乳酸杆菌在内的一些细菌菌株以及摄入的益生菌与调节行为变化有关。
注意
需要注意的是,当无菌小鼠在早期生活中重建了正常的微生物群,但在成年后没有重建时,行为模式和神经递质浓度正常化。
母乳喂养被发现可以促进大脑发育,并对婴儿的认知能力产生积极影响。一些因素,包括文化和社会信仰以及对母乳喂养的污名化、缺乏营养和教育、母亲压力和抑郁,都可能导致过早停止母乳喂养;所有这些都会对婴儿的肠道微生物群和早期和后期的认知发育产生负面影响。
生命早期营养、肠道微生物组和健康之间的相互关联在个体一生的稳态中起着关键作用。
生命最初营养、肠道微生物组和健康之间的关系

Mua B,et al.Comprehensive Gut Microbiota.2022
母亲和新生儿营养不良、喂养习惯和营养/益生菌补充对子宫、婴儿和儿童期微生物组的建立有很大影响。母体微生物组变化和过敏原/抗生素暴露也会影响儿童早期的微生物组组成。
微生物组组成和丰富性的变化会影响妊娠结局和产妇健康,并通过表观遗传编程使发育中的孩子在以后的生活中易患自身免疫、认知和代谢障碍。
生命的前1000天是一个“可塑性窗口”,在这个窗口中,后代的健康会根据母体和环境的影响进行变化。
由于饮食生活方式以及暴露于外来生物和其他环境压力源,代谢、免疫学和神经退行性疾病的患病率在全球范围内不断增加。
在微生物组水平上理解母亲和孩子之间的独特联系,有助于研究对孕期和婴儿期肠道微生物组的变化及其对母婴健康的直接和间接影响,使母亲和孩子在未来都拥有更健康的生活。
主要参考文献
Mua B , Nga B , Fjaa B , et al. The Gut Microbiota, Nutrition, and Long-Term Disease Risk: A Mother and Child Perspective[J]. Comprehensive Gut Microbiota, 2022:289-307.
Apostol, A.C., Jensen, K.D.C., Beaudin, A.E., 2020. Training the fetal immune system through maternal inflammationda layered hygiene hypothesis. Front. Immunol. 11, 1–14.
Cortes-Macías, E., Selma-Royo, M., García-Mantrana, I., et al., 2021. Maternal diet shapes the breast milk microbiota composition and diversity: impact of mode of delivery and antibiotic exposure. J. Nutr. 151 (2), 330–340.
Cunha, A.J.L.A., Santos, A.C., Medronho, R.A., Barros, H., 2020. Use of antibiotics during pregnancy is associated with infection in children at four years of age in Portugal. Acta Paediatr. 110 (6), 1911–1915.
Forgie, A.J., Drall, K.M., Bourque, S.L., et al., 2020. The impact of maternal and early life malnutrition on health: a diet-microbe perspective. BMC Med. 18 (1), 1–15.
Mesa, M.D., Loureiro, B., Iglesia, I., et al., 2020. The evolving microbiome from pregnancy to early infancy: a comprehensive review. Nutrients 12 (1), 1–21.
谷禾健康
当前合成基因簇预测限制较大
微生物基因组中的生物合成基因簇 (BGC) 编码具有生物活性的次级代谢物 (SM),它可以在微生物-微生物和宿主-微生物相互作用中发挥重要作用。
鉴于次级代谢物的生物学意义和当前对微生物组代谢功能的深刻兴趣,从高通量宏基因组数据中无偏见地鉴定生物合成基因簇可以为微生物群的复杂化学生态提供新的见解。
目前可用于从鸟枪法宏基因组预测生物合成基因簇的工具有几个局限性,包括需要计算要求高的读取组装、预测范围窄,以及不提供次级代谢物产品。
为了克服这些限制,最近发在mSystems的一篇技术文章:
《TaxiBGC: a Taxonomy-Guided Approach for Profiling Experimentally Characterized Microbial Biosynthetic Gene Clusters and Secondary Metabolite Production Potential in Metagenomes》
介绍了他们的研发成果,他们开发了生物合成基因簇(TaxiBGC)的分类指导识别,这是一种命令行工具,用于通过首先精确定位可能存在合成基因簇的微生物物种来预测宏基因组中实验特征化的合成基因簇(并推断其已知的次级代谢物)。
并在各种模拟宏基因组上对TaxiBGC进行了基准测试,表明与通过将测序读数映射到BGC基因上来直接识别BGC(平均F1得分,0.49;平均PPV得分,0.41)相比,该分类法指导的方法可以预测BGC,其性能大大提高(平均F1分数,0.56;平均PPV得分,0.80)。
接下来,通过将TaxiBGC应用于人类微生物组项目的2650个宏基因组和各种病例对照肠道微生物组研究,我们能够将BGC(及其SM)与不同的人体部位和多种疾病(包括克罗恩病和肝硬化)相关联。
总之,TaxiBGC提供了一个计算机平台来预测实验表征的生物合成基因簇及其在宏基因组数据中的次级代谢物生产潜力,同时展示了优于现有技术的重要优势。
TaxiBGC (Taxonomy-guided Identification of biosynthesis Gene Clusters),用于从鸟枪法宏基因组测序数据中预测实验表征的生物合成基因簇(BGCs)及其已知的次生代谢物(SMs)(也称为天然产物)。
SMs是一组低分子量、结构多样、具有生物活性的化合物,这些化合物包括细菌和真菌细胞间的信号分子、色素、细菌素和铁载体,已知它们主要介导了微生物生态系统中的关键相互作用。
此外,微生物次生代谢物是抗生素、抗真菌药、抗癌药、免疫抑制剂和其他药物的重要来源。例如,生物碱被发现对人类癌细胞系具有细胞毒性活性,并抑制耐甲氧西林金黄色葡萄球菌(MRSA)和耐万古霉素肠球菌(VRE)的生物膜形成。而微生物中主要负责合成、修饰和输出次生代谢物的基因通常存在于生物合成基因簇中。
TaxiBGC计算流程主要有三个步骤,如下图。
第一步使用Metaphan3对宏基因组进行物种注释。
第二步通过查询TaxiBGC参考数据库中的这些物种(第一步中得到的)来进行BGCs的初步预测。
第三步使用BBMap基于序列比对来对初步预测的结果进一步确认。

TaxiBGC参考数据库提供了实验表征的生物合成基因簇、相应的次级代谢物以及来源物种(种水平或菌株)三者的映射关系。
如下图,数据库内包含390个独特的携带BGCs的微生物物种,953个独特的实验表征的BGCs,以及总共1169个SMs。一个物种可携带的BGCs数量差异很大,在所有物种中,有217种(55.6%)只携带一个BGC(图B)。
BGC中的基因数量也有很大差异,953个BGCs中的大多数只有不到25个生物合成基因(图C),但大多数BGCs只产生1种SM(图E)。

在TaxiBGC中,确定宏基因组中是否存在BGCs主要取决于以下两条标准:
为了确定这两个阈值,研究人员在125个模拟宏基因组上测试了400对BGC基因存在的阈值(以5%的增量,5%~100%区间)和BGC覆盖率(以5%的增量,5%~100%区间)。将预测的BGCs与实际BGCs进行比较,计算出F1分值。
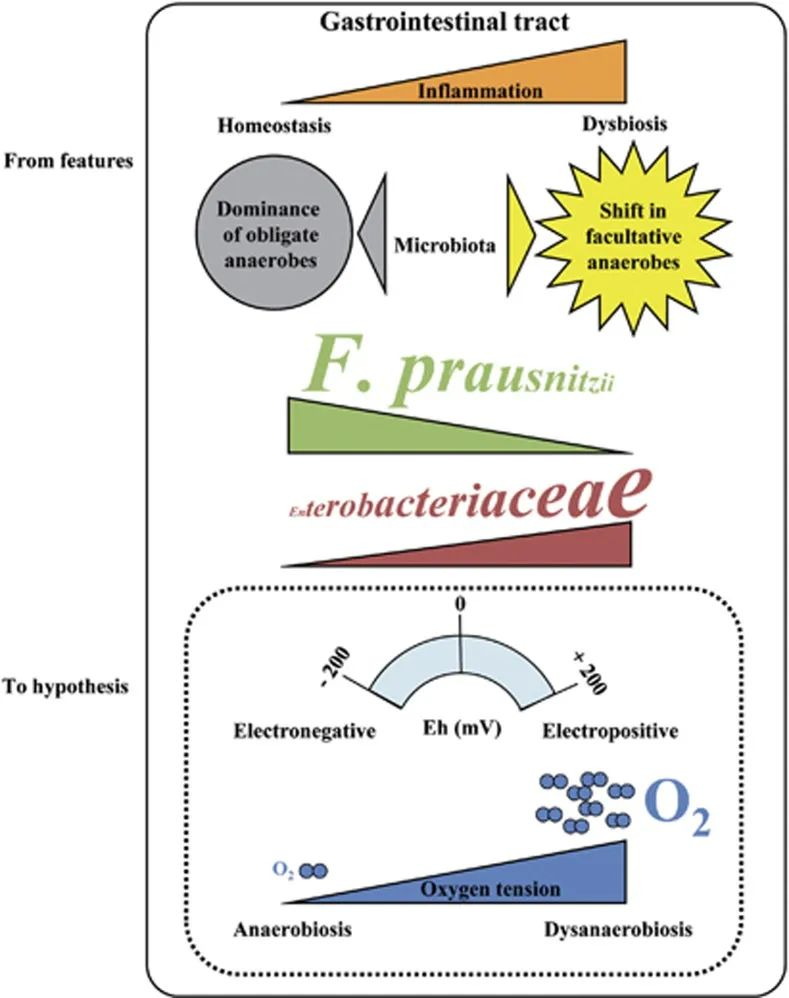
如图A,当BGC基因存在阈值为5%且BGC覆盖阈值为10%时,TaxiBGC在所有模拟宏基因组中预测BGC的性能最佳(mean F1 score=0.56)。
图BCD分别为在最佳阈值下,不同数量的宏基因组样本、文库大小、携带BGC的物种的相对丰度状态下对TaxiBGC预测准确性的影响,结果推荐在至少1000万读长的宏基因组上使用TaxiBGC。
★ 优势
1. 可以直接用于宏基因组,无需基因组装;
2. 预测模拟宏基因组中BGCs的能力优于直接检测BGCs的方法;
3. TaxiBGC已经应用于以下9项已发表的病例对照研究中的1433个肠道微生物组(即粪便宏基因组)样本:
在这些研究中都发现了与疾病相关的BGCs。
✦不足
1.当metaphan3无法识别所有携带BGCs的物种时,TaxiBGC将无法准确地预测整个BGCs的范围;
2.关于BGCs物种来源的预测需要谨慎解读,原因是在宏基因组的“mixed bag of genes”背景下,一个特定BGC的基因元件可能来自其它BGCs和多个物种;
3.虽然极力减少了假阳率,但可能出现假阴性;
4.TaxiBGC只提供少数SM产物的化学家族,而不提供特定的分子结构,如糖肽脂和胞外多糖;
5.TaxiBGC目前只用于预测已知的BGCs,其预测不能扩展未经验证的BGCs。
参考文献
Approach for Profiling Experimentally Characterized Microbial Biosynthetic Gene Clusters and Secondary Metabolite Production Potential in Metagenomes. mSystems. 2022 Nov 15:e0092522. doi: 10.1128/msystems.00925-22. Epub ahead of print. PMID: 36378489.
谷禾健康
过敏性鼻炎是个全球性健康问题,易反复发作,困扰着全世界大约着4亿人。自20世纪60年代以来,过敏性鼻炎的患病率持续上升。近几年,我国主要大中城市过敏性鼻炎的平均患病率从11.1%升高到17.6%。
过敏性鼻炎主要临床表现包括发痒、打喷嚏、鼻塞等,这些症状不加以改善,严重的话会导致睡眠障碍、学习障碍和行为改变等,最终影响患者的生活质量。
过敏性鼻炎与普通感冒不一样,它不是由任何病毒引起的,因此不会传染。过敏性鼻炎主要由过敏原引起,常见过敏原包括花粉、灰尘、动物毛发、皮屑等。
目前过敏性鼻炎的治疗主要基于鼻用皮质类固醇以及鼻用和口服H1-抗组胺药等。但这些药物的有效性是有限的,并且还具有多种副作用,会产生药物依赖性,药效下降等问题。
目前越来越多的研究表明,过敏性鼻炎是一个较复杂的免疫炎症反应疾病,其中肠道微生物群在该病的发生发展过程中扮演了不可替代的角色,针对菌群的干预,无论在动物还是人类临床上均显示出了较大的改善,以及作为药物治疗的补充综合改善措施。
本文我们来详细了解关于过敏性鼻炎的症状,发生过程,风险因素,与肠道微生物群的关系,益生菌在该病中发挥的作用,其他过敏性鼻炎相关治疗干预措施包括饮食、生活方式、益生元、合生元等。
【全文概览】
01 关于过敏性鼻炎,你需要知道
发病率、症状、风险因素、易感人群
与普通鼻炎的区别;与感冒的区别
02 过敏性鼻炎是如何形成的?
发病机理、如何与肠道相关联
03 过敏性鼻炎与肠道菌群之间的关系
04 肠道菌群在过敏性鼻炎中的重要作用(机理)
肠道菌群 ⇄ Th1/Th2 平衡
肠道菌群影响ILC2:过敏中的重要作用
肠道菌群对血清炎症因子的影响
肠道菌群对Treg/Th17细胞平衡的影响
肠道菌群对耐受树突状细胞活性的影响
肠道菌群对Toll样受体的刺激
05 过敏性鼻炎的治疗
06 基于菌群的干预,对过敏性鼻炎的改善
益生菌
益生元
合生元
细菌裂解物
粪菌移植
饮食
07 关于改善过敏性鼻炎的其他自然疗法
草药或补充剂等
锻炼
生活方式
在了解过敏性鼻炎是如何形成之前,我们先了解一下,什么是过敏性鼻炎?

据不完全统计,我国过敏性鼻炎的发病率在5%-25%之间,各个地区发病率不太一样,城乡差异也十分显著,估计全国患病人数在1亿以上。
尘螨在南方的致敏率最高,艾蒿、豚草和蒲公英则是西北最常见的过敏原。
大约 80% 的过敏性鼻炎症状在 20 岁之前出现,并在 20-40 岁达到高峰,然后逐渐下降。据报道,出生后头 5 年儿童过敏性鼻炎的发病率为 17.2%,诊断时的高峰年龄为 24 ~ 29 个月 (2.5%) .
过敏性鼻炎是一个常见病、多发病,可分为季节性(间歇性)或常年性(慢性),大约 20% 的病例是季节性的,40% 是常年性的,40% 的病例同时具有这两种特征。
最初可能出现的症状包括:
可能还会遇到其他较多症状,包括:
当身体对大多数人无害的物质(如花粉)反应过度时,就会发生过敏性鼻炎。
通常在接触某些物质后会出现过敏性鼻炎,过敏原一般分为以下四大类:
我们稍作展开讨论:
➤ 来自屋尘过敏原
实际上,携带过敏原的并不是尘螨本身,而是一种化学物质,在尘螨的排泄物中发现,一般会以人类皮屑为生,常见于家中的以下位置:
地毯、床垫、枕头、床单、窗帘等
➤ 来自树、草等花粉过敏原
根据一年中的不同时间,会出现不同类型的过敏原,因为从春季到深秋,树木、草都会产生花粉
树木包括:
桦木(非常常见)、雪松、榛、扁柏、角树、七叶树、菩提树、橄榄、松树、白杨、柳树等
草包括:
黑麦草、蒂莫西、艾蒿、荨麻、芭蕉、豚草等
➤ 来自动物毛发的过敏原
注意过敏原携带在动物的毛发上。引起过敏原的不是真正的毛发,而是毛发上携带的动物死皮屑、唾液、尿液等。
研究表明,早年接触通常携带过敏原的动物会降低晚年患此类过敏性鼻炎的患病率。
这类动物包括:
猫、狗(这两种非常常见)
牛、马、兔子、啮齿动物等
➤ 来自工作中明确遇到的过敏原
某些特定物质会在一些人身上引起过敏性鼻炎,因此如果职业要求接触以下的一种或多种过敏原,那么患过敏性鼻炎的风险就会增加。
过敏性鼻炎是由遗传和环境因素相互作用引起的。
父母或家庭成员患有过敏性鼻炎,则患过敏性鼻炎的几率更大。
根据卫生假说,过敏性鼻炎发病率的增加与环境因素的变化有关,例如:
近期发表的在小鼠实验中,万古霉素诱导的肠道菌群失调,通过改变短链脂肪酸,加剧肠粘膜屏障的破坏,增加小鼠过敏性鼻炎的易感性和严重性。
鼻粘膜的 H&E 染色
Zhen et al., Front. Microbiol. 2022
万古霉素诱导的肠道菌群失调加重了过敏性鼻炎的严重程度,加重了鼻粘膜的炎症细胞浸润和粘液分泌。
关于过敏性鼻炎,这里有几个需要注意的点:
鼻炎是鼻粘膜的炎症,它是一种上呼吸道疾病。鼻炎的临床症状包括阵发性打喷嚏、鼻塞、流鼻涕、流眼泪等,没有明显病因。而过敏性鼻炎作为鼻炎的一种,症状是由过敏原引发的。
很多人刚开始打喷嚏的时候,还以为是感冒了,赶紧吃感冒药,却发现并没有好转…
实际上过敏性鼻炎的症状往往与早期感冒的症状很相似。
一般来说,可以通过以下几点来区分到底是感冒还是过敏性鼻炎:
1
感冒通常伴有全身症状,如无力、发热、全身酸痛等,而过敏性鼻炎只是单纯的鼻部问题,除了可能有头痛,没有其他全身性疼痛症状。
2
过敏性鼻炎有可能会持续数周至数月,而感冒通常会在1-2周内自愈。
3
大多数过敏性鼻炎具有非常明显的季节性,尤其是春秋两季,而感冒一年四季都可能发生。
4
通过验血,大多数过敏性鼻炎在血液分析中显示嗜酸性粒细胞和 IgE 值升高,而其他值通常正常。相反,感冒通常具有升高的淋巴细胞值。
5
过敏性鼻炎过敏原阳性几率高,感冒几率低。
一旦过敏原吸入鼻腔,就会引起免疫反应。过敏原会和IgE抗体结合,激活肥大细胞。
也许对于普通人来说这没什么,但是对于过敏性鼻炎患者来说,就会引起过度反应,也就是说,免疫系统把花粉,灰尘等莫名扣上“通缉犯”,对其进行打击。
肥大细胞通过释放“组胺”,通知其他细胞,包括嗜酸性粒细胞、嗜碱性粒细胞、嗜中性粒细胞和T细胞等,会导致炎症和鼻粘膜充血:
• 本来好好的通道变窄了,气体很难通过就是鼻塞;
• 炎症刺激到神经,就是鼻子痒;
• 鼻粘膜分泌过多的粘液,结果就是流鼻涕…
过度分泌的粘液会堵塞两个鼻子的重要开口:
鼻泪管的作用是将眼泪从眼睛排到鼻子,一旦因为过敏性鼻炎,粘膜肿胀就会导致鼻泪管堵塞,这时候看起来像是“泪汪汪”的。

咽鼓管引流中耳分泌物,一旦因为过敏性鼻炎被堵塞,就会让人感觉到耳朵被塞住。

最后鼻腔内的神经受到刺激会开始打喷嚏

甚至,过敏性鼻炎患者会感到呼吸困难…

过敏性鼻炎的发病机理
鼻粘膜中的树突状细胞(DC)吸收过敏原 ➞ 引流淋巴结 ➞ 呈递给原始CD4+T细胞 ➞ 分化为过敏原特异性Th2细胞 ➞ 诱导B细胞活化产生浆细胞 ➞ 分化产生特异性IgE抗体 ➞ 在效应细胞(如肥大细胞和嗜碱性细胞)表面进行再循环和相互作用 ➞ 与IgE受体(FcεRI)结合 ➞ 炎症介质(如组胺、前列腺素、白三烯)释放 ➞ 介质与鼻感觉神经、血管系统和腺体相互作用,导致过敏性鼻炎症状
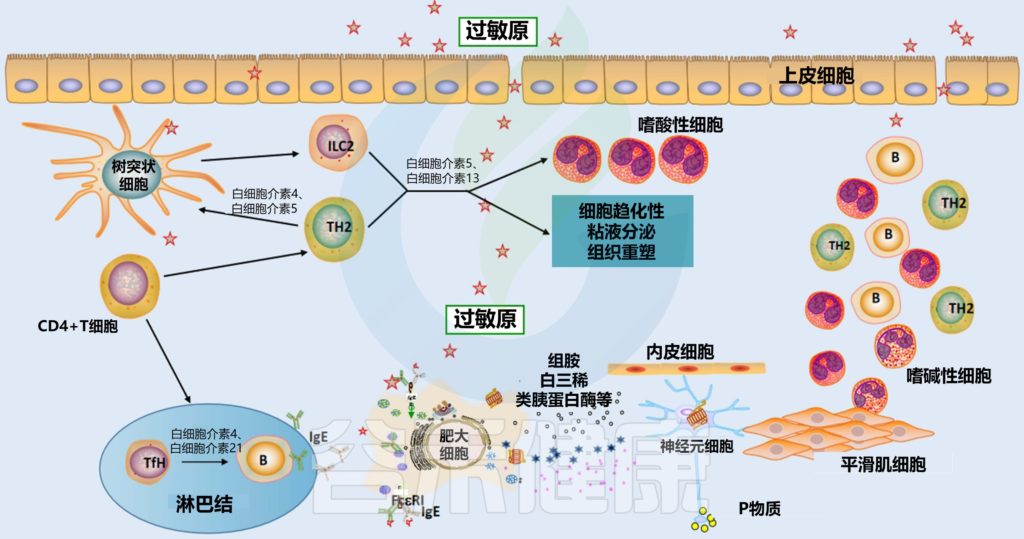
Liu P, et al., J Asthma Allergy. 2022
以上我们知道过敏性鼻炎涉及免疫反应,而人体内60%~70% 的免疫细胞集中在胃肠道中。肠道健康与过敏之间的联系始于免疫系统。
所有的免疫系统成分都直接或间接地受到微生物群的调节。
健康的微生物群会改变 Th1/Th2 细胞的比例,有利于 Th1 细胞,特应性疾病的特征在于对过敏原的 Th2 免疫反应。过敏性鼻炎以鼻腔黏膜Th2免疫反应为主的过敏性炎症反应,病变组织中存在大量Th2细胞因子浸润。
注:Th1细胞介导细胞免疫反应,直接攻击病原体或者促使其他细胞攻击病原体,就算病原体进入被感染的细胞,还会追进感染细胞里面去攻击;
Th2细胞介导体液免疫反应,它们会促使其他免疫细胞产生抗体,由这些抗体来攻击病原体。Th2细胞就不会进入被感染的细胞。
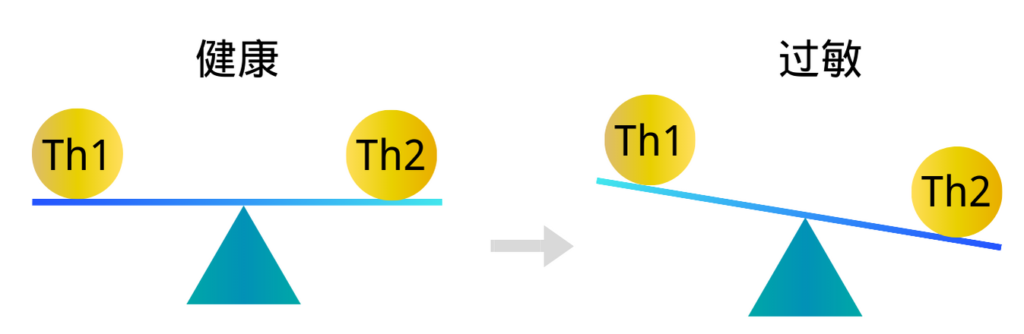
在免疫系统发育过程中,如果肠道失调通过将Th1/Th2细胞因子平衡向Th2反应转移,导致产生产生IgE的浆细胞,从而导致异常过敏反应。
越来越多的证据表明,平衡良好的肠道菌群对发育调节性T细胞(Tregs)至关重要,这对肠道耐受诱导至关重要。下一章节我们来讨论肠道菌群与过敏性鼻炎之间的关系。
注解:由于Th1细胞和Th2细胞都能分泌细胞因子促进自身的增殖并抑制对方的增殖,因此在正常情况下机体中 Th1细胞和Th2细胞处于相对平衡的状态。 但当机体发生功能异常时,常表现出平衡偏向其中一方,称为 “Th1/Th2漂移”。Th1细胞和Th2细胞之间的平衡状态被打破,会引起许多疾病的产生和发展。 包括肿瘤和一些自身免疫性疾病。
但是,不同的疾病表现出的Th1/Th2平衡漂移各不相同。如类风湿性关节炎、I型糖尿病、多发性硬化及慢性甲状腺炎等疾病中,Th1占优势状态;而在系统性红斑狼疮、硬皮病以及一些常见的变态反应性疾病比如过敏性鼻炎中,则Th2占优势状态。
我们知道,肠道菌群在人体中发挥着重要的生理作用,如影响维生素合成、免疫等,且与过敏性疾病的发生、发展相关。
肠道多样性的改变在过敏性疾病患者中较为常见。
目前已有的研究显示,与健康人相比,过敏性鼻炎患者的肠道菌群多样性显著较低(Chao1和Shannon多样性指数),其他菌群变化如下:
过敏性鼻炎患者肠道增加的菌群:
过敏性鼻炎患者肠道减少的菌群:
可见,健康个体和过敏性鼻炎患者的肠道菌群组成不同。
其中,普雷沃氏菌可能是影响免疫系统发育的重要微生物之一。
产丁酸盐的细菌,如梭状芽胞杆菌,可诱导调节性 T 细胞并通过预防肠道炎症来抑制过敏症状。
要解释肠道菌群是如何影响过敏性鼻炎的,我们要先从肠道菌群对免疫系统的塑造开始了解。
肠上皮细胞:将细菌和宿主的免疫系统连接起来
肠上皮细胞(IEC)翻译来自共生细菌的信号(细菌代谢物、细菌成分和细菌本身)并将它们发送到粘膜免疫细胞。可见,肠上皮细胞在肠道免疫中起关键作用。
微生物在肠道定植,并通过肠上皮细胞诱导血清淀粉样蛋白 A 的产生,从而改善 Th17 分化和 IL-22 的产生。
主要参与与定殖肠道细菌的串扰的免疫细胞主要见于固有层。其中,最常见的是树突状细胞(DCs)、Tregs、NK细胞和CD4+ T细胞。
树突状细胞:刺激 CD4+ T 细胞分化
树突状细胞在与先天性和适应性免疫反应的相互作用中起着至关重要的作用。它们迁移到次级淋巴组织并根据激活信号刺激 CD4+ T 细胞分化成亚型。
共生细菌衍生的代谢物影响树突状细胞的功能。例如,短链脂肪酸抑制 IL-12 并增加 IL-10 和 IL-23 的产生,降低 CCL3、CCL4、CCL5、CXCL9、CXCL10 和 CXCL11 的水平,间接调节 T 细胞功能。此外,它们通过树突状细胞的调制诱导 B 细胞IgA 类别转换和 IgA 产生,并调节其他适应性反应细胞功能。
巨噬细胞:摄取病原体
与肠上皮相关的巨噬细胞具有广泛的功能。它们可以摄取病原体,产生多种影响其他免疫细胞的细胞因子,并支持 Treg 的维持。
短链脂肪酸:促进巨噬细胞分泌抗炎 IL-10
微生物产生的短链脂肪酸促进巨噬细胞分泌抗炎 IL-10。此外,它们改变巨噬细胞的新陈代谢,降低 mTOR 激酶活性并增加抗菌肽的产生。
在正常情况下,微生物群和身体之间的相互作用是决定身体健康的基础,如果其中一个环节受损,可能会导致肠道菌群失衡。肠道微生物群的失调显著影响微生物群与宿主之间的代谢,并抑制宿主免疫系统。大多数过敏性疾病与肠道微生物群失衡有关,如过敏性鼻炎。
典型的过敏性鼻炎肠道菌群促进细胞因子的不利变化,从而促进过敏性鼻炎发展中涉及的 Th1/Th2 失衡。
过敏性鼻炎患者的肠道菌群失调及其对 Th1/Th2 平衡的影响
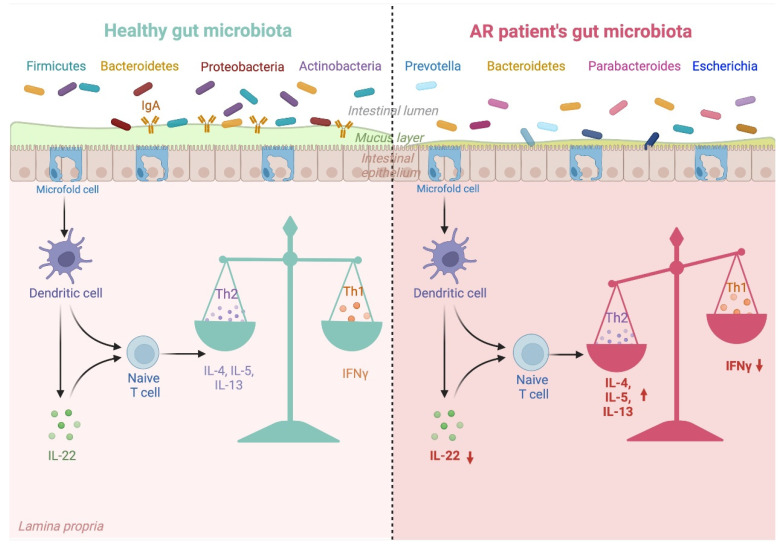
Kaczynska A, et al., Nutrients. 2022
肠道菌群的每一次紊乱都会对免疫系统产生负面影响,并破坏先天性和适应性反应。上图解释了改变的肠道微生物群组成与其对过敏性鼻炎患者免疫系统的影响之间的联系。
接下来章节,我们来详细了解,肠道菌群如何影响免疫系统从而引发过敏性鼻炎。
肠道菌群失调可能会破坏 Th1/Th2 细胞之间的稳态,这可能会对免疫耐受产生负面影响,破坏过敏原的正常清除,并增加过敏性鼻炎的风险。我们从以下六个方面详细展开讨论肠道微生物群在过敏性鼻炎中扮演的重要角色。
前面我们已经知道,过敏性鼻炎是一种I型过敏性疾病,与Th1/Th2平衡向Th2倾斜有关。
为什么生命早期肠道菌群多样性的变化会与过敏有关?
在生命早期,全身免疫反应偏向于Th2。研究表明,生命早期肠道菌群的多样性较低,会影响 IL-4 和 IFN-γ 的水平, IL-4 由Th2细胞产生的,IFN-γ由Th1产生,因此,这可能通过调节 Th1/Th2 平衡来影响气道炎症。
此外,在生命的前两年,较低的微生物多样性会延迟拟杆菌的定殖,并导致 Th1 型反应减少,从而导致Th1/Th2 平衡向Th2倾斜。
一些益生菌也能通过影响Th1/Th2 平衡,从而发挥作用。
植物乳杆菌(NR16)
从发酵韩国泡菜中提取的植物乳杆菌(NR16) 是一种强大的 Th1 诱导剂,当 NR16 与免疫细胞共培养时,它可以产生大量的 IFN-γ 和 IL-12,并且在同时口服 NR16 可降低小鼠气道高反应性和白细胞浸润。此外,口服 NR16 可以通过诱导 Th1 免疫反应来缓解过敏性鼻炎症状,这反过来又可以通过减少特定粘膜病变中 Th2 细胞因子的产生来重新平衡 Th1/Th2 比率。
植物乳杆菌可增加过敏性鼻炎小鼠模型中Th1型细胞因子(IFN-γ、特异性血清IgG2a)的产生,Th2型细胞因子(IL-4、IL-5、IL-13)减少并达到Th1/Th2的平衡。
泛福舒
一项随机对照研究表明,与对照组相比,泛福舒治疗后,泛福舒组鼻腔灌洗液中IL-4和IL-13的含量显著降低,而INF-γ的含量显著升高,导致IL-4/INF-γ的比值显著降低,泛福舒可以调节Th1/Th2细胞因子平衡,作为一种潜在的细胞信号机制,提高整体粘膜免疫。
短双歧杆菌
研究人员证实,口服短双歧杆菌可抑制 Th2 反应并诱导 CD4+CD25+Tregs 活性,但不引起 Th1 反应,但可调节 Th1/Th2 平衡并具有抗过敏作用。
其次,大剂量短双歧杆菌可显着减少打喷嚏的频率,同时降低血清IL-4和特异性IgE水平,增加脾脏中CD4+CD25+ Tregs的数量,显着降低鼻黏膜上皮的过敏反应,低剂量的短双歧杆菌只能轻微缓解过敏反应。
2型先天性淋巴细胞(ILC2)是一种先天性免疫细胞,缺乏表面标记物,因此难以识别。它们反映Th2型细胞,在过敏发展中发挥着重要作用。
我们知道,过敏性鼻炎是一种IgE介导的炎症,导致鼻粘膜中Th2细胞和II型细胞因子的数量增加。
研究人员发现鼻粘膜中ILC2的数量与过敏性鼻炎临床视觉模拟量表(VAS)评分呈正相关。
肠道微生物群失调如何影响过敏性鼻炎
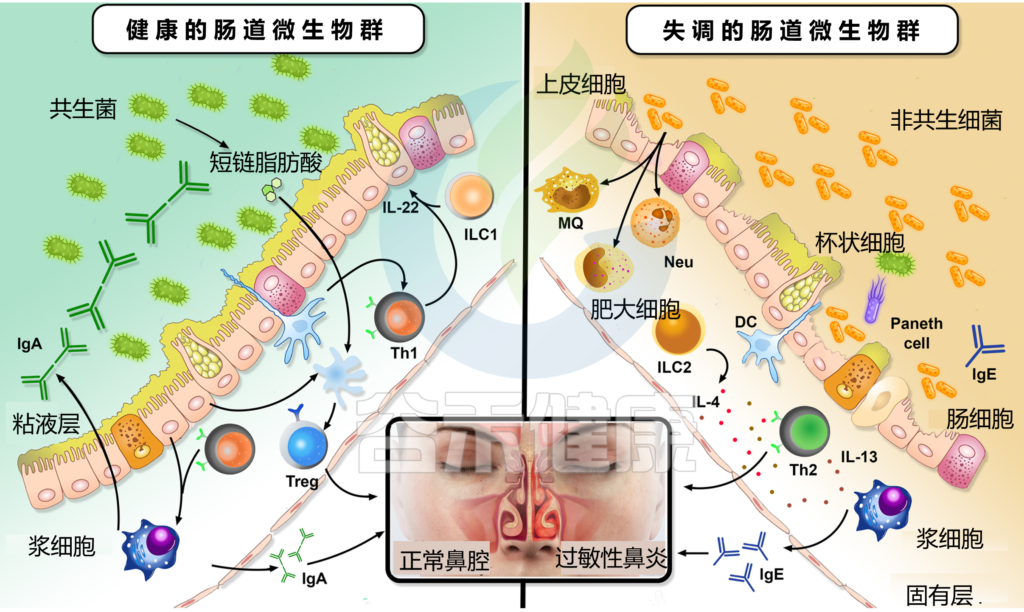
Li J, et al., Eur Arch Otorhinolaryngol. 2022
为什么ILC2在过敏性鼻炎的调节中起重要作用?
过敏性鼻炎患者中多种脂质受体上调,包括CysL1R(LTD4配体)和PGD2。尽管LTD4可激活ILC2中IL-4的产生,但过敏性鼻炎患者鼻分泌物中IL-4水平没有显著变化。
臭氧通过诱导ILC2释放IL-5和IL-13来加重过敏性鼻炎症状。
患有屋尘螨敏感的过敏性鼻炎的儿童外周血ILC2水平显著升高。所有这些发现表明ILC2在过敏性鼻炎的调节中起着重要作用。
肠道菌群对ILC2的影响
值得注意的是,肠道微生物群影响ILC2通过肠-肺轴从肠道向肺的迁移。例如,变形菌门显著促进了上述迁移,并促进了IL-33的产生。
此外,呼吸道过敏的发展与Ruminococcus gnavus的丰度增加有关联。
研究人员发现,肠道菌群失调刺激ILC2和树突状细胞产生2型细胞因子,并促进嗜酸性粒细胞和肥大细胞的肺浸润。
另一方面,肠道微生物群发酵膳食纤维产生的短链脂肪酸抑制ILC2的功能,防止肺部炎症。因此,研究表明ILC2s的活性受到肠道微生物群的调节,但其潜在机制尚未得到充分阐明。
益生菌可以通过抑制ILC2的激活来控制过敏性鼻炎的发生和发展
在一项木瓜蛋白酶诱导的BL6小鼠的研究中,益生菌大肠杆菌菌株Nisle 1917(ECN)的治疗导致IL-5的降低较小,IL-13,IL-33的水平显著降低。ECN处理的小鼠具有显著更低的CD3+CD4+IL5+和IL13+细胞频率。数据表明,ECN能够抑制Th2和ILC2的活化以及原型致敏IL-5和IL-13的产生。
然而目前的研究相对有限,需要更多的基础和临床研究来评估未来的长期治疗效果。
对于肠道菌群在人和动物过敏性鼻炎模型中的研究显示,在益生菌的作用下,大多数血清炎症因子都有不同程度的下降,如IL-4、IL-5、IL-13、IgE、特异性血清IgG1、嗜酸性粒细胞和嗜碱性粒细胞水平减少,但一些抗炎因子增加,如 IL-10、IFN-γ 和特异性血清 IgG2a 分泌增加。因此,益生菌可以通过提高血清中炎症因子的水平来缓解过敏性鼻炎患者的炎症反应,从而减轻他们的临床症状。
NVP-1703 益生菌混合物:IL-5↓ IL-13↓ IL-10↑
(长双歧杆菌IM55 和植物乳杆菌IM76)
一项关于多年过敏性鼻炎的成人研究评估了NVP-1703益生菌混合物(长双歧杆菌IM55和植物乳杆菌IM76)干预4周的疗效和安全性,IL-4血清中尘螨水平无明显变化,但尘螨特异性IgE水平显著降低。在第4周,与安慰剂组相比,NVP-1703组的血清IL-5和IL-13水平降低,而IL-10水平显著升高。
泛福舒:IL-4↓ IL-13↓ INF-γ↑
在早期研究中,60名过敏性鼻炎患者被随机分为泛福舒(BV)组和对照组。泛福舒治疗后,治疗组的药物评分明显低于对照组,且个体和总体鼻症状评分均显著低于对照组。
泛福舒组鼻腔灌洗液中的IL-4和IL-13水平显著降低,而干扰素γ(INF-γ)水平显著升高,这使得IL-4/INF-γ比值显著降低,嗜酸性粒细胞也显著减少,过敏性鼻炎患儿呼吸道病毒感染率/严重程度的增加可能由多种机制引起,但IFN-γ缺乏可能是其中之一,益生菌可以通过提高IFN-γ水平来改善呼吸道病毒感染。
植物乳杆菌:IL-4↓ IL-5↓ IL-13↓ IgE↓ IgG1↓ IFN-γ↑ IgG2↑
在过敏性鼻炎小鼠模型中,口服植物乳杆菌可减少过敏性鼻炎小鼠模型鼻腔和肺部浸润细胞数量,而支气管肺泡灌洗液和引流淋巴结标本显示免疫细胞计数减少,IL-4、IL-5、IL-13、血清IgE和特异性血清IgG1水平降低,IFN-γ和特异性血清IgG2a分泌增加,可改善过敏性鼻炎。
丁酸梭菌:IgE/G1↓ IL-10↑ 逆转Th1/Th2失衡
显着降低了肺阻力、肺气道炎症、肥大细胞脱粒、小鼠气道炎症重塑和 OVA 特异性 IgE/G1 表达。同时,它还逆转了Th1/Th2失衡,增加了抗炎血清因子IL-10.
益生菌发酵的红参:IL-4↓ IgE↓
益生菌发酵的红参(FRG)对卵白蛋白(OVA)诱导的小鼠过敏性鼻炎模型的影响是,FRG比红参更有效地降低支气管肺泡灌洗液、鼻液和血清中的IL-4和IgE水平,表明FRG比红参具有更好的免疫调节作用。 FRG 治疗可减少炎症。
瑞士乳杆菌SBT2171:IL-4↓ IL-13↓ IFN-γ↑ IL-10↑
瑞士乳杆菌SBT2171(LH2171)可在体外诱导抗原刺激的幼稚小鼠脾细胞产生细胞因子,从而抑制IL-4和IL-13的产生,并增加IFN-γ和IL-10的产生。
Treg作为免疫抑制性CD4+T细胞,而Th17作为炎性CD4+T细胞,两者之间的平衡是维持人体免疫系统稳定性的关键条件。 过敏性鼻炎患者Th1/Th2失衡。
益生菌可以通过调节Treg/Th17的平衡来改善过敏和免疫疾病的调节,并产生了一些具有相当效果的靶向治疗方法。
对变应性真菌性鼻窦炎患者的研究表明,血清中IL-1、IL-17、IL-21和TGF-β的分泌都有不同程度的增加,导致Th17/Treg平衡Th17方向的偏移。
研究数据证实,过敏性鼻炎患者外周血中炎性因子如IL-17、IL-35和Th17的分泌增加,炎性因子的增加导致Treg/Th17失衡,进而导致Th1/Th2失衡,导致一系列过敏性鼻炎典型临床症状和鼻粘膜纤毛破坏,鼻腺增生和炎性细胞浸润。
益生菌通过影响Treg / Th17的平衡调节自身免疫
梭菌孢子诱导CD4+FoxP3+Treg细胞可以抑制Th17细胞的促炎反应。
使用益生菌混合物VSL#3来诱导Treg细胞的增殖。
细胞实验表明,乳酸菌上清液可以减少CD4+T细胞、CD8+T细胞和粘膜相关恒定T细胞等的活化,乳酸菌的产物可以抑制这些细胞的增殖和脱颗粒。
其他研究表明,炎症引起的T细胞代谢变化会影响Treg细胞的免疫功能。例如,糖酵解过程中的烯醇化酶可以调节外显子中FoxP3的结合变体,以及应激状态引起的Treg代谢变化,这是触发自身免疫反应的重要部分。
使用干酪乳杆菌作为干预对照,结果表明,干预组脾脏中CD4+CD25+Foxp3+Treg的百分比增加,而CD4+IL-17A+Th17细胞的百分比降低,调节了Treg/Th17细胞比例的失衡。
另一项研究表明,鼠李糖乳杆菌GG(LGG)提取物可以通过Toll受体(TLR2)途径,降低IL-17+Th17的比率,增加CD25+Foxp3+Treg的比率,从而维持Treg/Th17的稳态。
树突状细胞(DC)是体内最有效的抗原呈递细胞(APC),通过调节对微生物抗原的耐受性和免疫性,可以有效诱导抗原特异性免疫应答。
益生菌可能通过调节树突状细胞成熟和免疫耐受性树突状细胞(TDC)产生,产生抗炎细胞因子,从而抑制炎症,影响免疫调节。
免疫耐受性树突状细胞在调节免疫耐受中发挥关键作用
其特征在于表达共刺激分子(CD80/CD86)的半成熟表型,其可通过TLR配体或通过暴露于特定细胞而激活,在因子环境中分化。
此外,它们还表达免疫调节分子并产生免疫抑制因子,半成熟的共刺激CD80/CD86信号通过CD28分子的作用影响T细胞上Treg的激活,进而诱导免疫耐受。
目前,一些临床试验正在进行,以探讨TDC作为免疫介导疾病的替代治疗方案的有效性。与抗炎分子相比,这些TDC具有半成熟表型,表现出低水平的T细胞共刺激特性,并且产生促炎细胞因子的能力降低,特别是通过调节性T细胞(Tregs)的扩增和/或诱导。
其他研究也表明,TDCs分泌抗炎细胞因子并调节T细胞,以促进小鼠和人类肠道中Foxp3+Treg的发育。在全球范围内,这些数据表明DC/Treg/B调节轴通过重新建立耐受性和调节Tregs在肠道中发挥中心作用。
菌群的免疫调节作用来自免疫细胞与肠道树突状细胞的相互作用
最近的证据表明,益生菌可能通过调节DC成熟和TDC产生,从而抑制炎症,从而影响体外和体内的免疫调节。益生菌的免疫调节作用来自免疫细胞与肠道DC的相互作用,从而调节先天和适应性免疫系统。
研究表明,益生菌能够与DC上的模式识别受体(PRR)反应,后者检测病原体上不同的进化保守结构(病原体相关分子模式,PAMP),或通过产生可溶性化合物,从而诱导TDCs。
不同种类和菌株的益生菌可能直接影响树突状细胞的成熟,益生菌可能调节抗炎细胞因子的水平,如转化生长因子β(TGF-β)、IL-10,并诱导Treg。
一项针对四种益生菌菌株(包括唾液乳杆菌、双歧杆菌、凝结芽孢杆菌和纳豆枯草杆菌)的研究,都诱导DC产生IL-10和TGF-β,双歧杆菌和凝结芽孢杆菌表现出更强的诱导IL-10和转化生长因子-β的能力。因此,益生菌诱导的树突状细胞活性产生抗炎细胞因子在免疫调节功能中起着关键作用。
总之,益生菌通过调节TDC活性是过敏性鼻炎治疗的潜在靶点。
Toll样受体(TLRs)是机体免疫的主要组成部分之一,是肠粘膜淋巴细胞和上皮细胞表面表达的识别受体,为入侵病原体和炎症反应提供防御屏障。
肠道共生菌群的一部分,可以通过与TLR相互作用,在控制免疫反应中发挥关键作用。
TLR位于细胞质膜和细胞内内体中,可检测细菌、病毒和真菌的一系列致病分子模式,树突状细胞中TLR的激活可影响适应性免疫反应。
许多微生物感染可以激活TLR4信号,而肠道共生微生物群的一部分,可以影响TLR4.
益生菌多糖胶囊可以通过调节Th1/Th2平衡、诱导T调节细胞分化和激活DC,进而通过TLR与肠道微生物群相互作用,在控制免疫反应中发挥关键作用。
在一项益生菌(鼠李糖乳杆菌GG)与舌下免疫疗法(SLIT)联合的研究中,组间分析表明,与SLIT维生素D组相比,SLIT益生菌组的CD4+CD25+Foxp3+诱导率显著增加,相比之下,TLR阳性细胞组的百分比降低更多。
研究表明,益生菌产生的瞬时蛋白可以诱导TLR的产生,这种蛋白可以缓解特定IgE引起的过敏反应。
此外,一些TLR可以刺激DC激活,进而导致Treg细胞产量增加。先前的研究指出,TLR可能是益生菌影响Treg细胞增殖和分化的潜在靶点。
菌群可以依赖TLR4/NF-κB途径调节过敏性炎症
在一项研究中,阐明了益生菌对TLR4/NF-kB通路在调节宿主对肺损伤和气道炎症的防御中的调节作用。过敏性婴儿哮喘和TLR有影响。
结果表明,β-乳蛋白刺激导致巨噬细胞TLR4/NF-κB信号通路的转导增加。
嗜酸乳杆菌KLDS 1.0738干预通过抑制TLR4通路显著减少过敏性炎症。此外,嗜酸乳杆菌KLDS 1.0738菌株可以显著降低TLR4转导和炎性细胞因子的产生,这与miR-146a水平的上调密切相关。
// 小结
总的来说,肠道菌群可以通过减少血清促炎因子、增加免疫细胞数量、调节Th1和Th2平衡、增加Treg数量和抑制Th17等方式来预防过敏性鼻炎的发生发展,此外,某些菌可以直接刺激TDC的形成或激活TLR通路以间接刺激DC,从而诱导Treg的形成。
通过增加有益细菌的水平可以调节肠道微生物群的稳定性,恢复肠道粘膜屏障,从而改善过敏性鼻炎。
可以根据疾病的具体严重程度、疾病类型和生活方式选择合适的治疗药物。
过敏性鼻炎的治疗选择

▸鼻用皮质类固醇
局部鼻用皮质类固醇起效迅速,尤其是缓解鼻塞。外用类固醇与特定的细胞质糖皮质激素受体 (GRs) 结合,激活抗炎基因转录并抑制促炎基因转录,外用类固醇的抗炎作用可减轻所有鼻部和眼部症状。
▸外用类固醇联合抗组胺药
MP Aze-Flu 是一种由盐酸氮卓斯汀和丙酸氟替卡松组成的鼻喷雾剂,在症状评分和生活质量方面比安慰剂或丙酸氟替卡松单独有效。
▸ 鼻塞减轻剂
由于鼻黏膜的反弹作用和习惯作用,连续使用最好不超过7天。大部分药物可使α肾上腺素受体起作用,引起血管舒张和收缩,可立即缓解鼻塞症状,主要包括伪麻黄碱、羟甲唑啉、三唑啉或去氧肾上腺素。
▸鼻用抗胆碱能药和色甘酸钠/肥大细胞稳定剂
主要影响鼻腔分泌物的鼻用色甘宁和抗胆碱能药有一些较早的研究,但没有足够的证据做出充分的推荐。
▸盐水冲洗
增加儿童的鼻腔冲洗是有益的,可以减少鼻嗜酸性粒细胞和中性粒细胞。
全身性糖皮质激素的所有机制均受 GR 的调节,GR 属于配体调节的核受体超家族,类固醇的抗炎作用可以通过三种广泛的分子机制来解释:促炎基因表达降低、抗炎炎症基因表达增加和非基因组机制。
▸口服抗组胺药
已在多种细胞上鉴定出四种组胺受体 H1 和 H2 受体,可刺激过敏反应的早期和晚期。第二代/第三代非镇静 H1 受体拮抗剂是过敏性鼻炎的首选抗组胺药。
许多研究表明西替利嗪是有效的,并且西替利嗪在症状缓解方面优于氯雷他定,并且具有良好的安全性。
▸白三烯受体拮抗剂(LTRA)
白三烯是炎症介质家族,包括LTA4、LTB4、LTC4、LTD4和LTE4,通过阻断半胱氨酸LT1(CysLT1)受体,LTRAs(如蒙特鲁甾醇)可以改善过敏性鼻炎和哮喘症状。目前,口服色甘酸作为肥大细胞稳定剂的研究不足。
迄今为止,过敏原免疫疗法是目前唯一可用于 IgE 介导的过敏性疾病患者的免疫调节和因果治疗。
过敏原免疫疗法的目的是对免疫系统进行重新编程以减少特异性IgE的产生,从而诱导对过敏原的耐受,可通过不同的给药途径分为皮下免疫和舌下免疫两种方式,通过不断增加过敏原剂量使患者脱敏。
同时,研究人员发现接种疫苗可以改善长期空气污染对过敏性呼吸道的负面影响。针对风疹、伤寒和天花的预防性免疫显示过敏性鼻炎的发生率较低,而麻疹疫苗的过敏性鼻炎发生率较高。
目前过敏性鼻炎的治疗仍然基于过敏原避免、症状缓解药物、抗炎治疗和过敏免疫治疗。现阶段过敏性鼻炎治疗药物不良反应多且无法治愈,症状易反复,免疫治疗疗程较长,依从性差,同时降低生活质量。
肠道微生物群正在成为早期治疗特应性疾病的新靶点,如过敏性鼻炎也是特应性疾病的一种。
益生菌可以用作宿主防御途径的免疫调节剂和激活剂,口服益生菌可以调节呼吸系统的免疫反应,并可以通过调节肠道微生物群和免疫反应的变化来预防和治疗上呼吸道疾病。
国际上对益生菌作为替代治疗方法的研究和应用正在增加,大多数研究表明益生菌可以显着改善过敏性鼻炎患者的症状。
接下来我们详细了解基于菌群干预的过敏性鼻炎疗法。
作为调节肠道菌群平衡的重要手段,益生菌包括多种细菌,其主要作用是维持免疫系统的平衡,改善菌群结构,恢复菌群平衡,同时,它可以减轻肠道局部黏膜炎症反应,恢复黏膜屏障,阻断外来病原体的入侵。
前面章节我们了解到,益生菌可以激活 Th1 或抑制 Th2,引起抗炎作用,还可以刺激免疫因子如IL-10的产生,其主要作用是抑制炎症反应。
因此益生菌治疗过敏性鼻炎的基础研究和临床应用越来越多。
➤ 关于益生菌改善过敏性鼻炎的研究
益生菌的使用可积极改善克雷伯菌与双歧杆菌的比例,并可预防过敏性疾病的发展。
对过敏性鼻炎大鼠的研究表明,婴儿双歧杆菌和长双歧杆菌的混合物LacB可以降低粘膜中H1受体和脱羧酶组氨酸的mRNA表达,从而减轻过敏性鼻炎表现。
在一项双盲安慰剂对照试验中,与安慰剂组相比,食用5个月的干酪乳杆菌(LcS)会导致IgG水平升高,IL-6、IL-5和干扰素γ(IFN-γ)水平显著降低。
研究人员还调查了嗜酸乳杆菌对患有实验性过敏性鼻炎的BALB/c小鼠的影响,并报告使用第二周后喷嚏明显减少,而对照干预措施在第四周减少了喷嚏。
在对1919名过敏性鼻炎患者的23篇论文进行的系统回顾和荟萃分析中,研究人员表明益生菌可能有效缓解过敏性鼻炎患者的症状和生活质量。
在另一项系统综述中,包括了11项关于使用益生菌治疗和预防过敏性鼻炎的随机对照试验。研究结果表明,益生菌的使用与过敏性鼻炎患者的生活质量和鼻腔症状的显著改善有关。
关于益生菌治疗过敏性鼻炎的研究


Liu P, et al., J Asthma Allergy. 2022
研究表明,添加益生菌可以通过恢复肠道菌群紊乱来调节过敏性鼻炎的免疫反应。
一项研究指出,用益生菌发酵乳治疗后,患者的血清特异性IgE显著降低,免疫功能显著改善,体内肠道菌群结构得到改善,肠道菌群平衡得到恢复,症状也显著缓解。
用从人类粪便和泡菜中分离的长双歧杆菌和植物乳杆菌的益生菌混合物(PM)进行过敏性鼻炎治疗,可以通过控制肠道菌群紊乱(显著抑制变形菌,增加拟杆菌和放线菌的组成)来缓解过敏性鼻炎。
也有结果表明,益生菌和L-谷氨酰胺可以有效调节过敏性鼻炎患儿治疗过程中胃肠肽的水平,恢复肠道菌群的平衡,并恢复肠黏膜的屏障功能,从而达到治疗目的。
基于上述研究结果,可以看出益生菌可以调节和恢复肠道微生物群紊乱以治疗过敏性鼻炎。
当然,也有研究中发现益生菌治疗后效果没有明显改善的,例如:
在一项关于益生菌治疗过敏性鼻炎疗效的研究中,患者的过敏症状没有明显缓解,但与治疗前相比,一些患者的鼻粘膜微环境有所改善。
17项纳入的研究发现,益生菌治疗至少在一个结果指标上比安慰剂有显著的治疗优势,而六项试验未发现效果。
目前,作为临床过敏性疾病研究的一个新方向,益生菌有望成为过敏性鼻炎控制和治疗的潜在新目标。益生菌治疗的可能机制如下图所示:
益生菌治疗过敏性鼻炎的简要机制

Liu P, et al., J Asthma Allergy. 2022
益生菌作为过敏性鼻炎的辅助疗法,不仅可以从深层次恢复肠道微生物群紊乱,缓解鼻过敏的典型症状,而且具有高性价比和低风险的优势。
然而需要注意的是,目前的关于益生菌的基础研究仍在进行中,益生菌的最佳菌株、剂量和持续时间还需要进一步探索,同时,在引入新的治疗方法的过程中,有必要注意其可能带来的副作用。
益生元是影响肠道微生物群组成和活性的特定膳食成分。常用的益生元是乳糖醇、乳果糖、菊粉、乳糖、低聚果糖、低聚半乳糖和大豆低聚糖等。
◣ 益生元对IgE水平高的过敏性鼻炎成人的影响
在52周内,患者接受乳糖,并测量其血清IgE水平。治疗一年后,血清IgE水平(尤其是花粉过敏原)显著降低,同时伴有过敏症状的缓解。
一项研究比较,干燥的Ma-al-Shaeer(一种富含纤维的传统伊朗药物,配方基于大麦)与非索非那定对成人过敏性鼻炎患者的影响。
受试者连续14天每天两次接受口头提及的制剂。两组过敏性鼻炎的临床病程均得到改善,而Ma al-Shaeer组的鼻塞、鼻后滴漏和头痛评分显著降低。
◣ 益生元被广泛用作婴儿配方奶粉的补充
一项研究评估了益生元寡糖对过敏的保护作用。
在这项随机对照试验中,具有特应性风险的健康婴儿在出生后的前六个月接受了补充益生元或补充安慰剂的配方奶粉喂养。随访期为五年。
补充益生元组的累计过敏表现发生率显著降低。该干预措施对预防过敏性鼻结膜炎和过敏性荨麻疹特别有益。
其他关于益生元预防/治疗哮喘或过敏性鼻炎的研究
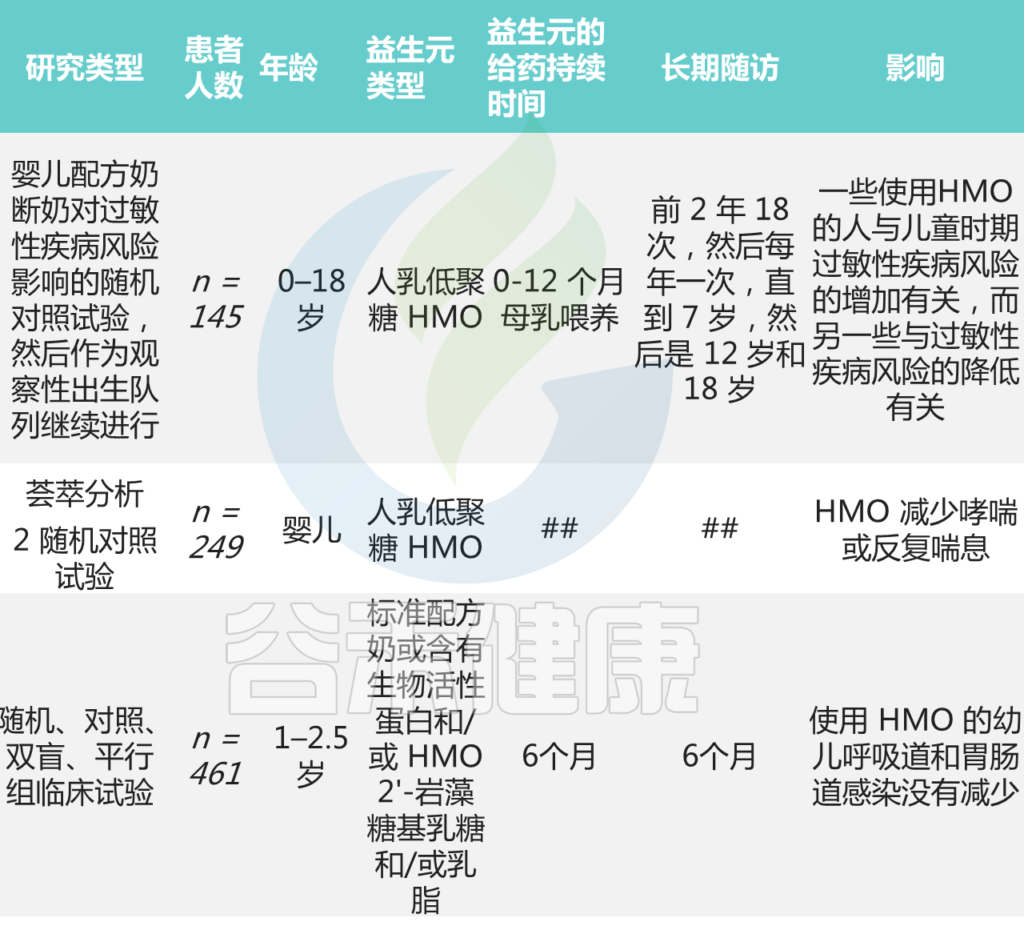
Meirlaen L, et al.,Nutrients. 2021
总之,关于益生元用于预防和治疗过敏性鼻炎的数据仍然不足。然而,它们调节细胞因子释放的能力,似乎是治疗过敏性疾病的一种新的、有前途的方法。
合生元治疗过敏性鼻炎的研究也很少,个别研究益生菌功效的试验实际上涉及合生元。
关于合生元预防/治疗过敏性鼻炎的研究
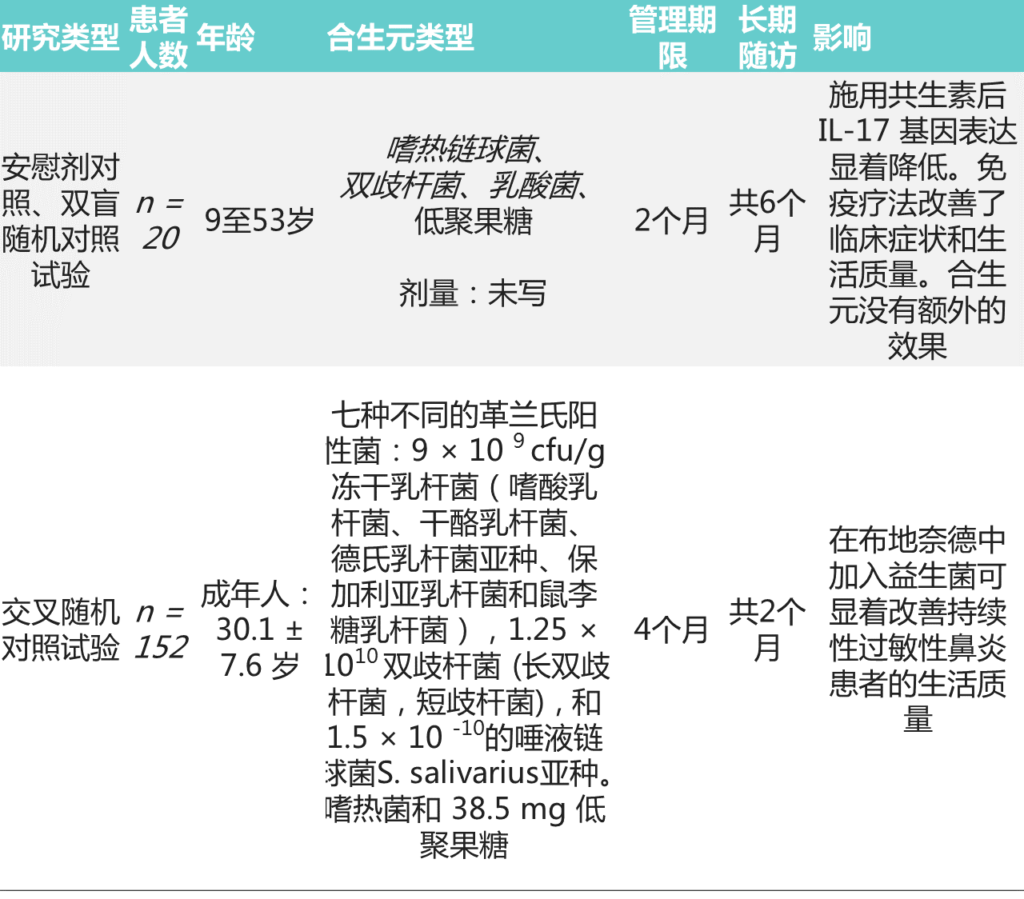
Meirlaen L, et al.,Nutrients. 2021
合生元对预防过敏性鼻炎的作用仍未得到解答,需要更多设计良好的研究,仅研究合生元对过敏预防和/或治疗的影响。
细菌裂解物是由源自呼吸道病原体的抗原组成的免疫调节制剂。最常见的是肺炎链球菌、流感嗜血杆菌、卡他莫拉菌、化脓性链球菌、绿色链球菌、金黄色葡萄球菌、肺炎克雷伯菌和奥扎纳克雷伯杆菌。
该制剂可通过化学或机械裂解获得。不同的生产方法可以产生不同的免疫效果。细菌裂解物可以口服、鼻内和舌下给药。这里讨论了口服给药对肠道环境的影响。
细菌裂解物的作用机制基于自然暴露于病原体抗原和随后的免疫反应。它们通过Toll样受体激活DC,促进抗病毒细胞因子释放、NK细胞活化和Th1/Th2平衡的恢复。
只有五项研究调查了细菌裂解物对过敏性鼻炎的影响。其中两个使用口服OM-85。
OM-85
一项开放标签的顺序研究,研究了在过敏性鼻炎、哮喘或慢性阻塞性肺疾病患者中使用OM-85对呼吸道感染率、原发病加重率和症状严重程度的影响。
减少过敏性鼻炎发作次数,严重程度减轻
患者分三个周期接受制剂,包括连续10天的摄入,然后休息20天。他们表明,与前一年相比,OM-85治疗减少了呼吸道感染和过敏性鼻炎发作的次数,并缓解了过敏症状的严重程度,而前一年患者只接受了标准的优化护理。
已证明血清和唾液IgA水平增加。为了进一步扩大这项研究,评估了60名常年过敏性鼻炎患者的临床效果。参与研究的参与者按照与前述研究相同的方案服用OM-85。治疗后,OM-85组的总鼻部症状评分、瘙痒评分、鼻溢评分、喷嚏评分和药物评分均显著下降。此外,观察到鼻IFN-γ增加,鼻IL-4和IL-13水平降低,鼻拭子中嗜酸性粒细胞数量减少。
细菌裂解物不会直接影响肠道细菌;然而,它们刺激的细胞因子可能会影响肠道环境。关于细菌裂解物对过敏性鼻炎的影响还需要更多的研究。
粪菌移植是将健康供体的粪便转化为粪便悬浮液,并将其施用于患者的肠道,以重建肠道微生物群的平衡的过程。目前,没有关于其在过敏性鼻炎治疗中的应用的研究;然而,这可能是恢复肠道细菌组成的一种有前途的方法。潜在地,它可能比益生菌更有效,因为其显著更丰富的注入微生物和永久定植肠道的能力。
一项研究证实了这一假设,他们研究了粪菌移植对成年特异性皮炎患者的影响。结果表明,粪菌移植后特应性皮炎评分显著降低。此外,在研究和随访期间,每周局部使用皮质类固醇的情况有所减少。
肠道微生物群的宏基因组分析显示,从供体到患者的细菌菌株传播显著。未观察到治疗的不良反应。
然而,关于其在过敏性疾病中的应用,仍然没有足够的数据;因此,需要更多的大样本研究。
高质量的饮食结构,如水果和蔬菜、高纤维食物、鱼、低脂食物、蛋白适量,可以增加肠道多样性,维持肠道菌群平衡,有助于平衡免疫反应。
研究表明饮食习惯和肠道微生物群与过敏性疾病有关。
一项研究招募了 186 名有过敏性鼻炎症状的参与者和 106 名没有过敏性鼻炎症状的对照受试者,该研究结果深入了解膳食营养素、肠道微生物组、肠道免疫系统和过敏性鼻炎发展之间的复杂相互作用。

维生素A
关联分析表明,视黄醇、维生素 A、隐黄素(维生素A原的一种)、铜与经年龄和性别调整后的过敏性鼻炎几率相关。
维生素A的主要膳食来源是动物性食物中的视黄醇,水果、蔬菜、蛋黄和黄油中的维生素A类胡萝卜素原。
在该研究人群中,维生素A和视黄醇的膳食摄入水平高度相关(R = 0.96).
维生素A对人体的多种功能至关重要,包括胚胎发育、良好视力、上皮分化和维持免疫功能,特别是在幼稚T细胞分化中。
如果没有维甲酸(注:维甲酸是维生素A的代谢产物),转化生长因子β(TGF-β)促进初始T细胞分化为Th17细胞,后者参与炎症、自身免疫和过敏性疾病。
在视黄酸的存在下,TGF-β帮助肠道树突状细胞介导幼稚T细胞分化为Treg细胞,从而抑制自身免疫反应。
在该研究中检测的类胡萝卜素中,只有隐黄素与过敏性鼻炎相关。
铜 和过敏性鼻炎之间:反向J形关系
铜是一种重要的微量金属,是许多氧化还原酶的辅因子,它参与铁代谢、抗氧化活性、神经肽合成和免疫功能。缺铜和过量铜都会对健康产生不利影响。
在该研究中,观察到铜和过敏性鼻炎之间的反向J形关系。这种反向J形曲线可能分别与铜在适当浓度和高浓度下的抗氧化和促氧化活性有关。
高膳食摄入视黄醇与类胡萝卜素与高丰度普雷沃氏菌的结合,可能对过敏性鼻炎的发展具有保护作用
该研究认为四种营养素(视黄醇、维生素A、隐黄质和铜)和两种肠道菌属(普雷沃氏菌属和大肠杆菌属)与过敏性鼻炎的年龄和性别调整几率相关。
此外,还观察到视黄醇和普雷沃氏菌的组合保护作用,与低视黄醇摄入量和低普雷沃氏菌丰度的受试者相比,高视黄醇摄入和高普雷沃氏菌丰度受试者的年龄和性别调整后的过敏性鼻炎几率低25倍。
绿叶蔬菜、时令水果,含有多种维生素和矿物质,有助于对抗过敏性鼻炎。
绿叶蔬菜包括菠菜、羽衣甘蓝、生菜、芝麻菜等,对于提高免疫系统非常重要。其他还包括黄瓜、大蒜、番茄、红椒、南瓜、红薯、西葫芦、西芹等,都是非常好的食物。水果包括香蕉、柠檬、橙子、蓝莓等。
当然并不是马上有效,这个饮食结构调整需要持续一定的时间。
生姜
生姜的抗炎特性有助于治疗花粉症引起的眼睛、鼻子和喉咙的瘙痒、刺激和炎症。
柑橘类水果
柑橘类水果有助于治疗过敏性鼻炎的症状以及由此引起的上呼吸道刺激。葡萄柚、柠檬、酸橙、橙子、浆果是维生素 C的丰富来源。
姜黄
姜黄抗炎和抗氧化特性,有助于治疗缓解过敏性鼻炎引起的症状。它有助于减少过敏引起的刺激和肿胀。 姜黄可以通过茶、药丸或酊剂服用,甚至可以添加到烹饪时食用的食物中。
西红柿
番茄红素是西红柿中的一种抗氧化化合物,有助于减少过敏引起的炎症。
洋葱
洋葱有抗炎和抗氧化特性,同时富含榭皮素,榭皮素是一种天然抗组胺剂,有助于减轻过敏性鼻炎的症状。
omega-3 脂肪酸
鱼(金枪鱼,三文鱼等)、杏仁、核桃、南瓜和亚麻籽富含的omega-3 脂肪酸的饮食,可以降低儿童和成人发生过敏的风险。
怀孕期间和产后早期摄入 omega-3 脂肪酸的母亲可能会调节免疫系统并降低孩子发生过敏症的风险。
其他饮食建议
易过敏体质尽可能从饮食中去除蛋,乳制品,麸质谷物等容易造成过敏的食品。尽可能减少摄入添加糖和加工食品。
研究发现,一些草药对过敏性鼻炎具有治疗作用,并显示出一些治疗前景。
Septilin
Septilin是一种阿育吠陀草药配方,含有苦皮草、堇叶天花粉、茜草、山茱萸、辣木和甘草,也显示出治疗过敏性鼻炎的巨大潜力。
在一项双盲研究中,190人接受了以上草药组合或标准抗组胺药(扑尔敏)治疗。结果表明,两种治疗方法同样有效。
在这项对32名健康人进行的双盲安慰剂对照试验中,使用Septilin 4周可显著减少皮下注射组胺引起的过敏反应。Septilin也被用作提高免疫力的治疗方法。
在一项针对40名持续性低度感染(如慢性咽痛或鼻窦感染)儿童的双盲安慰剂对照研究中,与安慰剂相比,服用Septilin1个月可显著改善病情。
异株荨麻
一项初步研究表明,异株荨麻 ( Urtica dioica ) 的冻干胶囊可减少患者的打喷嚏和瘙痒。推荐剂量为 600-900 mg TID。荨麻在植物医学中具有治疗咳嗽、肺结核和关节炎的历史用途。体外研究表明它还可能具有抗炎作用。
蓍草(Achillea millefolium)
蓍草是一种多年生草本植物,在欧洲和亚洲很常见。这种多用途草本植物具有抗氧化、健胃、解痉、收敛和透明的特性。传统上用于治疗感冒、流感和发烧,蓍草也可以是对抗过敏性鼻炎的有效药物。
它的抗菌和抗卡他性作用使其成为呼吸系统的理想草药,这种天然的治疗剂还治疗鼻窦炎和粉尘过敏。可以以茶的形式或作为酊剂服用。这是一种强效草本植物,不建议超过连续两周的限度。此外,如果对豚草过敏,应该避免这种草药。
蜂斗菜 ( Petasites hybridus )
在一项开放标签研究中,580名季节性过敏性鼻炎患者服用了50-75 mg BID的蜂斗菜提取物2周(每片含8 mg petasine)。
与基线相比,90%的患者在治疗后,改善了鼻漏、鼻塞、眼睛和鼻子发痒、眼睛发红和皮肤刺激等症状。
蜂斗菜也是一种温和的白三烯抑制剂,在一项研究中发现其与180 mg非索非那定一样有效。但蜂斗菜含有潜在的肝毒性吡咯里啶生物碱(PA),所以应谨慎使用,或者可以使用不含PA的提取物。它属于豚草科,因此对豚草过敏的人也应谨慎使用。
生蜂蜜
生蜂蜜含有很多种活性植物化学物质,有助于体内激素水平恢复正常,有助于构建强大的免疫系统,从而有助于预防过敏性鼻炎。一项随机对照试验表明,食用桦树花粉蜂蜜的过敏患者过敏症状减少了60%,在桦树花粉季节无症状天数增加了一倍。
维生素E
维生素E也可用于治疗过敏性鼻炎,因为它是一种温和的白三烯抑制剂。
一项研究发现,112名患有过敏性鼻炎的成年人在连续10周每天服用800IU维生素E后,鼻部症状明显改善。富含维生素E的饮食也被证明有助于预防过敏性鼻炎的症状,维生素的保护作用随着剂量的增加而增加。建议使用混合生育酚,而不是单独使用α.
注:生育酚,是维生素E的水解产物。天然的生育酚都是D-生育酚(右旋型),它有α、β、ϒ、δ等8种同分异构体,其中以α-生育酚的活性最强。作为抗氧化剂使用的生育酚混合浓缩物,是天然生育酚的各种同分异构体的混合物。
维生素 C
维生素 C具有抗组胺特性,有助于减轻过敏症状。此外,维生素C也有助于增强免疫系统。因此,它有助于预防感染,同时缩短过敏性鼻炎的持续时间。
因此,每天应多吃橙子、灯笼椒、西红柿、柠檬、草莓、豆芽、土豆、奇异果、西兰花、柚子等富含维生素C的食物。
金钗石斛
金钗石斛具有抗炎和免疫活性,近期的一项小鼠研究发现,石虎提取物的治疗抑制了PI3K/AKT/mTOR通路,在门和属水平上恢复了肠道菌群的平衡,并改善了调节T细胞分化,从而有效地扭转了过敏性鼻炎症状。
适度运动
定期锻炼有助于减少过敏反应,适度运动对有过敏症的人无害,过敏体质的人可以按照普通人群的运动建议进行。这包括每周至少 150 分钟的中等强度有氧运动或 75 分钟的高强度运动。
这些活动包括步行、跑步、骑自行车、跑步机锻炼、游泳等。
瑜伽
瑜伽可以通过很多种方式帮助缓解和治愈身体,甚至有助于缓解过敏性鼻炎的症状。瑜伽中的呼吸练习被称为调息,已被用作治疗哮喘的方法。它可能在减轻与过敏性鼻炎相关的症状方面发挥作用。
注意选择正规教师,一开始不要追求动作的完美,重要的是注意调息。
避免触发因素
一旦确定了过敏原,请尽量远离。例如:
洗鼻子
洗鼻液可以帮助清除鼻子中的过敏原。使用生理盐水喷雾有助于减少接触过敏原。
改善不良习惯
与其他过敏性疾病相比,肠道菌群在过敏性鼻炎发病机制中作用的证据仍然较少,但肠道菌群失调与 过敏性鼻炎之间的关系是显而易见的。
肠道微生物群的高度多样性有助于平衡免疫反应,其机制涉及增加代谢物(如短链脂肪酸)和减少炎症介质的产生。
肠道菌群结构异常与过敏性鼻炎的发生率密切相关,这为我们提供了一个新思路,即肠道菌群失调可能是过敏性疾病的重要预测因子。
目前很多研究已经发现益生菌在临床上治疗过敏性疾病的初步效果,可能会减少过敏症状的发生率和持续时间。然而也有一些研究发现,益生菌治疗并没有显着改善临床症状,这可能是因为临床试验包括许多变量,例如伴随疾病、年龄、性别和许多其他因素,还需进一步探索研究。同时,益生菌辅助联合疗法也是一个值得关注的领域。
总的来说,通过各种方式调节肠道微生物群,恢复肠道粘膜屏障,恢复免疫平衡,抑制炎症,有助于改善过敏性鼻炎,肠道菌群或将成为过敏性鼻炎早期干预的新靶点。
注:本账号内容仅作交流参考,不作为诊断及医疗依据。
主要参考文献:
Li J, Fang F, Mei M, Wu D. The gut microbiome and allergic rhinitis; refocusing on the role of probiotics as a treatment option. Eur Arch Otorhinolaryngol. 2022 Oct 14. doi: 10.1007/s00405-022-07694-z. Epub ahead of print. PMID: 36239785.
Zhou MS, Zhang B, Gao ZL, Zheng RP, Marcellin DFHM, Saro A, Pan J, Chu L, Wang TS, Huang JF. Altered diversity and composition of gut microbiota in patients with allergic rhinitis. Microb Pathog. 2021 Dec;161(Pt A):105272. doi: 10.1016/j.micpath.2021.105272. Epub 2021 Nov 2. PMID: 34740809.
Zhu L, Xu F, Wan W, Yu B, Tang L, Yang Y, Du Y, Chen Z, Xu H. Gut microbial characteristics of adult patients with allergy rhinitis. Microb Cell Fact. 2020 Sep 1;19(1):171. doi: 10.1186/s12934-020-01430-0. Erratum in: Microb Cell Fact. 2020 Oct 8;19(1):192. PMID: 32873292; PMCID: PMC7466420.
Kaczynska A, Klosinska M, Chmiel P, Janeczek K, Emeryk A. The Crosstalk between the Gut Microbiota Composition and the Clinical Course of Allergic Rhinitis: The Use of Probiotics, Prebiotics and Bacterial Lysates in the Treatment of Allergic Rhinitis. Nutrients. 2022 Oct 16;14(20):4328. doi: 10.3390/nu14204328. PMID: 36297012; PMCID: PMC9607052.
Liu P, Hu T, Kang C, Liu J, Zhang J, Ran H, Zeng X, Qiu S. Research Advances in the Treatment of Allergic Rhinitis by Probiotics. J Asthma Allergy. 2022 Oct 7;15:1413-1428. doi: 10.2147/JAA.S382978. PMID: 36238950; PMCID: PMC9552798.
Sahoyama Y, Hamazato F, Shiozawa M, Nakagawa T, Suda W, Ogata Y, Hachiya T, Kawakami E, Hattori M. Multiple nutritional and gut microbial factors associated with allergic rhinitis: the Hitachi Health Study. Sci Rep. 2022 Mar 1;12(1):3359. doi: 10.1038/s41598-022-07398-8. PMID: 35233003; PMCID: PMC8888718.
Huang J, Zhang J, Wang X, Jin Z, Zhang P, Su H, Sun X. Effect of Probiotics on Respiratory Tract Allergic Disease and Gut Microbiota. Front Nutr. 2022 Feb 22;9:821900. doi: 10.3389/fnut.2022.821900. PMID: 35295917; PMCID: PMC8920559.
Zoabi Y, Levi-Schaffer F, Eliashar R. Allergic Rhinitis: Pathophysiology and Treatment Focusing on Mast Cells. Biomedicines. 2022 Oct 5;10(10):2486. doi: 10.3390/biomedicines10102486. PMID: 36289748; PMCID: PMC9599528.
Meirlaen L, Levy EI, Vandenplas Y. Prevention and Management with Pro-, Pre and Synbiotics in Children with Asthma and Allergic Rhinitis: A Narrative Review. Nutrients. 2021 Mar 14;13(3):934. doi: 10.3390/nu13030934. PMID: 33799367; PMCID: PMC7999316.

谷禾健康

随着生活水平提升,我国养宠人士逐年增多。数据显示,我国城镇养宠人士达到6844万多人,且仍在不断增长。
其中养猫人群数占比59.5%,养狗人群数占比51.7%,养水族类占比8.3%,养爬行类宠物的占比为5.8%;啮齿类占比4.5%;鸟类占比3.6%。
养宠物,它们的健康绝对是重要的一方面。同时宠物的健康在一定程度上也会影响人们的健康。
胃肠道微生物在健康中起着重要作用。宠物的胃肠道 (GI) 微生物群也是与健康密不可分的代谢活跃器官。肠道微生物群有助于宿主新陈代谢、抵御病原体、影响免疫系统,并通过这些方式直接或间接影响宿主的大部分生理功能。
本文在这里主要介绍猫狗体内的肠道微生物,饮食与肠道微生物的关联以及肠道微生物的作用和对宿主健康的影响,并分析疾病中发生的变化。
在此基础上提出一些有助于恢复健康肠道微生物环境的建议,帮助宠物及主人拥有更好的健康。
本文主要从以下几个方面讲述
●猫狗体内的微生物
●肠道微生物的作用
●肠道菌群与宿主健康
●饮食对猫狗肠道微生物的影响
●宠物身上的微生物对主人的影响
●恢复猫狗肠道健康的方法
什么是微生物群?
微生物群是特定时间特定环境所有微生物有机体的总称,其组成包括非细胞结构的病毒(包括噬菌体)、原核生物中的真细菌和古细菌,以及真核细胞微生物。
微生物群对人类和宠物健康的广泛而深远的影响,胃肠微生物群现在被认为是具有独特代谢能力的器官。胃肠微生物群由位于消化道中的数万亿个细胞组成,从口腔开始,一直延伸到直肠。
微生物群的发育在出生前就开始了,微生物群会影响宿主健康的许多方面,包括生理学、解剖学、行为、繁殖和健康状况。
✦不同部位微生物群落不同
整个胃肠道的微生物群落不同,代表了每个肠段的微环境和生理功能,这已在狗和人类身上得到证实。
例如,对健康家犬的两项研究发现,小肠和大肠的微生物群之间存在显著差异,包括十二指肠中变形杆菌(Proteus)的比例高于结肠或直肠,以及大肠中毛螺菌属(Lachnospira)和瘤胃球菌属(Ruminococcus)的比例高于小肠。
健康狗不同部位的细菌群落组成
Pereira AM,et al.Top Companion Anim Med.2021
★ 主要肠道菌群
一般来说,猫和狗的肠道菌群组成相似。据报道,厚壁菌门(Firmicutes)、拟杆菌门(Bacteroides)、变形菌门(Proteobacteria)、梭杆菌门(Fusobacteria)和放线菌门(Actinobacteria)是猫和狗肠道中的主要微生物。
✦猫狗之间的细菌差异
然而,一些研究注意到猫与狗之间的肠道菌群还是存在某些差异。
• 猫比狗具有更高的α多样性
最近一项研究,基于粪便样本,比较46只猫和192只狗的肠道微生物组的差异,表明猫比狗表现出更高的α多样性。
与猫相比,在犬中增加的细菌门是肠球菌属、梭杆菌属、巨单胞菌属。
而在猫中的细菌门较多,包括另枝菌属(Alistipes)、双歧杆菌属(Bifidobacterium)、肉食杆菌属(Carnobacterium)、柯林斯菌属(Collinsella)、粪球菌属(Coprococcus)、脱硫弧菌属(Desulfovibrio)、普拉梭菌(Faecalibacterium)、颤螺菌属 (Oscillospira)、副乳杆菌属、消化球菌属、消化链球菌属、瘤胃球菌属和萨特氏菌(Sutterella).
在较早的分析中还观察到猫与狗之间的胃肠道微生物组更加多样化,然而,同一项研究也揭示了猫中大多数细菌丰度的个体间差异较小,而具有相同细菌属的猫数量较多。
✦猫狗之间的真菌差异
猫和狗之间的差异在真菌微生物组中也很明显,Nakaseomyces在狗中占主导地位,而酵母菌、曲霉属和青霉属在猫中含量更高。这种差异可能是由于微生物组对不同饮食的适应。
注:与猫的肉食性饮食相比,狗之间更大的个体间多样性可能是更多样化、杂食性饮食的产物。
✦ 狗和人的肠道菌群相似吗?
狗的微生物组比预期更接近人类。
欧洲分子生物学实验室 (EMBL) 研究人员发现,狗的微生物组的基因含量与人类肠道微生物组的相似性高于小鼠、猪的。
研究人员将小鼠、猪和狗微生物组中的基因内容映射到人类肠道基因目录中,发现分别有 20%、33% 和 63% 重叠。

注意
有证据表明,肠道中也有来自其他部位的微生物群。例如,已发现口腔微生物群的成员在患病的胃肠道下部定植。
由于品种、饮食、年龄、生活环境和不同研究分析方法等因素,同一物种的个体菌群比例也可能不同。然而,大多数研究只比较了少量动物,需要更大规模的队列研究来确认环境影响的存在并估计影响大小。
动物体内的肠道菌群数量庞大,类型复杂,与身体形成了一种“互惠互利”的共生关系。它们的生长依赖于身体提供的丰富营养和相对安全环境;同时它们在维护身体健康,促进正常发育等方面发挥着至关重要的作用。
正常菌群是能够在肠道中特定部位“安家落户”,即黏附、定植和繁殖,这个时候,菌群就能够在定植的部位表面形成一层“菌膜屏障”。
•维持微生态平衡状态
这层“菌膜屏障”就像是肠道表面的一层保护伞,对于流经消化道的外源性微生物(包括许多外源性病原体)形成了一种天然的隔绝,通过竞争、消化和分泌各种代谢产物和细菌素等,抵抗外源微生物定植和侵袭。
机体内的正常菌群通过这种拮抗作用,抑制并排斥机体不慎食入的病原菌在肠道的“安家落户”,维持体内微生态的平衡状态,使机体免于感染致病菌。
•提供能量
细菌代谢活动产生对细菌增殖和宿主都有用的能量和底物。主要活动是发酵酒精和不易消化的碳水化合物(淀粉、菊粉、纤维素、半纤维素、果胶和树胶)。
它发生在结肠中,它会导致产生气体和短链脂肪酸、乙酸盐、丙酸盐和丁酸盐,从而为肠上皮和其他组织提供能量。
•支持上皮细胞生长,利于物质吸收
短链脂肪酸合成导致肠道pH值降低,它支持肠上皮细胞的生长、增殖和分化。此外,当短链脂肪酸通过肠道吸收时,它们允许重新吸收Na+或K+离子。
微生物群的另一个重要作用是初级胆汁酸(胆酸和鹅去氧胆酸)和次级胆汁酸(脱氧胆酸和石胆酸)的转化,这对于肠道吸收膳食脂肪和脂溶性维生素至关重要。
共生菌对宿主免疫系统的诱导、塑造和功能具有重要作用,这反过来又对肠道结构的发育和共生菌病原体的鉴定具有重要意义。
微生物在局部和全身设置组织免疫基调的能力需要微生物的强直感应以及免疫系统先天和适应性成分之间的复杂反馈回路。肠黏膜是免疫系统与外部环境之间的界面。
•加快淋巴细胞、免疫球蛋白的增殖
几项研究的结果表明,无菌动物肠粘膜中的淋巴细胞密度较低,血清中的免疫球蛋白含量较低。这些动物接触共生微生物会导致肠道中淋巴细胞和免疫球蛋白以及血清中免疫球蛋白的快速增加。
1型和2型T辅助细胞的发育和调节受细菌的影响,细菌可以通过产生丁酸盐和乙酸盐来抑制NF-kB信号通路,并可以作用于与G蛋白偶联受体。
•诱导炎症介质产生和释放
免疫系统和微生物群之间存在动态关系。具有Toll 样受体的肠黏膜可诱导下降信号并引发炎症介质(细胞因子、吞噬细胞)的产生和释放。
•增强免疫细胞的杀伤力
此外,双歧杆菌(Bifidobacterium)能通过刺激免疫细胞产生重要的细胞因子白介素来促进动物机体内重要的免疫细胞——淋巴细胞的增殖、分化、成熟,增强免疫细胞的对病原体的杀伤力。
在健康条件下,宿主和微生物之间的串扰和交叉调节创造了细菌的稳态平衡,因此胃肠道保持健康并且没有潜在致病细菌的过度生长。
在那种情况下,存在一种共生状态。当这种体内平衡状态被破坏时,就会发生生态失调。在生态失调的情况下,细菌组成不平衡,肠道内的细菌代谢活动或细菌分布发生变化。
生态失调可以总结为以下三点:
减少细菌多样性;有益细菌的损失;病原体的过度生长。
✦肠道微生物失调可能与一些疾病有关
胃肠道微生物组直接或间接影响一系列生理和免疫功能。因此,胃肠道微生物组组成的破坏可能导致有害的后果,例如炎症性肠病、过敏、便秘、口腔疾病(即牙周病)、肥胖、糖尿病和肾脏疾病。
由于肠道微生物群影响胃肠道的环境栖息地,反之亦然,微生物相关的慢性肠病,特别是炎症性肠病的发病率和进展一直是研究的重点。
✦患有炎症性肠病的动物生物多样性降低
患有炎症性肠病的动物中更常见的生态失调的特点是微生物群落多样性普遍降低,尤其是产生短链脂肪酸减少。
•狗中大肠杆菌增加
与健康的狗相比,患有慢性肠病的狗的短链脂肪酸浓度和模式发生了改变,以及粪便微生物群的变化。
一项研究检查了来自患有炎症性肠病的狗的回肠和结肠粘膜微生物群样本,发现它们表现出附着在上皮细胞上或在这些采样部位侵入肠粘膜的肠杆菌科和大肠杆菌增加。
这些发现与最近的另一项研究一致,该研究还发现患有慢性肠病的狗结肠粘膜中的大肠杆菌增加,以及幽门螺杆菌和嗜黏蛋白阿克曼菌减少。
•猫中梭杆菌增多
对于猫,研究表明,与健康猫相比,有炎症性肠病的猫胃肠道微生物群发生了变化。一项研究还发现,患有胃肠道淋巴瘤的猫的回肠和结肠活检组织中梭杆菌属升高。然而,目前尚不清楚这种变化在胃肠道淋巴瘤发展中的任何作用。
有趣的是,最近有文献指出,与人类相比,嗜黏蛋白阿克曼菌在猫和狗的胃肠道中并不丰富,这表明这些细菌在动物粘液的微生物降解中作用还不明确。
✦改变食物可以有效减少肠病症状
两项内镜研究检查了饮食干预对诊断为炎症性的狗的影响。
这些研究发现,饮食的干预改变了位于十二指肠和结肠粘膜层的胃肠道微生物组,在几乎所有患有轻度疾病的狗中,仅改变食物就可以有效减少炎症性肠病的迹象。新型蛋白质和水解蛋白都是有效的,但水解蛋白在减少炎症性肠病症状方面稍微更有效。
此外,营养治疗对犬肠病微生物组的影响研究还分析了水解蛋白饮食对29只慢性肠病犬的微生物组和健康的影响。
参与这项研究的狗从目前的饮食改为治疗性水解蛋白饮食。在这种治疗性饮食2周后,69%的狗经历了慢性肠病的快速缓解,并持续了整个6周的研究。此外,慢性肠病的缓解与微生物群结构的改善和次级胆汁酸水平的增加有关。

•炎症性肠病改善的狗肠道微生物不同
另一项对患有炎症性肠病的狗进行的研究表明,炎症性肠病症状和体征消失的狗的微生物群与没有改善的狗不同。
那些对饮食有反应的狗的嗜胆菌属 (Bilophila)和伯克霍尔德菌(Burkholderia cepacia)占优势,拟杆菌丰富,而那些没有改善的狗的奈瑟菌科更丰富。伯克霍尔德菌尚未显示与狗的慢性肠病有关,拟杆菌可能具有保护性或毒性。
在患有食物敏感型慢性肠病的狗身上进行的一项研究发现,尽管微生物组成(β多样性)没有变化,但在喂食与合生元配对的水解蛋白食物时,细菌丰富度略有增加。
在动物中表现出胃肠道症状的食物过敏经常被误认为是炎症性肠病,因为症状重叠,最明显的是腹泻。
尽管在宠物和人类中开展的研究很少,但已发现在成年人中,花生和坚果过敏与较高的拟杆菌和梭菌、普雷沃氏菌和瘤胃球菌的减少有关。虽然坚果过敏可能与猫和狗不太相关,但这份报告表明微生物组的改变可能与过敏性疾病有关。
✦通过肠道微生物可以治疗过敏
由于过敏本质上是免疫疾病,并且肠道微生物组已被证明具有促炎和抗炎特性,这取决于定植生物体,因此针对胃肠道微生物组可能是治疗全身性过敏的一种合乎逻辑的方法,这已成为多项动物研究的主题。
✦益生菌治疗可以降低过敏反应
在狗中,发现添加益生菌会导致粪便中乙酸盐和丁酸盐浓度增加,以及改善细胞介导的对抗原攻击的免疫反应。然而,益生菌的免疫调节作用尚未在对食物反应性慢性肠病或腹泻的狗的研究中得到一致的证明。
经验证的犬特应性皮炎模型发现,早期接触益生菌(鼠李糖乳杆菌)可显著降低过敏原特异性免疫球蛋白lgE,并在生命的前6个月部分预防特应性皮炎。
这项研究的后续研究表明,在停用益生菌后,这些影响持续了3年。一项对确诊为特应性皮炎的狗进行的随机对照试验报告称,服用益生菌(清酒乳杆菌)2个月可显著降低所有接受益生菌的狗的特应性疾病严重程度。
不过应该指出的是,绝大多数评估使用益生菌治疗全身性过敏的研究都是在人类身上进行的。
猫和狗的便秘患病率没有得到很好的描述,很难量化宠物的排便频率。尽管如此,便秘可能是宠物中相对常见的临床问题,尤其是猫。

✦便秘与肠道微生物的关系还不确定
尚未确定便秘与胃肠道微生物组组成之间的明确联系,包括特定细菌群的丰度,以及肠道微生物群可能影响胃肠道感觉的确切机制和运动功能不清楚。尽管如此,证据表明存在联系,尽管主要来自人类研究,对动物的研究有限。
在一项针对20只猫的研究中,通过PCR分析的有限数量的细菌分类群在有和没有便秘的猫之间没有观察到显著差异。
对胃肠道微生物与便秘之间的机制关系的研究甚至更少,特定细菌类群对胃肠道运动的影响还远未得出结论。
•肠道细菌和产生的代谢物可能会影响肠道运动
一项体外研究表明,梭菌、乳杆菌、脱硫弧菌和甲基杆菌的丰度降低可能通过影响血清素受体来影响胃肠道运动,从而导致慢性便秘的发展。肠道细菌产生的短链脂肪酸,如乙酸盐和丁酸盐,也被认为是改变血清素可用性的一种手段,从而影响肠道的运动和分泌。
此外,某些胃肠道细菌菌株已被证明能从色氨酸中产生血清素。这不仅为治疗便秘开辟了一条新的途径,也为治疗受血清素水平影响的其他疾病开辟了新的途径。
✦纤维素可以调节猫的肠道微生物
对便秘可用的饮食疗法进行了回顾,主要关注纤维。纤维已被证明可以调节猫的肠道微生物群,尽管在对猫科动物便秘的纤维干预的有限研究中,没有进行微生物组分析。
✦益生菌可以改善肠道症状
一项针对便秘猫的干预试验评估了含有多种菌株的益生菌,包括:
Streptococcus thermophilus DSM32245;
Lactobacillus acidophilus DSM32241;
Lactobacillus plantarum DSM32244;
Lactobacillus casei DSM32243;
Lactobacillus helveticus DSM322422;
Lactobacillus brevis DSM27961;
Bifidobacterium lactis DSM32246;
B. lactis DSM32247
观察到猫慢性肠病指数显著下降,粪便评分和粘膜组织学有所改善。治疗后,链球菌和乳杆菌的数量显著增加,双歧杆菌和拟杆菌的数量有增加的趋势。不过这些猫的细菌分类群的上述变化对功能的影响尚未确定。
尽管关于猫和狗的数据有限,但一些综述总结了益生菌对人类便秘有益影响的研究。此外,最近的一项研究评估了益生菌对肠道蠕动的作用机制;第二项研究评估了益生菌对便秘患者自发排便的影响。
总体而言,这些研究支持使用益生菌治疗便秘、减少胃肠道转运时间、增加大便频率、改善大便稠度和改善胃肠道症状。
这些影响的潜在机制集中在肠腔环境、免疫系统、肠神经系统和中枢神经系统之间的相互作用,所有这些都高度相关并影响肠道运动。需要进一步研究益生菌对便秘猫和狗的微生物组的影响。
据报道76%的狗和68%的猫患有牙齿疾病,牙齿疾病是宠物中最常见的疾病。研究表明,临床上健康的狗和猫的口腔微生物群中始终有6种细菌门:放线菌门、拟杆菌门、厚壁菌门、梭杆菌门、变形菌门和螺旋体门。
已经评估了患有和不患有牙周病的猫和狗的口腔微生物群。总体而言,这些研究表明,牙科疾病与更多致病菌株替代与健康相关的菌株有关。
▸ 牙周疾病的猫
例如,在没有牙周病的猫中,研究表明最常见的采样门一直是拟杆菌门、厚壁菌门和变形菌门,而在患有牙周炎或牙龈炎的患者中,据报道致病菌的变异程度很高,但研究之间几乎没有相似之处。
▸ 牙周疾病的狗
另一方面,在没有牙周病的狗中,拟杆菌门、厚壁菌门和变形菌门占主要,尽管据报道放线菌在一些研究中占主导地位。
口腔疾病不同阶段微生物组成有所不同
对患有牙周病的狗的研究发现,根据口腔疾病的具体阶段,微生物组的组成会有所不同。
在一项对患有轻度牙周炎或牙龈炎的狗的研究中,毛螺菌科、梭菌目、消化链球菌科、消化球菌属和犬棒状杆菌属非常普遍。
另一项研究在患有牙周病晚期的狗中鉴定了血链球菌、消化链球菌属、大肠杆菌、奇异变形杆菌、韦荣氏球菌、金黄色葡萄球菌、唾液链球菌、放线菌属和粘性放线菌。牙周病已被证明与狗的全身性疾病有关。
✦饮食与牙周疾病
猫和狗的饮食之间的主要区别是食物是干的还是湿的。由于干粗磨食物的磨蚀性,通常喂食干粮以促进口腔健康。
尽管这些食物已被证明可以减少牙菌斑和牙龈炎,但尚未评估它们对微生物组的影响。

•喂养干粮的口腔微生物更多样化
一项针对只喂食干粮(高度精制、基于谷物的脱水口粮)或湿粮(罐装或新鲜肉类组合)食物的社区猫的研究表明,随着时间的推移,口腔微生物组存在差异,但无法确定是否这些差异影响了牙周病的风险。
然而,喂食干粮的猫的口腔微生物群更加多样化,富含与口腔健康和牙周病相关的细菌(牙龈卟啉单胞菌属和密螺旋体属的丰度更高)。
宠物肥胖是一个严重的问题。根据宠物肥胖预防协会最近的一份报告,60%的猫和56%的狗被归类为超重或肥胖。
肥胖还与多种其他疾病有关,例如糖尿病、骨关节炎、心血管疾病、皮肤病和寿命缩短。有几个因素会使动物易患肥胖,包括胃肠道微生物组、遗传、绝育、活动水平降低以及高脂肪和高能量饮食。
✦肥胖猫狗中的肠道微生物
一些报告发现,肥胖和瘦削的猫狗的胃肠道微生物组的组成不同。具体而言,与瘦狗相比,属于放线菌门和罗氏菌属的细菌在肥胖狗中的数量明显更多。
在猫中,与瘦猫相比,肥胖和超重猫的梭状芽孢杆菌、拟杆菌属和梭杆菌属的丰度较低,但属于肠杆菌科和梭菌簇IV组较高。
✦饮食对不同体重动物的肠道微生物影响不同
此外,多项研究发现,不同的饮食对肥胖动物和瘦动物的胃肠道微生物群有不同的影响。
例如,一项研究表明,与瘦狗相比,超重狗的微生物组对饮食干预更敏感。在4周的高蛋白/低碳水化合物饮食中,与瘦肉/正常狗相比,超重狗的微生物组成发生了显著的变化,这是由于乳酸杆菌、普氏杆菌、链球菌和Turicibacter的丰度变化较大所致。
✦肠道微生物与肥胖有关
肠道微生物组通过其对肠道的直接影响及其对远端器官的间接影响,与肥胖的发展有关。
胆汁酸利于脂质代谢
肠道微生物群已被证明会影响胆汁酸的代谢;细菌代谢产生的游离胆汁酸可以抑制细菌种群的生长,例如乳酸杆菌和双歧杆菌,它们被认为可以预防肥胖。
此外,肠道中的几种细菌(例如梭状芽孢杆菌、海莱蒙梭菌(Clostridium hylemonae)和Clostridium hiranonis)含有与胆汁酸代谢有关的基因。由于胆汁酸被认为有助于肠道激素分泌以及葡萄糖和脂质代谢,因此胃肠道微生物组对胆汁酸的影响也可能影响这些过程。
肠道微生物组破坏导致脂肪堆积
肠道黏膜屏障受到肠道微生物组的影响,这可能导致炎症增加,这是导致体重增加的已知因素。胃肠道微生物组的破坏已被证明会抑制脂蛋白脂肪酶,这会导致脂肪组织和肝脏、胰腺和心脏中的甘油三酯过度沉积。

✦肥胖的治疗
由于饮食、身体活动、遗传、新陈代谢和与体重增加相关的肠道微生物组之间的相互依赖关系,已经提出了许多饮食调整来减轻体重,包括消除高能量密度食物、改变饮食中的大量营养素组成(即高蛋白、高脂肪或高纤维饮食),并添加膳食甘油二酯和益生菌。
然而,目前针对猫和狗的体重管理指南并未考虑肠道微生物组。事实上,已经发现大约一半的肥胖猫和狗会在减肥计划后恢复体重,除非它们继续喂食专门配制的体重管理饮食而不是维持饮食,这表明可能需要持续喂养特定配方的饮食以维持体重减轻。
●狗减肥相关微生物变化
一些研究调查了与减肥相关的微生物群变化。
巨单胞菌和瘤胃球菌可能对体重减轻有负面影响
一项研究分析了18只食用限制性高蛋白/高纤维饮食的肥胖狗,18只狗中的8只也参加了锻炼计划。
两组的体重都有了相当的减轻,增加运动的组和单独饮食的组之间的微生物组没有差异。在这两组中,巨单胞菌的丰度都与体重下降呈负相关,而瘤胃球菌科的种群数量越少,体重下降越快(≥每周1%)。
此外,体重减轻较快的狗的乙酸和丙酸浓度降低。由于巨单胞菌和瘤胃球菌科产生这些酸,这些结果表明,产生这些短链脂肪酸的胃肠道微生物组可能对狗的体重减轻产生负面影响。
低脂肪饮食增加了肠道微生物多样性
一项类似的小型研究表明,17周的限制性低脂肪/高纤维饮食显著增加了6只肥胖比格犬的肠道微生物多样性。
在这项研究结束时,用这种饮食喂养的比格犬的Allobaculum数量也有所增加,梭状芽孢杆菌、乳酸杆菌和Dorea数量有所减少。
●猫的体重减轻与微生物群的关系暂不明确
然而,一项研究评估了中等蛋白质/高纤维饮食对肥胖猫体重和粪便微生物群的影响,结果与上述结果不一致。
八只成年雄性家猫进行了限制性饮食,以实现每周约1.5%体重的减重,持续18周。第18周时,平均体重比基线下降了近20%。尽管体重减轻与放线菌的比例更高和拟杆菌的比例更低相关,但微生物组多样性没有显著差异。
此外,一项类似的研究发现,与17只瘦猫相比,10周的标准减肥饮食对14只肥胖猫的粪便微生物群的影响很小。
因此,需要更多的研究来更好地了解猫的体重减轻与粪便微生物群之间的关系。

糖尿病在猫和狗中的患病率正在增加。虽然狗几乎只患有1型糖尿病,但猫更可能患有2型糖尿病。
各种模型系统中微生物组研究的进展表明,胃肠道微生物组在糖尿病等肠外疾病中发挥作用。改变的肠道微生物群组成与猫和狗的糖尿病的发展有关。
•1型糖尿病的狗肠道菌群失调
例如,最近的一项研究表明,患有自然发生的1型糖尿病的狗肠道菌群失调,粪便中浓度发生变化,表现出与患有2型糖尿病的人类相似的模式。
•糖尿病的猫肠道微生物多样性降低
此外,与同龄的健康猫相比,患有糖尿病的猫的肠道微生物多样性显著降低,产生丁酸盐的细菌也减少了。
✦药物通过微生物介导治疗糖尿病
用于治疗糖尿病的药物已被证明会影响胃肠道微生物组。在一项研究中,抗糖尿病药物二甲双胍通过显著提高拟杆菌门的丰度来改变胃肠道微生物组。
其他用于治疗糖尿病的药物(如阿卡波糖和二甲双胍)的功效也已被证明是通过微生物组介导的。基于微生物组的方法可能需要个性化,以有效管理与代谢相关的疾病,例如糖尿病,以解决微生物组组成和功能的个体间差异。
✦益生菌能改善糖尿病
•减少炎症反应
支持在糖尿病中使用益生菌的证据表明,益生菌可以减少炎症反应和氧化应激,增加胃肠道上皮细胞内粘附蛋白的表达,从而降低肠道通透性。已经提出这些机制导致胰岛素敏感性增加和自身免疫反应减少。
•降低发病率
一项针对256名女性的研究发现,妊娠早期的益生菌干预降低了妊娠糖尿病的发病率。含有双歧杆菌的益生菌也被证明可以改善糖尿病小鼠模型的葡萄糖耐量。
虽然不知道对猫和狗是否可行,但2型糖尿病或高血压患者严格遵循以高碳水化合物和高纤维植物为基础的素食饮食,其血红蛋白A1c降低,空腹和餐后血糖水平有所改善。这些影响还伴随着胃肠道微生物组中拟杆菌门和厚壁菌门比例的降低。
小结
由于大量营养素影响胃肠道微生物的组成,而微生物群的相关功能产物会影响宿主健康,因此通过营养来管理猫和狗的糖尿病是合乎逻辑的。
尽管目前数据有限,但正在进行几项研究以进一步研究益生元对代谢疾病的影响。总之,显然需要更好地了解不同的营养干预措施如何影响糖尿病中的胃肠道微生物组成和功能,这将为开发更有效的糖尿病营养干预措施提供信息。
慢性肾脏病 (CKD) 是猫和狗最常见的疾病之一,但迄今为止,关于这些物种的胃肠道微生物和肾脏疾病的研究很少。
✦慢性肾病的猫微生物丰富性和多样性降低
最近的一项研究表明,与健康猫相比,患有慢性肾脏病的猫的粪便微生物组的丰富性和多样性降低,这与先前对患有慢性肾脏病的人类肠道微生物的研究一致。
确定生态失调与肾脏疾病之间因果关系的研究正在进行中。潜在的微生物组成被认为会影响个体对慢性肾脏病的易感性,有证据支持在猫和狗中发现的这种联系。例如,据报道患有严重牙周病的动物患肾病的风险增加。
胃肠道转运时间慢、蛋白质同化受损和膳食纤维消耗减少等因素也与肾病患者的生物失调有关。
✦使用益生菌可能对减少肾结石有益
肾结石是猫和狗中常见的一种疾病,平均会使猫的寿命缩短约3年。动物的肾结石和膀胱结石大部分由草酸钙或磷酸铵镁(鸟粪石)组成,结石的形成是一个复杂的过程,涉及遗传和环境因素。
人类和动物的研究表明,草酸杆菌和乳酸杆菌通过草酸盐的降解防止结石形成。需要更多研究胃肠道微生物对猫和狗肾脏功能和肾脏疾病的影响,以及营养对这些微生物群的影响。
如前所述,猫和狗的肠道微生物群组成通常相似,但也有一些差异。肠道微生物组与宿主之间存在复杂的关系,这受到猫与狗的独特解剖学和生理学的影响。
关于猫和狗之间的消化和生理差异如何影响微生物组的证据是有限的。可以通过研究食物如何通过产生微生物后生元来影响每个物种的健康。
后生元——后生元是益生菌经加工处理后的益生菌代谢物成分统称,包括菌体与代谢产物。
食品、肠道微生物群和宿主之间的三方相互作用
Wernimont SM,et al.Front Microbiol.2020
宠物食品、胃肠道微生物群和宿主之间的三方相互作用分8个阶段。
(1) 摄入:狗和猫以提供给它们的宠物食品的形式摄入碳水化合物、蛋白质和脂质等营养物质。
(2) 营养素:宠物食品中的营养素进入胃肠道,可供宿主和微生物组消化。
(3)宿主消化:宿主的消化包括糖解、蛋白水解和脂肪分解等过程,释放出单糖和双糖、氨基酸和脂肪酸。
(4)宿主吸收:通过宿主消化产生的单糖和双糖、氨基酸和脂肪酸可以被宿主细胞吸收利用。
(5) 微生物消化:未被宿主消化或吸收的营养物质可通过糖解、蛋白水解和脂肪分解被微生物组消化,释放出单糖和二糖、氨基酸和脂肪酸。
(6) 微生物吸收:微生物消化产生的单糖和双糖、氨基酸和脂肪酸可以被微生物组吸收和利用。
(7) 微生物发酵:超过宿主和微生物吸收能力的营养物质被绕过到下消化道,在那里它们可以进行微生物发酵以产生可以在胃肠道内局部影响宿主健康的后生元。
(8) 宿主吸收:微生物衍生的后生元也可以被宿主吸收,从而影响胃肠道以外部位的宿主健康。
当提供多种口味相似但营养素含量不同的食物,并允许通过在食物中自由选择喂养来自行选择常量营养素摄入量时,这导致在不同物种之间观察到显著不同的后生元。
例如,在28天的自由选择喂养期后,狗的循环血浆微生物代谢物均未发生变化,而猫的38种代谢物浓度中有16种发生了变化。
✦家猫的身体结构
家猫是一种专性食肉动物,因此从动物蛋白质的消耗中获取能量。猫科动物基因组高度保守区域的分析和饮食适应直系基因的评估揭示了淀粉和蔗糖代谢途径中基因家族的缺失,反映了它们的肉食性。
家猫特有的代谢和生理特性
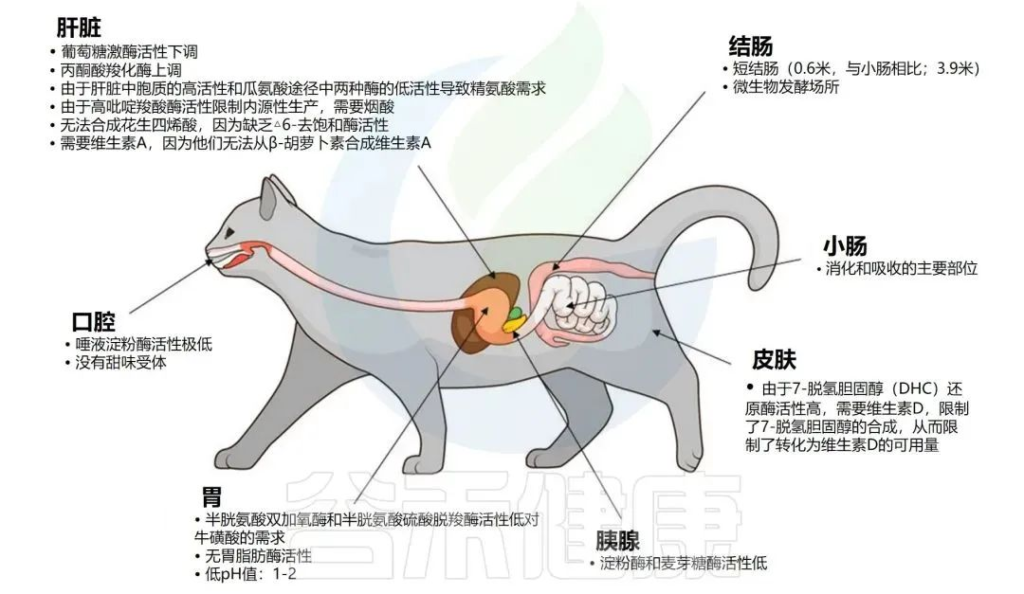
Butowski CF,et al.N Z Vet J.2022
✦家狗的身体结构
相比之下,狗被归类为兼性食肉动物,在营养上通常被视为杂食动物,因为它们消耗和利用植物和动物材料。通过驯化,狗保留了许多祖先特征,尽管已经观察到与人类文明一起适应碳水化合物含量较高的饮食。
家狗特有的代谢和生理特征
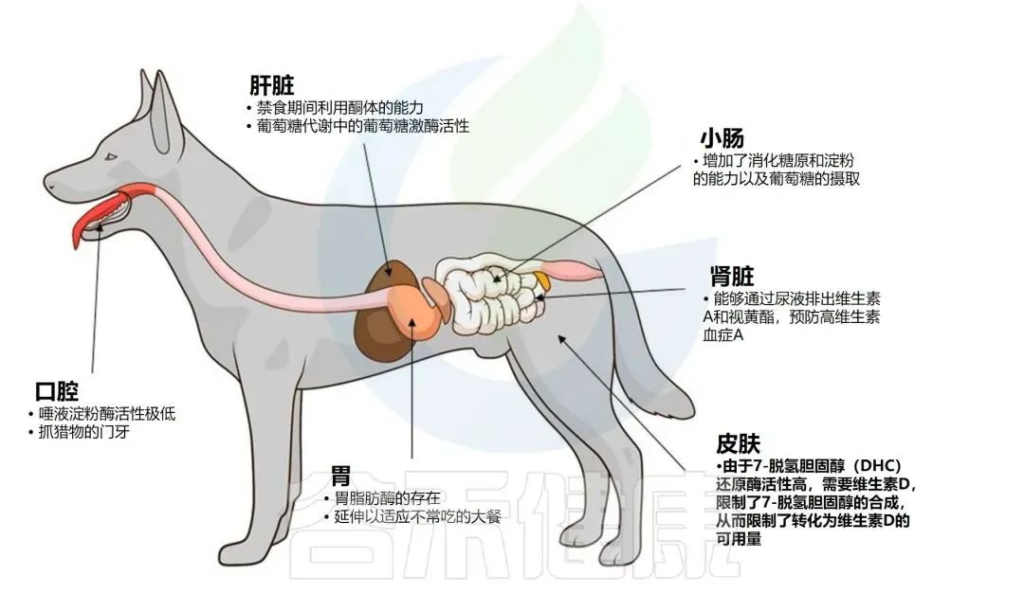
Butowski CF,et al.N Z Vet J.2022
✦不同的身体结构导致营养代谢不同
猫和狗之间的这些差异,无论是在首选的常量营养素摄入量还是在微生物组对选定的常量营养素摄入量的代谢反应方面,都为优化猫和狗的营养摄入带来了独特的挑战和益处。
▸
最近,低加工或生的高动物蛋白(肉类)饮食越来越受欢迎,更“天然”的宠物食品的需求,这些食品反映了动物的肉食性。这些宠物食品通常以生(新鲜或冷冻)、空气压缩或冻干形式出售。
这些高肉粮通常含有高粗蛋白,含有中高水平的粗脂肪,碳水化合物含量最低。从营养充足性的角度来看,生肉饮食可以制造完整和平衡的饮食。
✦狗吃生食的影响
一些研究评估了以肉类为基础的生食对健康狗肠道微生物的影响。与对照饮食相比,以肉类为基础的生食通常在常量营养素含量方面存在很大差异,蛋白质含量更高,碳水化合物和纤维含量更低。
不同饮食对狗粪便微生物组的影响

Pilla R,et al.Vet Clin North Am Small Anim Pract.2021
•厚壁菌和拟杆菌总体下降
喂食生食的狗的厚壁菌门和拟杆菌门总体下降。大多数细菌减少与膳食中碳水化合物产生短链脂肪酸相关,表明由于摄入量减少导致碳水化合物发酵减少。变形杆菌门、梭杆菌门和与蛋白质相关的属大量增加。
•微生物多样性增加
一项对6只狗喂食生食超过1年的研究发现,微生物的多样性增加 ,产气荚膜梭菌和梭杆菌的丰度增加,这两种细菌都可以从蛋白质中产生丁酸盐,表明对饮食的适应。
•梭状芽胞杆菌与蛋白质消化有关
尽管梭状芽胞杆菌科可能与胃肠道疾病有关,但有人认为,当给狗喂食富含蛋白质的饮食时,梭状芽胞杆菌的增加可能不会损害它们的健康,但与蛋白质消化有关。
此外,还发现梭状芽孢杆菌科与蛋白质消化率和更坚硬的粪便评分呈正相关,与粪便蛋白质含量负相关(即,梭状芽胞杆菌科越多,粪便中未消化的蛋白质越少)和粪便排出量越少。
在猫中,罐头饮食是一种额外的高蛋白替代品,通常单独喂养或与膨化饮食结合喂养。研究在猫身上使用潮湿的食物,它们的摄入会导致饮水量增加,减少自愿能量摄入量,并降低尿液比重,这可能对某些健康状况有益。
不同饮食对猫粪便微生物组的影响


Pilla R,et al.Vet Clin North Am Small Anim Pract.2021
研究评估了断奶到高蛋白/低碳水饮食小猫中的微生物,研究之间存在一定的一致性。
•高蛋白/低碳水饮食增加了物种多样性
有趣的是,高蛋白/低碳水饮食增加了物种多样性,在高蛋白/低碳水喂养的小猫中增加5个属是已知的丁酸盐生产者:梭状芽胞杆菌和真杆菌可以通过从碳水化合物产生丁酸盐,或通过从蛋白质产生丁酸盐,而Faecalibacterium、Ruminococcus和Blautia也是丁酸盐的生产者。
两种饮食方式的小猫之间的差异影响了代谢途径,包括与氨基酸生物合成和代谢相关的途径,表明蛋白质:碳水化合物的比例对微生物组功能有显著影响。然而,这种代谢物差异对整体健康的影响仍然未知。
小结
虽然饮食可以显著改变微生物的组成,并导致代谢途径和代谢物产生的变化,但这些变化通常比伴随疾病的变化要小得多。
在患病动物中,特别是那些患有胃肠道疾病(例如慢性肠病)的动物中,微生物组的多样性迅速降低,许多核心物种,如C.hiranonis、梭杆菌属和普拉梭菌减少。
养宠物益处也有很多,他可以让老人的心情更加舒畅,预防心绪管系统疾病,而且还在无形中增加运动量,起到强身健体的作用;也可能传播疾病。
与养狗相关的菌群:
养狗与室内灰尘中的细菌丰富度和多样性呈正相关。
最近关于宠物和人类微生物相互作用的研究表明,在家养狗会增加同居成年人之间的共同皮肤微生物群。
✦降低哮喘风险
研究表明,婴儿接触农场动物与降低日后发生哮喘的风险有关。最后,已证明围产期宠物暴露会影响肠道微生物群的组成差异,并保护儿童免受早期喘息。
许多科学家认为,婴儿和儿童需要接触无害的微生物,以“训练”他们正在发育的免疫系统来区分自身分子和外来分子,而不是过度反应并最终损害自身组织,与狗同住有助于这种免疫系统训练。
✦ 心血管疾病患者中,养宠物患者代谢综合征和肥胖风险小
一项研究分析了162 名冠心病患者的肠道微生物群,养宠物 ( n = 83) ,不养宠物 ( n = 79).
养宠物的患者患代谢综合征 (MetS) (OR = 0.462) 和肥胖症 (OR = 0.519) 的风险较低,养宠物的患者中发现了沙雷氏菌属Serratia和粪球菌属的优势,不养宠物的患者中瘤胃球菌属、肠杆菌科和Anaerotruncus的未知属占优势。
养宠物可能通过塑造肠道菌群成为预防代谢综合征的保护因素。
最近人们还发现了人畜共患的现象,并且可以在人与动物关系中的微生物交换中进行干预。
✦引起皮肤真菌病
皮肤真菌病(癣)由多种皮肤真菌引起,可感染人类和动物。感染源包括人类、家畜、宠物和野生动物(主要是兔子和啮齿动物)。
狗或猫可能表现出临床症状,由于主人经常接触宠物,会导致真菌病在宠物与家庭成员之间传染。
由于遗传因素、先前存在的皮肤病(如过敏性皮炎)或免疫功能受损状态,一些人更容易患上皮肤真菌病。
胃肠道微生物
胃肠道疾病是宠物与其主人比较常见的疾病。此外,沙门氏菌(Salmonella)和弯曲杆菌(Campylobacter)等特定细菌性肠道病原体是有充分记录的人畜共患病,对宠物与其主人都会带来健康影响。
注:感染沙门氏菌或弯曲杆菌会引起急性肠炎,主要症状有腹泻、发热、腹痛和血便,还伴有乏力、肌肉酸痛、视觉模糊、躁动不安和嗜睡。
狗还可能藏匿并脱落原生动物寄生虫蓝氏贾第虫的囊肿,或者携带有蛔虫。两者都是导致人类感染的常见潜在人畜共患疾病。
注意:感染蓝氏贾第虫会出现上腹部不适,有时伴有腹痛、腹鸣、胃肠胀气及慢性腹泻粪内带有粘液,量多并有臭味,重者可伴有脂肪。此外,尚可有厌食、低热、体重减轻、失眠、头痛及多汗等症状。但不发生贫血,亦无舌炎、口炎、手足抽搐等热带口炎。
其他微生物
✦巴尔通体病
巴尔通体病是一种媒介传播的人畜共患疾病,在世界范围内都有分布,可以感染人类和大量哺乳动物,包括小型伴侣动物(猫和狗)。
至少有十三种Bartonella已被确认为人类疾病的病原体。主要有B. clarridgeiae、B. elizabethae、B . henselae 、 B . koehlerae、B. quintana、B. rochalimae和B. vinsonii berkhoffii。
•家猫引起的巴尔通体病
猫是B. henselae的主要但不是唯一的宿主,B. henselae是人类猫抓病的病原体。
家猫也是B.clarridgeiae和B.koehlerae的主要宿主。人们认为受感染的猫很少会出现临床症状。然而,在受感染的猫中经常可以检测到慢性复发性菌血症,而复发性菌血症的潜在长期后果尚不清楚。
猫也可能感染B. bovis, 但家猫在这种巴尔通体的流行病学中的作用尚未明确。
•犬类引起的巴尔通体病
狗也可能是B. henselae的宿主,犬科动物被认为是B. vinsonii berkhoffii的主要宿主,可引起狗和人类的心内膜炎。
加利福尼亚州的土狼 等野生犬科动物和潜在的家犬已被描述为B. vinsonii berkhoffii的主要储存宿主,因为这些动物也会发生长期菌血症。
注:汉氏巴尔通体属最常感染宠物狗,普通狗也会被感染。
随着年龄或药物的影响,健康宠物的肠道微生物群动态平衡可能会被破坏,从而引发各种疾病。
了解宠物的肠道健康状况,最好的方法是进行肠道微生物检测,直观了解微生物的种类及数量。将得到的检测结果与同年龄、同品种的健康犬进行比较,可以比较全面地了解宠物的肠道微生物状况,来更好地进行对应的治疗。
在谷禾肠道菌群检测报告中,就有这样的特殊案例,来自宠物的肠道菌群。
报告显示,其样本菌群构成非常单一,实际测序深度很高,达到10万,但仅检出167种菌,绝大部分是大肠杆菌。
下面的表是根据人的菌群结果评估的,可以看到构成多样性非常低。
下面是主要菌门和属还有种的构成,种部分列出了注释有菌名称的丰度大于0.1%以上的菌。
下图是菌属构成表:
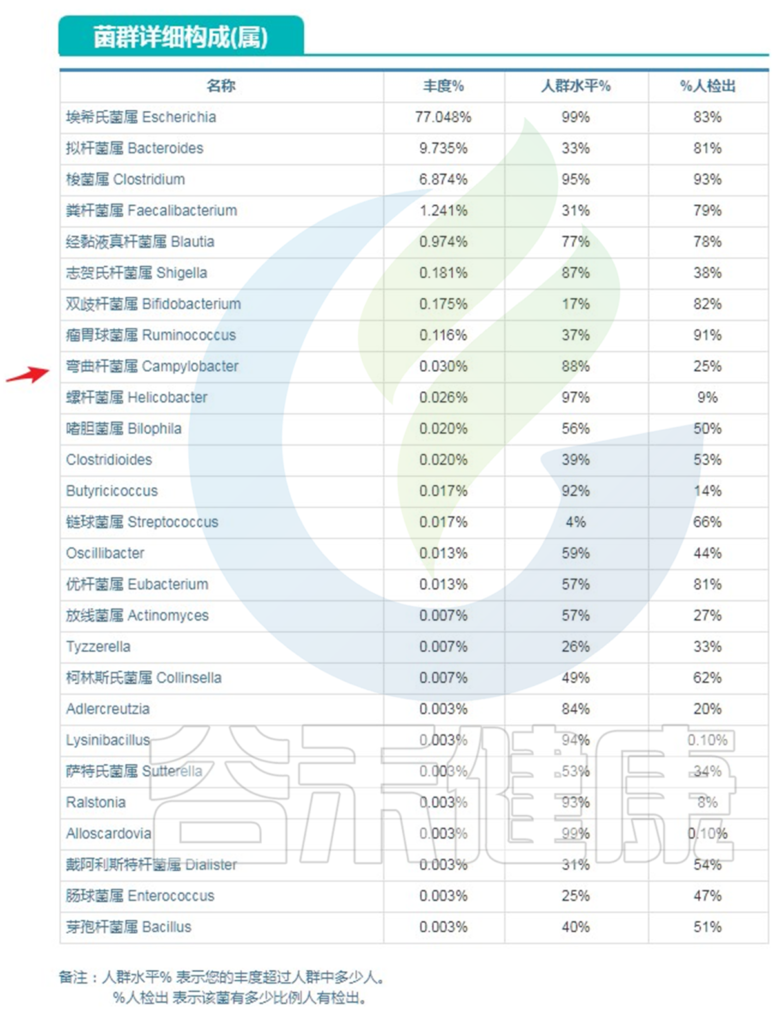
报告显示,菌属构成中弯曲杆菌占比较高。
除此之外,其他的病原和机会致病菌主要检出了大肠杆菌,占比77%,属于严重超标,空肠弯曲杆菌,产气夹膜菌和痢疾志贺氏菌都有超标:
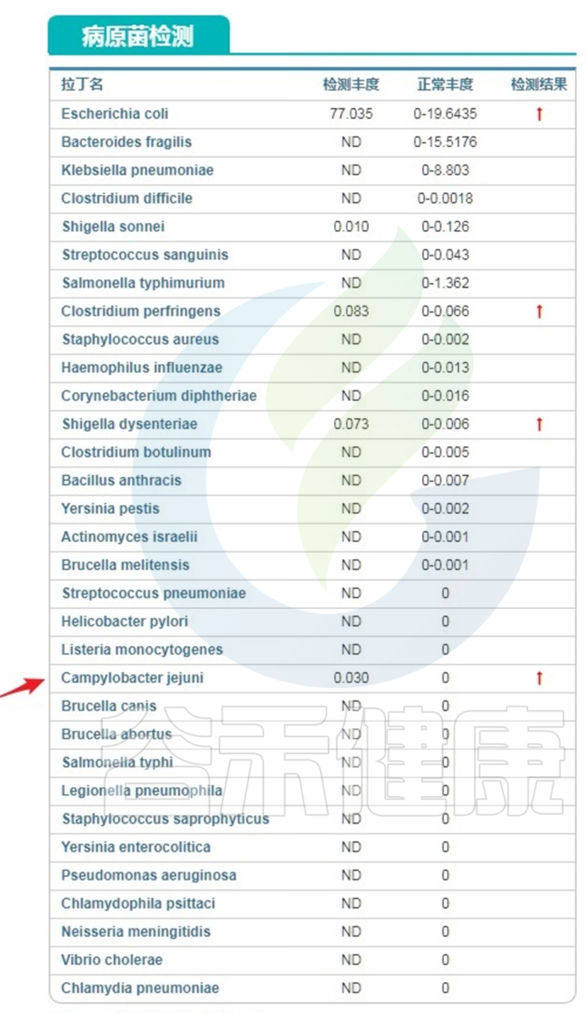
编辑
注:空肠弯曲菌(上图中红色箭头指向菌Campylobacter jejuni),有内毒素能侵袭小肠和大肠黏膜引起急性肠炎。
经过与送检者沟通后,我们了解的情况如下:
主人反映该宠物猫有腹泻,其有长期腹泻情况,因此送检了其本人和养的宠物猫的粪便样本做肠道菌群检测,了解菌群构成,找出腹泻原因,以便后续治疗。
了解猫狗的肠道微生物状况后,需要进行相应的治疗来帮它们恢复健康,谷禾在这里罗列了一些常见的治疗方式。
在疾病状态期间,所应用的疗法旨在改变微生物群落。
蛋白质、碳水化合物是大部分宠物必需的营养物质,是促进机体发生生长的重要营养素。宠物肠道中丰富的微生物菌群生长都离不开碳水化合物,前面也有提到一些饮食对疾病的影响作用。因此,合理控制宠物蛋白质、碳水化合物的摄入是维持肠道健康的关键。

•需要根据不同的宠物制定相应的饮食
不同年龄段的宠物对脂肪的吸收能力不同。老年犬猫由于肠道消化能力逐渐退化,不能较好地吸收脂肪。适量的功能性脂肪酸,如Omega-3脂肪酸可以增强宠物机体免疫力,预防炎症,减轻其胃肠道疾病的发生。
存在关于无谷物狗粮的争论。有些兽医认为不应该用任何谷物喂养宠物,有些人则说它可以适量喂养。常见的谷物包括大米、燕麦、玉米和小麦。
不建议吃的原因包括体重增加、胃肠道炎症增加、过敏等。如果狗不耐受谷物,可能会出现皮肤发痒、呕吐、胃部不适、脱毛、腹泻、感染和胀气。
换句话说,如果出现上述症状,可以尝试一下无谷物食物并监测症状是否有所改善。
骨汤含有多种有益营养素,但与肠道健康最相关的是胶原蛋白。胶原蛋白是一种结缔组织,有助于维持包括肠道和皮肤在内的身体器官的结构。
狗狗的肠道内部衬有一层叫肠粘膜的组织。粘膜的作用是防止食物分子和细菌等危险物质从肠道进入血液。
然而,粘膜可能会受损,导致肠道变得可渗透。换句话说,像细菌这样的物质可以通过。这就是所谓的“肠漏”。
通过给狗狗吃富含胶原蛋白的食物,比如骨头汤,可以加强粘膜中的结缔组织,从而减少肠漏程度。
宠物食品制造商在其产品中添加的一些成分会对狗的肠道菌群和整体健康产生负面影响。人工色素和抗氧化剂等食品添加剂减少肠道细菌的数量。
最好能阅读食物的配料表。
除了饮食之外,益生菌、益生元的施用也会影响和改变微生物群的组成。
益生菌和益生菌的使用在人类医学中广泛传播,以保持或恢复健康状况。
✦益生元治疗
▸ 益生元
根据2015年给出的第一个定义,它们是“一种不易消化的化合物,通过肠道微生物的代谢,调节肠道微生物群的组成或活性,从而赋予对宿主有益的生理影响”。
猫和狗接受益生元的治疗效果

Mondo E,et al.Open Vet J.2019
一些研究报告了在宠物饮食中添加益生元的好处。事实上,它们能调节肠道微生物群并保护动物免受肠道感染。
•益生元促进炎症性肠病缓解
几项研究评估了益生元治疗对诊断为炎症性肠病的狗的影响。这些分析的结果表明,多菌株益生元治疗促进了诊断为炎症性肠病的狗的临床缓解,并与其他一些益处相关,包括抗炎和抗增殖作用、增加紧密连接蛋白表达和上调多胺水平。
•益生元治疗改变肠病中微生物组成
关于微生物组的组成,用益生元治疗的炎症性肠病狗的粪杆菌属和乳酸杆菌显著增加。然而,与那些接受标准治疗的人相比,这些结果在研究之间并不一致。除了对炎症性肠病的有益作用外,多项双盲、安慰剂对照研究表明,益生元给药还可以减少猫和狗的腹泻。
✦狗使用益生元的疗效
有一些关于益生元在国内犬类饮食中的使用研究发现,在狗中,摄入1.5%的菊粉可以降低粪便的pH值并增加双歧杆菌的数量。
使用16S rRNA 测序表明,喂食相对少量膳食纤维的狗会改变肠道微生物群的结构,增加厚壁菌门的密度并减少梭杆菌的密度。另一项研究强调了低聚果糖的膳食补充剂如何诱导有益效果,例如双歧杆菌的生长,并且它提高了狗整个胃肠道中几种矿物质的消化率。
✦猫使用益生元的疗效
很少有关于猫科动物营养和益生元使用的研究。两项研究描述了猫饮食中典型的高蛋白饮食摄入主要诱导粪便梭状芽孢杆菌的生长。
发现在猫科动物饮食中添加低聚果糖会增加双歧杆菌浓度并减少大肠杆菌数量。同一项研究表明,在猫营养品中添加果胶提高了产气荚膜梭菌(Clostridium perfringens)和乳酸杆菌的浓度。
✦益生菌治疗
▸ 益生菌
数千年前,人类发现了发酵食品带来的好处。因此,益生菌的使用比益生元更古老。它们被定义为“当施用足够量时,可以为宿主带来健康益处的活微生物”。
无论是对人类还是宠物,益生菌对宿主健康都有许多有益的影响,尤其是在免疫系统的调节和压力状态下。益生菌在牲畜中的使用已广泛传播,而在宠物营养中的使用仍在发展中。
益生菌治疗效果的研究总结

Mondo E,et al.Open Vet J.2019
•益生菌促进了T细胞表达
对患有慢性肠病的狗进行了体外研究。这项研究证实了含有三种不同乳酸杆菌菌株的益生菌混合物对细胞因子表达的积极作用,主要是通过调节T细胞。
发现益生菌的施用促进了T细胞表达的增强。在这项研究中,为患有炎症性肠病的狗配制了一种类似于人类VSL#3的益生菌混合物。数据强调了T细胞靶点的增加、粪杆菌数量的减少以及生态失调的恢复。
从断奶到1岁,幼犬的饮食通常通过添加益生菌来补充。事实上,已经证明粪肠球菌在肠粘膜水平和全身水平都存在辅助作用。这些影响可能与断奶期间保护性免疫反应的改善有关。
当饮食改变不起作用时,患有慢性肠病的狗和猫会接受抗生素治疗。最常用的分子是甲硝唑和泰乐菌素。甲硝唑作用于细菌和原生动物。通常,它同时用于营养治疗和饮食改变,因此很难知道其真正的效果。
泰乐菌素用于治疗对泰乐菌素有反应的慢性腹泻,这通常会影响成年犬。许多研究强调了它的效率,但其作用机制仍然未知。
恩诺沙星是另一种用于肠病的抗生素。它是一种氟喹诺酮,可用于治疗肉芽肿性结肠炎。
●抗生素同时还会减少有益菌
需要注意的是,使用抗生素治疗某些疾病存在禁忌症。事实上,大量使用抗生素可能会减少有益菌的数量,促进潜在病原体数量的增加,并促进抗菌素耐药现象的发生。
一些研究人员表明,抗生素实际上会改变微生物组成,从而降低细菌多样性,因此它们会导致生态失调的发生。在过去的几年中,抗菌素耐药性的现象不断增加,并具有重要意义。人类与宠物的密切同居会导致抗菌素耐药性转移到对人类也有影响的细菌。
最近,已开发出一种新方法,该方法通过引入健康的细菌菌群来恢复结肠菌群。它被命名为粪便微生物群移植 (FMT)。
粪菌移植是一种医学非药物实验治疗,旨在恢复微生物多样性。它包括将粪便菌群从健康供体移植到受胃肠道疾病影响的患者中。
•粪菌移植后肠道生态失调得到改善
在人类医学中,该方法用于治疗艰难梭菌感染,有效率为87%–90%,并用于治疗炎症性肠病。
粪菌移植在兽医学中很有前景,但是应用的研究还很少。这种治疗方法已用于受胃肠道疾病影响的狗,如炎症性肠病和产气荚膜梭菌感染。
最近的一份病例报告描述了粪菌移植用于治疗一只患有难治性炎症性肠病的狗和一只患有无反应性慢性肠病的猫。在这两种情况下,粪菌移植后24小时内粪便稠度得到改善。
即使粪菌移植似乎是治疗生态失调的有效疗法,但仍需要进行更多的临床研究以更好地了解其机制和接受这些输注的患者的潜在风险。如今,只有有限的数据可用。
噬菌体是一种能够侵染细菌的病毒,是生物圈中最丰富的物种。
●噬菌体可以裂解消灭有害菌
噬菌体通过尾丝蛋白与宿主菌表面受体特异性结合侵染细菌使其裂解,精准消灭有害菌,不影响有益菌。30分钟内可杀灭99.9%的宿主菌,且不受细菌耐药性限制。面对细菌耐药、抗生素残留等问题,噬菌体作为天然的细菌杀手,是防治细菌性疾病的最佳选择。
调节肠道菌群
噬菌体一经发现,就被人类作为治疗细菌性疾病的利器之一。有研究表明,噬菌体可以裂解肠道中的有害菌例如沙门氏菌和大肠杆菌,降低了肠道有害菌数量,有益于肠道有益菌(如乳酸菌类)的繁殖和生长,起到了调节肠道菌群的作用。
建议
噬菌体能显著降低肠道内有害菌数量,提高肠道有益菌比例;并且有利于免疫器官的发育和体液免疫功能的提高。与抗生素相比,噬菌体在增强肠道活性,降低腹泻率方面,与抗生素差异不大,可以作为替代抗生素的候选产品之一。
研究表明,压力会对肠道微生物群的健康产生负面影响。当肠道微生物组受损时,它会导致压力增加,从而导致周期性模式。
压力会引起体内激素的变化,从而引起肠道微生物组的变化。特别是,压力会触发皮质醇激素的释放。皮质醇对身体有多种负面影响,包括血压升高和肠道健康受损。
狗的压力可以由多种因素引发,包括:
注意狗狗的压力迹象和症状。一些可能表示狗有压力的迹象包括:
可以为狗提供舒适的环境,以最大程度地减少压力。如果狗生病了,给它吃药,吃它最喜欢的食物,并给她一个舒适的地方睡觉。这会使狗平静下来,有助于减轻它的一些压力。
让狗狗进行体育锻炼
让你家狗狗参加各种体育锻炼,如散步、跑步、玩耍等。
研究表明,体育锻炼通过刺激体内内啡肽的释放来减轻压力。内啡肽是中枢神经系统释放的神经递质。它们的主要作用是减轻疼痛和增强快感。
身体也会在其他愉快的活动中释放内啡肽,体育活动对健康很重要。
定期对宠物进行身体检查
应该至少每年带狗狗去看一次兽医。兽医有专业知识来识别可能错过的狗的潜在健康问题。
让你的狗定期接受兽医检查可以降低疾病未被诊断的风险。如果不进行治疗,肠道疾病往往会加重,因为消化系统每天工作多次。
如果狗身体健康,兽医每年看一次就足够了。
如果你的狗患有髋关节发育不良或糖尿病等慢性疾病,应该多看兽医。
此外,随着肠道菌群检测技术的不断成熟,不久的将来通过宠物肠道菌群检测也能发现一些疾病风险,不用让宝贝宠物承受各类监测设备的心理困扰,简单便捷。
人体的研究表明肠道菌群影响并反映着身体的健康,同样肠道微生物群也对猫狗以及其他哺乳动物的健康至关重要。
对于猫狗的肠道菌群仍然有很多未知和亟待发掘的意义,有望成为一种非常有价值的检测和干预渠道。谷禾欢迎更多相关领域的合作伙伴共同推进和完善猫狗相关肠道菌群的研究和应用。
主要参考文献:
Pilla R, Suchodolski JS. The Gut Microbiome of Dogs and Cats, and the Influence of Diet. Vet Clin North Am Small Anim Pract. 2021 May;51(3):605-621. doi: 10.1016/j.cvsm.2021.01.002. Epub 2021 Feb 27. PMID: 33653538.
Wernimont SM, Radosevich J, Jackson MI, Ephraim E, Badri DV, MacLeay JM, Jewell DE, Suchodolski JS. The Effects of Nutrition on the Gastrointestinal Microbiome of Cats and Dogs: Impact on Health and Disease. Front Microbiol. 2020 Jun 25;11:1266. doi: 10.3389/fmicb.2020.01266. PMID: 32670224;PMCID: PMC7329990.
Mondo E, Marliani G, Accorsi PA, Cocchi M, Di Leone A. Role of gut microbiota in dog and cat’s health and diseases. Open Vet J. 2019 Oct;9(3):253-258. doi: 10.4314/ovj.v9i3.10. Epub 2019 Sep 1. PMID:31998619; PMCID: PMC6794400.
Pilla R, Suchodolski JS. The Role of the Canine Gut Microbiome and Metabolome in Health and Gastrointestinal Disease. Front Vet Sci. 2020 Jan 14;6:498. doi: 10.3389/fvets.2019.00498. PMID: 31993446; PMCID: PMC6971114.
Pereira AM, Clemente A. Dogs’ Microbiome From Tip to Toe. Top Companion Anim Med. 2021 Nov;45:100584. doi: 10.1016/j.tcam.2021.100584. Epub 2021 Sep 10. PMID: 34509665.
Butowski CF, Moon CD, Thomas DG, Young W, Bermingham EN. The effects of raw-meat diets on the gastrointestinal microbiota of the cat and dog: a review. N Z Vet J. 2022 Jan;70(1):1-9. doi: 10.1080/00480169.2021.1975586. Epub 2021 Sep 19. PMID: 34463606.

谷禾健康
肠道菌群 & 性激素
青春期是生命的一个关键阶段,与性成熟相关的生理变化有关,是一个受多种内分泌和遗传控制调控的复杂过程。
青春期发育可以在适当的时候,早熟或延迟。
青春期发育异常会给患者带来痛苦,也可能是潜在病理的征兆。

青春期是由激素驱动的,它会影响肠道微生物群。性别之间的肠道微生物群差异出现在青春期开始时,证实了微生物群和性激素之间的关系。在不同的研究中已经提出了肠道微生物群和性激素之间的双向相互作用。
本文介绍了性早熟发育,以及性早熟中肠道微生物群的变化,便于从儿科内分泌学的角度考虑性激素-肠道菌群轴的作用。
肠道菌群的改变可能发生在患有中枢性早熟的女孩身上的证据,为预测和预防性早熟提供了一个有趣的发现。
加深对性激素与微生物群变化作用之间联系的理解,可以通过提供儿科内分泌学的视角,在青春期疾病中实施微生物群靶向治疗。
在了解性早熟与肠道菌群的关系之前,我们先了解一下青春期发育的相关生理过程,以及关于性早熟的基本知识。
青春期特征是:
正常的青春期是由于下丘脑-垂体-性腺轴(HPG)的长期成熟活动所致。
下丘脑以脉动的方式将促性腺激素释放激素释放到垂体门静脉系统,在那里它刺激LH和FSH分泌(也是脉动的)。
注:
LH(促黄体生成素):主要刺激睾丸中的间质细胞和卵巢中的卵泡膜细胞分泌雄激素。
FSH(卵泡刺激素):主要刺激卵泡或生精小管形成雌激素、抑制素、卵子或精子。
间质、管状和卵泡隔室通过旁分泌过程共同作用,产生雌激素,并调节性类固醇的产生和配子的发育。类固醇激素对促性腺激素释放激素和促性腺素分泌有内分泌负反馈作用。
FSH分泌被抑制素、孕酮和雌二醇的负反馈抑制。在成年女性受试者中,临界雌二醇浓度刺激LH激增,从而启动排卵。
HPG轴出生时短暂激活,青春期完全重新激活
出生时,由于缺乏抑制HPG轴的胎盘类固醇,这一轴会被激活,从而导致类固醇激素的产生增加,这是青春期继续进行的第一步。这种短暂的激活大约在出生后一周开始,几个月(大约6个月)后停止。
HPG轴在整个儿童期并不完全休眠,尤其是女性,其FSH浓度略高于男性。有时,也可以用超声波检查卵巢卵泡。在青春期,HPG轴经历完全重新激活。
最重要的GnRH抑制系统是γ-氨基丁酸能神经元(产生γ-氨基丁酸的神经元)和阿片受体;吻肽、神经激肽B和强啡肽A这三种存在于弓状核(ARC)中的神经肽被认为是影响GnRH释放的基本生成物,因为它们对男孩和女孩的青春期生理学有重要贡献。
厌食因子——瘦素:在青春期发挥重要作用
瘦素是一种主要由脂肪细胞产生的细胞因子,它作为一种厌食因子,通过抑制下丘脑神经肽Y(NPY),从而抑制食欲,在控制体重、食物摄入和能量平衡方面发挥重要作用。儿童时期必须达到正常的体重和组成,以避免青春期功能障碍。
除了瘦素与NPY的相互作用外,一些研究表明瘦素通过与KiSS-1基因直接相互作用而影响青春期和生殖功能。GnRH神经元缺乏瘦素受体,但KiSS-1神经元表达瘦素受体。瘦素直接刺激kisspeptin释放并介导GnRH的脉动释放。
青春期是一个复杂的过程,具有广泛的生理变化。调节青春期开始的机制涉及遗传、营养和环境相互作用。
胎儿营养异常以及内分泌系统可能导致发育改变,从而永久影响结构、生理和代谢。
生长关键时期激素和营养之间的相互作用对于代谢适应反应控制和青春期发育预期至关重要。
越来越多的证据表明,产前和产后早期是青春期开始规划的重要时期。各种研究表明,产前暴露于不利环境因素,如导致儿童出生SGA(小于胎龄)和/或IUGR(宫内生长受限)的因素,会影响青春期时机。儿童出生的SGA可能会经历几次青春期改变,如性早熟。
➡ 性早熟如何定义?
性早熟(PP)定义为女性青少年在8岁之前和男性在9岁之前出现变化:
性早熟患者表现出性和身体生长加快,同时出现生长突增。如果不治疗,骨骺生长加快可能会导致骨骺过早闭合,导致成年后身材矮小。
➡ 性早熟分类
根据潜在的生理病理过程,病理性性早熟分类如下:
• 中枢性性早熟
中枢性性早熟是最常见的性早熟形式,女孩多于男孩。一般异常位于大脑。
由于先天性或后天性中枢神经系统(CNS)损伤或单基因缺陷导致的HPG轴过早成熟,从而导致的中枢性性早熟(CPP)或促性腺激素依赖性性早熟(或真正的性早熟),也可能是特发性的。
• 外周性性早熟
一般异常不在大脑中,而是在睾丸、卵巢或肾上腺中。
外周性性早熟(PPP)或促性腺激素非依赖性性早熟(或假性早熟),由于遗传或肿瘤病因、分泌hCG的生殖细胞肿瘤(仅适用于男孩的人绒毛膜促性腺素)或外源性来源导致的性腺性激素或肾上腺激素分泌过多。
➡ 中枢性性早熟病例男女有别
据评估,每5000-10000名儿童中就有1名患有中枢性性早熟,女性的发病率是男性的10倍。
大多数女性中枢性性早熟病例似乎是特发性的,而男性中枢性性早熟患病率较高似乎通常是由病理性脑损伤引起的。特别是,下丘脑错构瘤是引起中枢性性早熟的最常见的脑损伤。
注:下丘脑错构瘤,是临床极为罕见的先天性脑组织发育异常性病变。
➡ 性早熟的临床检查评估
准确的个人和熟悉的病史、完整的体检、荷尔蒙和放射检查对性早熟诊断至关重要。
——青春期体征
临床检查应侧重于发育学数据、根据Marshall和Tanner分类对青春期体征的评估、过去6-12个月的生长模式,青春期体征(女孩的乳腺芽、男孩的睾丸体积、两者的阴毛)和其他青春期体征(痤疮、油性皮肤、勃起、男孩夜间排泄物、女孩阴道分泌物和月经出血)的进展率。
——基线LH水平
基线LH水平是诊断中枢性性早熟的有希望的生物标志物;基础晨LH值超过0.2 mUI/ml通常被认为是青春期的标志。在成瘾中,LH与FSH的比值高于0.6与中枢性性早熟有关。
——GnRH刺激试验
GnRH刺激试验仍然是鉴别中枢性性早熟的金标准,大于5 IU/L的LH截止峰值水平被广泛用于诊断中枢性性早熟。
——其他激素评估
其他激素评估应包括甲状腺测试、睾酮、雌二醇、17-羟基孕酮(17-OHP)、癌胚抗原(CEA)、癌抗原125(CA125)、甲胎蛋白和β-hCG,具体取决于患者的病史。
——骨龄
为了确定孩子的生物年龄,需要对非优势(左手)手和手腕进行骨龄X光检查。超过2.5标准差(SD)或超过2年的晚期骨龄更可能与病理性性早熟相关。
——盆腔超声
在女孩中,盆腔超声是评估卵巢早熟发育和排除卵巢囊肿或肿瘤的有用工具。
——脑部MRI检查
建议对患有中枢性性早熟的患者进行脑部MRI检查,以排除CNS损伤,应在男孩(<6岁)中进行常规检查。
性激素和肠道菌群之间的关系在最近的研究中得到了广泛的探讨,并且是一个不断扩大的研究领域,可能会为各种与性有关的疾病带来新的治疗选择。
20世纪80年代,最早的研究之一是在细胞水平上进行的,其中发现孕酮促进了拟杆菌和中间普氏杆菌的生长。
2012年一项研究在对91名女性的粪便样本进行测序时发现,无论健康状况如何,在怀孕期间,尤其是在孕晚期,当雌激素达到峰值时,肠道微生物组明显改变。
2015年,一项欧洲研究表明,健康男性的普氏拟杆菌丰度高于生育女性,而绝经后女性的微生物群与男性没有差异。
这两项研究都证明了雌激素和相关的雌性激素在调节肠道微生物组的组成方面是至关重要的。
因此,微生物群会影响雌激素水平,反过来,雌激素水平可能会受到微生物群组成和多样性的影响。
➤ 微生物群对雌激素的影响
微生物组能够通过表达B-葡萄糖醛酸酶(一种介导膳食和非膳食雌激素解偶联的酶)代谢雌激素。
未结合的雌激素可以通过作用于α和β雌激素受体而进入全身血流并具有代谢活性,这些受体在多种器官和组织中表达;雌激素活性不仅对生殖健康有影响,而且对心血管风险、代谢和骨稳态以及中枢神经系统也有影响。
微生物群多样性与绝经后妇女和男性的尿雌激素水平较高有关,而绝经前妇女的雌激素水平似乎不受微生物群组成的影响,这表明微生物群主要影响非卵巢雌激素水平。
►►
补充植物雌激素能够促进特定细菌的肠道定植,富含植物雌激素的饮食可能与亚洲绝经后妇女代谢综合征的风险降低有关。
➤ 反过来,性激素水平也可能影响微生物组的组成
雄激素过量,如多囊卵巢综合征患者,也可能导致生物失调和细菌多样性降低。多囊卵巢综合征(PCOS)是一种内分泌疾病,其特征是雄激素水平较高,雌激素水平较低,几项研究表明,多囊卵巢综合症患者的肠道失调与细菌多样性较低有关,导致丁酸生成减少,BMI升高,睾酮血清浓度升高。
此外,肠道微生物组通过产生有助于减少炎症反应的短链脂肪酸在决定胰岛素分泌方面发挥重要作用;菌群失调可能导致胰岛素抵抗和糖代谢改变,如多囊卵巢综合征;较高的胰岛素水平刺激卵巢产生雄激素,从而使多囊卵巢综合征的发病机制永久化。
➤ 微生物群及其代谢产物也可能影响肠道菌群定植
微生物群及其代谢产物也可能通过定殖阴道,以及一些作者认为的子宫内膜和胎盘,影响女性生育、怀孕、胚胎发育和分娩的各个阶段。微生物群的改变与促炎细胞因子的分泌和早产有关。剖宫产新生儿肠道菌群多样性较低,可能是因为他们没有通过阴道被母体肠道菌群定植。
➤ 性激素信号和脑-肠轴功能中的应激反应之间存在复杂的相互作用
我们知道,肠道和中枢神经系统之间的双向沟通途径,根据肠道细菌是大脑和内分泌系统之间的重要媒介。肠道菌群是调节脑-肠轴的中枢,肠道屏障短链脂肪酸,除了是能够调节肠道运动和伤口愈合的炎症调节剂外,还代表了微生物组和肠-脑轴之间的联系。
功能性胃肠疾病的发生率,如功能性消化不良和肠易激综合征,导致运动能力受损和/或敏感性改变,在女性中明显更高,这可能是因为性激素信号和脑-肠轴功能中的应激反应之间存在复杂的相互作用。
▸ 雌激素激活脑-肠轴的受体,间接干扰胃肠动力
具体而言,已观察到雌激素通过直接激活位于脑-肠轴的受体,并通过调节其他受体系统间接干扰胃肠动力和敏感性。在卵巢周期的卵泡期,当雌激素水平较高时,女性的胃肠动力降低。
此外,支持循环雌激素在胃排空延迟中起重要作用的假设,绝经前和绝经后女性接受激素替代疗法与未接受激素治疗的绝经后妇女相比,胃排空速度较慢,而绝经后的女性与同龄男性相类似。相比之下,睾酮或雄激素似乎对胃动力或胃超敏反应没有影响。
性激素和肠道菌群之间的相互关系
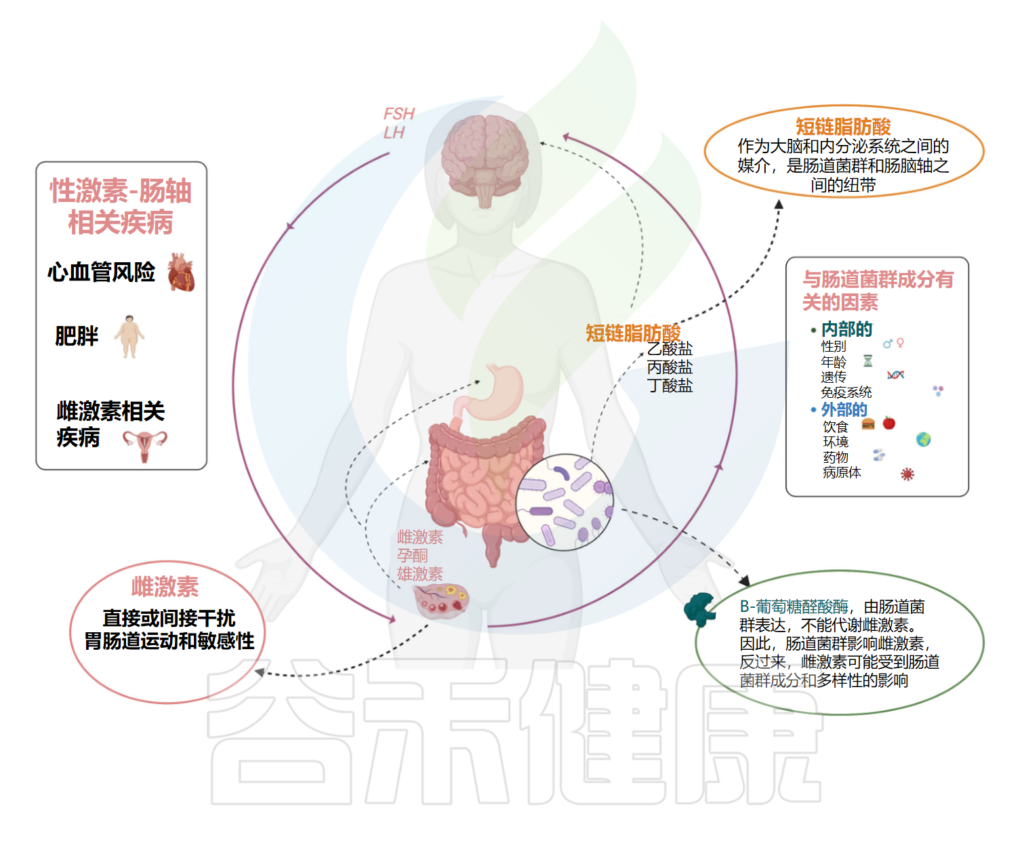
Calcaterra V, et al., Front Endocrinol (Lausanne). 2022
雌激素通过对核受体的作用,以及通过与膜G蛋白偶联的雌激素受体1 (ER 1)受体的激活,实现其快速、非基因组的作用机制。
▸ 雌激素干扰疼痛调节
雌激素受体在中枢神经系统和涉及内脏疼痛感知的通路中广泛表达,包括下丘脑、杏仁核和中脑,所有这些都已被证明向参与胃肠功能调节的迷走神经细胞发送广泛的投射。
具体而言,在外周内脏传入中,雌激素似乎通过改变离子通道的开放和受体表达的调节来调节伤害感受,以及激活胆酸速激肽-神经激肽1受体并诱导P物质的释放。
最后,除了干扰疼痛调节外,雌激素还参与中枢神经系统的内脏信息处理。
脑成像研究发现,与患有IBS的男性相比,患有IBS女性在对不良内脏刺激的反应中表现出更大的情绪回路激活,包括杏仁核和蓝斑。
众所周知,随着年龄的增长,微生物群的组成逐渐发生变化,需氧菌和兼性厌氧菌的数量普遍减少,专性厌氧菌种群数量增加。
传统上,普遍的观点是,在1-2岁之间,人类肠道菌群开始类似于成年人,主要由厚壁菌门、拟杆菌门、变形杆菌门和放线菌门的物种组成。然而,青少年和成人粪便微生物群在属水平上观察到许多差异。
非青春期和青春期菌群类别存在差异
一项研究评估青春期儿童的远端肠道菌群表明,双歧杆菌属和梭状芽孢杆菌属(已知定植于新生儿肠道并在2至18岁之间逐渐减少的物种)成员的丰度在青春期儿童中显著高于成年人。这些属的流行率以前在青春期前和青春期年龄组中没有被认识到。
2020年的一项横断面研究,通过16S rRNA测序分析了不同青春期阶段(5-15岁)的肠道菌群生物多样性。非青春期和青春期受试者之间的α或β多样性没有发现差异,但研究证明两组之间的细菌类群存在差异。
特别是,非青春期受试者的特征主要以下菌群:
另一方面,青春期组以β变形菌纲(Burkhollderiales)的流行率较高。
进一步分析血清性激素与菌群丰度之间的关系,结果表明:
睾酮水平与Adlercreutzia、Dorea、Clostridium和拟副杆菌属的丰度有关。作者假设这些细菌可能受到性激素的影响。
几项研究已经调查了肠道微生物与性类固醇激素之间的关系。Shin等人证明了肠道菌群特征与人类睾酮/雌激素状态之间的关系:
不动杆菌、多利亚菌、瘤胃球菌和巨单胞菌与睾酮水平显著相关,而Slackia菌和丁酸单胞菌则与雌二醇水平显著相关。
青春期两性之间的肠道菌群差异更加明显
据报道,肠道菌群似乎不受儿童性别的影响,但在青春期开始时就出现了差异。微生物门相关疾病也表现出性别偏见,支持肠道细菌与性别之间的关系可能是双重的。
最近的一项横断面调查发现,在青春期,两性之间的肠道菌群差异更加明显。
比较青少年和成年人的微生物群,发现双歧杆菌的数量,特别是在一些研究中,随着年龄的增长而减少,也报道了与拟杆菌门和厚壁菌门的年龄相关的联系。
Hollister等人比较了青春期和成人的肠道菌群组成,指出在青春期发育期间,女孩的肠道菌群逐渐发生变化,越来越像成年女性的肠道菌群,与她们的青春期发育程度成正比。
在雄性和雌性中,优势类群都是梭状芽孢杆菌和拟杆菌,表明微生物群成熟的要素是:
梭状芽胞菌和拟杆菌类菌群优势的变化
事实上,在青春期,梭状芽孢杆菌的相对丰度逐渐增加,拟杆菌的相对减少,逐渐类似于成人微生物群的组成。就门而言,随着青春期的进展,厚壁菌门的数量增加,而拟杆菌门的数量减少。
然而,尽管Hollister等人观察到男孩和女孩的肠道菌群变化,但由于男性青春期发育较晚,仅在女性青少年中获得了具有统计学意义的数据。
青春期,肠道菌群组成和预测的代谢谱存在性别显著差异
Yuan等人证实了这些数据,他们确定了不同青春期状态下两种性别的肠道菌群特征。对89名5-15岁的中国参与者进行了肠道菌群分析。参与者被分为青春期前和青春期组,男性(n=49)和女性(n=40)。
这项横断面研究表明,在青春期之前,肠道菌群组成和预测的代谢谱存在性别差异,在青春期变得更为显著。
实验结果表明,Dorea、Megamonas、Bilophila、Parabacteries、Phascolactobacterium属代表青春期受试者的微生物标记。
他们认为,性别依赖的肠道菌群多样性部分是由于性激素,部分是由于其他非激素影响因素。
“
以上是肠道菌群在生理性青春期发育中的作用的证据。而肠道菌群在病理性青春期中的作用越来越受到关注。
青春期到来的时间可能受到肠道菌群的影响,特别是某些梭菌属物种,包括调节宿主性激素水平的瘤胃球菌科、粪杆菌属和瘤胃球菌属。
肠道菌群影响雌激素代谢
Ruminococcus和Faecalibacterium的β-葡糖醛酸酶能够裂解雌酮和雌二醇,而拟杆菌物种只能代谢雌酮。
因此,尿液中雌激素-雌激素代谢物比率与瘤胃球菌的相对丰度呈正相关,与拟杆菌的相对丰量呈负相关。
根据这些数据,肠道菌群可能通过其雌激素代谢部分调节青春期的开始。
肠道菌群通过能够代谢雌激素的特定肠道微生物似乎能够调节青春期,但反过来也可能。性激素可以通过引导肠道菌群的成熟,直接影响特定菌群的生长。
肠道菌群代谢物影响内分泌系统
最近的研究发现,肠道菌群产生的代谢物可以影响人体内分泌系统,激活肠道神经系统。
一些关于微生物群功能的最佳研究强调了肠道微生物通过产生短链脂肪酸为宿主提供能量,包括丁酸和丙酸,这两种物质都参与胆汁盐代谢,并在脑肠轴中发挥重要作用。
已经证明,内源性受体游离脂肪酸受体(FFAR)2和FFAR3与短链脂肪酸相互作用,并在肠内分泌细胞中表达,肠内分泌细胞产生肽YY(一种厌食激素),从而参与调节宿主能量、食欲、脂肪组织储存和荷尔蒙平衡,影响青春期时间。
肥胖 & 青春期 & 肠道菌群失调
肥胖和青春期之间有着密切的联系;尤其是性早熟与体重指数(BMI)呈正相关。基于这一信息,并考虑到受性早熟影响的儿童往往肥胖,已假设肠道菌群可能参与性早熟的发病机制。
一项研究阐明了特发性中枢性性早熟(ICPP)患者(n=25)和健康女孩(n=23)之间肠道菌群的差异。
特发性中枢性性早熟肠道菌群与肥胖菌属相似
作者应用16S rDNA测序来比较两组之间的肠道菌群,观察到,特发性中枢性性早熟中鉴定的肠道属与肥胖相关的肠道属相似,特别是吉米格瘤胃杆菌属、示波杆菌属和XIVb梭状芽孢杆菌属。
考虑到微生物种类水平,患有特发性中枢性性早熟的女孩富含Rumicoccus bromii, Ruminococcus gnavus, Ruminococcus leptum,前两种是在肥胖人群中发现的;它们可以促进脂肪组织的能量吸收和增生,而据报道,Ruminococcus leptum会影响人体体重变化。
这些结果突出了肥胖、特发性中枢性性早熟和肠道菌群失调之间的关联。作者假设,肠道菌群失调会导致青春期前女孩发生类似于肥胖患者的过程,脂肪细胞的增殖和沉积会引发性早熟。
然而,肠道失调也可能导致下丘脑-垂体-性腺轴(HPGA)的早期激活。
不同的研究已经研究了肠道菌群在雌激素、FSH和LH分泌机制中的作用,但仍不清楚。
三种临床生物标志物(FSH、LH和胰岛素抵抗)与肠道菌群之间的关系
考虑到特发性中枢性性早熟女孩,作者证明了FSH与梭杆菌、LH与Gemmiger之间的正相关,LH与Romboutsia之间的负相关。此外,胰岛素抵抗与吉米格菌、瘤胃球菌、巨单胞菌和双歧杆菌呈正相关。
特发性中枢性性早熟:部分菌群高产短链脂肪酸
肠道菌群、激素分泌和肥胖之间的密切联系激发了对肠道菌群触发特发性中枢性性早熟机制的研究。
研究人员在工作中调查的特发性中枢性性早熟女孩的特征是与产短链脂肪酸相关的菌群:
短链脂肪酸诱导瘦素基因表达,激活HPGA轴
瘦素在女性青春期发病中的重要作用众所周知。瘦素是一种脂肪细胞代谢肽,参与其表达的基因与短链脂肪酸相关。
短链脂肪酸产生与特发性中枢性性早熟之间的关系可以通过高浓度短链脂肪酸诱导瘦素基因表达的机制来解释,瘦素基因激活下丘脑-垂体-性腺轴,从而导致青春期的开始。
Li等人招募了27名中枢性性早熟女孩、24名超重女孩和22名健康对照,以探讨肥胖与中枢性性早熟之间的关系。
肠道菌群代谢物激活HPGA轴
这项研究表明,中枢性性早熟患者表现出过多的Alistipes、Klebsiella、Sutterella,这通常出现在神经系统疾病患者中。这些微生物产生具有神经递质活性的代谢物(血清素和多巴胺),这些代谢物会引发早熟,激活下丘脑-垂体-性腺轴。
肠道菌群代谢物促进胰岛素抵抗
作者在中枢性性早熟和超重组中都发现了普雷沃氏菌;支链氨基酸的产生可促进胰岛素抵抗。这一机制可以解释中枢性性早熟患者肥胖的高发生率。
此外,在两组中,均观察到一氧化氮合成升高,这是一种重要的气体神经递质,可刺激促性腺激素释放激素的分泌并促进胰岛素抵抗。
这些情况,肠道菌群表达的改变,可以解释中枢性性早熟和肥胖之间的联系,如下图所示。
性早熟 – 肠道微生物组和肥胖:密切相关
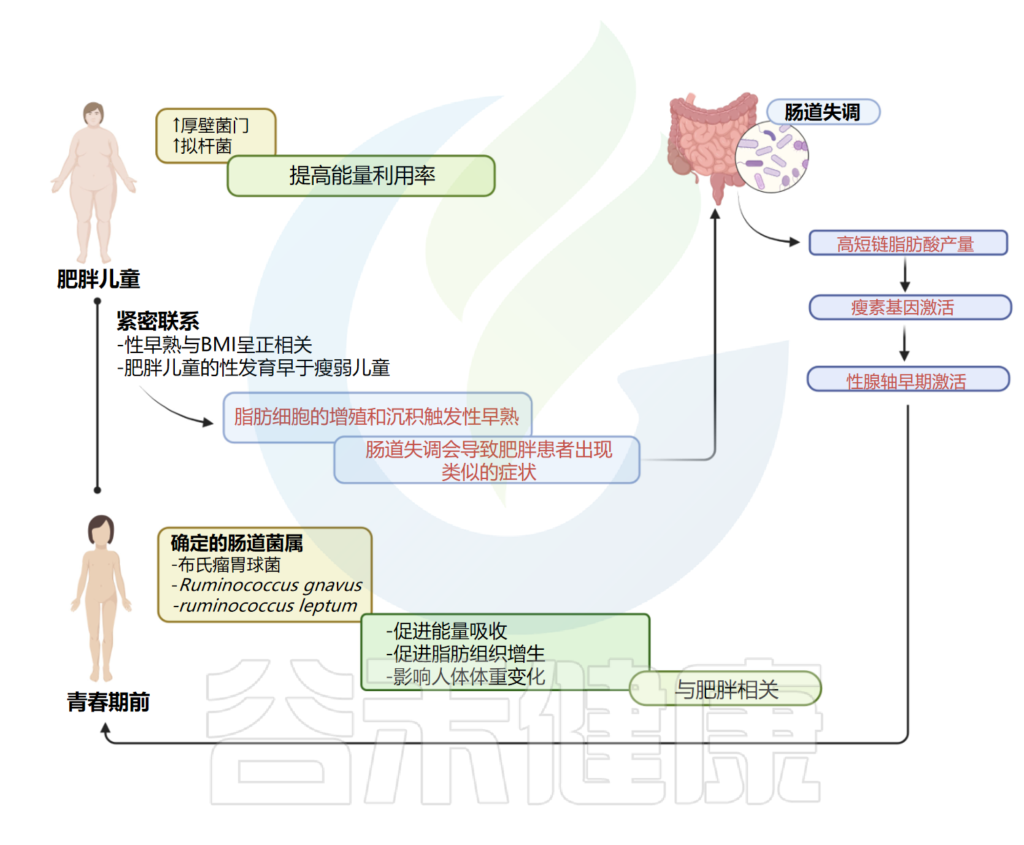
Calcaterra V, et al., Front Endocrinol (Lausanne). 2022
高脂饮食:过早激活HPG轴,诱导性早熟
大量营养素食物含量,如高脂肪摄入,可能会调节HPG轴的过早激活,诱导青春期的性早熟。
最近,在实验模型中,研究人员表明,高脂饮食对性早熟的影响受肠道微生物群和激素的相互作用调节。
断奶后的高脂饮食导致性早熟,下丘脑中的血清雌二醇、瘦素、脱氧胆酸和GnRH增加。特别是,GnRH与脱硫弧菌、Lachnoclostridium、GCA-900066575、链球菌、厌氧菌、双歧杆菌呈正相关,这表明这些细菌可能在促进性发育方面发挥作用。
此外,作者报道,“高脂饮食微生物群”移植促进了小鼠的性早熟,支持肠道菌群调节促进性早熟的局部和全身性类固醇水平。
性早熟治疗的最重要目标是保持成人身高并减少相关的心理社会压力。
促性腺激素释放激素激动剂,1个月或3个月储存制剂,是中枢性性早熟的标准护理。GnRH激动剂治疗被广泛认为是安全的。
最常见的不良反应包括局部皮肤反应和绝经后症状。需要定期验证青春期进展、生长速度和骨骼成熟。
PPP的治疗因发病机制而异,治疗的主要目的是消除性类固醇的内源性或外源性来源。
肾上腺和性腺肿瘤需要手术治疗。
其他生活中的注意事项如下,供参考。
生活方式
消除外源性雌激素(塑料、食品添加剂和杀虫剂)和其他内分泌干扰物(例如美容产品中的邻苯二甲酸盐)。薰衣草油和茶树油与乳突有关,尤其是男孩的男性乳房发育症。
营养
消除添加激素的乳制品、鸡蛋和肉类。考虑消除大豆、亚麻和芝麻,因为它们是植物雌激素,年轻组可能对这些非常敏感。
缺乏维生素 D 的 5-12 岁女孩面临青春期提前的风险是维生素 D 水平较高的女孩的两倍。
晒太阳是增加维生素 D 摄入量以预防和减缓青春期提前的一种方法。
其他食物补充包括:金枪鱼和鲑鱼等多脂鱼、橙汁、豆浆等。
肝脏解毒支持减少外源性激素作用。
食物
深色绿叶蔬菜、西兰花、甜菜、朝鲜蓟、姜黄、柠檬、蒲公英根等。
减少肾上腺激素输出的植物药:
刺五加 ;睡茄;红景天
父母的反应会影响孩子的应对能力
当孩子的家庭氛围不好,他们的病情无法得到家人的支持,会增加孩子的负面心理情绪和父母的养育压力。加强家庭成员之间的沟通至关重要。
一些导致性早熟的风险因素(例如性别和种族)无法避免。但是,有一些措施可以降低孩子出现性早熟的风险,包括:
不同的研究都提出了肠道菌群与性激素之间的双向相互作用。青春期期间,身体发育变化主要由激素驱动;因此,这一动态和过渡期是评估潜在激素对肠道菌群影响的机会。
不同青春期阶段的肠道菌群存在多样性,并且患有中枢性性早熟的女孩肠道菌群可能改变,这是预测和预防性早熟发育的一个有趣的发现。通过提供儿科内分泌学的观点,加深对性激素和微生物群变化作用之间的联系的理解,可以在青春期疾病中实施微生物群靶向治疗。
主要参考文献:
Calcaterra V, Rossi V, Massini G, Regalbuto C, Hruby C, Panelli S, Bandi C, Zuccotti G. Precocious puberty and microbiota: The role of the sex hormone-gut microbiome axis. Front Endocrinol (Lausanne). 2022 Oct 21;13:1000919. doi: 10.3389/fendo.2022.1000919. PMID: 36339428; PMCID: PMC9634744.
Li Y, Shen L, Huang C, Li X, Chen J, Li SC, Shen B. Altered nitric oxide induced by gut microbiota reveals the connection between central precocious puberty and obesity. Clin Transl Med. 2021 Feb;11(2):e299. doi: 10.1002/ctm2.299. PMID: 33634977; PMCID: PMC7842634.
Dong G, Zhang J, Yang Z, Feng X, Li J, Li D, Huang M, Li Y, Qiu M, Lu X, Liu P, Zeng Y, Xu X, Luo X, Dai W, Gong S. The Association of Gut Microbiota With Idiopathic Central Precocious Puberty in Girls. Front Endocrinol (Lausanne). 2020 Jan 22;10:941. doi: 10.3389/fendo.2019.00941. PMID: 32038493; PMCID: PMC6987398.

谷禾健康

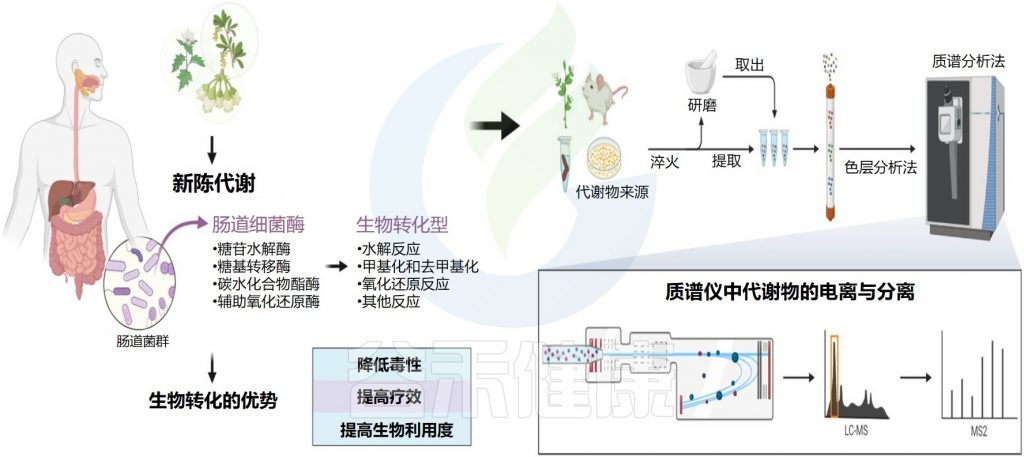

什么是天然产物?
天然产物是指动物、植物、昆虫或微生物体内的组成成分或其代谢产物以及人和动物体内许多内源性的化学成分,是自然产生的小分子。值得注意的是,天然产物来源中,植物来源占85%以上。
谷禾在这里主要介绍植物来源的天然产物,包括营养素和药物。它们很容易与肠道微生物群相互作用,因为它们的成分复杂,在肠道中的停留时间长。通常,外源物质在小肠中的停留时间为1-6小时,在结肠中的停留时间为1-3天。特定的肠道微生物分解和转化天然产物,产生丰富的代谢物和功能化合物,具有宿主本身无法合成的生理活性。
天然产物在食品、药品、保健品领域均有运用。天然产物是极为重要的新药来源。近年来临床应用的药物,三分之二左右源自天然产物、天然产物衍生物以及天然的生物大分子,几乎涵盖了疾病治疗的各个方面。这在防治癌症及传染类疾病领域中的表现尤为明显。
天然产物在临床上得到了广泛的应用,其特点是多组分、多靶点、药效学物质多、作用机理复杂、生理活性多样。
对于口服天然产物,肠道菌群与临床疗效密切相关,但这种关系尚不明朗。肠道微生物在酶系统多样性引起的天然产物的转化和利用中起着重要作用。黄酮类化合物、生物碱、木酚素和酚类等有效成分不能通过人体消化酶直接代谢,但可以通过肠道微生物产生的酶转化,然后加以利用。因此,重点是通过肠道微生物群进行天然产物的代谢。
本文介绍了肠道微生物群及其对天然产物各组分生物转化的影响的研究,并强调了所涉及的常见菌群,反应类型,药理作用和研究方法。为临床疾病防治中的应用提供理论支持,以及日常的选择健康的药物提供一定的参考,并为基于肠道生物转化的天然产物研究提供新思路。
基于肠道微生物的天然产物的生物转化和代谢
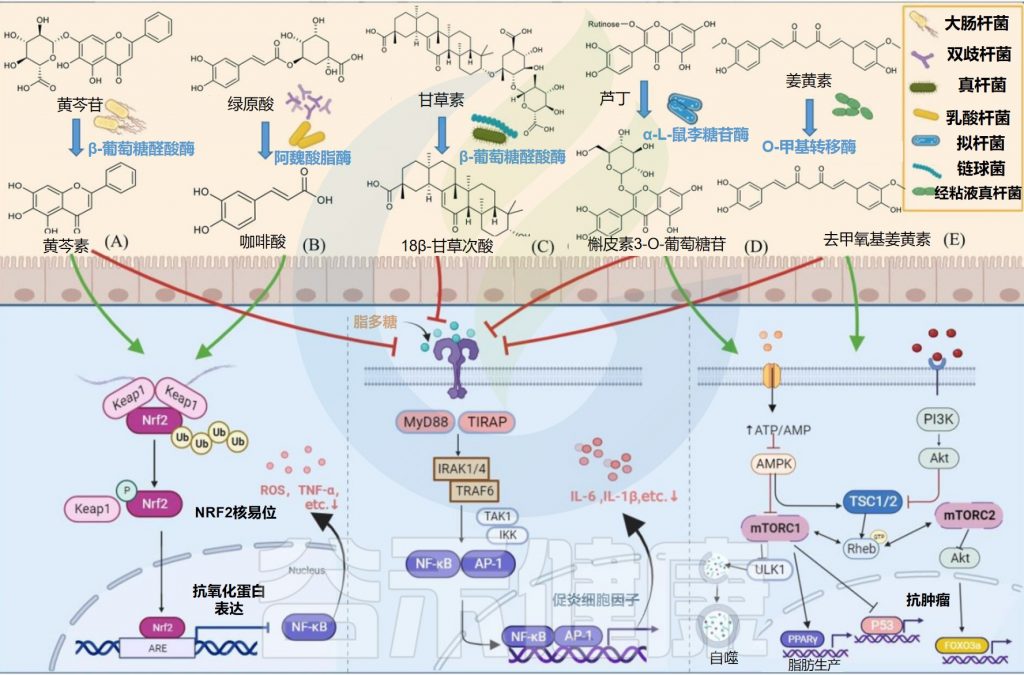

Zhao Y,et al.Front Microbiol.2022
★人体肠道中的微生物
肠道微生物群由1000-1250种细菌组成,这些细菌以各种形式与人类相互作用,例如共生和寄生,这种相互作用通过微生物代谢物作为信号分子极大地影响人类健康。
肠道微生物构成了一个动态和多样化的微生态系统,这是抵抗致病细菌的天然屏障。肠道微生物具有丰富的酶系统,包括葡萄糖苷酶,还原酶,裂解酶,转移酶等,并大大扩展了人体内的代谢反应池。
✦肠道菌群影响口服给药的效果
口服给药是药物递送的首选途径,口服药物占市场最畅销药物的大部分。近年来,肠道微生物群对天然产物口服给药稳定性的影响受到广泛关注。
肠道具有丰富的细菌,有助于正常的消化功能,其中健康受试者中约98%的肠道微生物可分为四个门,厚壁菌门(Firmicutes),拟杆菌门(Bacteroidetes),变形菌门(Proteobacteria)和放线菌门(Actinobacteria)。
一些肠道微生物如大肠杆菌,双歧杆菌,真杆菌,乳酸杆菌,拟杆菌和链球菌参与天然产物的生物转化,其部分代谢物有利于肠道吸收并发挥显著的药理作用。
关键肠道微生物对天然产物的生物转化

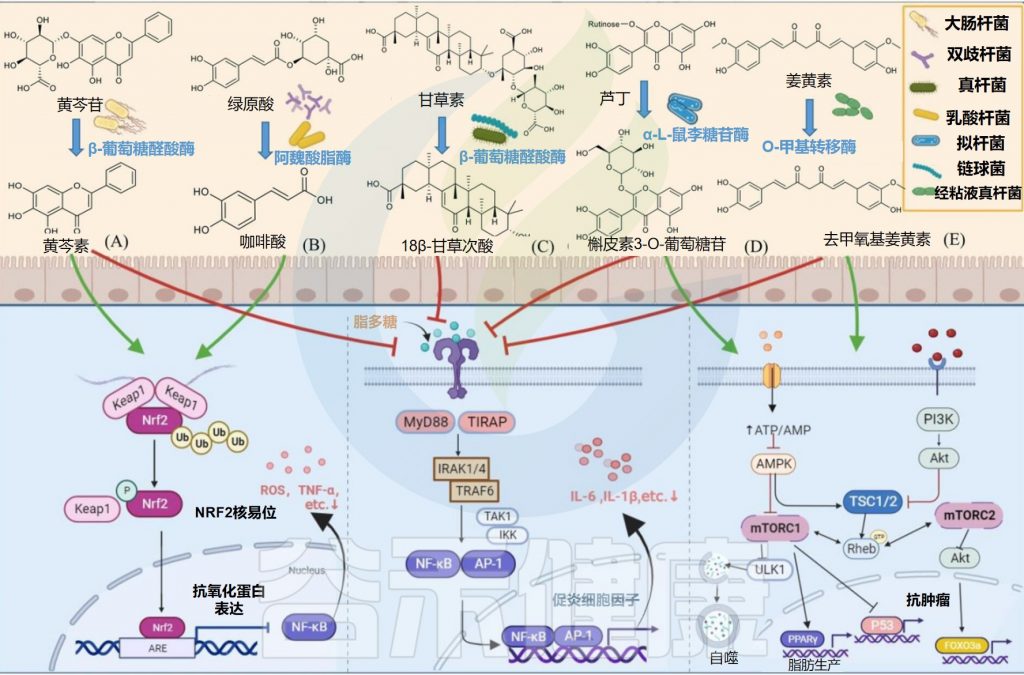
Zhao Y,et al.Front Microbiol.2022
▸
大肠杆菌(Escherichia coli),又叫大肠埃希氏菌,是一种革兰氏阴性,无孢子,兼性厌氧细菌,主要栖息在脊椎动物的肠道中。
✦水解黄芩苷而具有抗炎抗氧化作用
部分大肠杆菌可以产生糖苷酶参与外源物质的转化,从而产生其有益作用。例如,E.coli HGU-3产生β-葡萄糖醛酸酶,水解黄芩苷中的糖苷键以产生黄芩素。
在相同剂量下,黄芩素比黄芩蒿素更有效地抑制组胺诱导的抓挠行为,并通过抑制Nrf2-ARE和NF-κB信号通路而具有抗炎和抗氧化作用。
✦在脂肪肝变性中有治疗益处
一些大肠杆菌菌株具有较高的姜黄素转化活性。E.coli DH10B的高表达NADPH依赖性姜黄素/二氢姜黄素还原酶(CurA)将姜黄素还原为二氢姜黄素(DHC)和四氢姜黄素(THC),其全基因组序列已经确定。
NADPH是一种辅酶,叫还原型辅酶Ⅱ,学名烟酰胺腺嘌呤二核苷酸,在很多生物体内的化学反应中起递氢体的作用,具有重要的意义。
二氢姜黄素和四氢姜黄素通过调节SREBP-1C和PPARα的mRNA和蛋白质表达水平来降低细胞中的甘油三酯水平,并以依赖性方式衰减肝脏脂肪生成;二氢姜黄素和四氢姜黄素在肝脂肪变性中比姜黄素具有新的治疗益处。
✦水解肉桂酸后有抗氧化和抗癌特性
E.coli Nu, E.coli MC和E.coli WC-1具有肉桂酰酯酶活性,可通过水解共轭羟基肉桂酸和游离羟基肉桂酸酯释放羟肉桂酸,在体外和体内均显示出抗氧化和抗癌特性。
目前,对大肠杆菌的遗传和生化特征的良好理解可能有助于在体外合成具有各种健康活性的天然产物衍生物。
▸
双歧杆菌(Bifidobacterium)是属于放线菌门的广泛而丰富的属,是人类肠道微生物群的首批定植者之一。人类肠道中最常见的双歧杆菌包括青春期双歧杆菌,B.angulatum, B.bifidum, B. breve, B.catenulatum, B.dentium, B.longum, B.pseudocatenulatum和B.pseudolongum,占成人微生物组的10%,它们与宿主健康有关。
✦预防急性肝损伤
某些种类的双歧杆菌可以通过表达阿魏酰酯酶产生酚酸。例如,动物双歧杆菌的阿魏酰酯酶可以将绿原酸(CHA)水解成咖啡酸(CAA)。咖啡酸可以通过增加Nrf2转录来预防对乙酰氨基酚诱导的小鼠急性肝损伤。
✦调节胆汁酸和降低胆固醇
部分双歧杆菌的参与促进了黄烷酮,糖苷和皂苷在肠道中的代谢。B.longum R0175中的β-葡萄糖苷酶和去甲基化酶通过环裂解和脱甲基作用促进3-(3′-羟基苯基)丙酸和3-苯丙酸的产生。
B.longum SBT2928水解六种主要的人类和两种动物胆汁盐。因此,双歧杆菌可以调节胆汁酸代谢并降低体内胆固醇水平。
✦抗肿瘤和提高免疫
此外,B.breve ATCC 15700产生β-葡萄糖苷酶,在人参皂苷Rd的C-3和C-20位置裂解糖苷,生成脱糖基化的人参皂苷。
人参皂苷主要存在于人参和马铃薯药材中
人参皂甙的作用和功能是抑制肿瘤细胞的生长,诱导肿瘤细胞死亡,研究肿瘤的活性功能,肿瘤的异常逆行分化,提高人体免疫功能。
这些天然产物具有潜在的益处,代谢特征使双歧杆菌成为共生发展的主要候选者。
▸
真杆菌(Eubacterium)菌株的属是革兰氏阳性菌,它是人类肠道微生物群的核心属之一,并显示出在人类肠道的广泛定植。
一些真杆菌产生糖苷酶,还原酶等,并参与外源性物质的代谢。
✦抗炎抗氧化
E. ramulus是研究最广泛的类黄酮降解肠道细菌之一,它在人体肠道中很普遍。广泛存在于人体肠道中。来自E. ramulus的查尔酮异构酶和黄烷酮/黄烷醇裂解还原酶降解某些类黄酮产生查尔酮和二氢查尔酮。
二氢查尔酮及其代谢物具有抗炎和抗氧化作用,可以下调促炎细胞因子的分泌,并挽救脂多糖诱导的氧化磷酸化。
✦降解黄酮类化合物
研究了E.ramulus strain wK1对槲皮素和木犀草素的降解,发现静止细胞和酶制剂通过2,3位双键的还原和随后的环分裂将这些黄酮转化为3,4-二羟基苯基乙酸和3-(3,4-二羟基苯基)丙酸。
来自E.ramulus strain wK1的根皮素水解酶将邻近根皮素芳香A环的C-C键水解为3-(4-羟基苯基)丙酸和间苯三酚。
E.cellulosolvens ATCC 43171T可通过释放的葡萄糖部分的发酵促进类黄酮和葡萄糖苷的去糖基化。
注意:葡萄糖苷的去糖化仅由细菌酶催化。
✦预防气道过敏性炎症
Eubacterium L-8将甘草酸(GL)水解为18β-甘草次酸(18β-GA)。18β-甘草次酸通过抑制NF-κB磷酸化和增强Nrf2/HO-1通路来预防气道过敏性炎症。
NF-kB——核因子κB,参与细胞对外界刺激的响应,在细胞的炎症反应、免疫应答等过程中起到关键性作用
Nrf2/HO-1信号通路已成为细胞抗氧化应激的主要防御机制之一
这些代谢转化体现从真杆菌中获得的各种益处。然而,还需要进一步的体内研究,以最大限度地发挥真杆菌属的潜在益处。
▸
乳酸菌属(Lactobacillus)属于厚壁菌门,可以平衡微生物群落并保护胃肠粘膜。一些乳杆菌属富含代谢酶,如α-鼠李糖酶,单宁酶,没食子酸酯脱羧酶等,它们转化外源性物质。
✦抗炎、抗氧化作用
L. rhamnosus NCTC 10302具有β-葡糖苷酶和α-鼠李糖苷酶活性,通过水解,环裂变和脱氢将橙皮素7-O-葡萄糖苷和柚皮素-7-O-芸香糖苷转化为各自的糖苷元和3-(苯基)丙酸。
L. plantarum表达单宁酶水解没食子酸酯,具有短脂肪醇取代基的原儿茶酸酯和复杂的没食子单宁以产生没食子酸。没食子酸通过抑制MAPK/NF-κB途径并激活Akt/AMPK/ Nrf2途径,在脂多糖诱导的炎症和氧化应激中起保护作用。
MAPK是信号从细胞表面传导到细胞核内部的重要传递者。
Akt,蛋白激酶B,又称PKB或Rac,在细胞存活和凋亡中起重要作用。
✦预防代谢紊乱
观察到,没食子酸和邻苯三酚是由L.plantarum WCFS1中没食子甘氨酸代谢酶降解没食子甘肽而产生的。这项研究意味着益生元-益生菌相互作用在预防饮食诱导的代谢紊乱方面的潜在作用。
✦改善骨质疏松
具有大豆苷元还原酶活性的Lactobacillus sp. Niu-O16。二氢大豆苷元抑制NF-κB活化和MAPK磷酸化,从而改善骨质疏松症。
L.casei, L.plantarum和L.acidophilus影响白藜芦醇苷到白藜芦醇的去糖基化。这种转化对于提高白藜芦醇苷的生物利用度和生物活性非常重要。来自L.reuteri, L.helveticus和L.fermentum的阿魏酰酯酶水解绿原酸以释放咖啡酸。
这些发现为乳杆菌在促进健康的制药和食品应用中的作用开辟了新的视角。然而,潜在的转化机制值得进一步研究。
▸
拟杆菌属(Bacteroides)的成员是革兰氏阴性专性厌氧菌,占结肠中细菌总数的25%,在人类肠道细菌组中起着多种作用。在临床中经常检测到拟杆菌物种,例如脆弱拟杆菌,B.distasonis, B.ovatus和B.thetaiotaomicron。
✦抑制炎症反应
拟杆菌属拥有一系列水解酶,并通过转化外来物质参与与其微生物邻居的物种间关联。体外共孵育实验表明,某些拟杆菌物种参与类黄酮的生物转化。
Bacteroides sp. 45表达α-L-鼠李糖苷酶和β-芦丁糖苷酶,用于将芦丁水解成槲皮素3-O-葡萄糖苷,槲皮素和白花青素。
槲皮素3-O-葡萄糖苷比其他形式的槲皮素吸收得更好,并且可以通过抑制NF-κB和MAPK信号通路来抑制结肠炎小鼠的炎症反应。
Bacteroides sp. 54将槲皮苷代谢为羟基槲皮素和去甲基槲皮素。槲皮苷也被α-L-鼠李糖苷酶降解为槲皮素,并通过Bacteroides sp.45进行进一步的环裂解以产生3,4-二羟基苯甲酸。
β-葡萄糖醛酸酶由拟杆菌J-37表达,将甘草酸代谢为18β-甘草次酸。
天然产物在拟杆菌作用下进行生物转化,产生具有不同功能活性的代谢物。了解人体内天然产物的整个过程以评估其对人体健康的影响是很重要的。
▸
链球菌属(Streptococcus)是革兰氏阳性菌,呈球形或卵形,通常成链排列或成对排列,广泛存在于人类粪便和鼻咽中。
宏转录组学分析表明,磷酸转移酶系统主要由链球菌表达,这表明这些细菌是小肠中可用碳水化合物的主要利用者。
✦抗癌、抗过敏作用
Streptococcus LJ-22表达β-葡萄糖醛酸酶将甘草酸代谢为18β-甘草次酸-3-O-β-D-葡萄糖醛酸(GAMG)。GAMG对脂多糖诱导的RAW264.7细胞具有抗过敏活性。
甘草酸和甘草次酸均有一定的防癌和抗癌作用。甘草次酸可抑制原癌细胞的信息传递和基因表达.甘草酸对多种恶性肿瘤均有抑制作用。甘草次酸还具有抗病毒感染的作用,对致癌性的病毒如肝炎病毒,EB病毒及艾滋病毒的感染均有抑制作用。
此外,单宁酸被Streptococcus gallolyticus subsp.Gallolyticus(SGG)的单宁酶降解以产生邻苯三酚。SGG可能通过消除单宁酸对肿瘤细胞的毒性来促进结直肠癌的发展。因此,有必要进行进一步的体内研究,以确定消除这些单宁酸降解微生物是否可以支持结直肠癌的有效治疗。
✦降低血压,抗氧化
S.thermophilus GIM 1.321很高的β-葡萄糖苷酶生产能力,用于将果实花青素降解为绿原酸,咖啡酸和阿魏酸。
CAA和CHA(10/15毫克/千克/天)的施用可以降低血压并发挥抗氧化作用。
链球菌菌株可能是肠道中的共生、致病和机会性病原体,需要更多关于其对人类健康影响的信息。更好地了解链球菌如何代谢天然产物,可以调节肠道微生物组以提高治疗效果。
▸
经黏液真杆菌(Blautia)属物种严格无氧,不可移动,通常为球形或椭圆形,广泛存在于哺乳动物的肠道和粪便中。越来越多的证据表明,经黏液真杆菌的益生菌特性对天然产物的生物转化有影响。
✦影响生物转化
在类黄酮生物转化过程中,Blautia催化的反应包括去甲基化,去糖基化以及环裂解,其可能被相应的酶催化,例如O-糖苷酶和β-葡萄糖苷酶。
研究表明,Blautia sp. MRG-PMF1菌株分别将5,7-二甲氧基黄酮和5,7,4-三甲氧基黄酮转化为生物活性白杨素和芹菜素,对芳基甲基醚官能团具有水解能力。Blautia sp. MRG-PMF1还具有去糖基化活性,并且发现各种异黄酮,黄酮和黄酮被代谢成相应的糖苷元。
✦去甲基产物具有抗炎、抗癌、抗氧化能力
Blautia sp. MRG-PMF1在菌株进一步代谢具有雌激素作用的去甲基香菜素。该菌株还可以催化姜黄素以产生具有抗炎和抗癌特性的去甲氧基姜黄素。
此外,Blautia sp. AUH-JLD56能够单独生物转化牛蒡子苷或牛蒡子苷元,制成具有更好抗氧化能力的去甲基化产物。
最近,关于Blautia对草本植物和功能性食品的生物转化和代谢研究越来越多。探索Blautia的生物转化对于开发新的酶和生物活性代谢物具有重要意义。
复杂的微生物酶催化肠道中天然产物的代谢,产生有利于宿主利用/排泄的亲脂性和低分子量代谢物。与人类遗传学不同,肠道微生物组的特征是可改变的,使其成为优化治疗的潜在治疗靶点。
口服天然产品进入消化道后,首先会接触大量肠道微生物及其产生的活性酶。因此,天然产物的肠道生物转化可能发生在通过肝脏的第一次传递效应之前,也可以被运输到肝脏进行修饰/结合,然后排泄到肠道,与肠道微生物反应形成一系列代谢产物。
因此,与健康或疾病相关的特定菌株、特定代谢途径和特定酶的组合对于确定肠道微生物对宿主的影响非常重要。
✦水解提高生物活性和生物利用度
某些天然产物具有高分子量和低脂溶性,并且它们难以在肠道中被人体吸收并且具有低生物利用度。通过肠道微生物介导的水解,它们的物理性质发生了变化,它们的生物活性和生物利用度大大提高。
大多数糖苷具有低活性,被认为是“天然前体药物”。在与肠道微生物相互作用后,糖苷的糖基被去除,然后,糖苷部分被肠细胞吸收以发挥生理作用。水解反应是进一步转化所必需的,产物(例如糖)参与促进肠道微生物的生长和存活。
肠道微生物对天然产物的水解反应



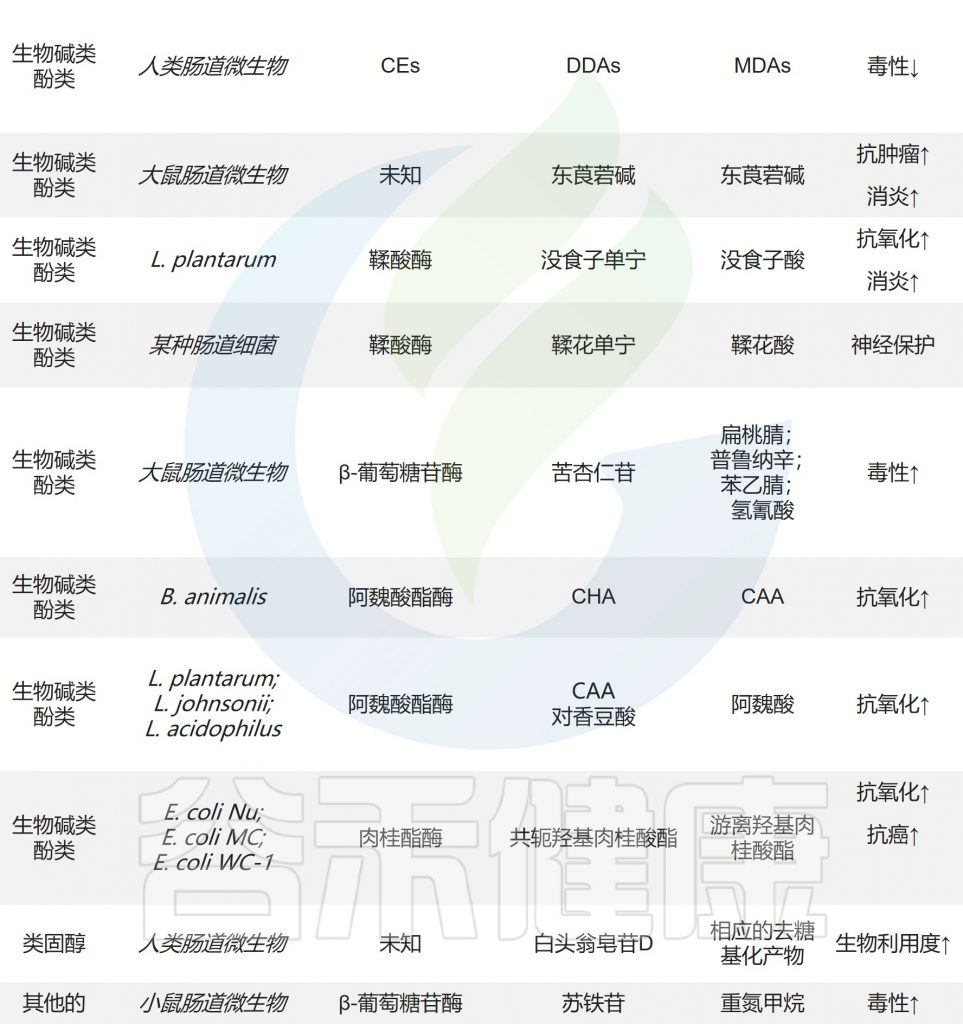




Zhao Y,et al.Front Microbiol.2022
✦类黄酮
类黄酮是天然酚类化合物,大量存在于水果和蔬菜中。肠道微生物可能是黄酮类化合物(糖苷形式)功效的部分原因,由于存在水溶性糖成分,其生物利用度较低。
具有3羟基黄酮碱和平面环体系的黄烷醇构成了一类重要的黄酮类化合物。异鼠李素-3-O-新橙皮苷首先被Escherichia sp.23脱糖基化为异鼠李苷-3-O–葡糖苷,去糖基化成苷元异鼠李甙。
•肠道酶代谢比肠道微生物更快
肠道微生物和衍生酶共同控制通过体外测定确定的淫羊藿类黄酮的代谢。在目前的研究中,肠道酶代谢类黄酮的速度比肠道微生物更快。
来自Bacteroides thetaiotaomicron VPI-5482的α-L-鼠李糖苷酶可以水解淫羊藿定C的α-1,2糖苷键以产生芸香苷。
芸香苷,又叫芦丁。具有抗炎、抗氧化、抗过敏、抗病毒等功效。
•肠道酶在水解中起着重要作用
E. ramulus和Clostridium saccharogumia将花青素-氰苷3-葡萄糖苷转化为氰苷。人类肠道酶如β-葡糖苷酶在汉黄芩苷水解成汉黄苷素中起着关键作用。
茶氨酸菌素A是红茶中发现的一种生物活性儿茶素二聚体,通过人类粪便微生物群脱乙酰产生茶氨酸霉素C。
•空间位阻会限制酶降解
观察了黄烷醇的代谢差异,结果表明,在肠道微生物发酵过程中,空间位阻可能限制细菌酶降解部分黄烷醇环。
在肠道微生物的作用下,许多其他类黄酮也会发生水解反应。值得注意的是,考虑到类黄酮的结构差异,肠道微生物对类黄酮的降解程度差异很大,从而影响其生物可利用性。需要进一步研究肠道代谢在类黄酮生物利用度和吸收中的作用,以及可能的细菌类黄酮相互作用活性。
✦萜类化合物
萜类化合物是具有抗癌,抗炎和神经保护作用的最大一类天然产物。部分萜类化合物也可被肠道微生物水解。
萜类化合物广泛存在于自然界,是构成某些植物的香精、树脂、色素等的主要成分。如玫瑰油、桉叶油、松脂等都含有多种萜类化合物。另外,某些动物的激素、维生素等也属于萜类化合物。
肠道微生物也可以水解部分萜类化合物。京尼平苷在Eubacterium sp. A-44表达的β-葡萄糖苷酶的作用下产生京尼平。芍药苷在β-葡萄糖苷酶的作用下转化为PM-I,该酶由L. brevis和脆弱拟杆菌(B. fragilis)表达。通过与大鼠厌氧肠道微生物群孵育,芍药苷也被脱糖并脱苯基为小分子量的白花苷和酰基白花苷。
•肠道微生物中的酶促进水解作用
研究证明,几种具有酯酶的双歧杆菌物种可以在体外将白芍苷水解为苯甲酸。体外研究表明积雪草苷被糖苷键水解酶逐渐去糖基化,并产生相应的苷元。柴胡皂苷B1在β-葡萄糖苷酶和β-D-聚焦酶的作用下逐渐水解为原柴胡皂素和柴胡皂甙A,由Eubacterium sp. A-44表达。
除上述化合物外,萜类人参皂苷Rh2、阿迪普西洛苷I、罗汉果苷III和具栖冬青苷也可在肠道微生物的作用下发生水解反应。
肠道微生物在萜类化合物代谢中起着重要作用,其代谢产物对肠道微生物组和人体健康的影响有待进一步研究。
✦其他化合物
具有极低生物利用度的尿石素只有在来自Gordonibacter urolithinfaciens, Gordonibacter pamelaeae和Ellagibacter isourolithinifaciens的鞣酸酶作用下水解成鞣花酸和尿石等衍生物时才能发挥药理作用。
尿石素——存在于水果和坚果中的一类化合物鞣花单宁的天然代谢产物
从大黄中提取的蒽醌糖苷被肠道微生物水解为蒽醌苷元。Sennoside A是大黄提取物的主要成分,通过Bifidobacterium sp. strain SEN的β-葡萄糖苷酶代谢为大黄蒽酮。
大黄蒽酮具有泻下攻积、清热泻火、解毒、活血祛瘀、利胆退黄等功效。
在肠道微生物表达的羧酸酯酶(CE)的作用下,二酯二萜生物碱(DDAs,如乌头碱)水解C-8和C-14的酯键,产生毒性较小的单酯二萜生物碱。生物碱东莨菪碱、类固醇化合物白头翁皂苷D和半胱氨酸在肠道微生物的作用下也会发生水解反应。
小结
水解反应是肠道微生物代谢天然产物的重要步骤,是生物活性表达和进一步生物转化所必需的。
应重点关注参与该反应的特定微生物和酶,以充分了解天然产物的最终命运及其对人体健康的影响,并为个性化治疗提供依据。
肠道微生物可以通过亲核取代反应表达转移酶并在两种底物之间移动官能团。
肠道微生物将甲基添加到外源物质中需要化学活化的辅底物,如乙酰辅酶A、三磷酸腺苷或腺苷甲硫氨酸,而去甲基化需要可以进行亲核催化的辅因子。
甲基化修饰可以优化天然产物的生理活性,去甲基化可以释放极性基团以进一步结合和排出体外,并为肠道微生物的生长提供碳源。
下图显示了肠道微生物作用下天然产物的甲基化和去甲基化以及带来的影响。
肠道微生物对天然产物的甲基化和去甲基化



Zhao Y,et al.Front Microbiol.2022
✦类黄酮甲基化后具有抗癌活性
类黄酮甲基化修饰可以在类黄酮结构中的C-2,C-3,C-4,C-5,C-6,C-7和C-8位置进行,甲基化类黄酮的生物利用度大大提高。
甲基化类黄酮具有显著的抗癌活性和对肝脏代谢的抵抗力。在大鼠口服芦丁后,在粪便样品中检测到许多甲基化代谢物,如甲基芦丁,甲基异槲皮素和甲基槲皮素硫酸盐。
作用过程
甲基化的异黄酮类化合物在E.limosum ATCC 8486的作用下进行去甲基化以产生大豆苷元和染料木黄酮。异氧杂环丁酚通过苌香产生去甲基化产物8-异辛基柚皮素。橙皮苷,5,7-二甲氧基黄酮,黄腐酚和5,7,4′-三甲氧基黄酮也可以在肠道微生物的作用下进行去甲基化反应。
✦生物碱具有抗癌性和抗病毒活性
生物碱是含氮化合物,由海洋和陆地生物生物合成,它们具有抗癌性和抗病毒活性。
绝大多数生物碱分布在高等植物,尤其是双子叶植物中,如毛茛科、罂粟科、防己科、茄科、夹竹桃科、芸香科、豆科、小檗科等。
在肠道微生物表达的酶的作用下,苦木中的主要生物碱成分准碳质酮被甲基化为准碳质碱丁基。异喹啉生物碱巴马汀通过体外厌氧培养产生去甲基产物,如哥伦比亚胺、药根碱、去甲基小檗碱和去甲基小蘖碱。通过离子阱电喷雾电离串联质谱法证明了肠道微生物对乌头碱的去甲基作用,并产生了去甲基乌头碱。
✦木酚素可以抗炎防心血管疾病
膳食木酚素是植物雌激素,主要存在于种子,坚果,豆类和蔬菜中。
木酚素在微生物作用下的一些转化
牛蒡苷可由Eubacterium sp. ARC-2菌株去甲基化为二羟基内酯和其他产物。从人类粪便细菌中分离出一种名为Lautia sp. AUH-JLD56的细菌,该物种可以有效地将牛蒡苷或牛蒡苷元转化为去甲基化代谢物3′-去甲基牛蒡苷(3′-DMAG)。
Secoisoolaricinol是亚麻籽中最常见的木脂素之一,可在Blautia producta、Gordonibacter和Lactonifactor longoviformis的存在下去甲基,形成肠内酯和肠二醇。
芝麻素通过甲基化、去甲基化和肠道微生物的其他反应代谢为哺乳动物木脂素内酯和肠二醇。罗汉松树脂酚和连翘脂素也可以去甲基化以产生内酯。水飞蓟宾A和B被人类粪便微生物群去甲基为去甲基水飞蓟宾A和脱甲基水飞蓟宾B。
✦其他化合物
多酚化合物姜黄素被Lautia sp. MRG-PMF1去甲基化,以产生代谢物去甲基姜黄素(DMC)和双去甲基姜黄素(bDMC)。二氢异铁酸的去甲基化产物,如二氢咖啡酸,也在粪便代谢物中获得。
研究发现,甲基化反应发生在甘草皂苷22β-乙酰氧基甘草酸糖链的内部和外部葡萄糖醛酸残基处,产生22β-乙氧基甘草酸甲酯。
丹参素,萜类化合物,二苯乙烯类化合物和类固醇化合物在肠道微生物的作用下经历甲基化和去甲基化。
小结
甲基化和去甲基化反应是肠道微生物代谢的重要途径。甲基化能引起染色质结构、稳定性及蛋白质相互作用方式的改变,从而控制基因表达。去甲基化则诱导了基因的重新活化和表达。
然而,介导这种反应的基因/酶尚未完全确定,还需要进一步的实验研究。
肠道微生物可以表达许多氧化还原酶并通过调节各种官能团转化天然化合物,如烯烃、羧酸衍生物、硝基、氧化物和a,b不饱和羧酸衍生物,这些官能团影响体内天然产物的活性。
下图显示了肠道微生物作用下天然产物的氧化和还原反应。
肠道微生物对天然产物的还原和氧化反应






Zhao Y,et al.Front Microbiol.2022
✦类黄酮
黄酮类化合物大豆苷元在Clostridium sp. strain HGH6和Lactobacillus. sp. Niu-O16的作用下还原为二氢大豆苷元和进一步的四氢大豆苷元。还原产物二氢染料木黄酮是由染料木黄酮在人类粪便细菌的作用下产生的。
通过分析,在厌氧条件下与槲皮素一起孵育,在大鼠肠液培养液中鉴定出脱氧代谢物山奈酚和双键氢化还原产物西叶素等化合物。
从Flavonifractor plautii ATCC 49531中发现了黄酮还原酶,该酶特异性催化黄酮/黄烷醇C环的C2-C3双结合的氢化作用,并在黄酮类化合物整个生物降解途径的初始步骤中起作用。
去甲黄腐酚,一种查尔酮化合物,被分枝杆菌还原为去甲-α,β-二氢黄腐酚
•药理作用
黄酮类化合物分布广泛,具有多种生物活性。
1.黄酮类化合物具有抗自由基和抗氧化作用;2.防治心血管疾病方面均具有良好的效果;3.抑菌抗免疫作用;4.对动物激素的调节作用。
✦生物碱
•小檗碱具有杀菌消炎的功效
由肠道微生物产生的硝酸还原酶催化生物碱中的醚和配位键反应。小檗碱(BBR)作为黄连的主要成分,可以通过肠道微生物表达的硝基还原酶还原为二氢小檗碱,这种还原产物具有很高的极性。
二氢小檗碱可以在肠道中被吸收,然后被氧化成原型小檗碱进入血液。二氢小檗碱在肠道中的吸收率是小檗碱的五倍。同时还发现,肠道微生物可以通过氧化将小檗碱转化为氧小檗碱。
小檗碱的功效和作用主要就是起到杀菌消炎的作用,抗菌谱比较广,主要用于治疗各种肠道感染和菌痢等。
•其他生物碱产物
血红素是小檗碱的一种新代谢产物,可能是一种值得探索的生物活性剂。黄连碱是一种天然的原小檗碱生物碱,具有与小檗碱相同的母体结构。口服黄连后,C-O键打开并断裂,随后发生还原反应,生成氢化小檗碱。阿南酰胺被小鼠和人类肠道微生物群还原为二氢阿南酰胺,生物利用度更高。
✦苯丙酸
•咖啡酸具有抑菌、抗病毒作用
咖啡酸(CAA)作为食品和饮料中的主要膳食多酚,在酯化后很容易进入结肠并与肠道微生物群发生反应。
苯丙酸通过C4双键还原和脱氢作用转化为3-羟基苯基丙酸,然后通过体外肠道微生物的β氧化迅速转化为3-苯基丙酸。苯丙酸也可以脱羟基化为间香豆酸或氢化为二氢咖啡酸。
咖啡酸片具有较普遍的抑菌效果,可用于抑菌、抗病毒。除此之外,还具有中枢兴奋、解毒凝血等作用。
丹参素是丹参的主要单体酚酸,通过肠道微生物群进行脱氢和脱氧,生成3-苯基-2-羟基丙酸、3-(3,4-二羟基苯基)-2-丙烯酸(咖啡酸)和3-(3,4-二羟基苯)丙酸。
✦其他化合物
甘草次酸通过盲肠中的Ruminococcus sp. po1-3的3β-羟基类固醇脱氢酶生成3-氧代甘草次甲酸。
•通便作用
番泻甙是一类天然蒽醌衍生物和二聚糖苷,首先被β-葡萄糖苷酶水解生成番泻甙-8-O-单糖苷,然后在体内被链球菌还原为具有通便作用的大黄蒽醌。
二萜类白藜芦醇被Slackia equolifaciens和Eggerthella lentaATCC 4305还原为二氢白藜芦醇。
此外,二酮姜黄,类固醇化合物地高辛和其他化合物马兜铃酸也可以在肠道微生物的存在下减少。肠道微生物黄酮还原酶和硝基还原酶具有特殊的催化选择性,填补了肠道微生物转化途径的关键空白。
然而,介导肠道微生物减少的特定基因和酶尚未完全确定。
肠道微生物对天然产物的其他反应
Zhao Y,et al.Front Microbiol.2022
如图中所示,肠道微生物也通过环分裂、硫化、芳构化和其他反应转化天然产物。
龙胆苦苷是一种天然的环烯醚萜苷,可通过肠道微生物β-葡萄糖苷酶水解为龙胆醛,然后通过N-杂环反应水解为含氮化合物。
京尼平丙酮醇的部分开环导致肠道微生物形成二醛。奎宁酸可以在肠道微生物存在下芳香化为马尿酸。
原花青素B2和A2与人类肠道微生物体外发酵,获得了主要的水解和环裂解代谢物,即苯甲酸、2-(3,4-二羟基苯基)乙酸和5-(3,4-二羟基苯)-γ-戊内酯。
口服木犀草素后,在大鼠粪便样品中检测到硫酸盐和氢还原代谢物。由肠道微生物促进的大豆苷元转化为雌马酚是另一个有趣的例子。
木犀草素,多以糖苷的形式存在于多种植物中,具有镇咳和祛痰作用。
雌马酚的作用:1.抗氧化,雌马酚属于多酚类物质,可作为氢/电子受体,清除自由基;2. 免疫调控,雌马酚的免疫保护作用可能是有其抗氧化作用所介导的,涂抹雌马酚对皮肤有免疫保护作用。
SesA是一种来自Sinomonas sp.no.22的芝麻素代谢酶,通过环裂解催化亚甲基从芝麻素或芝麻素单儿茶酚转移到四氢叶酸,产生芝麻素一儿茶酚或二儿茶酚和5,10-亚甲基四氢叶酸酯。
萜类化合物,类黄酮,苯酚,生物碱和脂肪酸都可以在肠道微生物的作用下进行生物转化反应,产生活性代谢物。
这些研究证明了各种肠道微生物组的巨大代谢潜力。天然产物的肠道微生物代谢及其在宿主健康中的作用应该是未来研究的重点。
小结
本节总结了来自单个反应的肠道微生物群介导的天然产物的生物转化。
但是,观察到一些限制。首先,考虑到肠道微生物的复杂性和肠道微生物酶的多样性,天然产物在肠道中经历复杂的转变。单个反应只能描述一定的新陈代谢过程。可以通过激活/抑制这一过程来优化治疗。
此外,考虑到肠道微生物含有各种潜在的多功能酶,可以预期肠道微生物会有更多的生物转化反应被天然产物所低估。
为了阐明肠道微生物代谢如何影响人类健康,研究人员应该将功能与基因和酶联系起来。
除了调节肠道微生物对天然产物的处置外,天然产物对肠道微生态学的调节作为潜在的功效机制也很重要。
越来越多的肠道微生物群研究逐渐揭示了大多数天然产品的高药理作用与低口服利用率之间的关系。大多数糖苷具有复杂的母体结构,很难被肠细胞吸收,从而限制了它们的组织特异性生物可及性。
这些化合物通过依赖于微生物/肠道微生物酶的降解反应转化为小分子代谢物/独特代谢物,从而对宿主产生广泛影响。肠道微生物还作用于膳食酚类物质,产生有助于宿主健康的功能代谢物。
✦增强抗肿瘤、抗炎、降脂作用
肠道微生物的生物转化促进了天然产物的治疗效果。人参皂苷对化合物K(CK)的典型代谢模型已被广泛报道,具有增强的抗肿瘤,抗炎和降脂作用。
人参皂苷的生物转化和代谢物化合物k的功效

编辑
Zhao Y,et al.Front Microbiol.2022
1 —降脂
在20μM时,化合物K通过激活AMPK减少人肝细胞癌细胞中的肝脂堆积
2–抗癌
在50μM时,化合物K通过上调半胱天冬酶-3,半胱天冬酶-8,半胱天冬酶-9和环磷酸腺苷依赖性蛋白激酶来抑制胶质母细胞瘤细胞的生长。
3–减弱炎症
化合物K通过自噬诱导和调节NF-κB、p38蛋白和JNK/MAPK信号来减轻巨噬细胞炎症和泡沫细胞形成。
✦姜黄素可以抑制炎症
姜黄素代谢物的生物利用度取决于微生物群依赖性。例如,去甲基姜黄素增加PPARγ表达,导致自噬和核转录因子κB抑制,随后抑制脂多糖诱导的炎症。
PPARγ——是一种过氧化物酶体增殖物激活受体
MAPK——即AMP依赖的蛋白激酶,是生物能量代谢调节的关键分子
去甲基姜黄素通过抑制炎症因子的分泌和MAPK和NF-κB途径的激活来减轻体内和体外的炎症反应。由于在其原型苯环结构中不存在甲基,去甲基姜黄素的化学稳定性增加,从而解释了姜黄素的强大有益作用。
姜黄素来源:姜黄素是从植物根茎中提取,主要来源于生姜,然后就是那些植物中,胡萝卜、番茄以及辣椒,咖喱,芥末中也含有一些姜黄素。
✦尿石素具有抗炎和神经保护等作用
值得注意的是,尿石素A(UA)是一种天然化合物,由肠道微生物从摄入的鞣花单宁和鞣花酸中产生,具有显著的抗炎和神经保护作用。
在1μM时,尿石素A足以降低聚(I:C)诱导的RAW264.7细胞中肿瘤坏死因子和MCP-1的产生,并使TLR3/TRIF信号失活。尿石素A提高高脂饮食小鼠的全身胰岛素敏感性并降低肝脏白细胞介素1β水平。
MCP-1,是一种由星形胶质细胞分泌的促进炎症的蛋白质。
Toll样受体3(TLR3)是TLR家族的成员,介导I型干扰素、促炎细胞因子和趋化因子的转录诱导
尿石素A通过降低皮层和海马体中白细胞介素6、白细胞介素1β和肿瘤坏死因子的水平来改善小鼠的认知障碍,并抑制神经炎症。
小结
这些研究强调了鉴定天然产物微生物代谢的重要性。此外,许多体外药理活性测量应与微生物代谢产物一起进行,微生物代谢产物实际上与体内的生化受体相互作用。
肠道微生物的组成,结构,功能和代谢物已成为天然产物发挥有益作用和降低毒性的潜在目标。
例如,肠道微生物可以通过羧基酯酶催化双酯型二萜生物碱的C-8和C-14的酯键水解,或催化C-8的酯交换以产生毒性较小的单酯二萜烯生物碱。
大肠杆菌的地高辛还原型菌株含有强心苷还原酶,它可以还原地高辛环上的α和β-不饱和内酯,并将其代谢为活性较低的二氢地高辛,从而抑制其可能的心脏毒性。
地高辛,主要用于心脏类疾病的治疗,对心脏的作用表现为正性肌力作用,减慢心率,抑制心脏传导。
然而,这种能力是有限的,并且50%的地高辛可以通过肠道微生物转化而失活。强心苷还原酶可能是地高辛失活的有效生物标志物,其表达可以被精氨酸抑制。
•饮食可能调节微生物代谢活动
饮食可以解释地高辛还原的个体间差异,并可能调节体内微生物代谢活动。相比之下,有毒化合物可以由肠道微生物产生。桦木素在来自肠道微生物的β-葡萄糖苷酶的作用下水解成致癌性重氮甲烷。
建议
应开发微生物肠道酶的小分子抑制剂,以在这个复杂的栖息地的特定转化中发挥调节作用。肠道微生物群转化的代谢物与前体物质之间的毒性差异值得进一步研究。
此外,过量的药物可能导致肠道微生物失衡和不良反应,不同剂量的天然产物对肠道微生物和新陈代谢的影响也需进一步研究。
考虑到肠道微生物可以增加宿主对药物或天然产物的复杂和可变反应,这一过程值得研究。
生物转化的方法
(1)肠液转化。转化产物的大规模制备可以通过肠液生物转化来实现;
(2)与宿主微生物群的样品一起孵育。原型药物和代谢物的类型和数量可以使用该方法检测。它具有准确表示个体的整个肠道微生物组的优点;
(3)代表性菌株的孵育。该方法具有高通量潜力,这对于大规模药物研究很有价值,并有助于有益代谢物的工业生产。
✦模型分析有利于认识微生物代谢
器官微生理系统,胃肠道类器官的各种预测/计算工具可能有助于提高我们对未来微生物代谢的理解。
此外,在动物模型中已经研究了天然产物代谢与肠道微生物之间的关系,其结果可用于研究代谢物的分布和形式。无菌/抗生素处理的动物与传统动物进行了比较,以证明肠道微生物在天然产物代谢中的关键作用。
这种方法的局限性在于人类和啮齿动物之间存在固有的胃肠道和微生物差异。在临床试验中从受试者收集的粪便进行详细微生物群和代谢物分析可以全面反映天然产物在体内的代谢过程,并用于解释个体差异。
✦增加测序技术的应用
增加测序技术的应用,以研究微生物的转录活性和代谢谱。通过使用单细胞法,可以表征肠道微生物的生理结构,以确定其代谢活性。
转录组测序技术(RNA-Seq)可以直接分析人体肠道中具有强代谢活性的微生物的基因表达谱。
单细胞方法,宏转录组学和宏基因组学的组合已被用于鉴定和表征肠道微生物群的活性亚群,并确定它们对天然产物的代谢反应。
肠道微生物群是编码各种代谢酶的基因库。大多数天然产物的生物活性和潜在健康益处的激活极度依赖肠道微生物作为底物加工工厂。
了解微生物如何独特地调整天然产物以及这些代谢物对宿主健康的影响。已经得出以下结论:
(1)肠道微生物可以改变天然产物;
(2)天然产物可以调节肠道微生物的组成和丰度;
(3)肠道微生物可以介导天然产物的多组分协同作用。
此外,肠道微生物的巨大可塑性和个体间差异是值得注意的。因此,需要提高对肠道微生物对天然产物代谢的生理,化学和微生物贡献的理解,以帮助解释天然产物反应的个体差异,并为个性化治疗提供支持。
确认生物转化中极其参与的象征性功能及其物质基础将有助于探索天然产物与肠道微生物群之间相互作用的治疗模式。
主要参考文献
Zhao Y, Zhong X, Yan J, Sun C, Zhao X, Wang X. Potential roles of gut microbes in biotransformation of natural products: An overview. Front Microbiol. 2022 Sep 29;13:956378. doi: 10.3389/fmicb.2022.956378. PMID: 36246222; PMCID: PMC9560768.
Abookleesh F. L., Al-Anzi B. S., Ullah A. (2022). Potential antiviral action of alkaloids. Molecules 27:903. doi: 10.3390/molecules27030903.
Agatonovic-Kustrin S., Kustrin E., Gegechkori V., Morton D. W. (2020). Anxiolytic terpenoids and aromatherapy for anxiety and depression. Adv. Exp. Med. Biol. 1260, 283–296. doi: 10.1007/978-3-030-42667-5_11.
Al-Ishaq R. K., Liskova A., Kubatka P., Büsselberg D. (2021). Enzymatic metabolism of flavonoids by gut microbiota and its impact on gastrointestinal cancer. Cancers 13:3934. doi: 10.3390/cancers13163934.
Augusti P. R., Conterato G. M. M., Denardin C. C., Prazeres I. D., Serra A. T., Bronze M. R., et al.. (2021). Bioactivity, bioavailability, and gut microbiota transformations of dietary phenolic compounds: implications for COVID-19. J. Nutr. Biochem. 97:108787. doi: 10.1016/j.jnutbio.2021.108787.
Berlinberg A. J., Brar A., Stahly A., Gerich M. E., Fennimore B. P., Scott F. I., et al.. (2022). A novel approach toward less invasive multiomics gut analyses: a pilot study. Microbiol. Spectr. 10:e0244621. doi: 10.1128/spectrum.02446-21.
Bess E. N., Bisanz J. E., Yarza F., Bustion A., Rich B. E., Li X., et al.. (2020). Genetic basis for the cooperative bioactivation of plant lignans by Eggerthella lenta and other human gut bacteria. Nat. Microbiol. 5, 56–66. doi: 10.1038/s41564-019-0596-1.